peptides
spectra
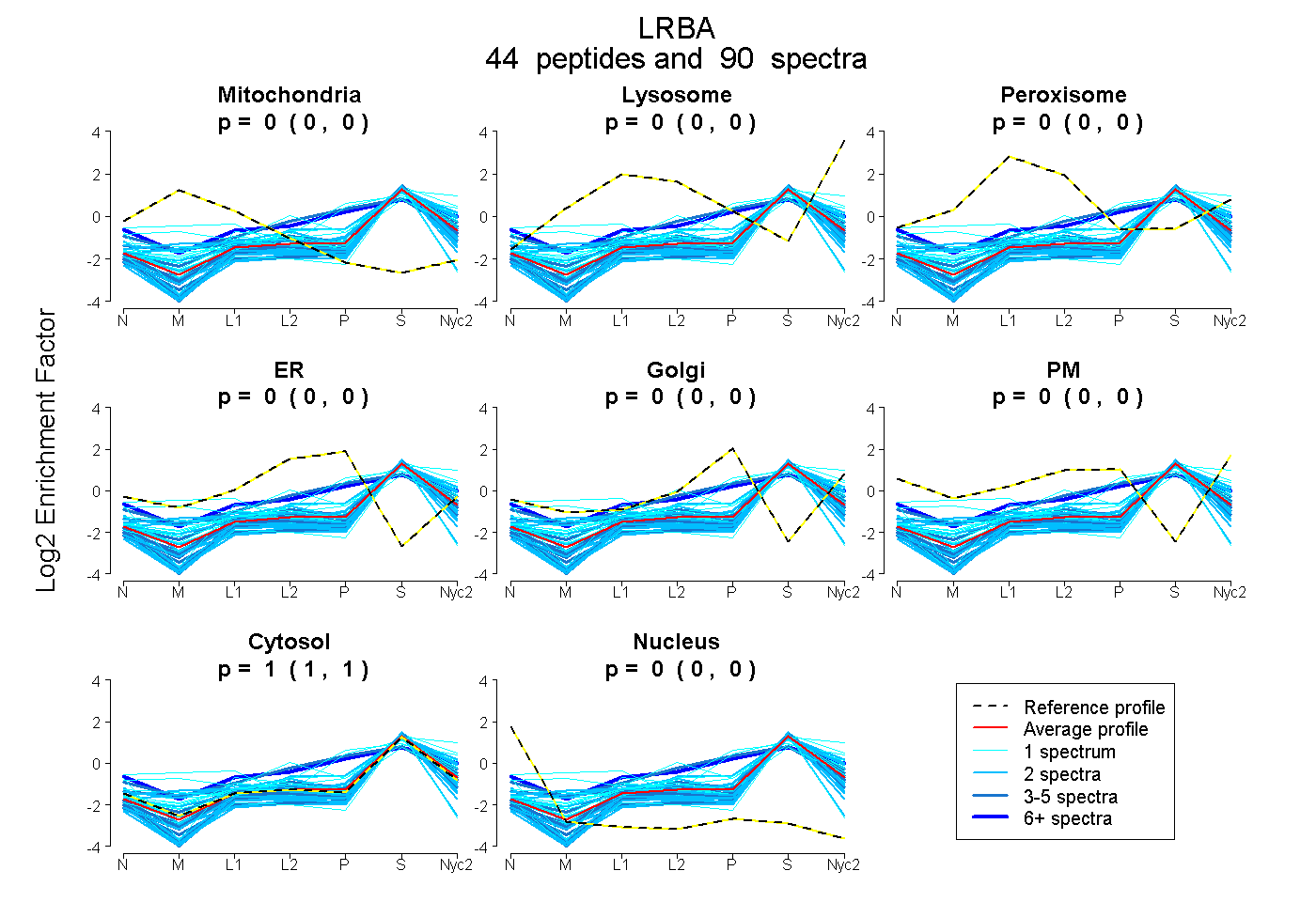
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.996 | 1.000
0.000 | 0.000
peptides
spectra
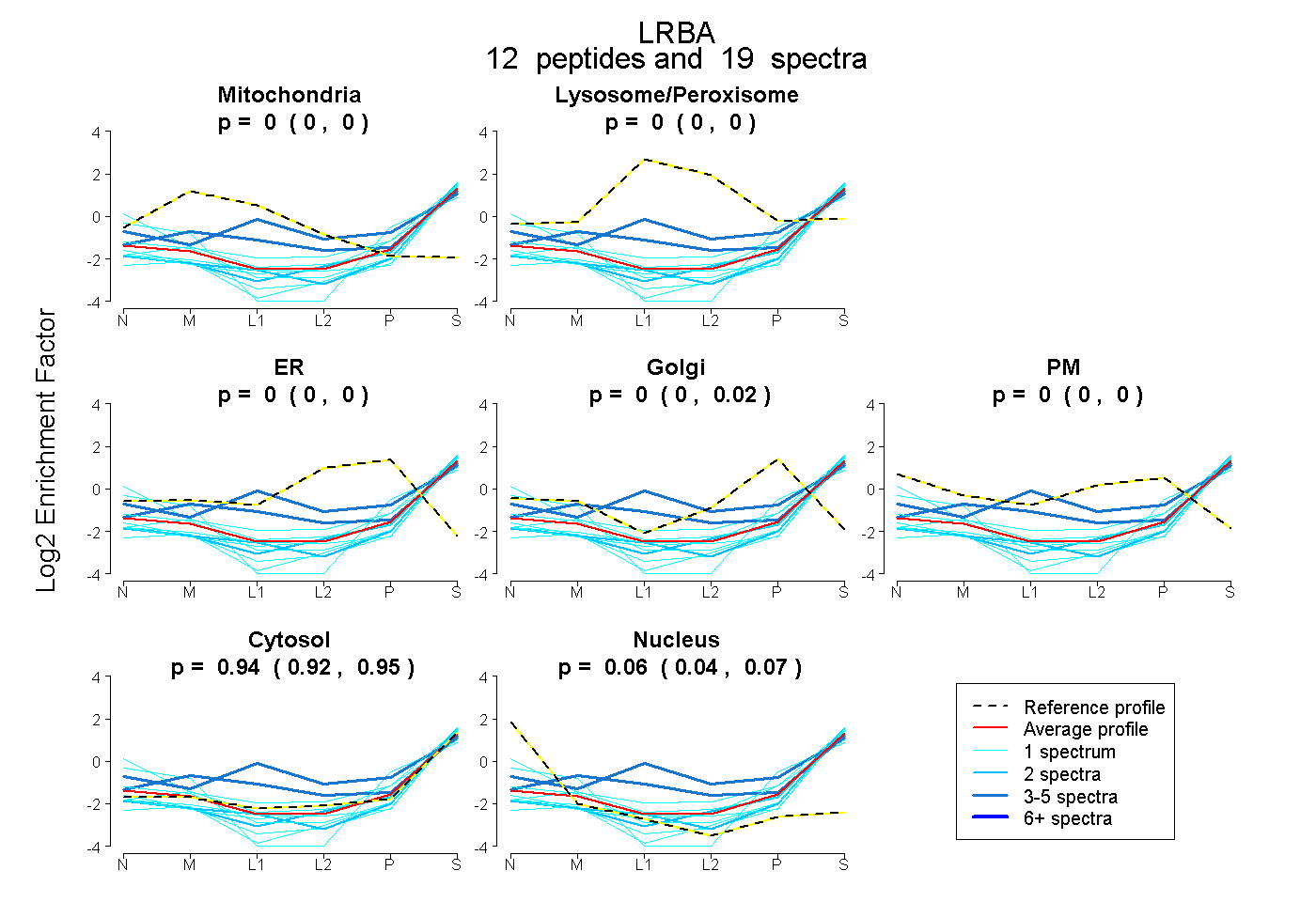
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.016
0.000 | 0.000
0.925 | 0.948
0.042 | 0.070
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.998 0.996 | 1.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.016 |
0.000 0.000 | 0.000 |
0.939 0.925 | 0.948 |
0.059 0.042 | 0.070 |
| 1 spectrum, ASTSTEAPQPQR | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.635 | 0.257 | |||
| 1 spectrum, VGVGTSFGLPQTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.895 | 0.105 | |||
| 2 spectra, VANEAEFILSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.972 | 0.028 | |||
| 3 spectra, LFNNSR | 0.127 | 0.133 | 0.000 | 0.000 | 0.000 | 0.740 | 0.000 | |||
| 1 spectrum, VLNLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.989 | 0.011 | |||
| 1 spectrum, VVNYLPR | 0.000 | 0.000 | 0.000 | 0.010 | 0.000 | 0.990 | 0.000 | |||
| 2 spectra, SPVDIVTGGISPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VIATLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LVCAVAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.923 | 0.077 | |||
| 4 spectra, AVHSLVPVGR | 0.000 | 0.373 | 0.000 | 0.000 | 0.000 | 0.595 | 0.033 | |||
| 1 spectrum, LDYWEDDLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, ATDAQLCLESSPK | 0.000 | 0.022 | 0.000 | 0.000 | 0.171 | 0.662 | 0.145 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
57 spectra |
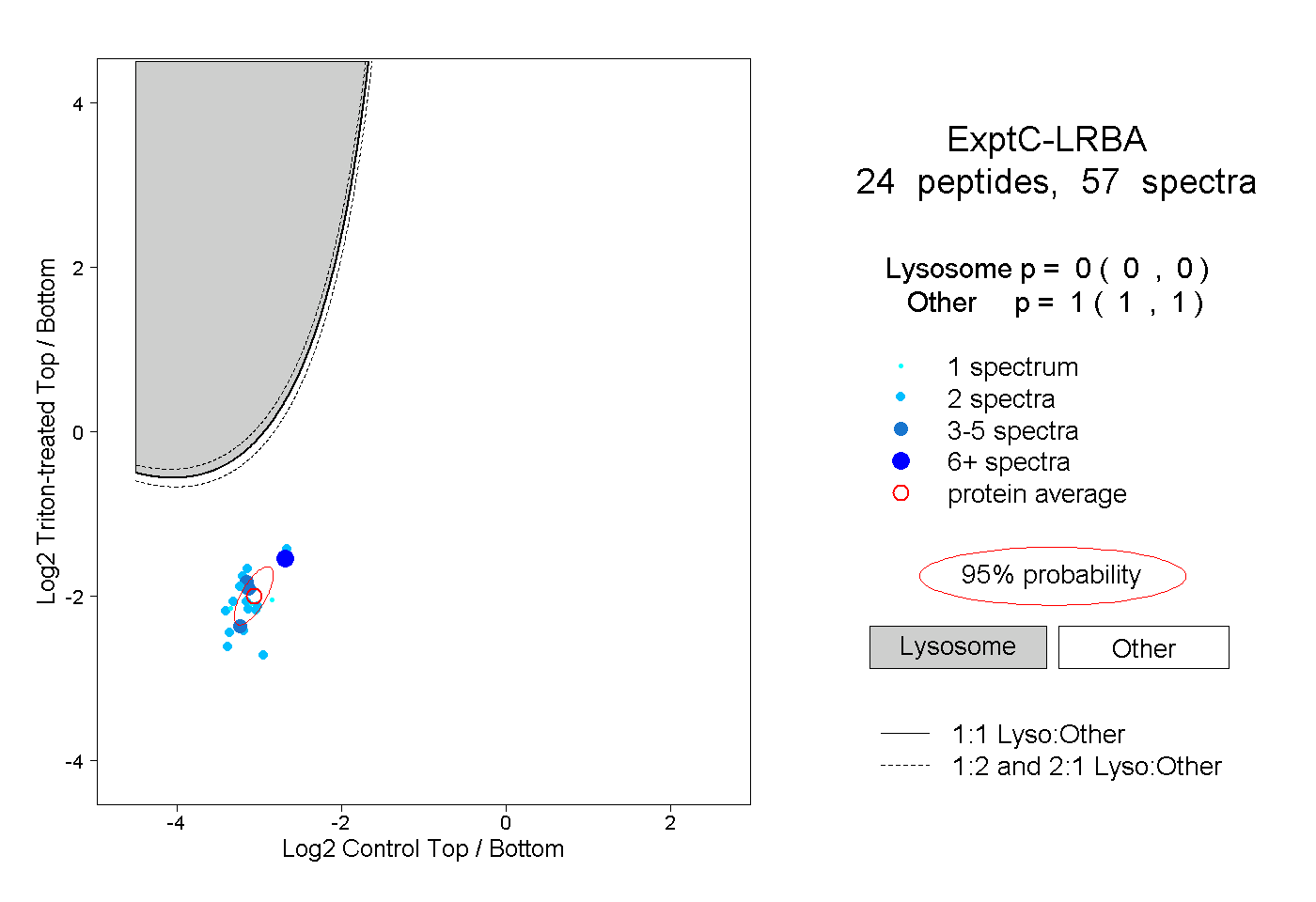 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
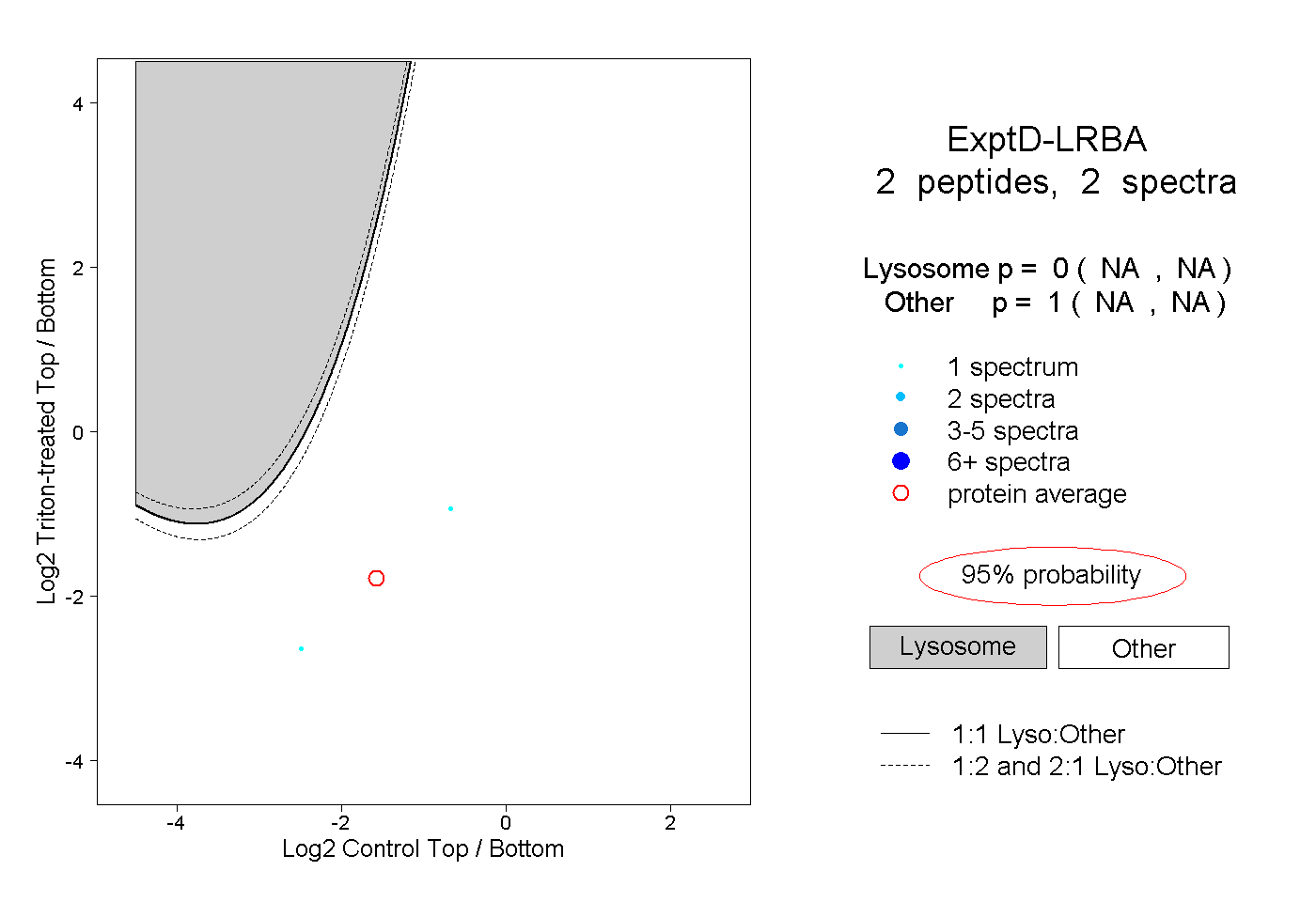 |
0.000 NA | NA |
1.000 NA | NA |