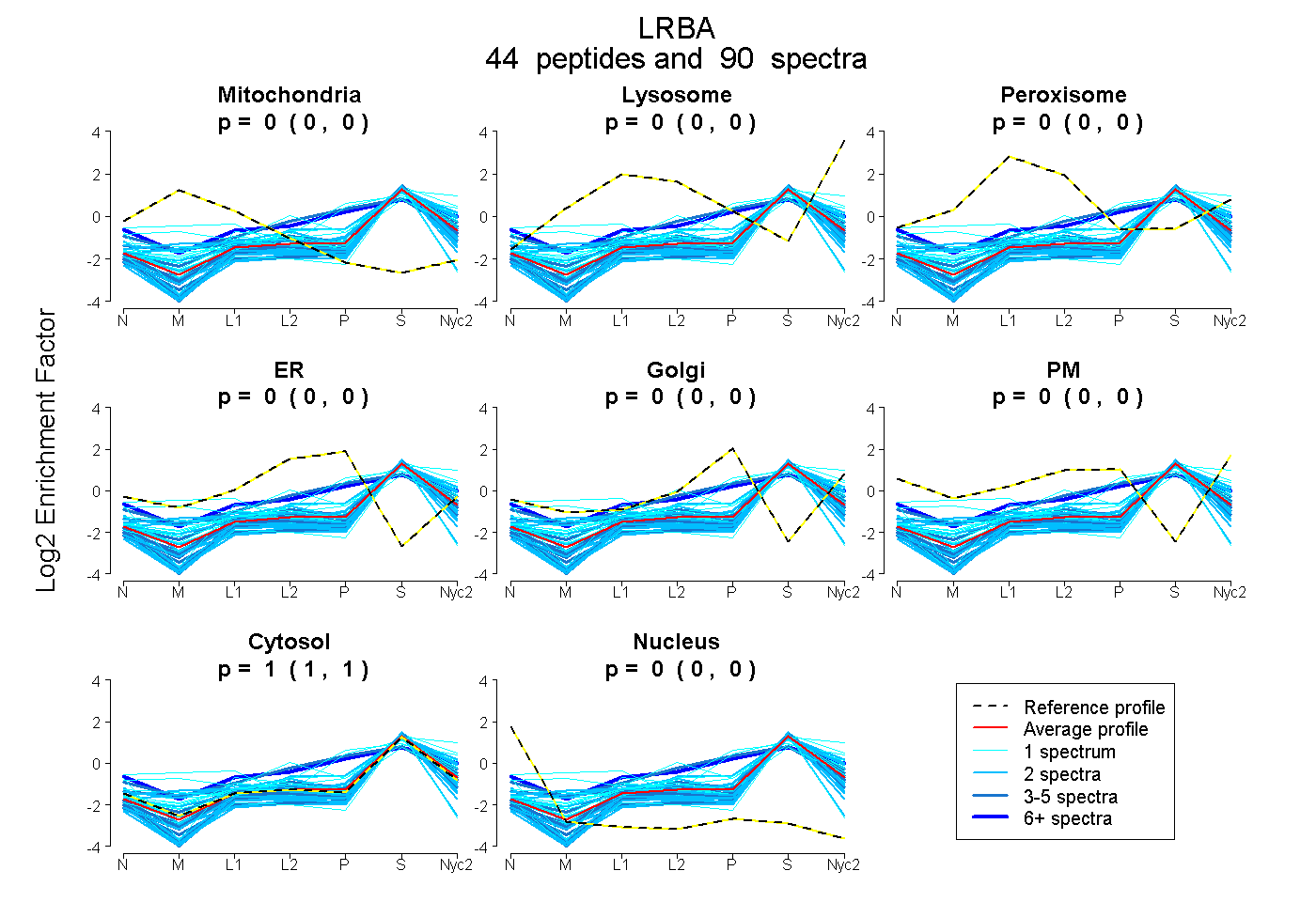
peptides
spectra
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.996 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.998 0.996 | 1.000 |
0.000 0.000 | 0.000 |
| 3 spectra, NMSSGGILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ASTSTEAPQPQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ENLANIFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, CFLGSSETADANR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, YAPDAFFNFPGK | 0.000 | 0.064 | 0.000 | 0.000 | 0.000 | 0.000 | 0.936 | 0.000 | ||
| 1 spectrum, TLLGSHGQELLIEGTSLVCMK | 0.247 | 0.077 | 0.058 | 0.000 | 0.000 | 0.000 | 0.618 | 0.000 | ||
| 1 spectrum, NAGLAFIELVNEGR | 0.000 | 0.123 | 0.000 | 0.000 | 0.000 | 0.000 | 0.877 | 0.000 | ||
| 1 spectrum, GFLVIGYSLEK | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 5 spectra, ASNMTQR | 0.073 | 0.051 | 0.000 | 0.000 | 0.000 | 0.000 | 0.876 | 0.000 | ||
| 1 spectrum, VEGIEGSPAEEAR | 0.010 | 0.190 | 0.030 | 0.000 | 0.000 | 0.124 | 0.646 | 0.000 | ||
| 2 spectra, EILSLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.026 | ||
| 2 spectra, WLFTEIR | 0.060 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | ||
| 3 spectra, AEDIHR | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.000 | ||
| 1 spectrum, VGVGTSFGLPQTR | 0.000 | 0.069 | 0.015 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 3 spectra, VANEAEFILSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LFNNSR | 0.000 | 0.176 | 0.000 | 0.000 | 0.000 | 0.000 | 0.824 | 0.000 | ||
| 2 spectra, EIFVDFAPFLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, LLLYDGK | 0.000 | 0.013 | 0.000 | 0.000 | 0.074 | 0.000 | 0.913 | 0.000 | ||
| 2 spectra, ILAYTEGLHGK | 0.064 | 0.019 | 0.058 | 0.000 | 0.000 | 0.000 | 0.858 | 0.000 | ||
| 2 spectra, VIATLLR | 0.000 | 0.098 | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | ||
| 1 spectrum, NCLECQQHSQLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.845 | 0.155 | ||
| 3 spectra, ALGYFLK | 0.000 | 0.064 | 0.000 | 0.000 | 0.000 | 0.000 | 0.936 | 0.000 | ||
| 1 spectrum, LLQDMDINR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, LDVSSVASDTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 7 spectra, AVHSLVPVGR | 0.000 | 0.009 | 0.130 | 0.000 | 0.254 | 0.009 | 0.598 | 0.000 | ||
| 2 spectra, DVDVSEGPQHSDR | 0.000 | 0.000 | 0.000 | 0.082 | 0.000 | 0.000 | 0.904 | 0.014 | ||
| 2 spectra, AESDLFLAEHHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.969 | 0.031 | ||
| 1 spectrum, NSPQCPESMEVR | 0.000 | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.976 | 0.000 | ||
| 2 spectra, VTFEIHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, IISVLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.234 | 0.000 | 0.766 | 0.000 | ||
| 4 spectra, ILLYHAVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.010 | ||
| 2 spectra, MCDHLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.980 | 0.020 | ||
| 1 spectrum, GLDGPRPNQK | 0.023 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | 0.896 | 0.000 | ||
| 3 spectra, GFQHCVK | 0.000 | 0.000 | 0.017 | 0.311 | 0.000 | 0.000 | 0.672 | 0.000 | ||
| 2 spectra, LVCAVAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.927 | 0.073 | ||
| 1 spectrum, VTPSVPVSK | 0.000 | 0.146 | 0.000 | 0.000 | 0.000 | 0.000 | 0.854 | 0.000 | ||
| 3 spectra, LEHALEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LPAEHQAEEACQPAER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.983 | 0.017 | ||
| 2 spectra, AAPLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DILEPQDER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, VVNYLPR | 0.000 | 0.053 | 0.000 | 0.000 | 0.280 | 0.000 | 0.667 | 0.000 | ||
| 2 spectra, SPVDIVTGGISPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 | ||
| 1 spectrum, QHPDPDSTVK | 0.003 | 0.072 | 0.000 | 0.014 | 0.106 | 0.000 | 0.805 | 0.000 | ||
| 2 spectra, LDYWEDDLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
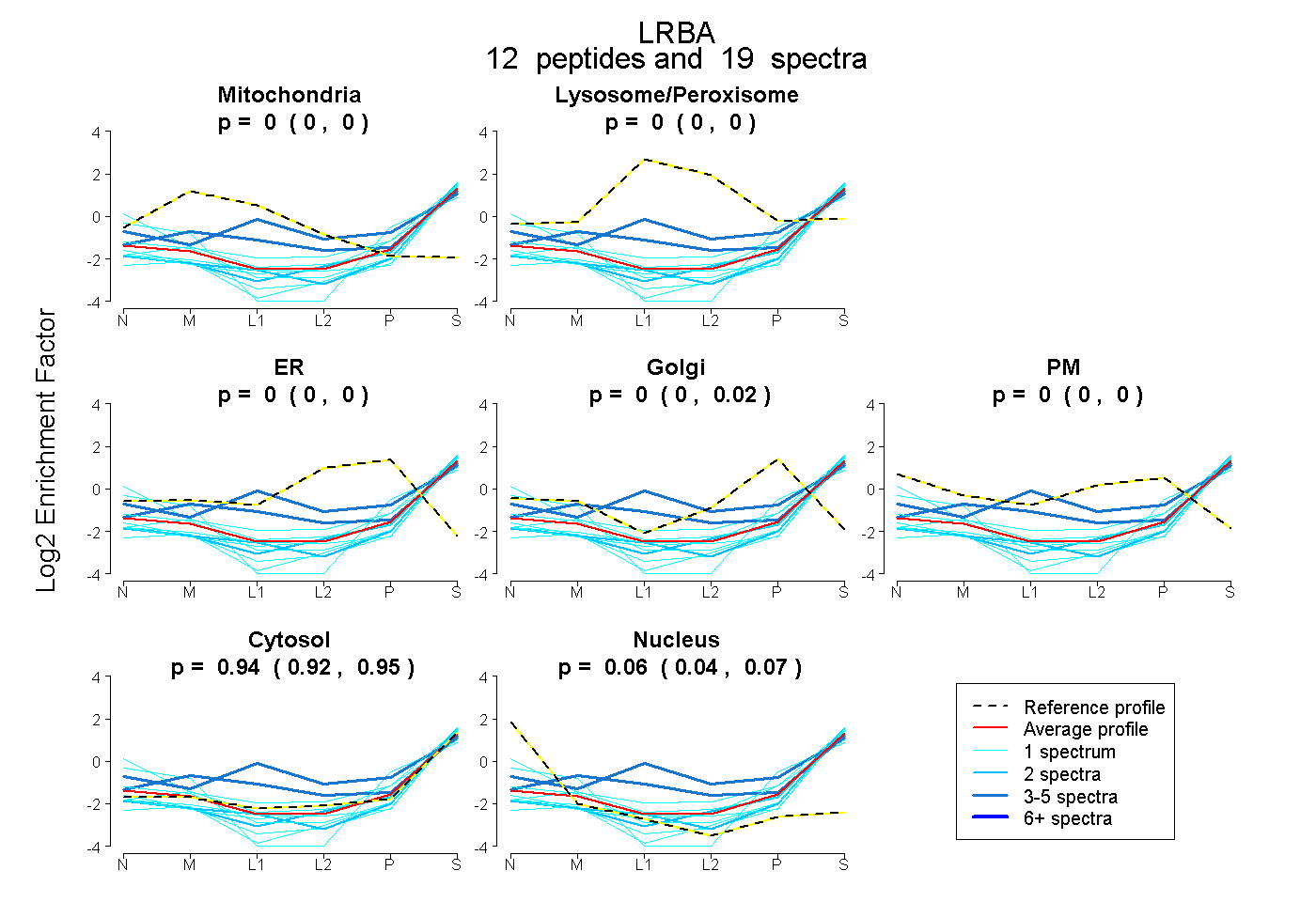
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.016 |
0.000 0.000 | 0.000 |
0.939 0.925 | 0.948 |
0.059 0.042 | 0.070 |
|||
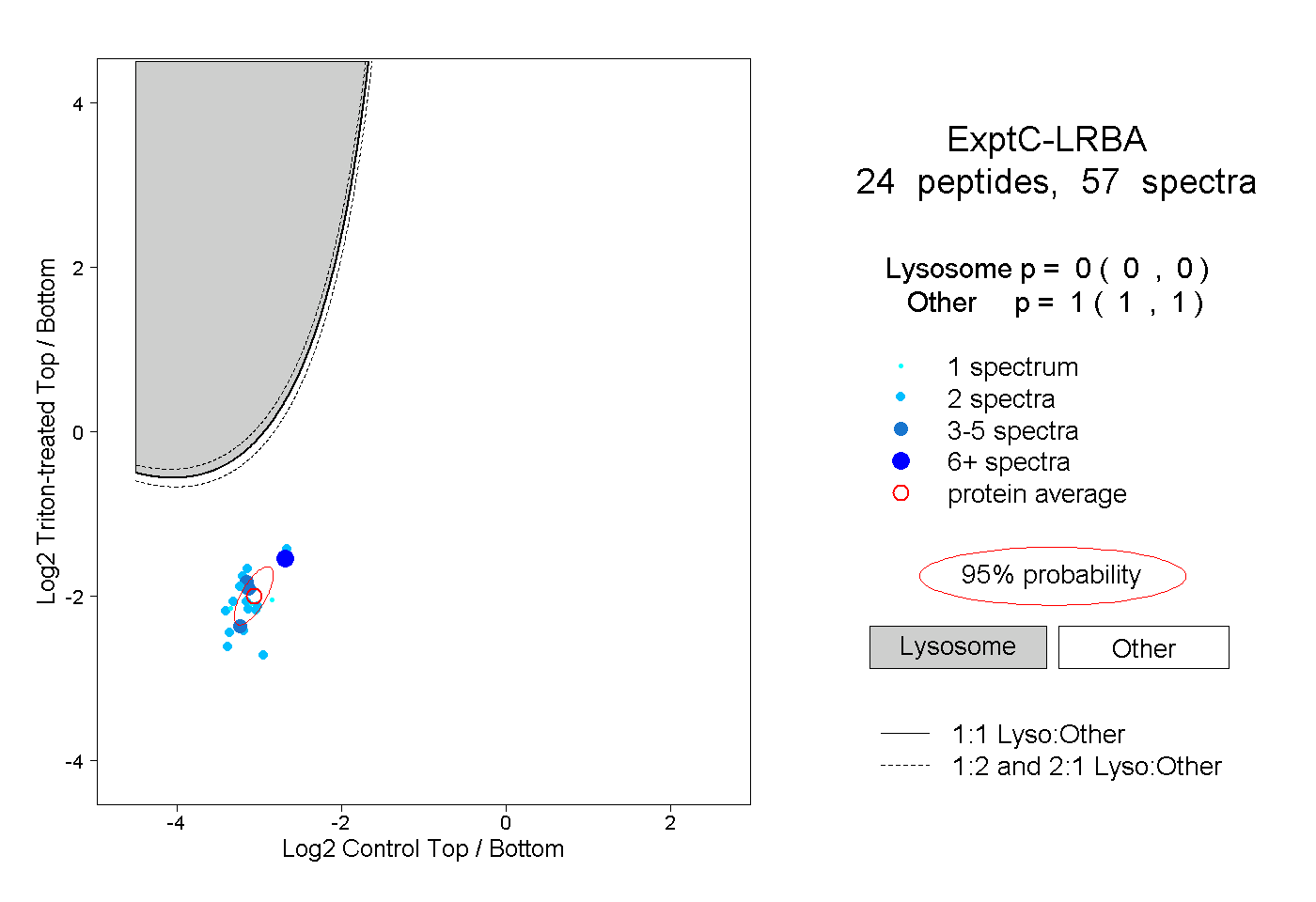
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
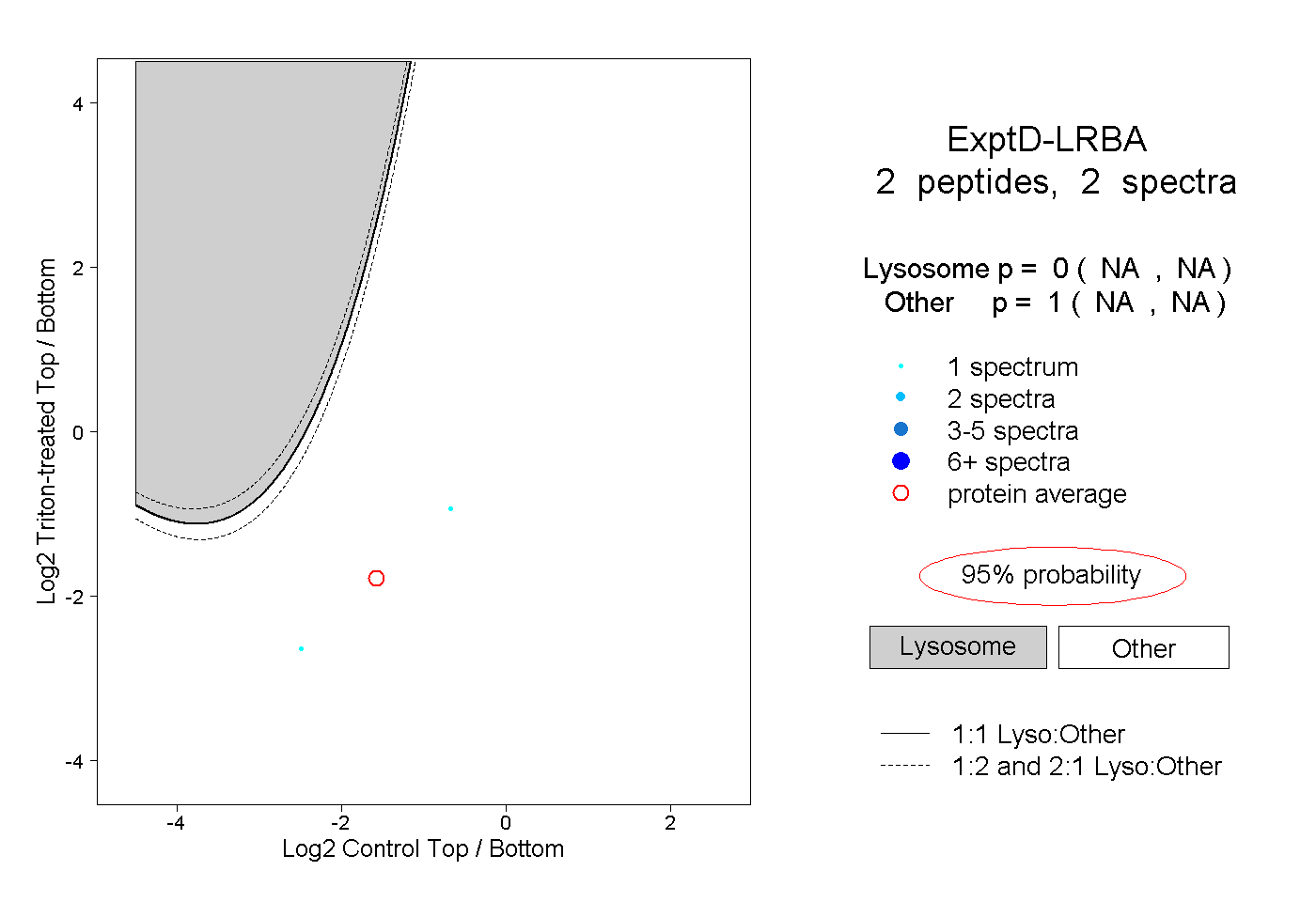
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
 |
0.000 NA | NA |
1.000 NA | NA |