peptides
spectra
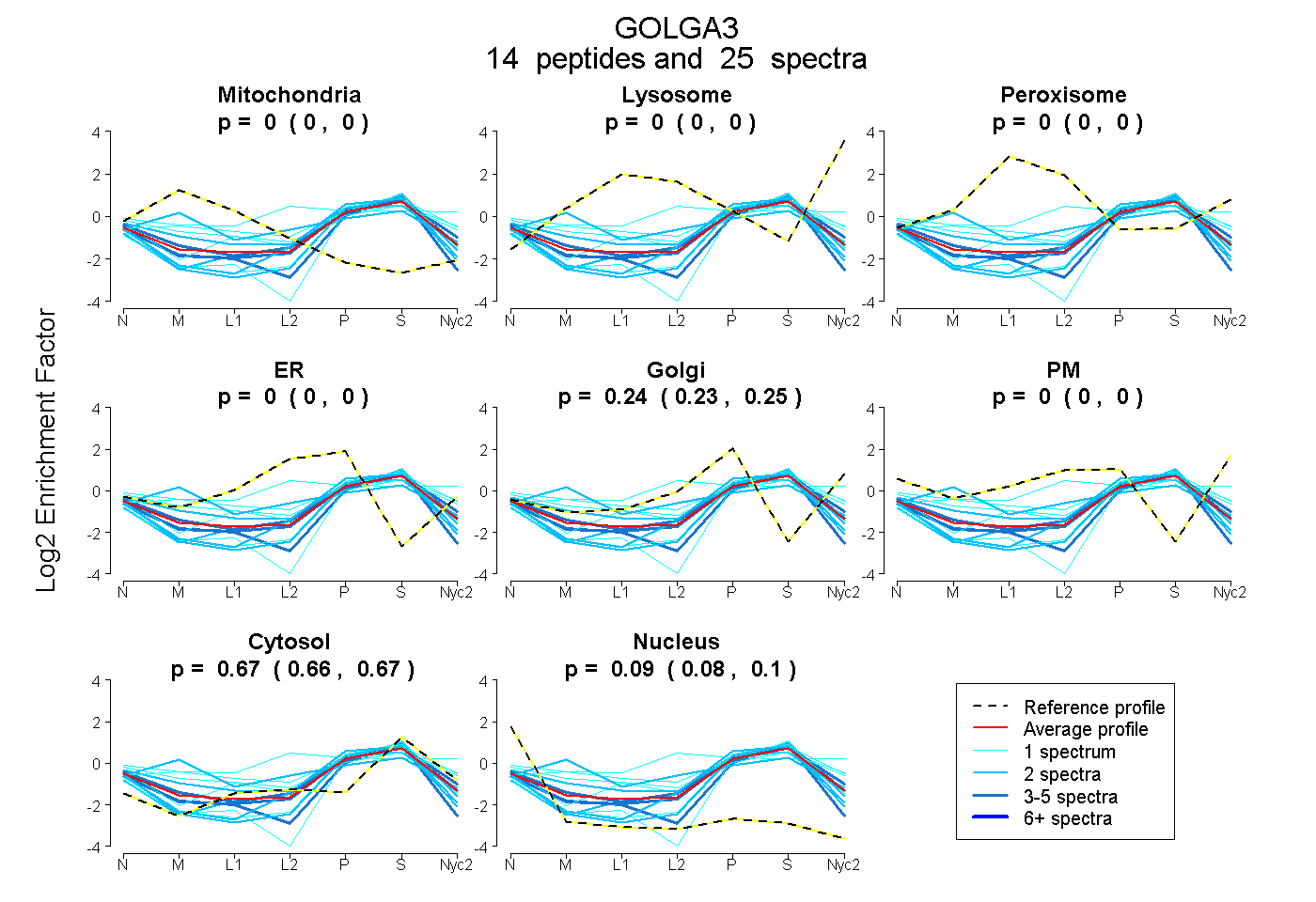
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.233 | 0.249
0.000 | 0.000
0.661 | 0.673
0.081 | 0.098
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.242 0.233 | 0.249 |
0.000 0.000 | 0.000 |
0.667 0.661 | 0.673 |
0.090 0.081 | 0.098 |
| 3 spectra, EDAIHFLQNEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.049 | 0.000 | 0.712 | 0.239 | ||
| 1 spectrum, LQASQAEITSLQQAR | 0.000 | 0.000 | 0.179 | 0.074 | 0.000 | 0.330 | 0.417 | 0.000 | ||
| 1 spectrum, ELEGTQQTLQTIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.299 | 0.000 | 0.701 | 0.000 | ||
| 2 spectra, SNQVEHLQQETATLR | 0.108 | 0.000 | 0.000 | 0.000 | 0.278 | 0.000 | 0.580 | 0.034 | ||
| 1 spectrum, VADAAASLEQQLEQVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.150 | 0.000 | 0.707 | 0.144 | ||
| 2 spectra, DQLINELK | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | 0.792 | 0.081 | ||
| 1 spectrum, TTLTSK | 0.117 | 0.000 | 0.111 | 0.000 | 0.263 | 0.000 | 0.509 | 0.000 | ||
| 3 spectra, TMVEEDLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.266 | 0.000 | 0.667 | 0.067 | ||
| 2 spectra, LTLFQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | 0.695 | 0.209 | ||
| 1 spectrum, LALELEHER | 0.000 | 0.000 | 0.000 | 0.000 | 0.036 | 0.000 | 0.761 | 0.202 | ||
| 1 spectrum, EHLVQTLQAEVDELQIQEGK | 0.117 | 0.000 | 0.010 | 0.000 | 0.185 | 0.118 | 0.569 | 0.000 | ||
| 3 spectra, EATDAELNQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.214 | 0.000 | 0.691 | 0.095 | ||
| 2 spectra, VLELEDELQESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.171 | 0.000 | 0.670 | 0.158 | ||
| 2 spectra, TVEVEHSR | 0.276 | 0.000 | 0.020 | 0.113 | 0.127 | 0.000 | 0.464 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
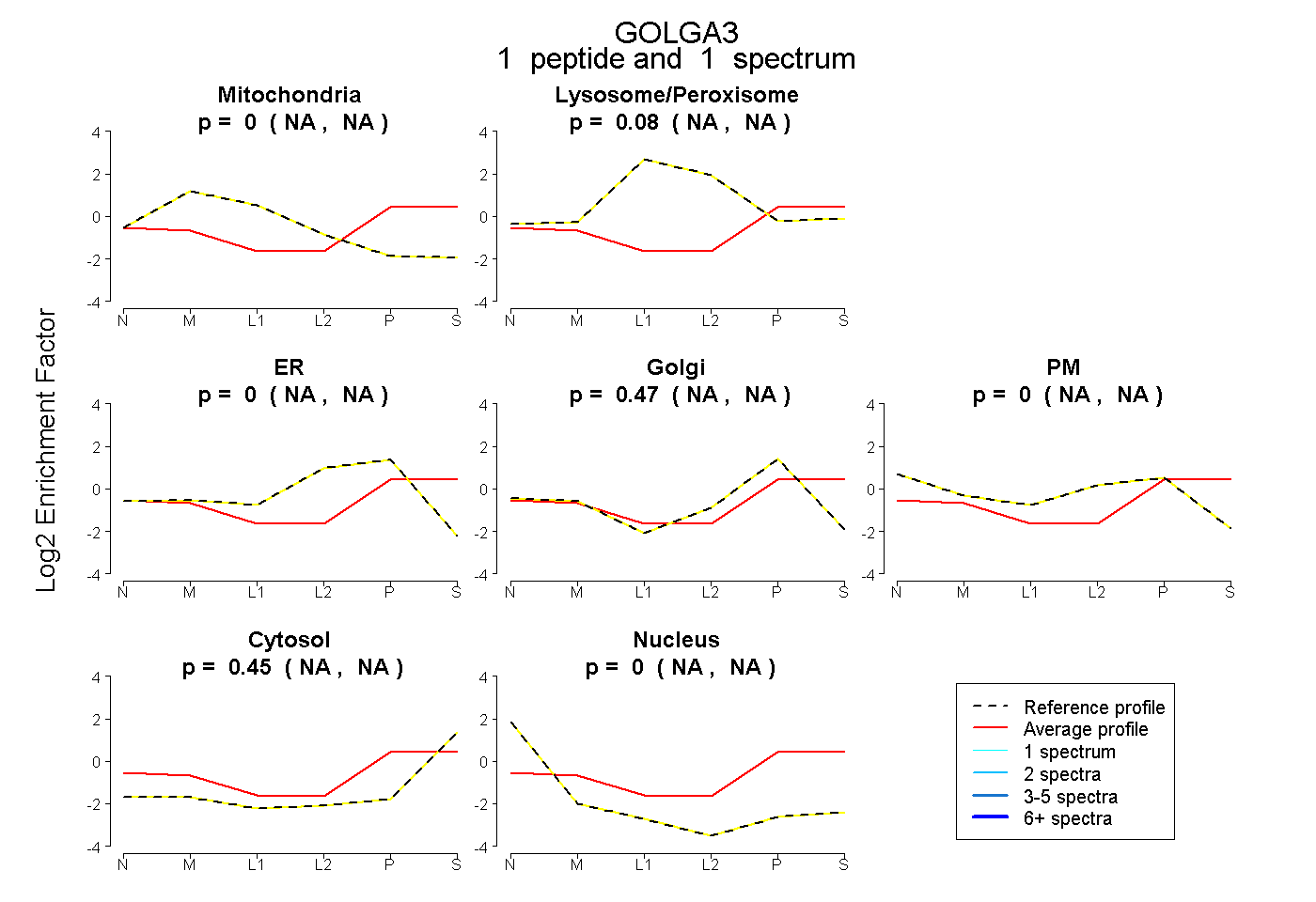 |
0.000 NA | NA |
0.079 NA | NA |
0.000 NA | NA |
0.467 NA | NA |
0.000 NA | NA |
0.453 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7 spectra |
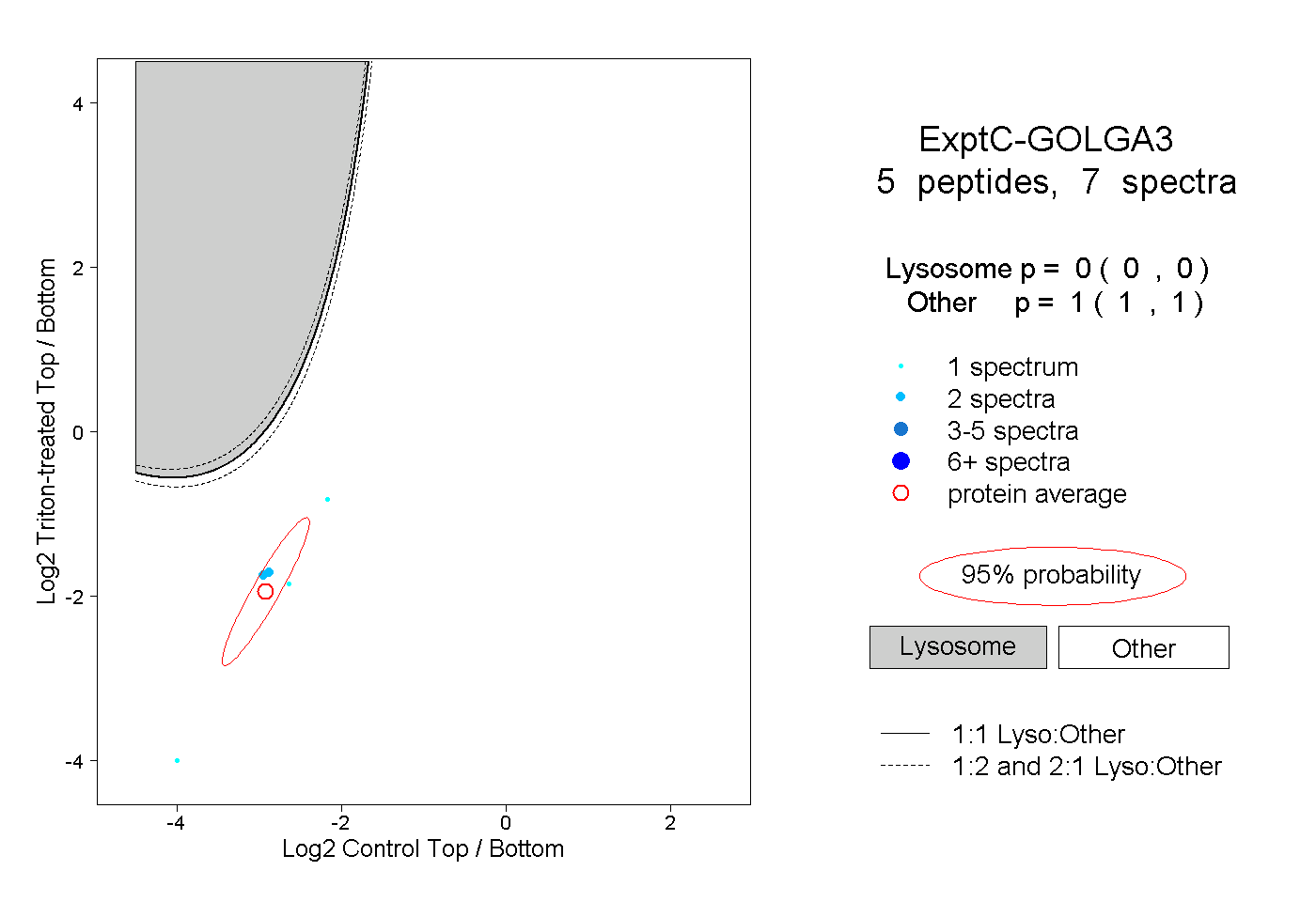 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |