peptides
spectra
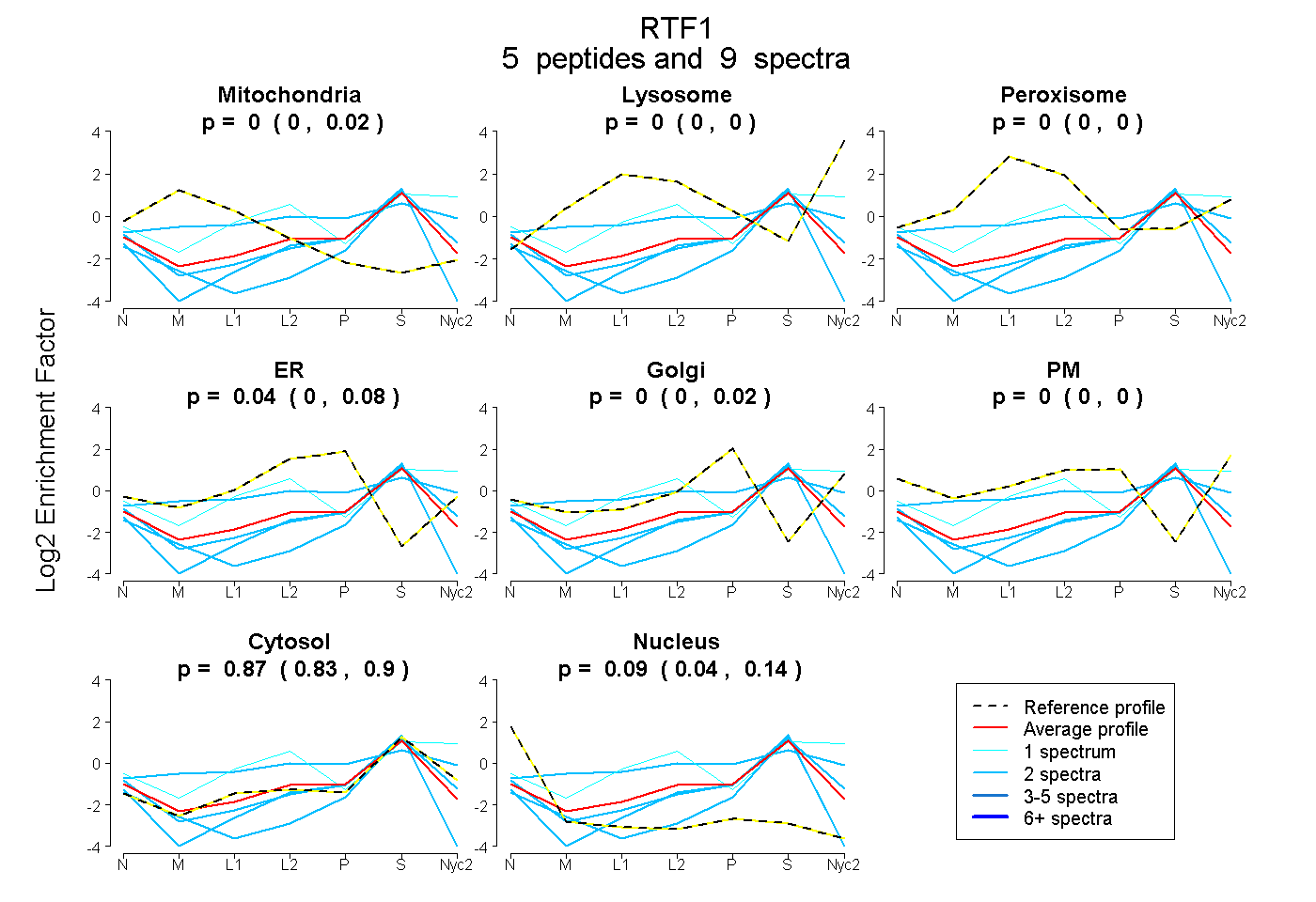
0.000 | 0.023
0.000 | 0.000
0.000 | 0.000
0.000 | 0.077
0.000 | 0.020
0.000 | 0.000
0.828 | 0.896
0.036 | 0.136
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.023 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.000 | 0.077 |
0.000 0.000 | 0.020 |
0.000 0.000 | 0.000 |
0.866 0.828 | 0.896 |
0.092 0.036 | 0.136 |
| 2 spectra, VAEITGVVETAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.639 | 0.361 | ||
| 2 spectra, QIQDQLNELEER | 0.007 | 0.000 | 0.303 | 0.000 | 0.202 | 0.000 | 0.487 | 0.000 | ||
| 1 spectrum, SQPVSLPEELNR | 0.000 | 0.214 | 0.180 | 0.000 | 0.000 | 0.000 | 0.606 | 0.000 | ||
| 2 spectra, FNDQDIEEIVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.740 | 0.260 | ||
| 2 spectra, AMAEDLGDQDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.890 | 0.110 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
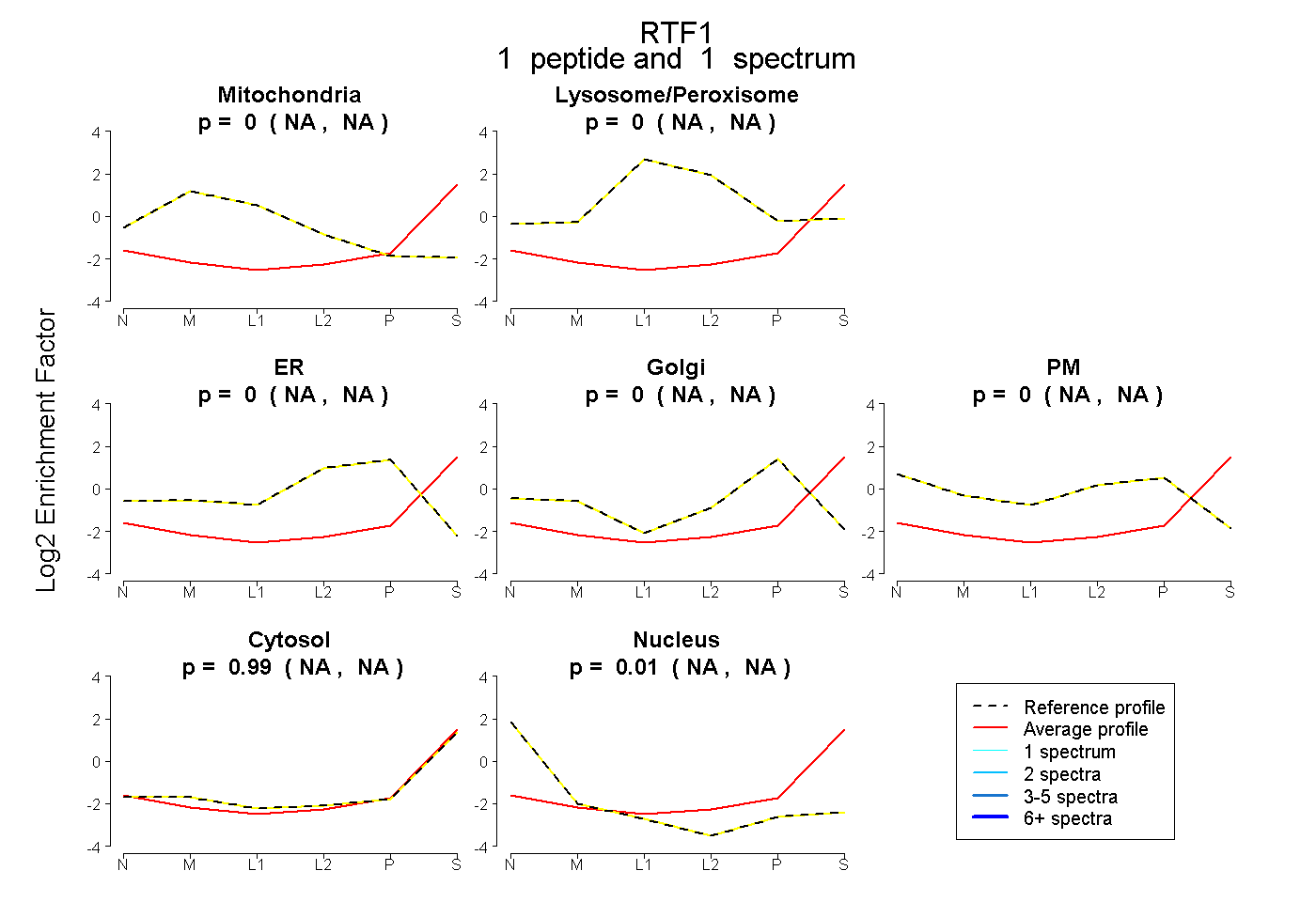 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.989 NA | NA |
0.011 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
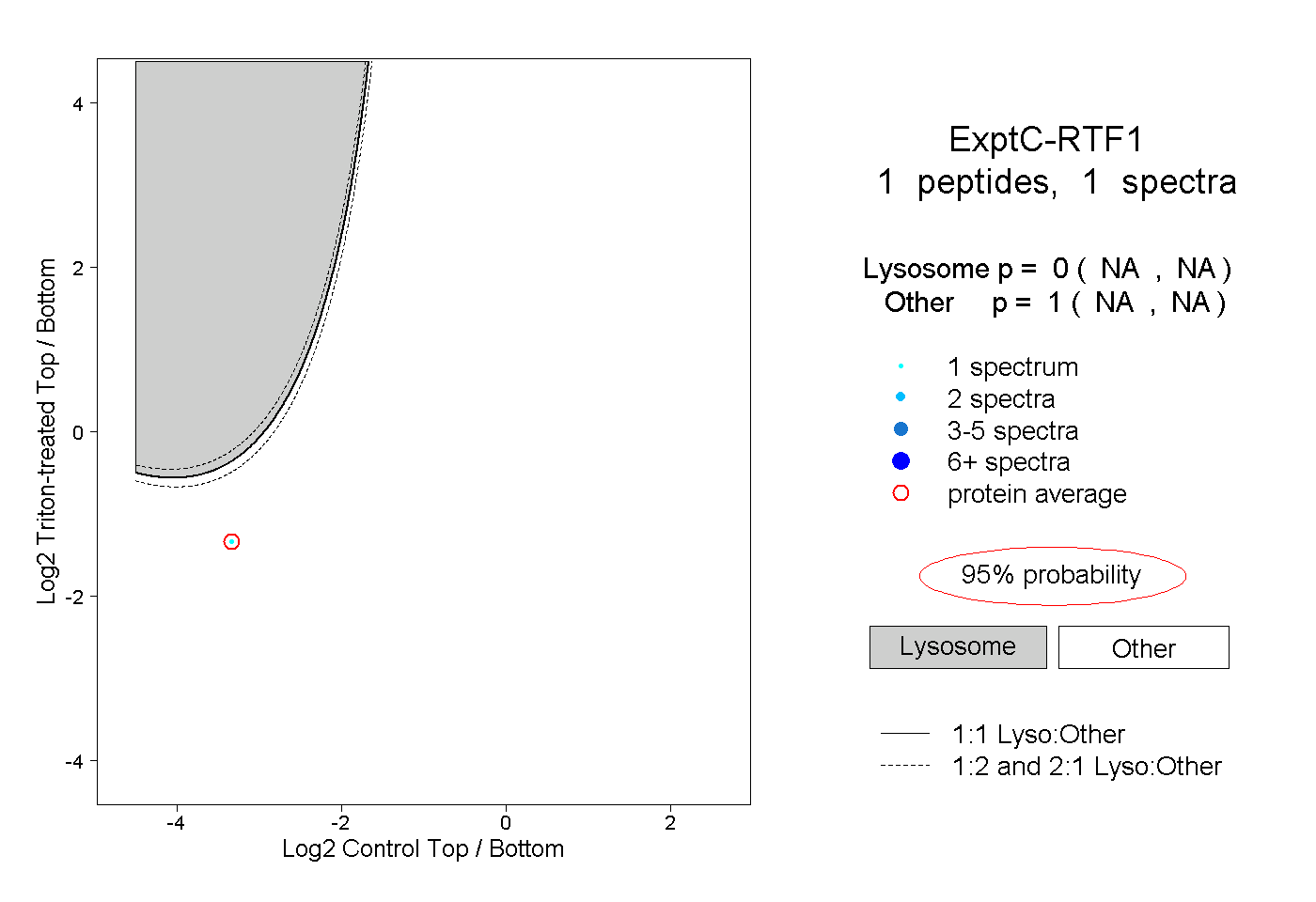 |
0.000 NA | NA |
1.000 NA | NA |