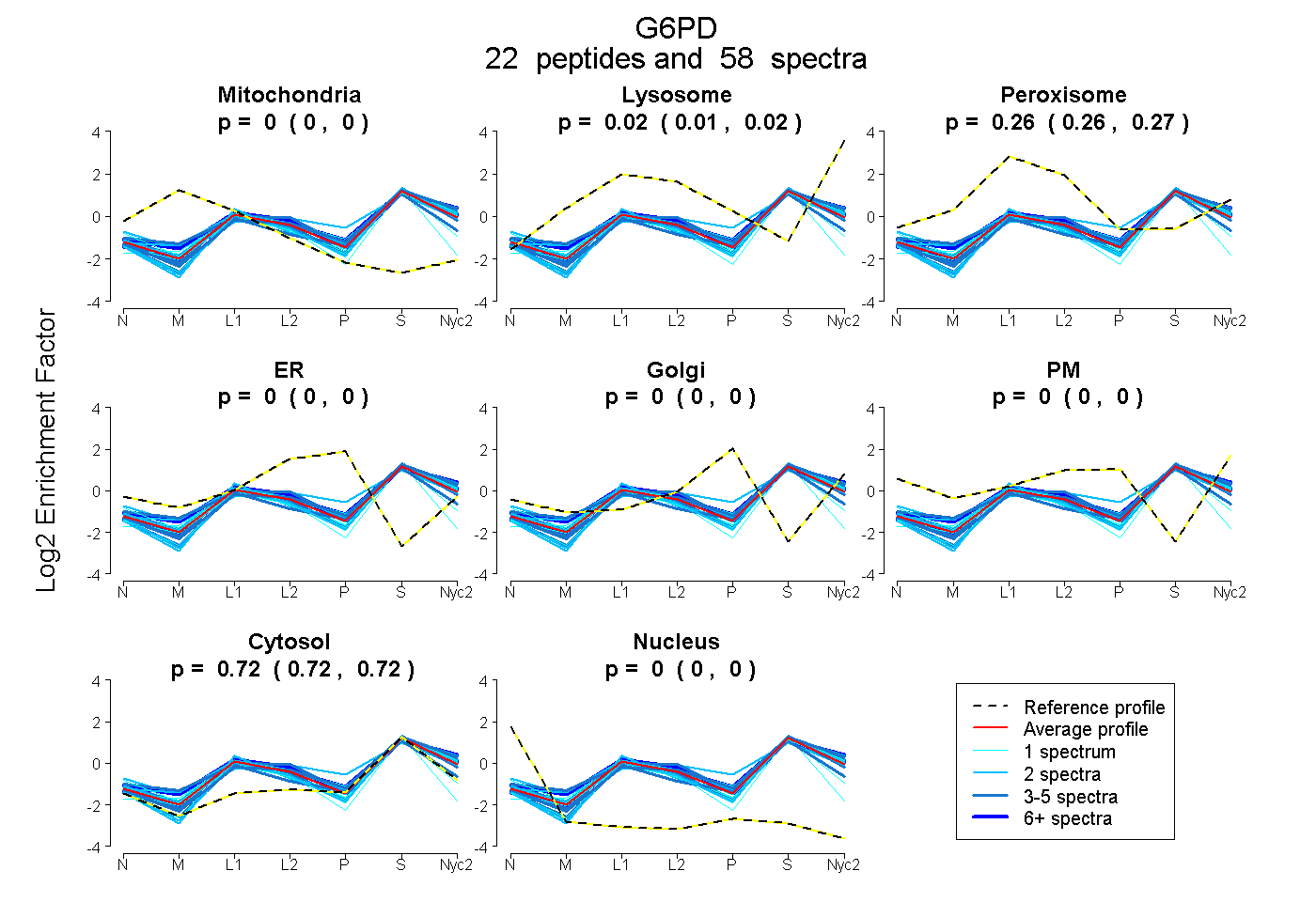
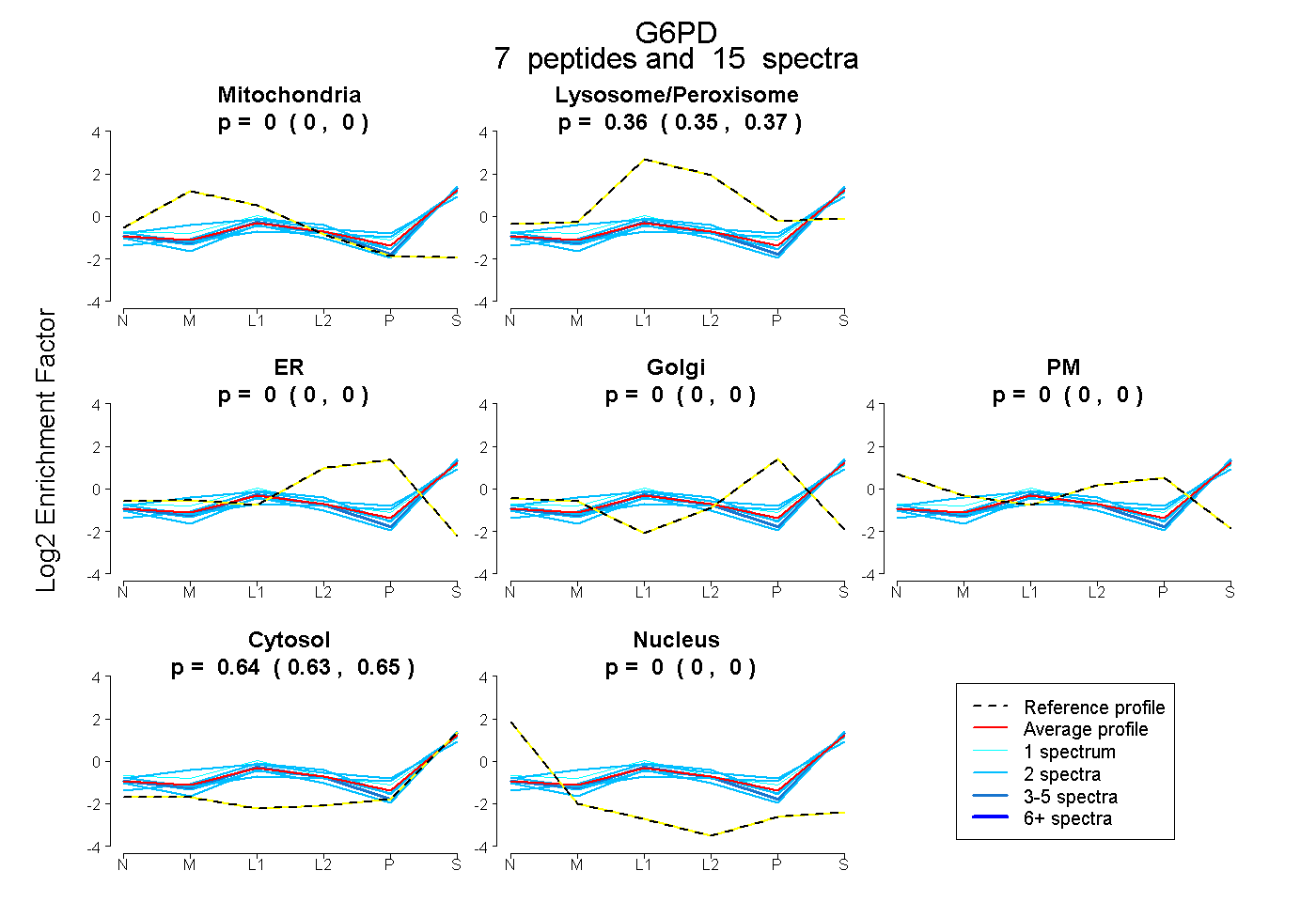
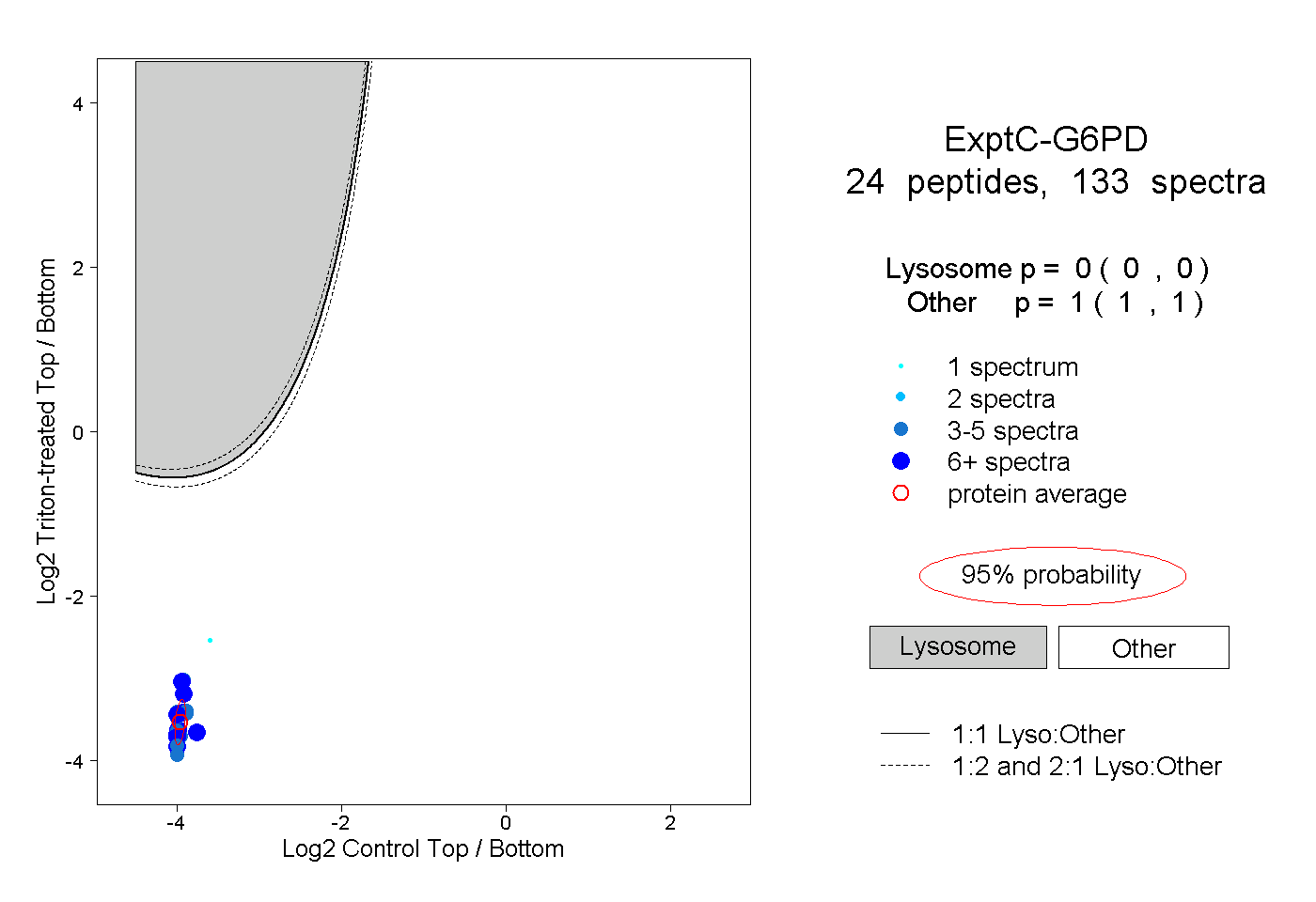
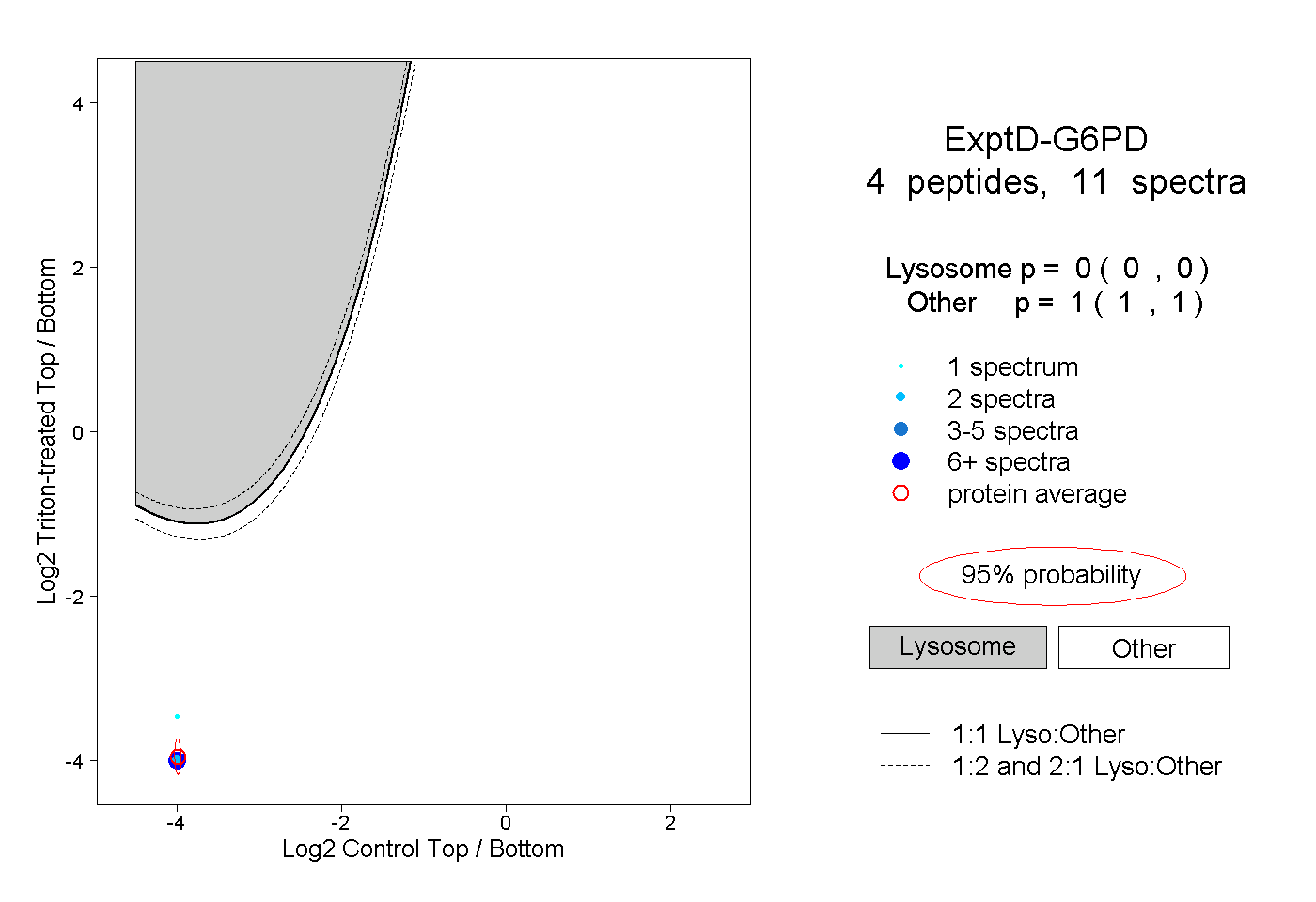
| 4 spectra, WDGVPFILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VGFQYEGTYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GGYFDEFGIIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IIVEKPFGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LPDAYER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, IFTPLLHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EDQIYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WVNPHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LEEFFAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, EKPQPIPYVYGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NELVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EMVQNLMVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IFGPIWNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QSEPFFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EPFGTEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IDHYLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VQPNEAVYTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LTVDDIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, VTPEERPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GPTEADELMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DGLLPEDTFIVGYAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, KPGMFFNPEESELDLTYGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DVAGDIFHQQCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NSYVAGQYDDPASYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |