peptides
spectra
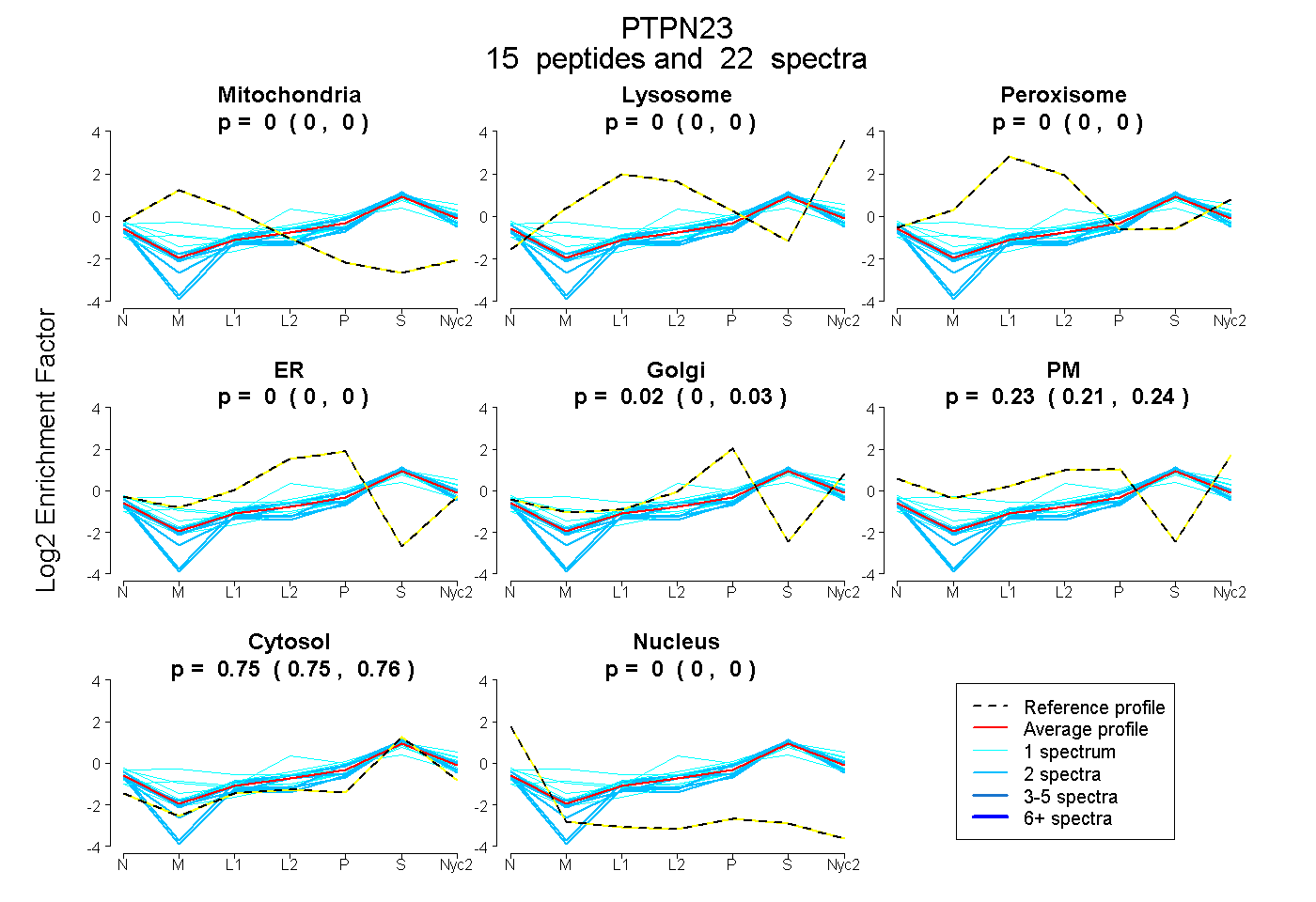
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.005 | 0.031
0.211 | 0.241
0.748 | 0.759
0.000 | 0.000
peptides
spectra
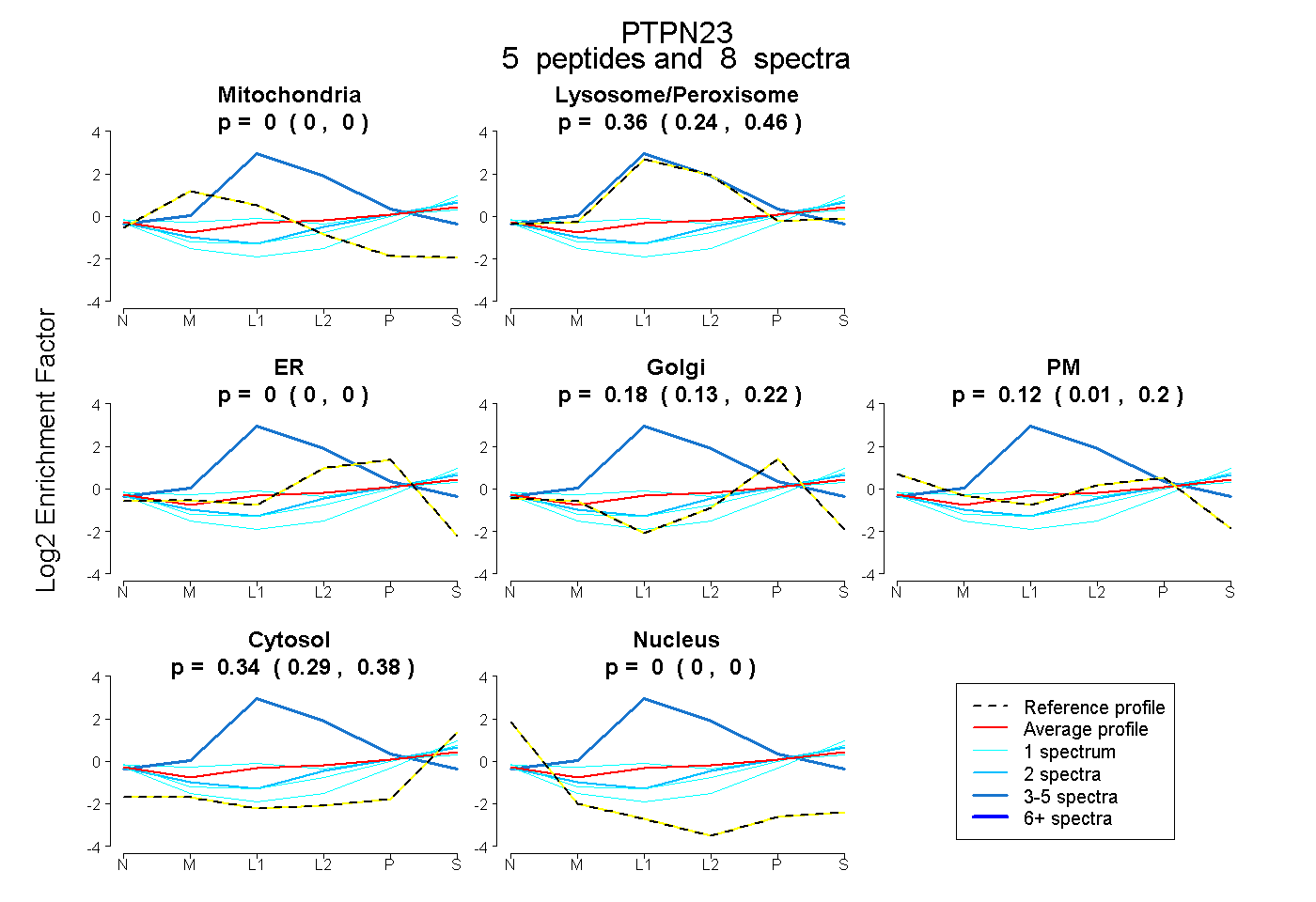
0.000 | 0.000
0.244 | 0.457
0.000 | 0.000
0.130 | 0.216
0.008 | 0.200
0.295 | 0.384
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.005 | 0.031 |
0.228 0.211 | 0.241 |
0.754 0.748 | 0.759 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.357 0.244 | 0.457 |
0.000 0.000 | 0.000 |
0.178 0.130 | 0.216 |
0.122 0.008 | 0.200 |
0.343 0.295 | 0.384 |
0.000 0.000 | 0.000 |
| 1 spectrum, VAALLER | 0.000 | 0.000 | 0.000 | 0.083 | 0.257 | 0.659 | 0.000 | |||
| 3 spectra, LLSGPLDQVR | 0.000 | 0.971 | 0.029 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SFLVAR | 0.000 | 0.185 | 0.000 | 0.189 | 0.183 | 0.442 | 0.000 | |||
| 1 spectrum, GQPDTVQDALR | 0.000 | 0.354 | 0.000 | 0.127 | 0.210 | 0.309 | 0.000 | |||
| 1 spectrum, VLSLQFR | 0.000 | 0.129 | 0.000 | 0.085 | 0.288 | 0.498 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
25 spectra |
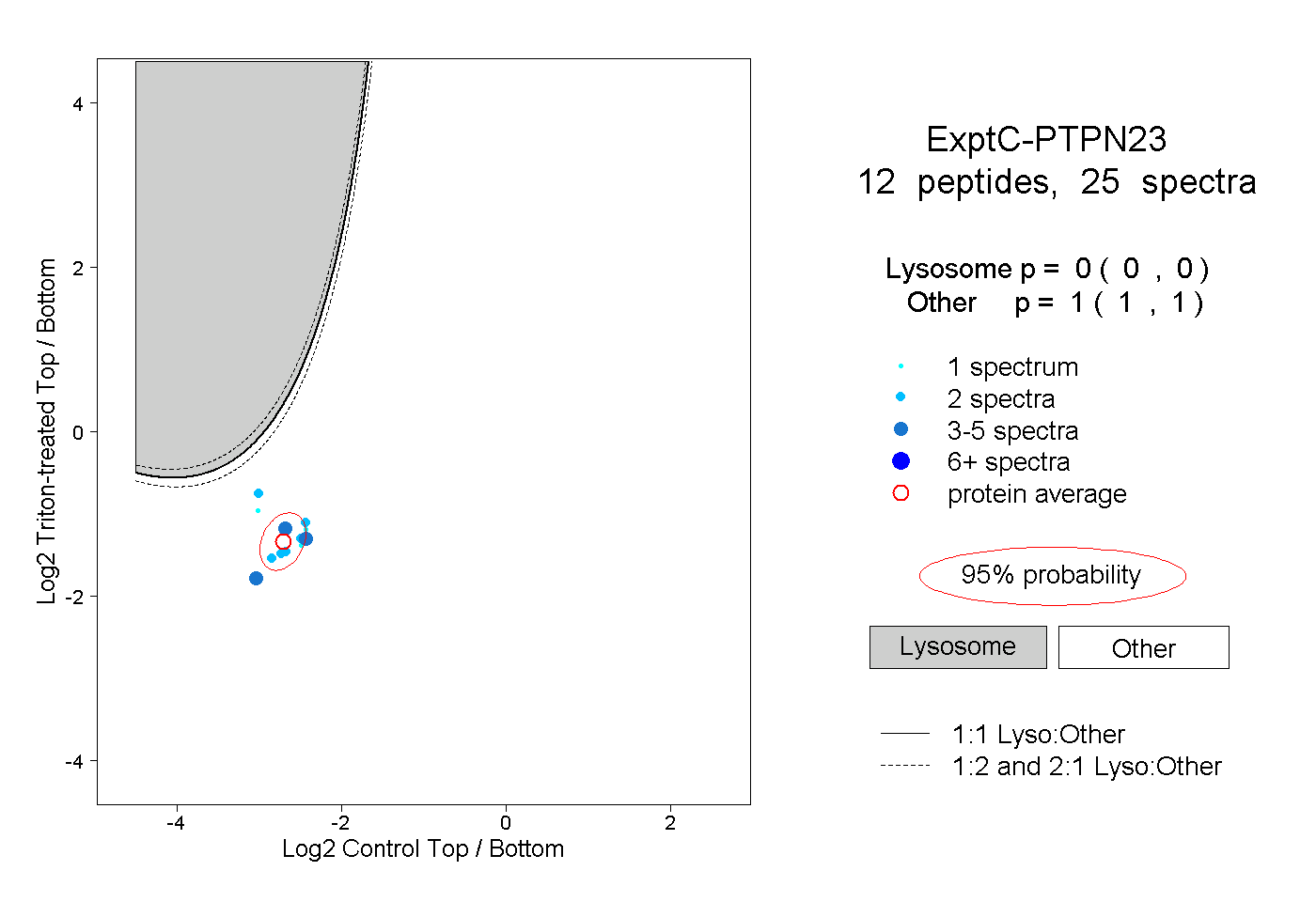 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
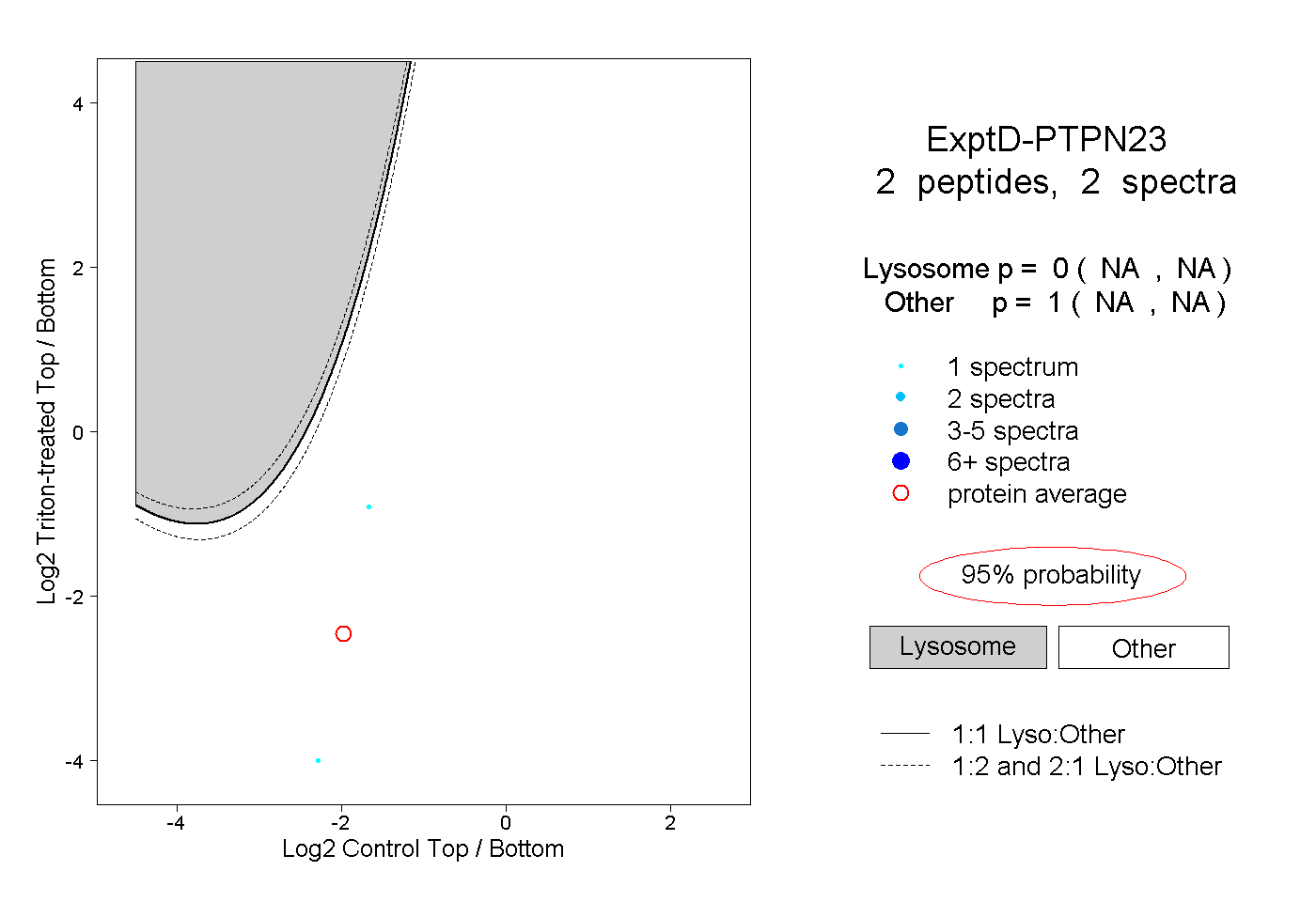 |
0.000 NA | NA |
1.000 NA | NA |