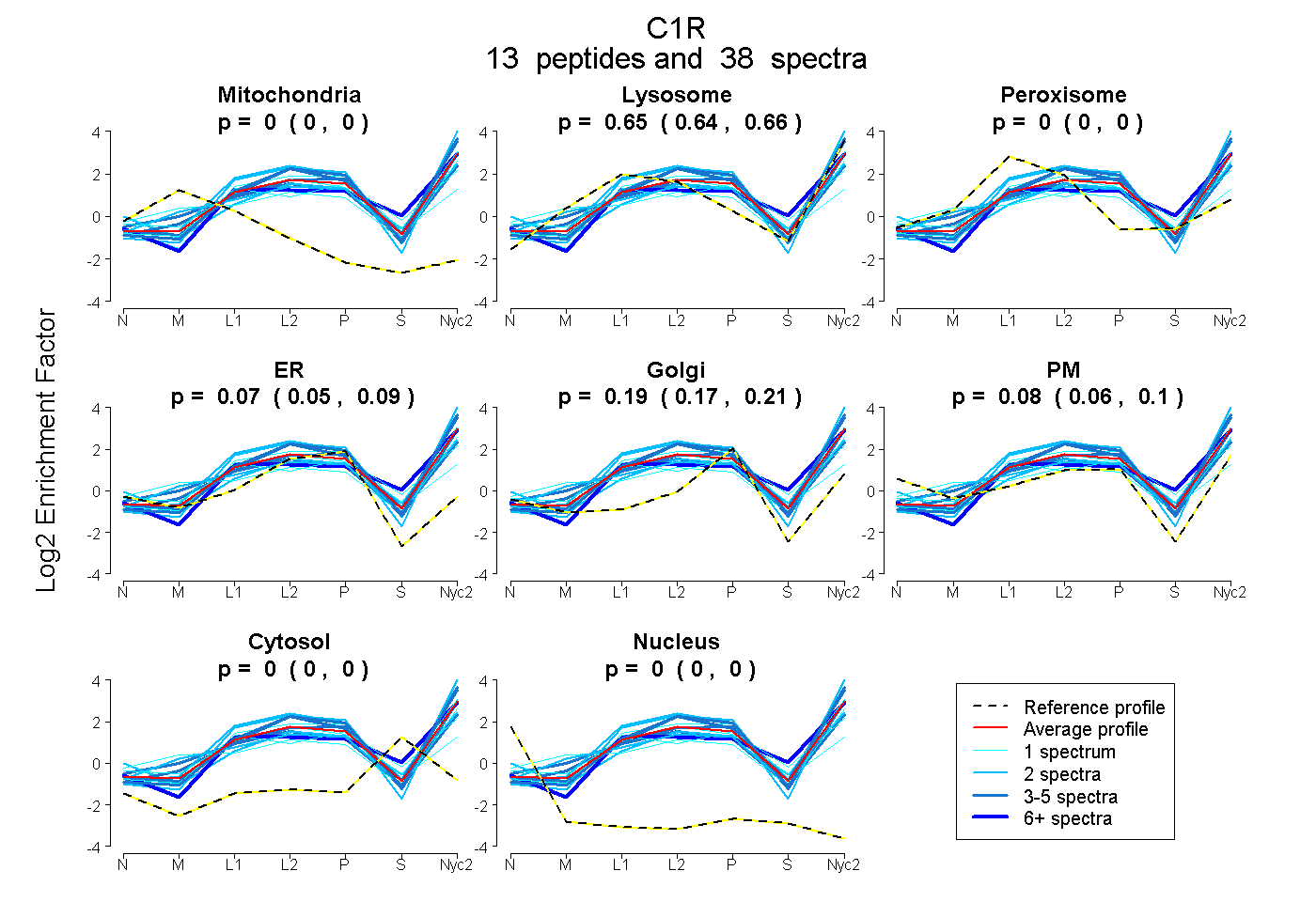
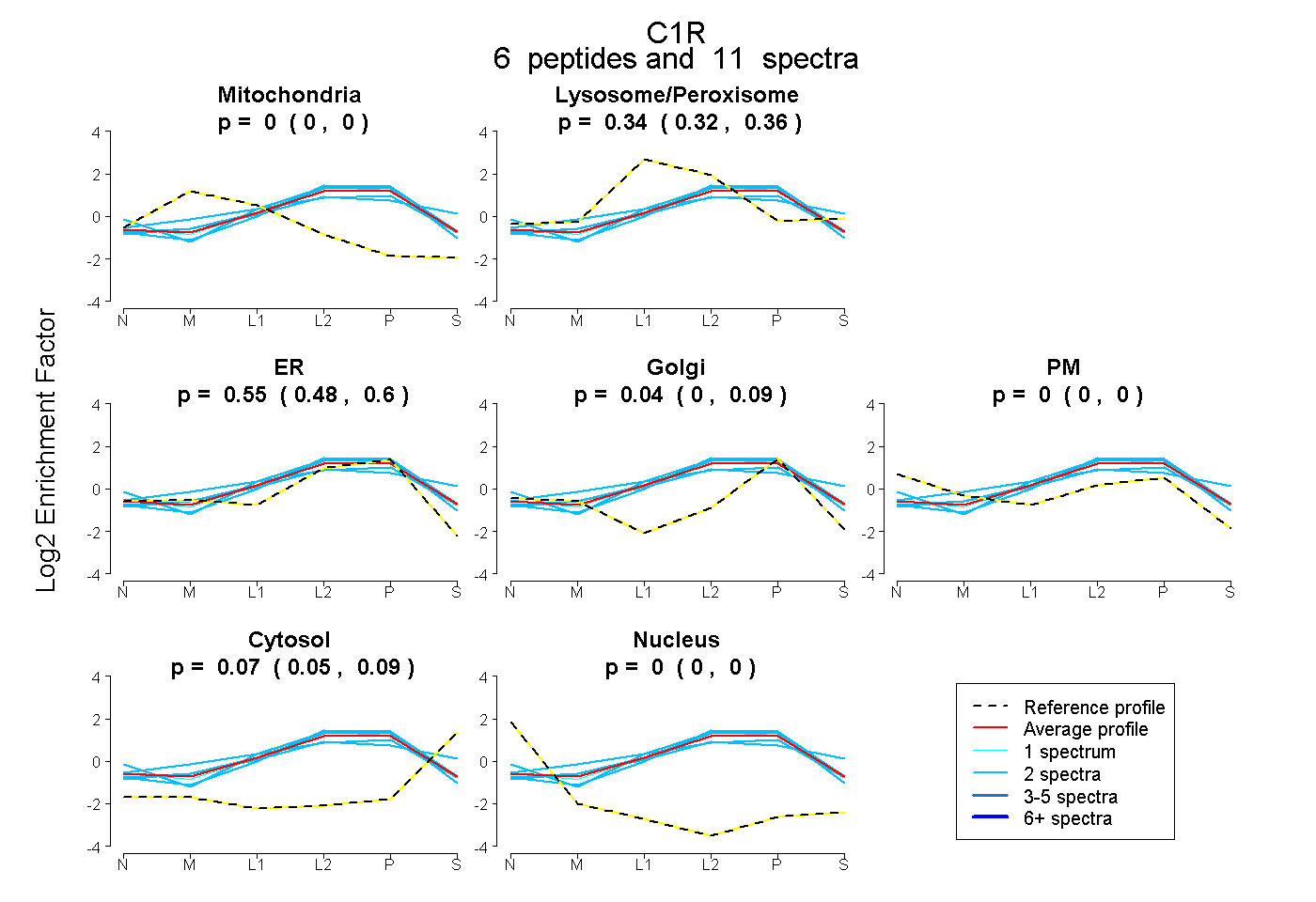
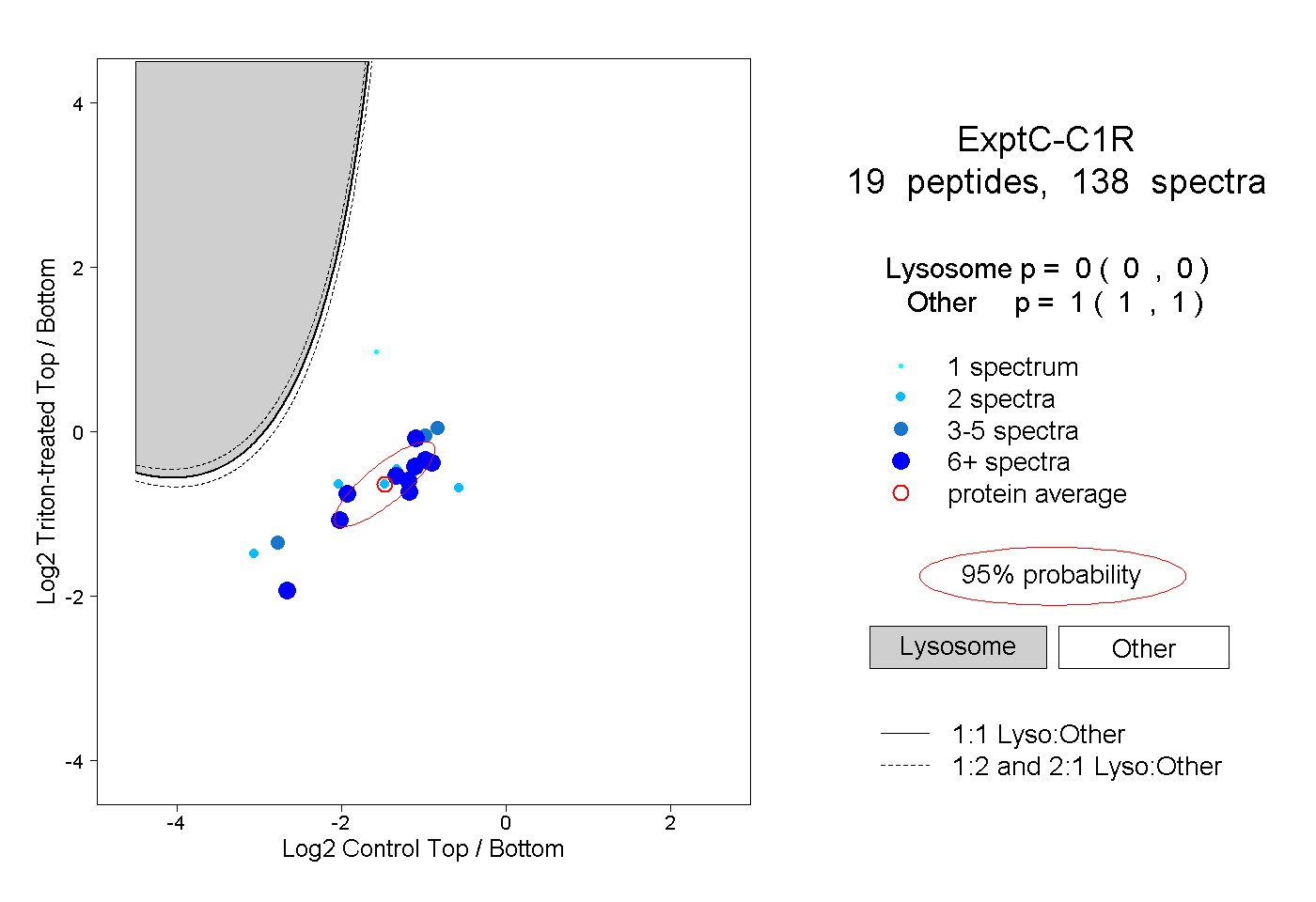
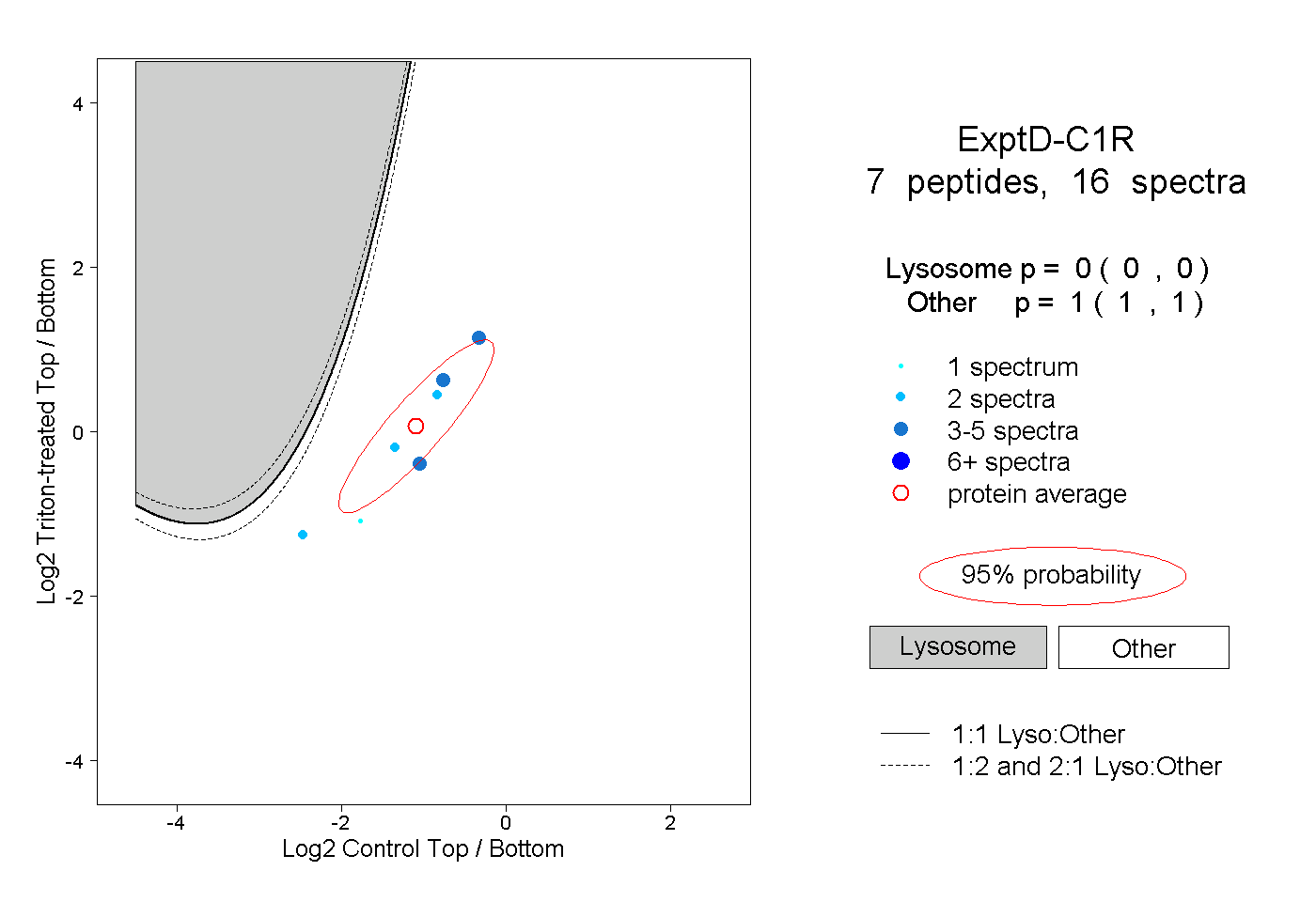
| 4 spectra, FCGQQDSPQGNPPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, GVNTYEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NEEEGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LPIADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, IIGGQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GGGALLGDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, CLPVCGKPVNPVTQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SLSNGDFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, WILTAAHTIYPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DVFLGHTNVEEIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VIIHPDYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IQYYCHDPYYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LGHHPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EFMSQGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, HDACQGDSGGVFAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ANPGNFPWQAFTNIHGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, DYFIVTCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, GLTVHLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, IAFNLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |