peptides
spectra
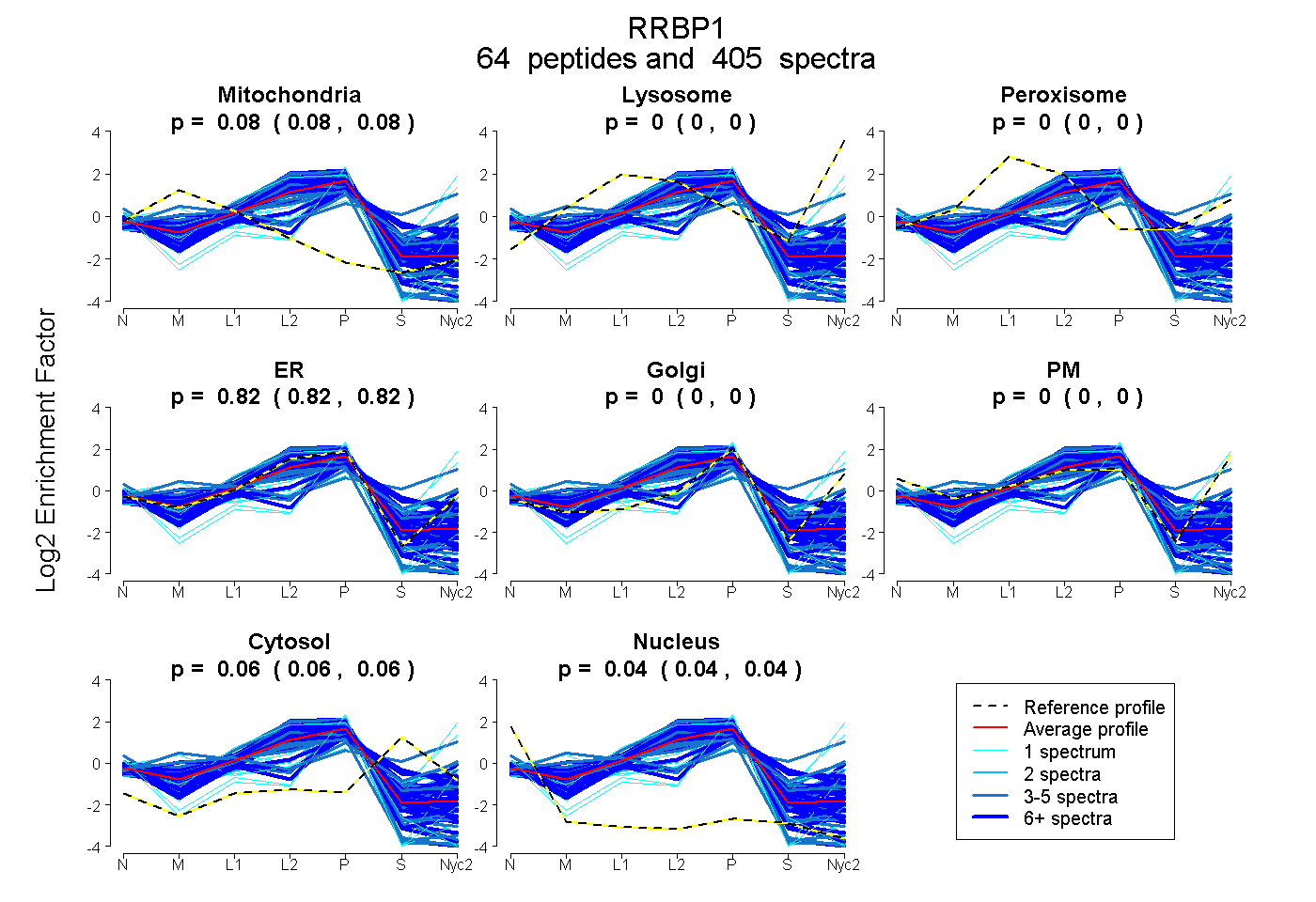
0.075 | 0.078
0.000 | 0.000
0.000 | 0.000
0.817 | 0.819
0.000 | 0.000
0.000 | 0.000
0.060 | 0.063
0.042 | 0.045
peptides
spectra
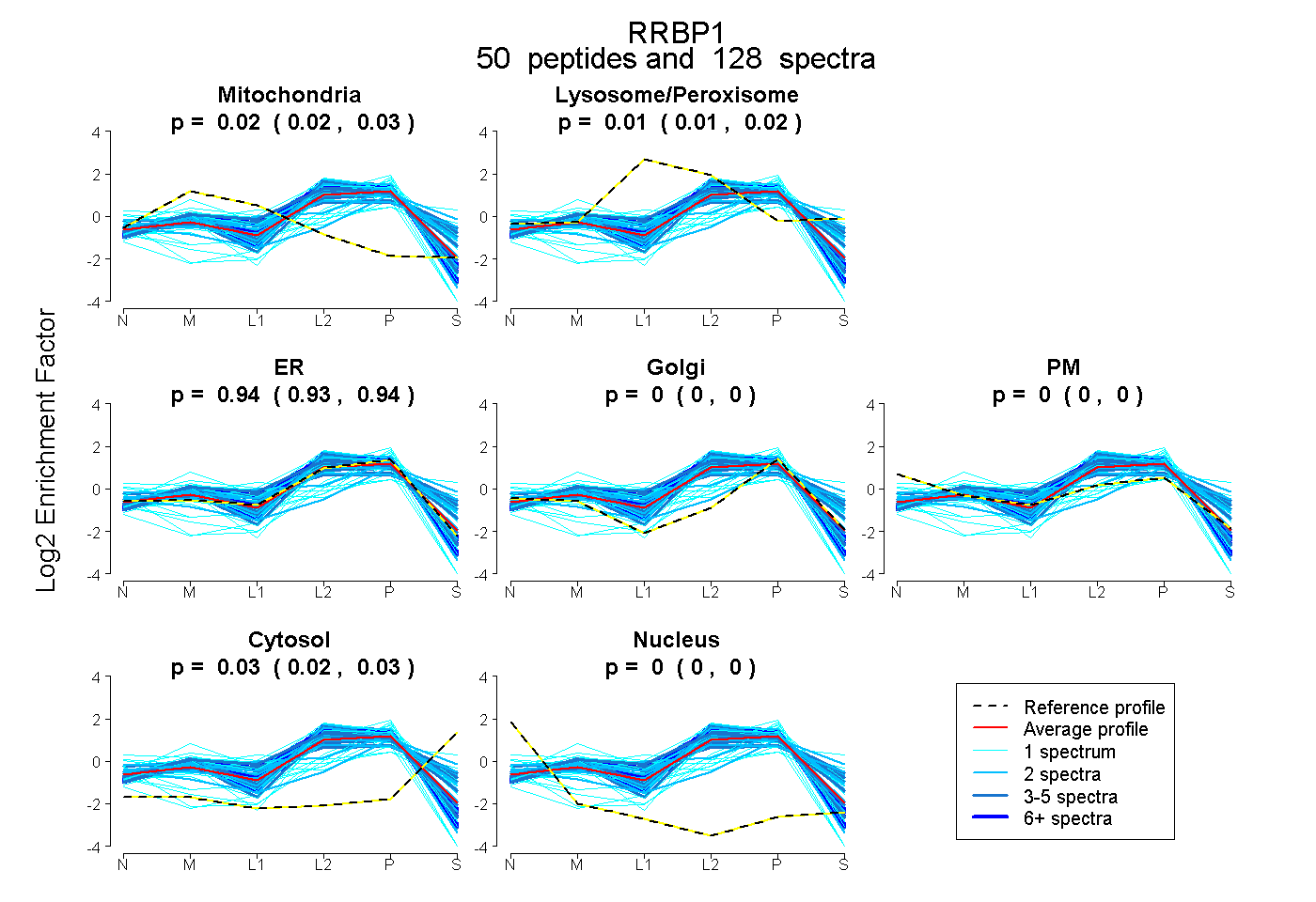
0.017 | 0.026
0.007 | 0.015
0.934 | 0.942
0.000 | 0.000
0.000 | 0.000
0.024 | 0.032
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
405 spectra |
 |
0.077 0.075 | 0.078 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.818 0.817 | 0.819 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.062 0.060 | 0.063 |
0.044 0.042 | 0.045 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
128 spectra |
 |
0.022 0.017 | 0.026 |
0.011 0.007 | 0.015 |
0.939 0.934 | 0.942 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.024 | 0.032 |
0.000 0.000 | 0.000 |
| 1 spectrum, SEGSPNQGK | 0.000 | 0.000 | 0.397 | 0.603 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VGAAEEELQK | 0.000 | 0.330 | 0.263 | 0.245 | 0.045 | 0.117 | 0.000 | |||
| 2 spectra, QLHLAEAQTK | 0.052 | 0.037 | 0.911 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QQLSDMR | 0.000 | 0.078 | 0.866 | 0.005 | 0.000 | 0.052 | 0.000 | |||
| 3 spectra, QILQLQASHK | 0.000 | 0.152 | 0.659 | 0.000 | 0.000 | 0.189 | 0.000 | |||
| 2 spectra, SVEEEER | 0.000 | 0.222 | 0.545 | 0.166 | 0.000 | 0.067 | 0.000 | |||
| 2 spectra, GDPVAVLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IPEHDLDPNVTIILK | 0.111 | 0.000 | 0.889 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AEGVQSQGK | 0.000 | 0.000 | 0.489 | 0.511 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, LIEILSEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EVPMVAVPPVGSK | 0.000 | 0.242 | 0.000 | 0.733 | 0.000 | 0.025 | 0.000 | |||
| 3 spectra, LTAEFEEAQSTACR | 0.000 | 0.000 | 0.911 | 0.089 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TILAETEGMLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LQEELEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LLATEQEDAAVAK | 0.000 | 0.398 | 0.147 | 0.365 | 0.000 | 0.090 | 0.000 | |||
| 1 spectrum, EMASEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, AMEALALAER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TEATLEDEQTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QNTELAK | 0.000 | 0.207 | 0.472 | 0.000 | 0.000 | 0.321 | 0.000 | |||
| 6 spectra, LQQENSILR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GEANQNQAK | 0.000 | 0.130 | 0.352 | 0.409 | 0.000 | 0.108 | 0.000 | |||
| 2 spectra, TPVATVPAMPQEK | 0.000 | 0.170 | 0.000 | 0.604 | 0.000 | 0.226 | 0.000 | |||
| 1 spectrum, ESEEALQK | 0.000 | 0.121 | 0.873 | 0.000 | 0.000 | 0.005 | 0.000 | |||
| 2 spectra, SEMTPAQGK | 0.000 | 0.376 | 0.063 | 0.561 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AQTSHANLR | 0.000 | 0.447 | 0.000 | 0.464 | 0.076 | 0.014 | 0.000 | |||
| 3 spectra, DALNQATSQVESK | 0.064 | 0.000 | 0.920 | 0.000 | 0.000 | 0.016 | 0.000 | |||
| 1 spectrum, EAEETQNSLQAECDQYR | 0.364 | 0.000 | 0.500 | 0.136 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TGVIQDTWHK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TLQEQLENGPNTQLAR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SIEALLEAGQAQDSQASR | 0.044 | 0.226 | 0.612 | 0.076 | 0.000 | 0.042 | 0.000 | |||
| 5 spectra, QSNELALVR | 0.000 | 0.046 | 0.843 | 0.000 | 0.000 | 0.111 | 0.000 | |||
| 3 spectra, LTSDLGR | 0.026 | 0.000 | 0.974 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EHTSHLEAELEK | 0.000 | 0.399 | 0.000 | 0.176 | 0.297 | 0.128 | 0.000 | |||
| 4 spectra, VAELHSK | 0.045 | 0.144 | 0.811 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ASAPATSSQGK | 0.000 | 0.000 | 0.446 | 0.418 | 0.000 | 0.136 | 0.000 | |||
| 2 spectra, GELESSDQVR | 0.000 | 0.004 | 0.910 | 0.000 | 0.000 | 0.086 | 0.000 | |||
| 3 spectra, LQSSEVEVK | 0.034 | 0.000 | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ETSYEEALANQR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, HMAAASAECQNYAK | 0.132 | 0.218 | 0.000 | 0.210 | 0.430 | 0.011 | 0.000 | |||
| 1 spectrum, AAAGEAK | 0.000 | 0.152 | 0.489 | 0.000 | 0.311 | 0.048 | 0.000 | |||
| 5 spectra, EQEIAAVQAR | 0.000 | 0.119 | 0.754 | 0.000 | 0.000 | 0.128 | 0.000 | |||
| 7 spectra, HLEDLVEK | 0.009 | 0.093 | 0.898 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, CEELSDLHGQLK | 0.000 | 0.267 | 0.624 | 0.000 | 0.000 | 0.110 | 0.000 | |||
| 4 spectra, EVQQLQGK | 0.000 | 0.316 | 0.181 | 0.285 | 0.158 | 0.061 | 0.000 | |||
| 1 spectrum, QEAPAK | 0.000 | 0.000 | 0.805 | 0.195 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GEGAQNQAK | 0.000 | 0.000 | 0.860 | 0.140 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LQELIK | 0.000 | 0.000 | 0.732 | 0.000 | 0.265 | 0.003 | 0.000 | |||
| 1 spectrum, AEDGSSSK | 0.000 | 0.000 | 0.799 | 0.201 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, AENSQLTER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TTQEQLTK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
816 spectra |
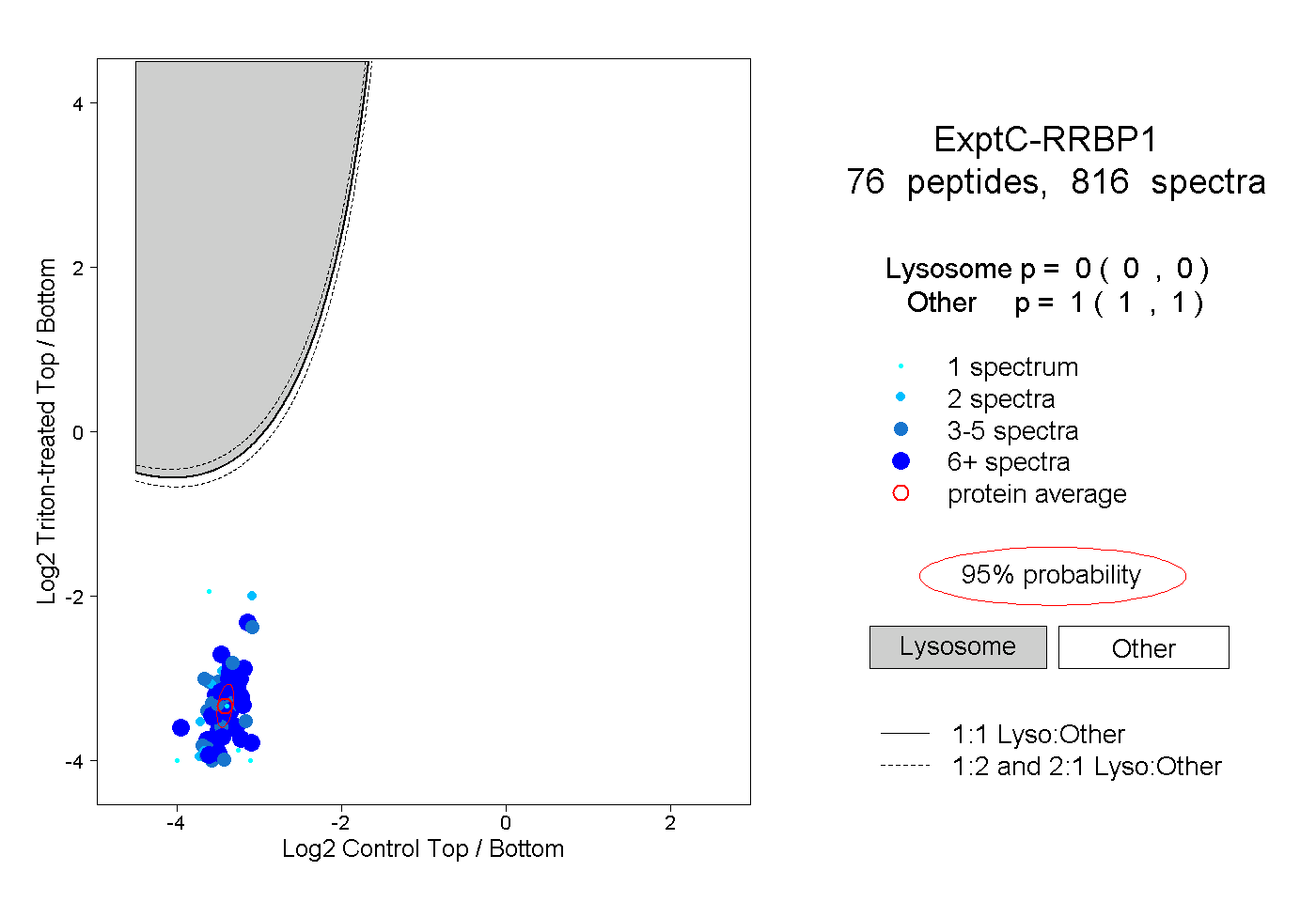 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
91 spectra |
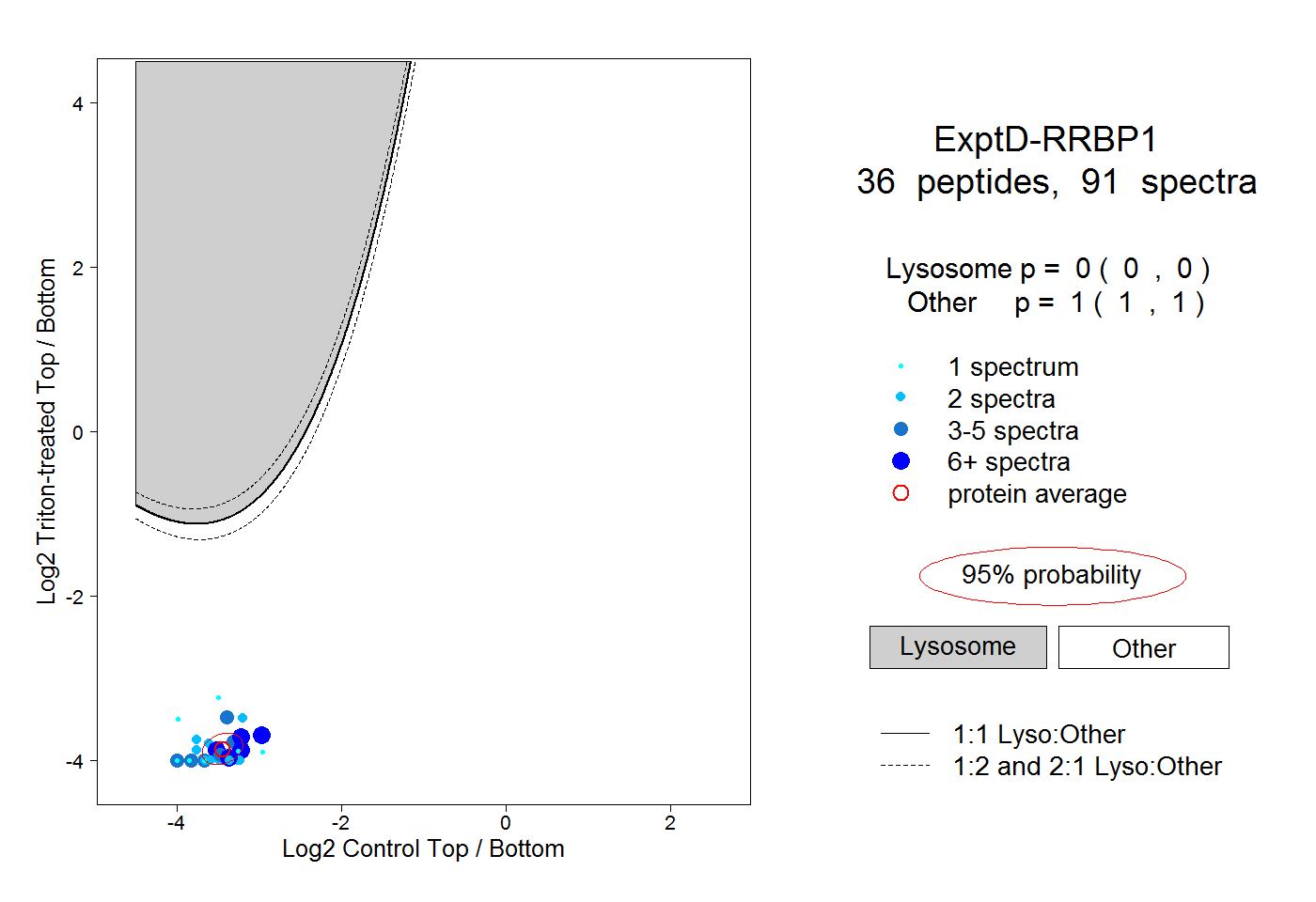 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |