peptides
spectra
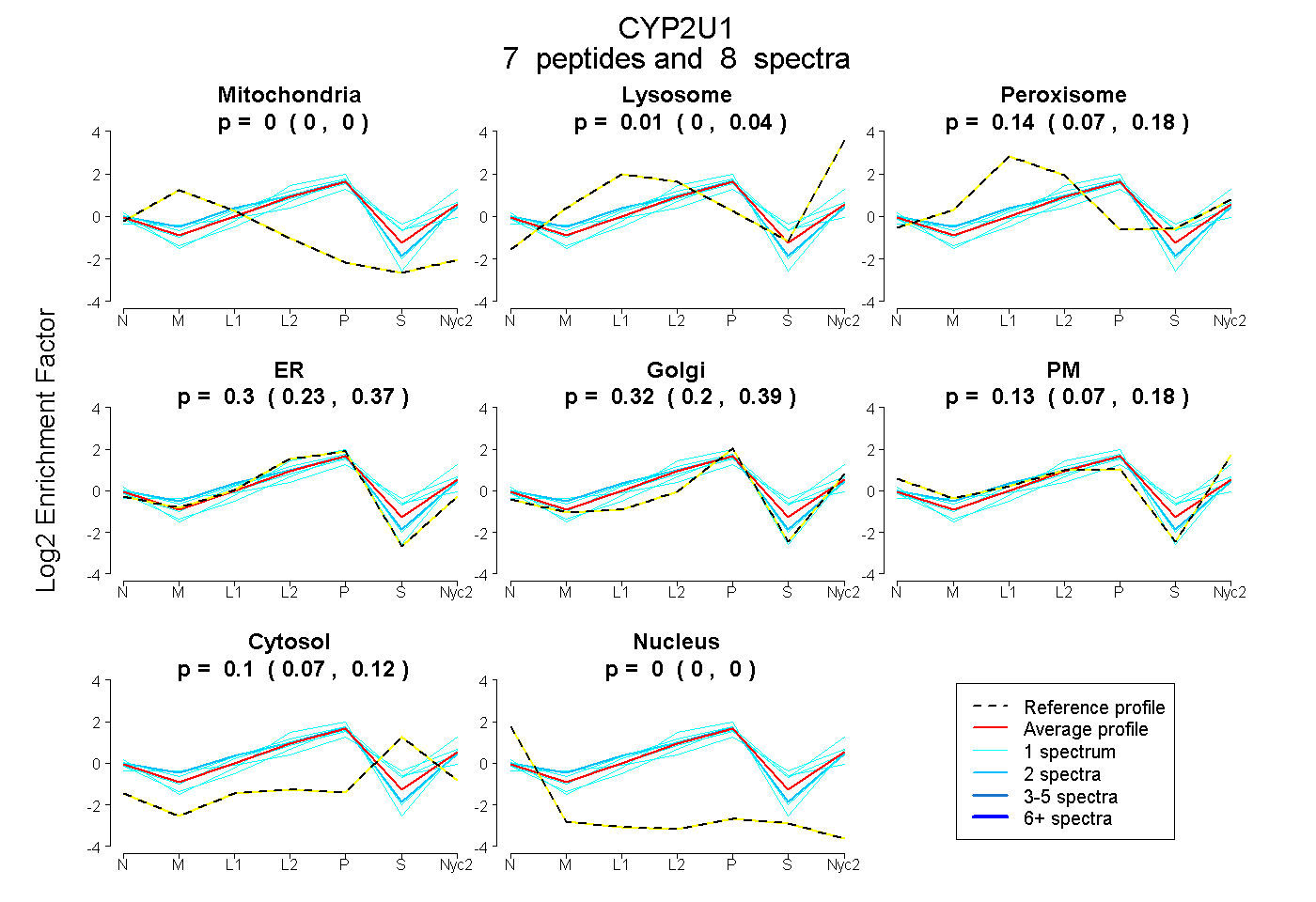
0.000 | 0.000
0.000 | 0.044
0.072 | 0.182
0.233 | 0.374
0.204 | 0.392
0.074 | 0.177
0.071 | 0.124
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.008 0.000 | 0.044 |
0.142 0.072 | 0.182 |
0.303 0.233 | 0.374 |
0.319 0.204 | 0.392 |
0.131 0.074 | 0.177 |
0.097 0.071 | 0.124 |
0.000 0.000 | 0.000 |
| 1 spectrum, HVYLAR | 0.000 | 0.000 | 0.024 | 0.488 | 0.212 | 0.005 | 0.271 | 0.000 | ||
| 2 spectra, GIVFAHYGPIWK | 0.000 | 0.000 | 0.193 | 0.365 | 0.321 | 0.121 | 0.000 | 0.000 | ||
| 1 spectrum, LSLEPR | 0.000 | 0.220 | 0.018 | 0.229 | 0.170 | 0.207 | 0.156 | 0.000 | ||
| 1 spectrum, ETFIPFGIGK | 0.000 | 0.047 | 0.259 | 0.000 | 0.512 | 0.000 | 0.182 | 0.000 | ||
| 1 spectrum, IIEEFAYVK | 0.000 | 0.000 | 0.000 | 0.585 | 0.199 | 0.216 | 0.000 | 0.000 | ||
| 1 spectrum, LVVVLSDFQSVR | 0.000 | 0.000 | 0.125 | 0.475 | 0.210 | 0.191 | 0.000 | 0.000 | ||
| 1 spectrum, EALVQQAEVFSDRPR | 0.000 | 0.000 | 0.208 | 0.222 | 0.354 | 0.060 | 0.156 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
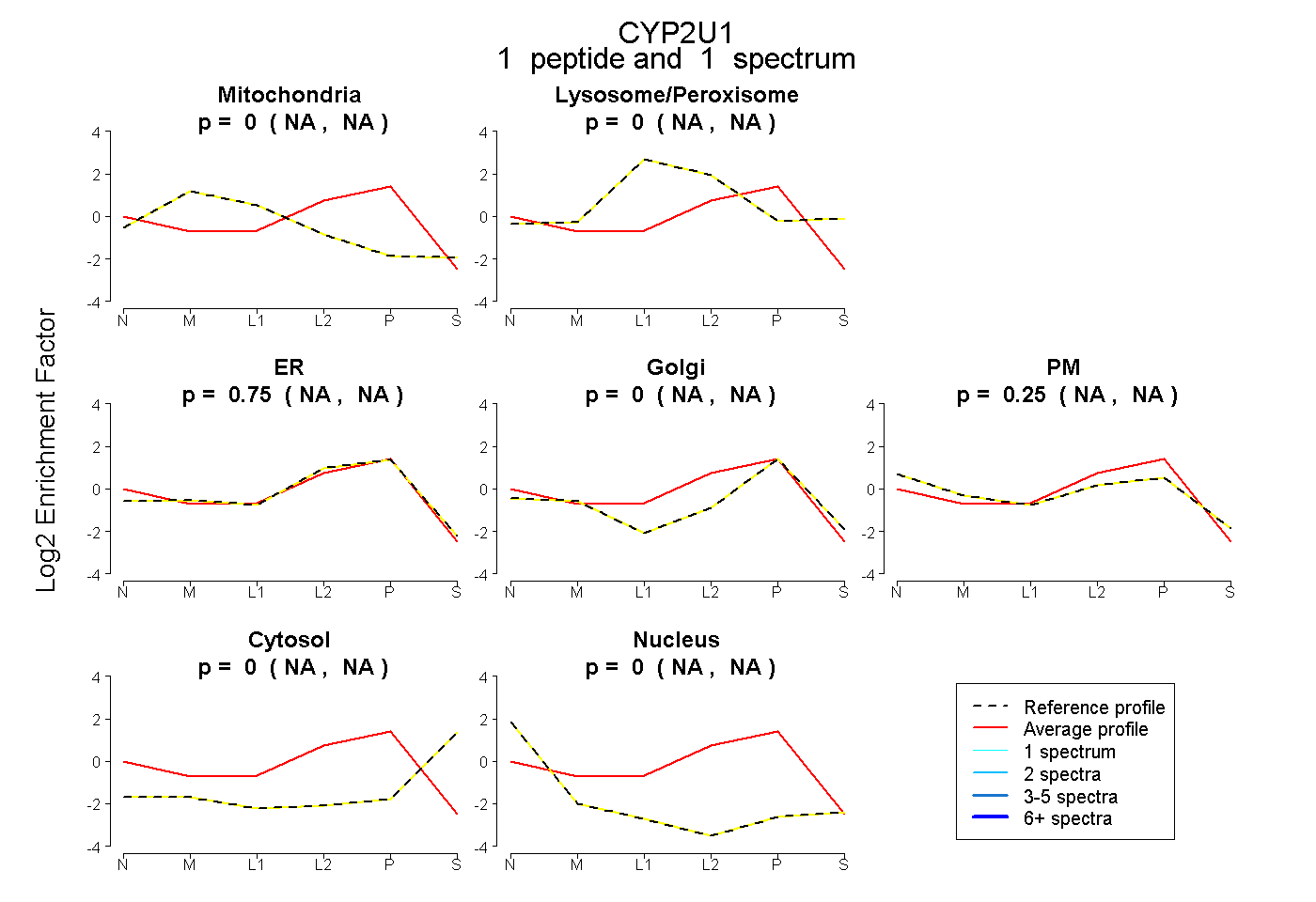 |
0.000 NA | NA |
0.000 NA | NA |
0.751 NA | NA |
0.000 NA | NA |
0.245 NA | NA |
0.000 NA | NA |
0.003 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
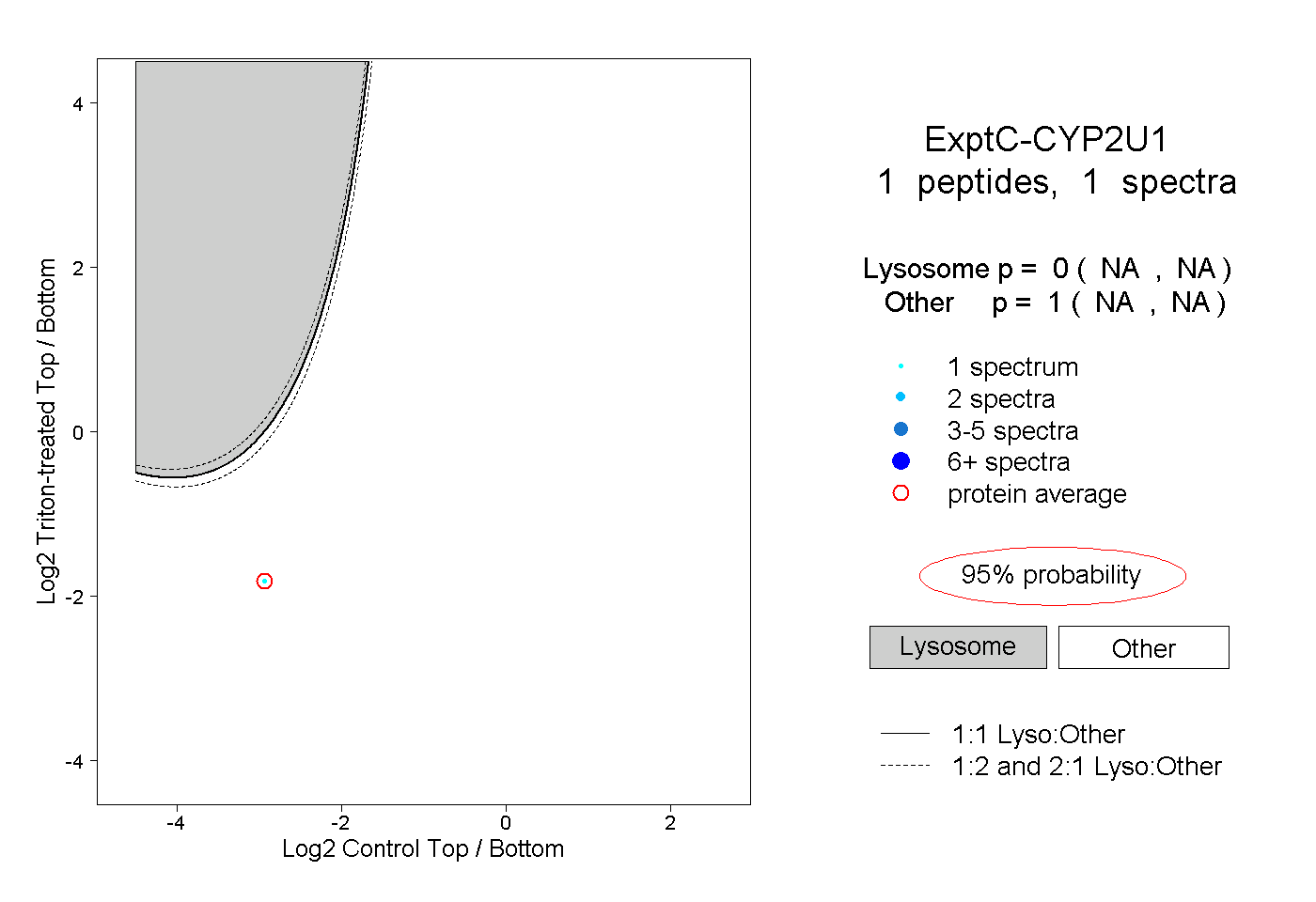 |
0.000 NA | NA |
1.000 NA | NA |