peptides
spectra
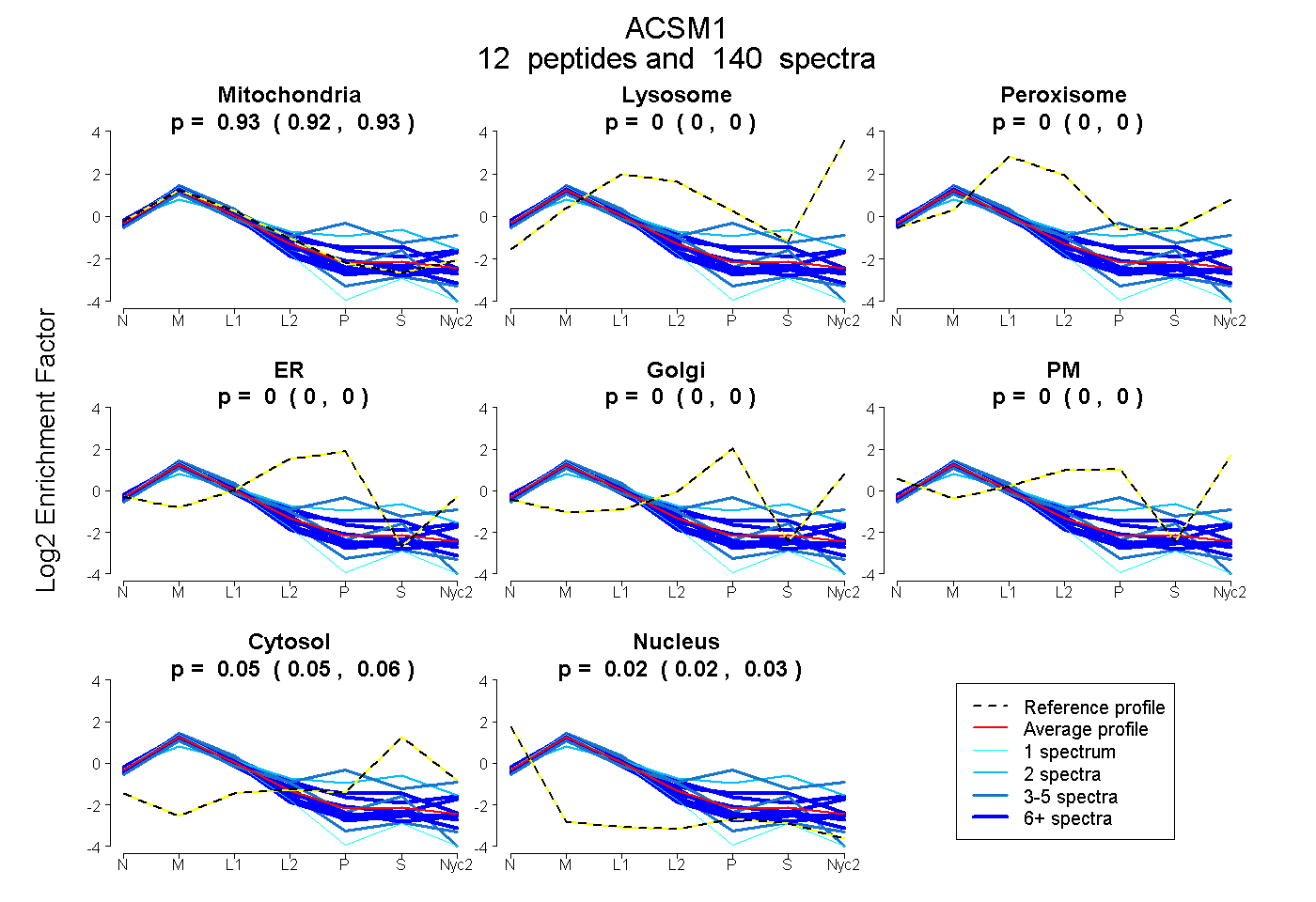
0.923 | 0.928
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.047 | 0.056
0.019 | 0.025
peptides
spectra
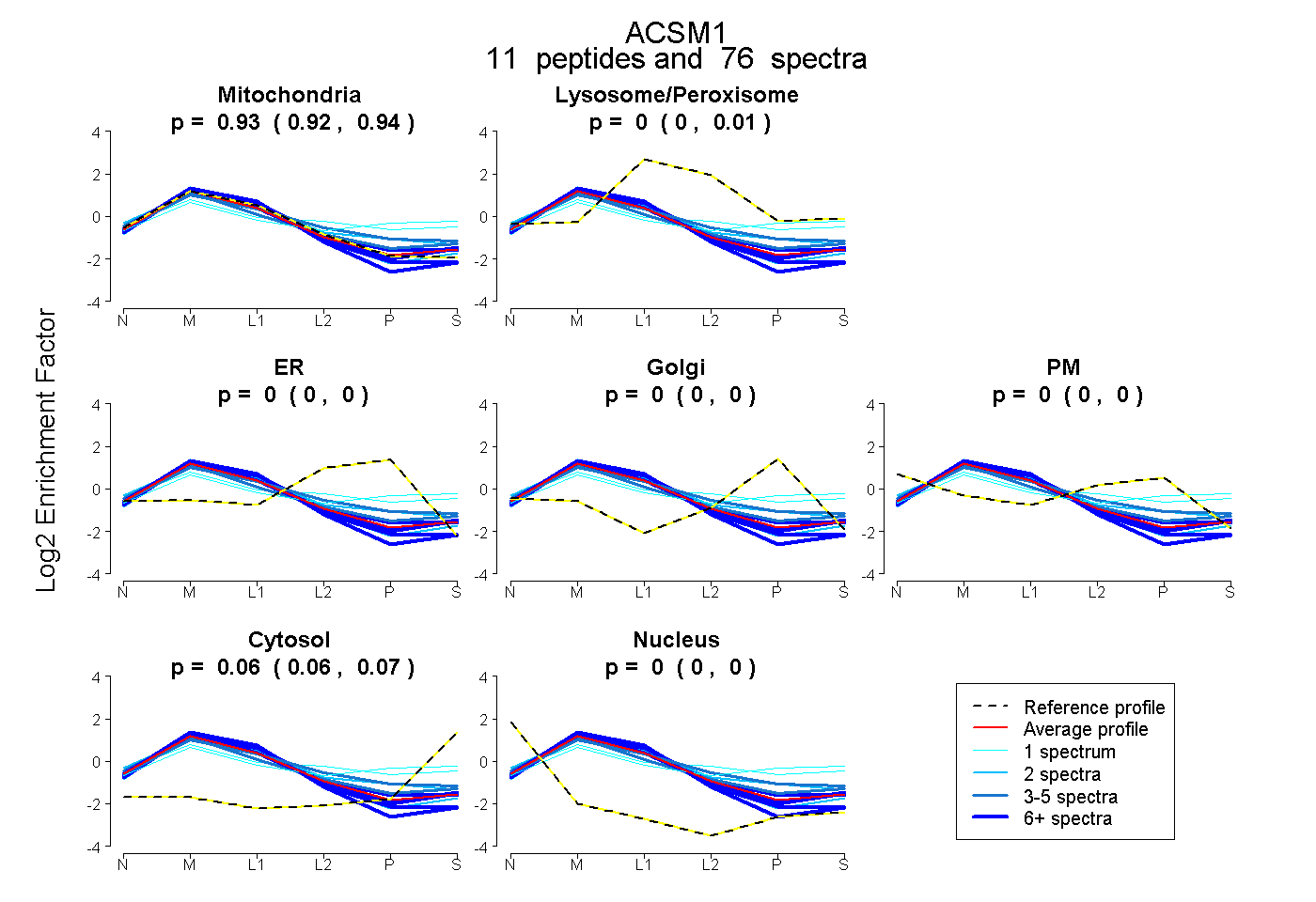
0.924 | 0.937
0.000 | 0.008
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.060 | 0.068
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
140 spectra |
 |
0.926 0.923 | 0.928 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.052 0.047 | 0.056 |
0.022 0.019 | 0.025 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
76 spectra |
 |
0.931 0.924 | 0.937 |
0.004 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.065 0.060 | 0.068 |
0.000 0.000 | 0.000 |
| 10 spectra, VIVETLFK | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | |||
| 18 spectra, LALILPR | 0.991 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | |||
| 3 spectra, VPEWWLVTVGCIR | 0.672 | 0.150 | 0.000 | 0.114 | 0.000 | 0.065 | 0.000 | |||
| 5 spectra, SSVPSCR | 0.808 | 0.015 | 0.000 | 0.000 | 0.078 | 0.099 | 0.000 | |||
| 12 spectra, TGVIFIPGTAQMK | 0.925 | 0.000 | 0.000 | 0.000 | 0.000 | 0.075 | 0.000 | |||
| 1 spectrum, WLISGDGAQR | 0.338 | 0.224 | 0.000 | 0.230 | 0.000 | 0.207 | 0.000 | |||
| 2 spectra, IQMSQAK | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | |||
| 8 spectra, AANVFEQTCGLQHGDR | 0.949 | 0.007 | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | |||
| 1 spectrum, DPMVIFFTSGTTGYPK | 0.404 | 0.234 | 0.000 | 0.126 | 0.081 | 0.155 | 0.000 | |||
| 2 spectra, SASPDHTCVK | 0.733 | 0.120 | 0.000 | 0.120 | 0.002 | 0.025 | 0.000 | |||
| 14 spectra, HNQGLAFR | 0.913 | 0.047 | 0.000 | 0.007 | 0.000 | 0.033 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
371 spectra |
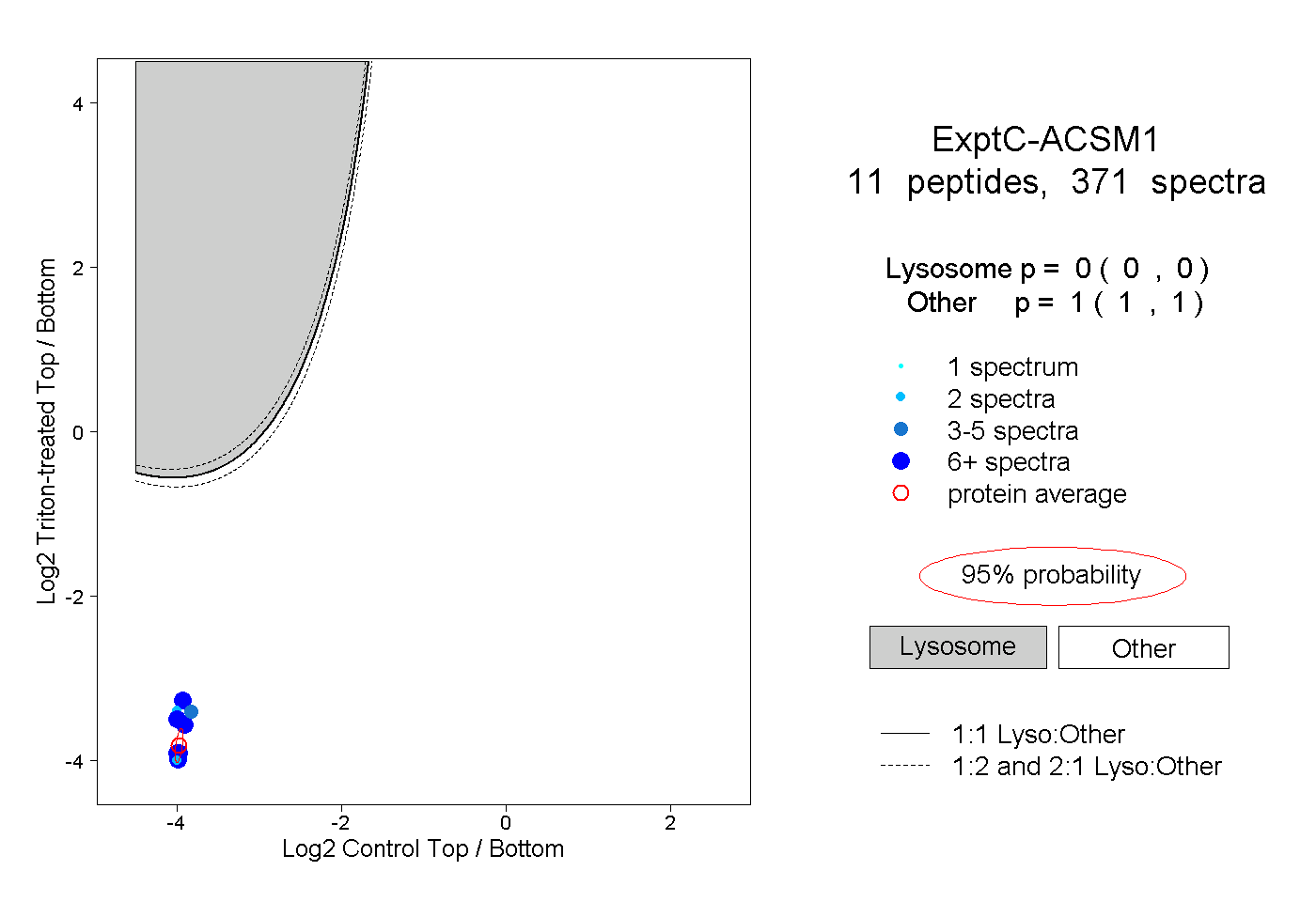 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
43 spectra |
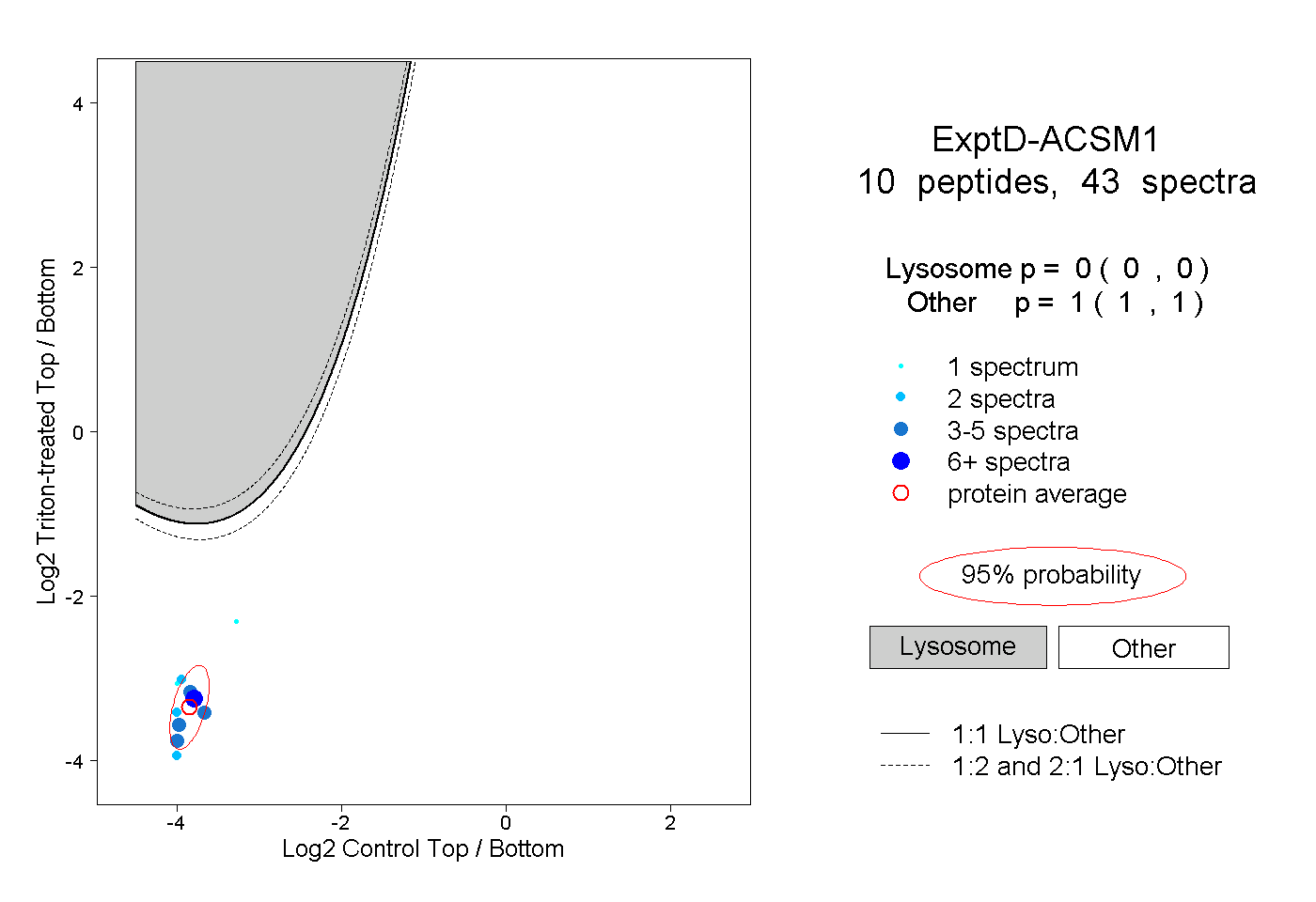 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |