peptides
spectra
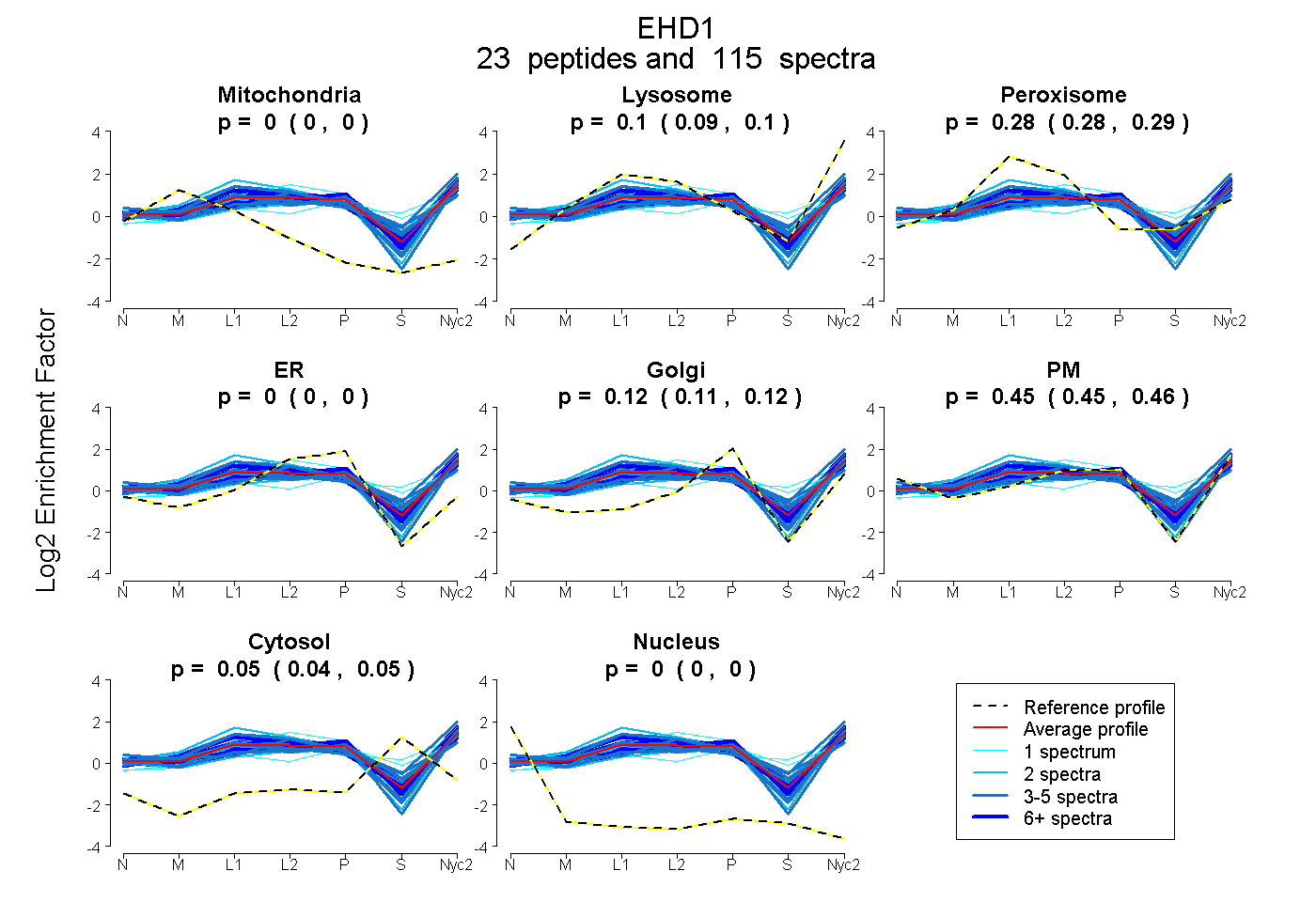
0.000 | 0.000
0.094 | 0.101
0.279 | 0.289
0.000 | 0.000
0.111 | 0.122
0.447 | 0.459
0.044 | 0.049
0.000 | 0.000
peptides
spectra
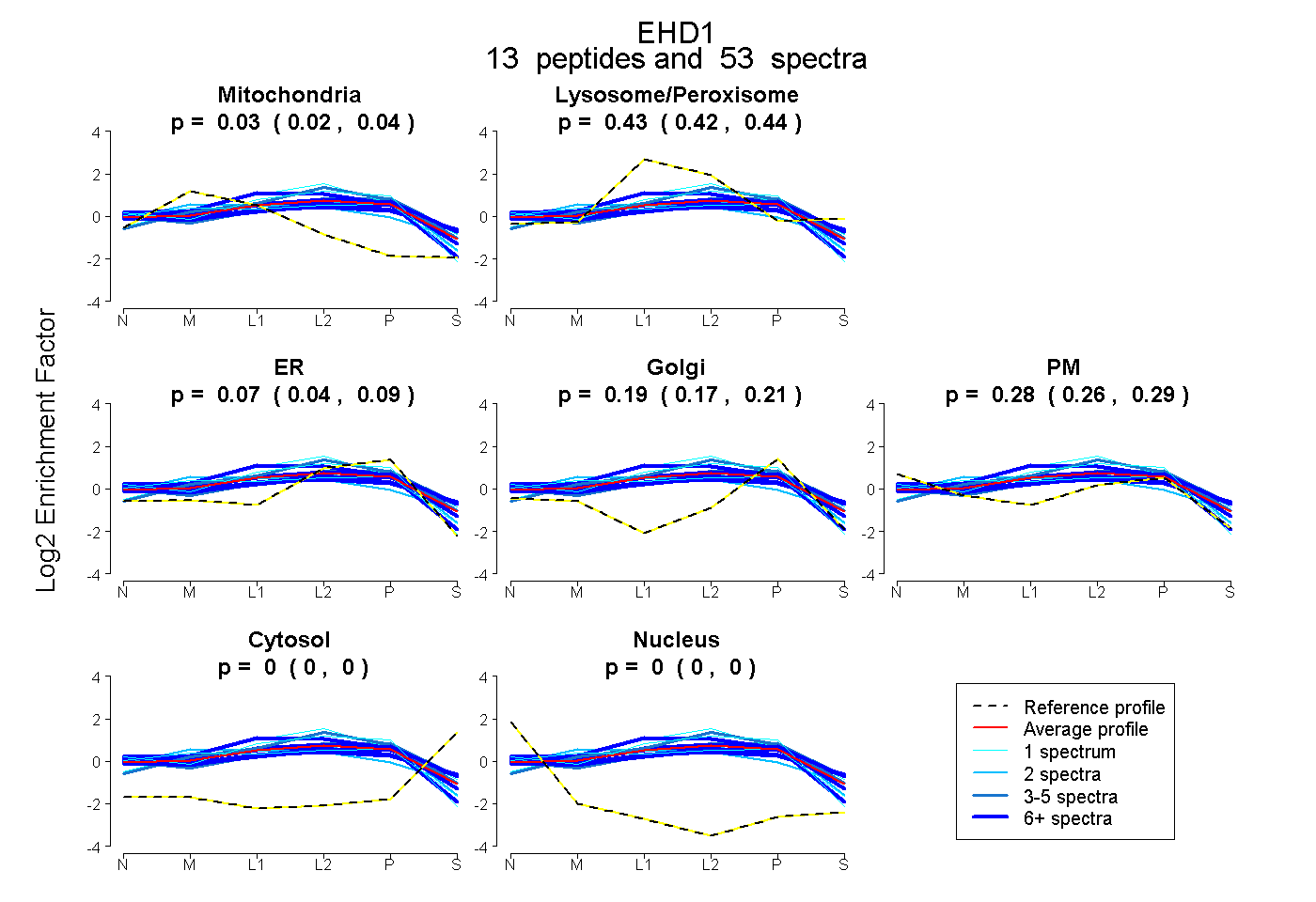
0.022 | 0.036
0.419 | 0.443
0.043 | 0.089
0.172 | 0.212
0.261 | 0.287
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
115 spectra |
 |
0.000 0.000 | 0.000 |
0.098 0.094 | 0.101 |
0.285 0.279 | 0.289 |
0.000 0.000 | 0.000 |
0.117 0.111 | 0.122 |
0.454 0.447 | 0.459 |
0.047 0.044 | 0.049 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
53 spectra |
 |
0.029 0.022 | 0.036 |
0.432 0.419 | 0.443 |
0.069 0.043 | 0.089 |
0.195 0.172 | 0.212 |
0.275 0.261 | 0.287 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, LMVMVR | 0.044 | 0.430 | 0.488 | 0.038 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ELVNNLGEIYQK | 0.042 | 0.454 | 0.000 | 0.163 | 0.304 | 0.036 | 0.000 | |||
| 6 spectra, IINTPEVVR | 0.095 | 0.377 | 0.271 | 0.000 | 0.257 | 0.000 | 0.000 | |||
| 1 spectrum, EHQISSGDFPSLR | 0.043 | 0.528 | 0.429 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, LFEAEEQDLFK | 0.000 | 0.452 | 0.000 | 0.302 | 0.211 | 0.035 | 0.000 | |||
| 7 spectra, LNAFGNAFLNR | 0.000 | 0.454 | 0.000 | 0.388 | 0.144 | 0.013 | 0.000 | |||
| 1 spectrum, LNDLIK | 0.174 | 0.207 | 0.288 | 0.000 | 0.331 | 0.000 | 0.000 | |||
| 8 spectra, IILLFDAHK | 0.000 | 0.365 | 0.135 | 0.027 | 0.473 | 0.000 | 0.000 | |||
| 1 spectrum, QLYAQK | 0.000 | 0.318 | 0.448 | 0.000 | 0.233 | 0.000 | 0.000 | |||
| 2 spectra, HLIEQDFPGMR | 0.270 | 0.366 | 0.000 | 0.172 | 0.192 | 0.000 | 0.000 | |||
| 6 spectra, LLPLEEHYR | 0.044 | 0.420 | 0.000 | 0.213 | 0.249 | 0.074 | 0.000 | |||
| 2 spectra, ADQIETQQLMR | 0.049 | 0.278 | 0.304 | 0.013 | 0.355 | 0.000 | 0.000 | |||
| 4 spectra, DIQSLPR | 0.000 | 0.460 | 0.046 | 0.327 | 0.167 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
130 spectra |
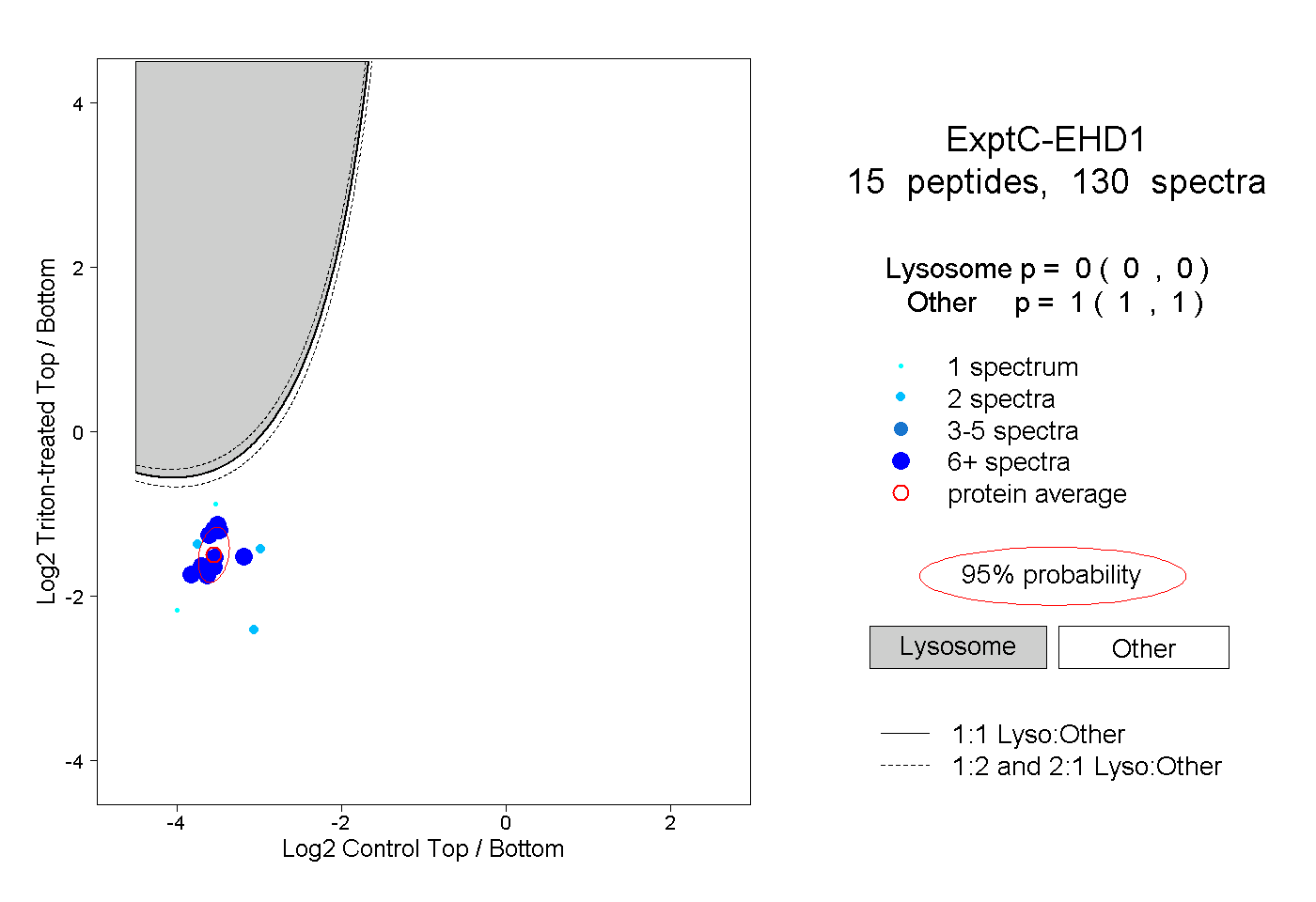 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
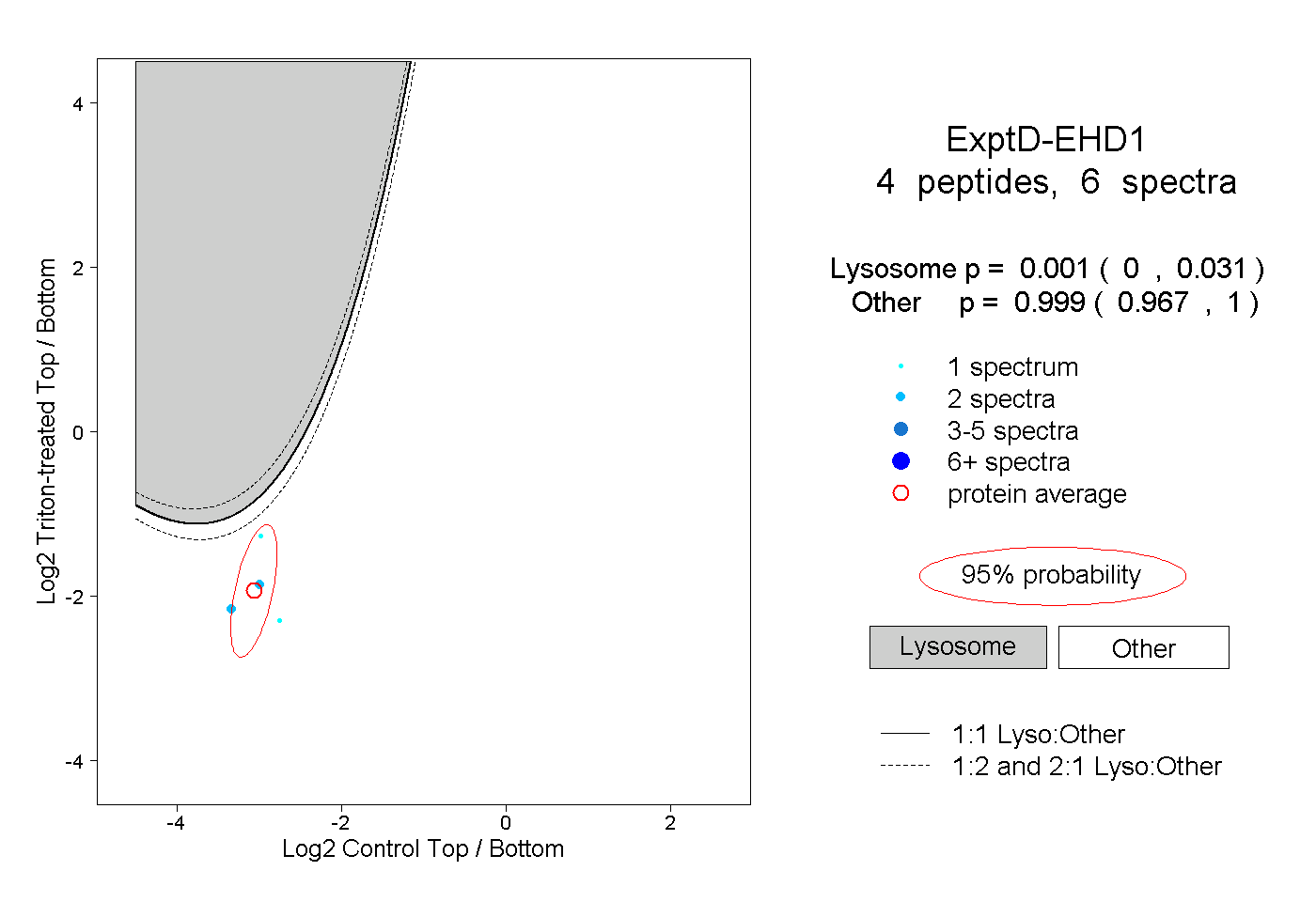 |
0.001 0.000 | 0.031 |
0.999 0.967 | 1.000 |