peptides
spectra
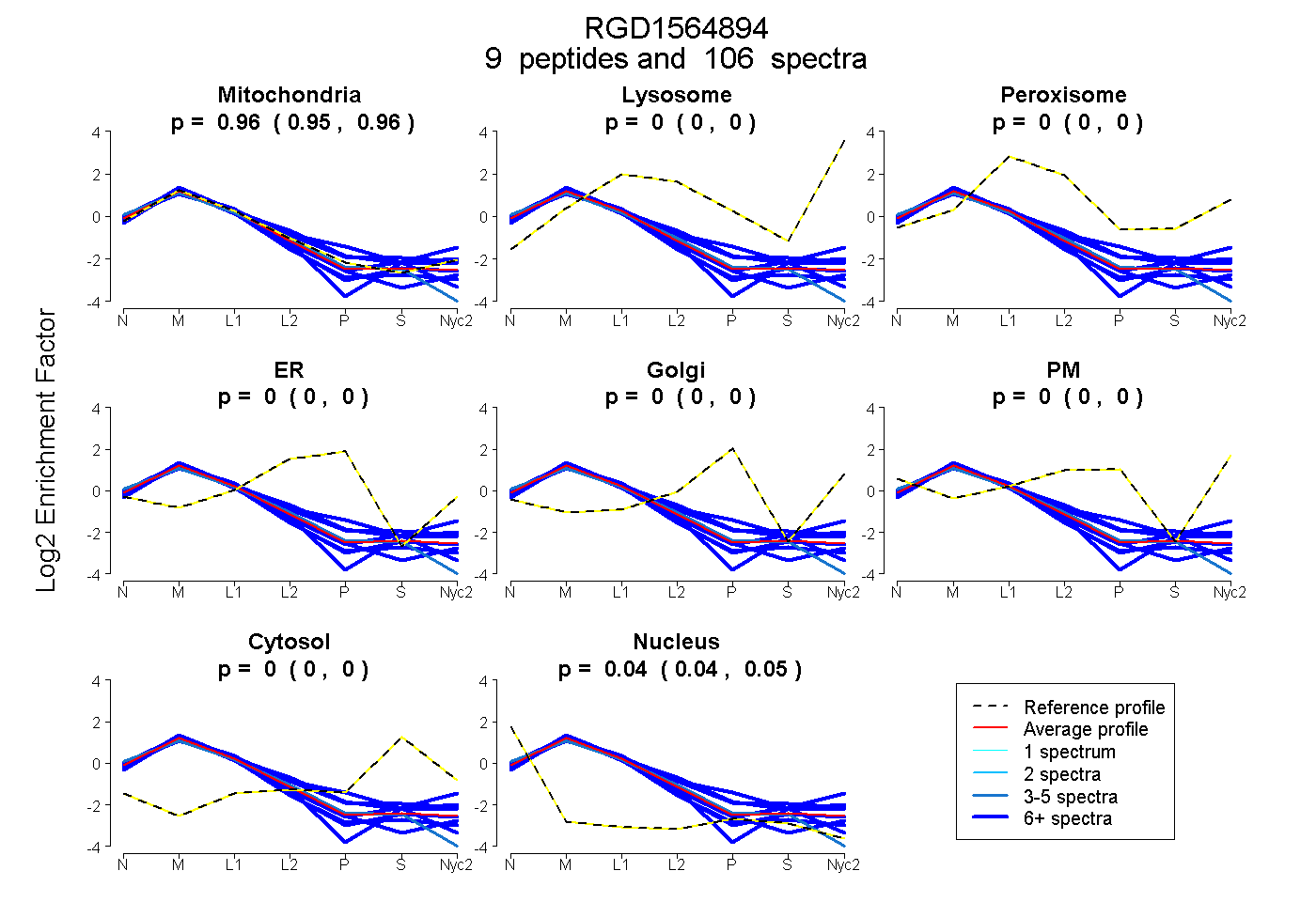
0.954 | 0.959
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.041 | 0.045
peptides
spectra
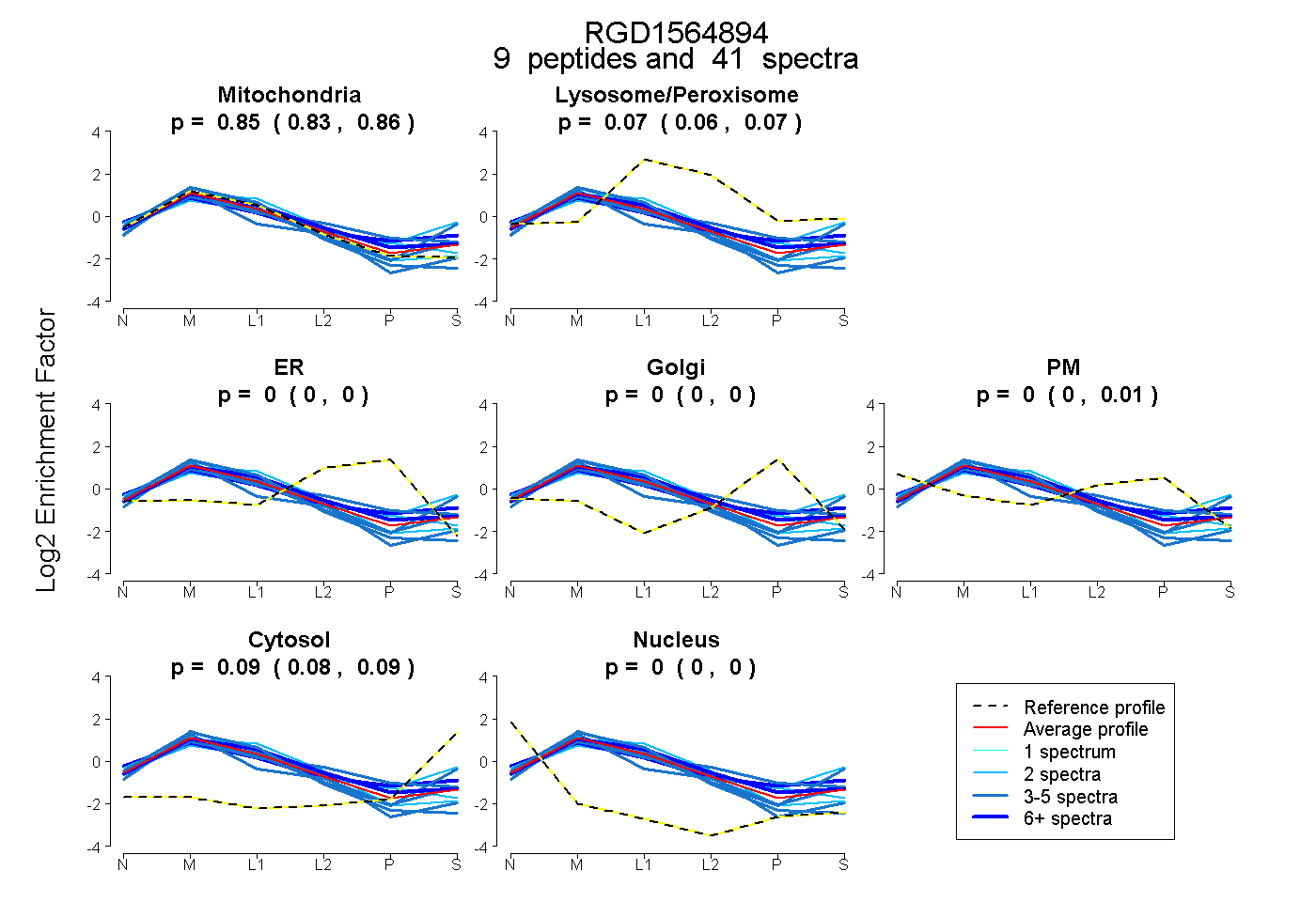
0.831 | 0.859
0.055 | 0.072
0.000 | 0.000
0.000 | 0.000
0.000 | 0.010
0.078 | 0.095
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
106 spectra |
 |
0.957 0.954 | 0.959 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.043 0.041 | 0.045 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
 |
0.846 0.831 | 0.859 |
0.065 0.055 | 0.072 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.010 |
0.088 0.078 | 0.095 |
0.000 0.000 | 0.000 |
| 4 spectra, YLPESLK | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | |||
| 7 spectra, GYPVYNHTEK | 0.619 | 0.101 | 0.000 | 0.000 | 0.138 | 0.142 | 0.000 | |||
| 2 spectra, AQGLISHIIYAQTLVMDK | 0.790 | 0.041 | 0.000 | 0.003 | 0.165 | 0.000 | 0.000 | |||
| 3 spectra, SSQMLQMLESSLR | 0.828 | 0.000 | 0.000 | 0.000 | 0.000 | 0.172 | 0.000 | |||
| 2 spectra, FWQFGGSER | 0.543 | 0.216 | 0.000 | 0.000 | 0.008 | 0.234 | 0.000 | |||
| 4 spectra, MAGTVPDYR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QCLAFLGTPDVINWK | 0.918 | 0.082 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LVPFLLEDTENLDR | 0.677 | 0.089 | 0.000 | 0.000 | 0.000 | 0.234 | 0.000 | |||
| 14 spectra, TQCILYMMPETAK | 0.740 | 0.143 | 0.000 | 0.059 | 0.000 | 0.058 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
359 spectra |
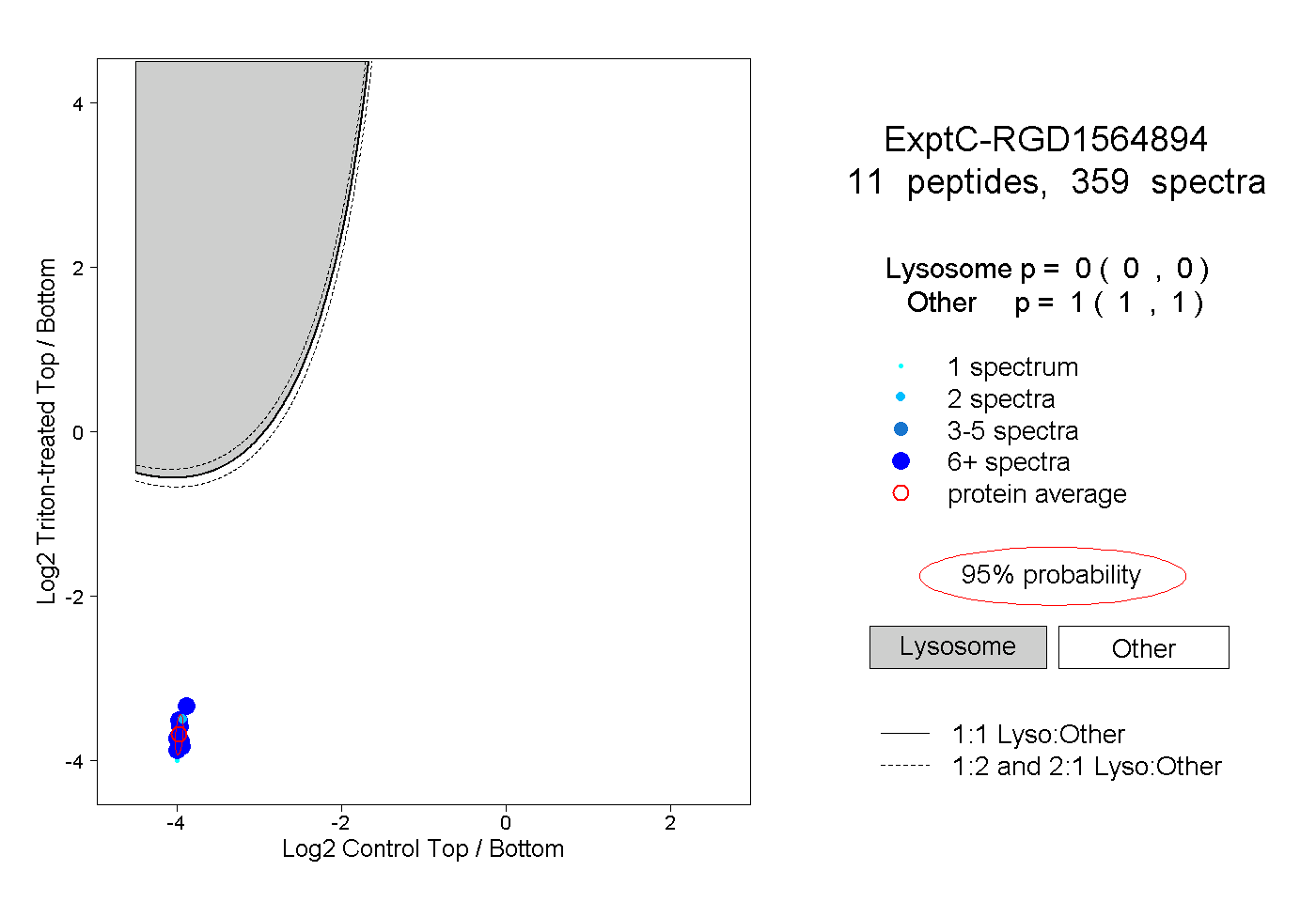 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
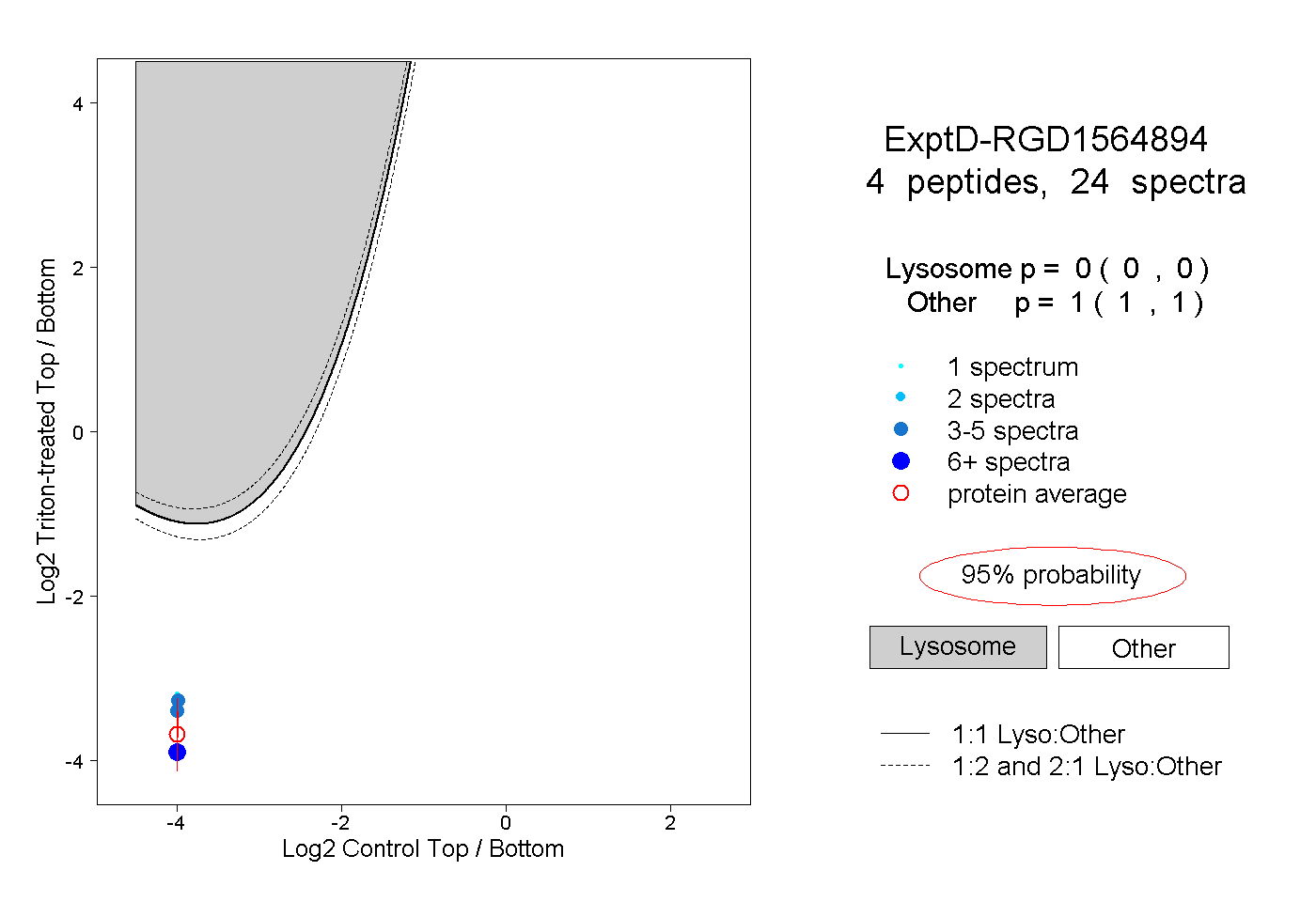 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |