CSDE1
[ENSRNOP00000051275]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 25
25
peptides |
67
spectra |
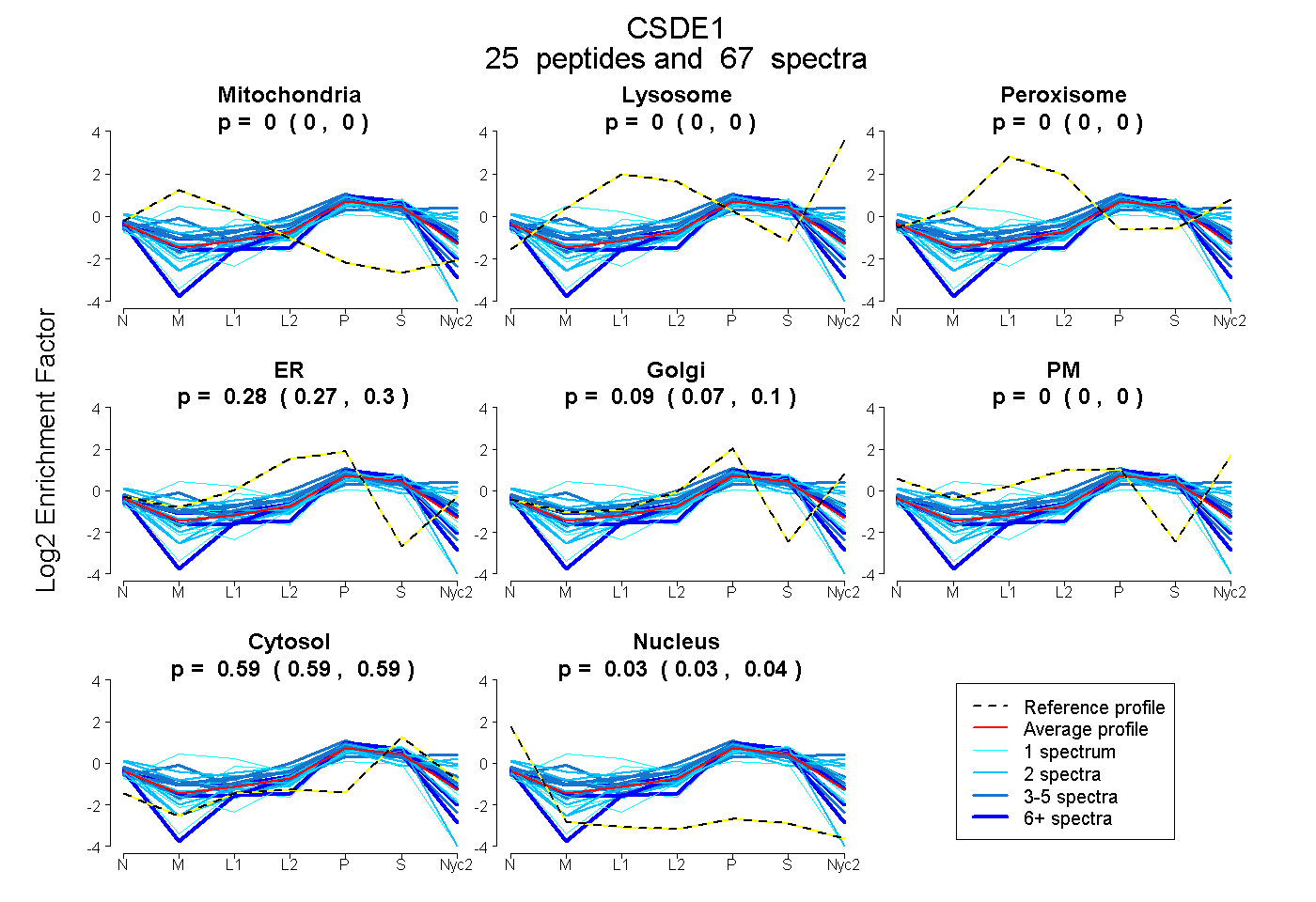 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
0.284
0.269 | 0.296 |
0.090
0.071 | 0.105 |
0.000
0.000 | 0.000 |
0.592
0.590 | 0.595 |
0.034
0.029 | 0.038 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 13
13
peptides |
24
spectra |
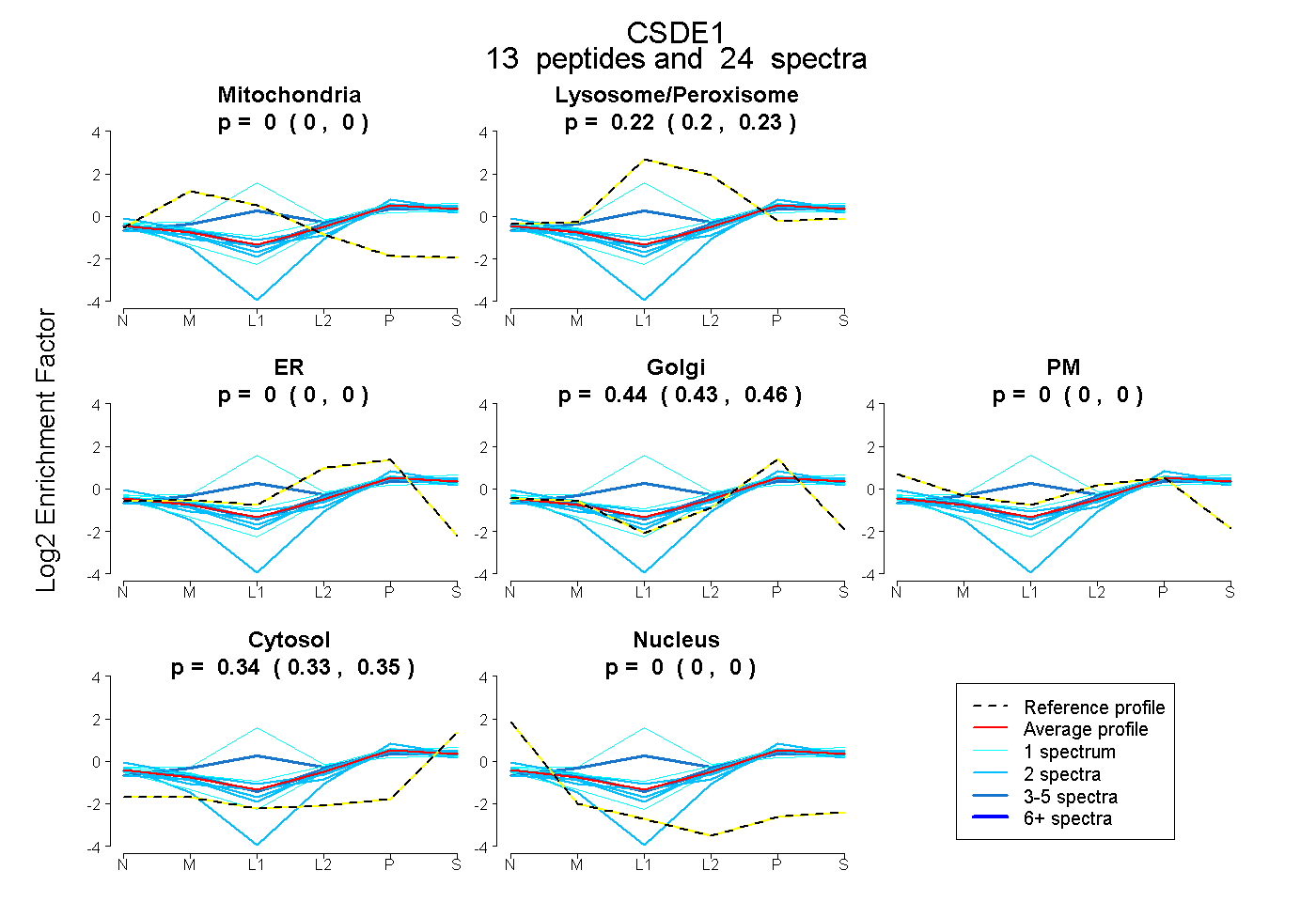 |
0.000
0.000 | 0.000 |
|
0.216
0.195 | 0.231 |
|
0.000
0.000 | 0.000 |
0.444
0.430 | 0.456 |
0.000
0.000 | 0.000 |
0.340
0.333 | 0.346 |
0.000
0.000 | 0.000 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
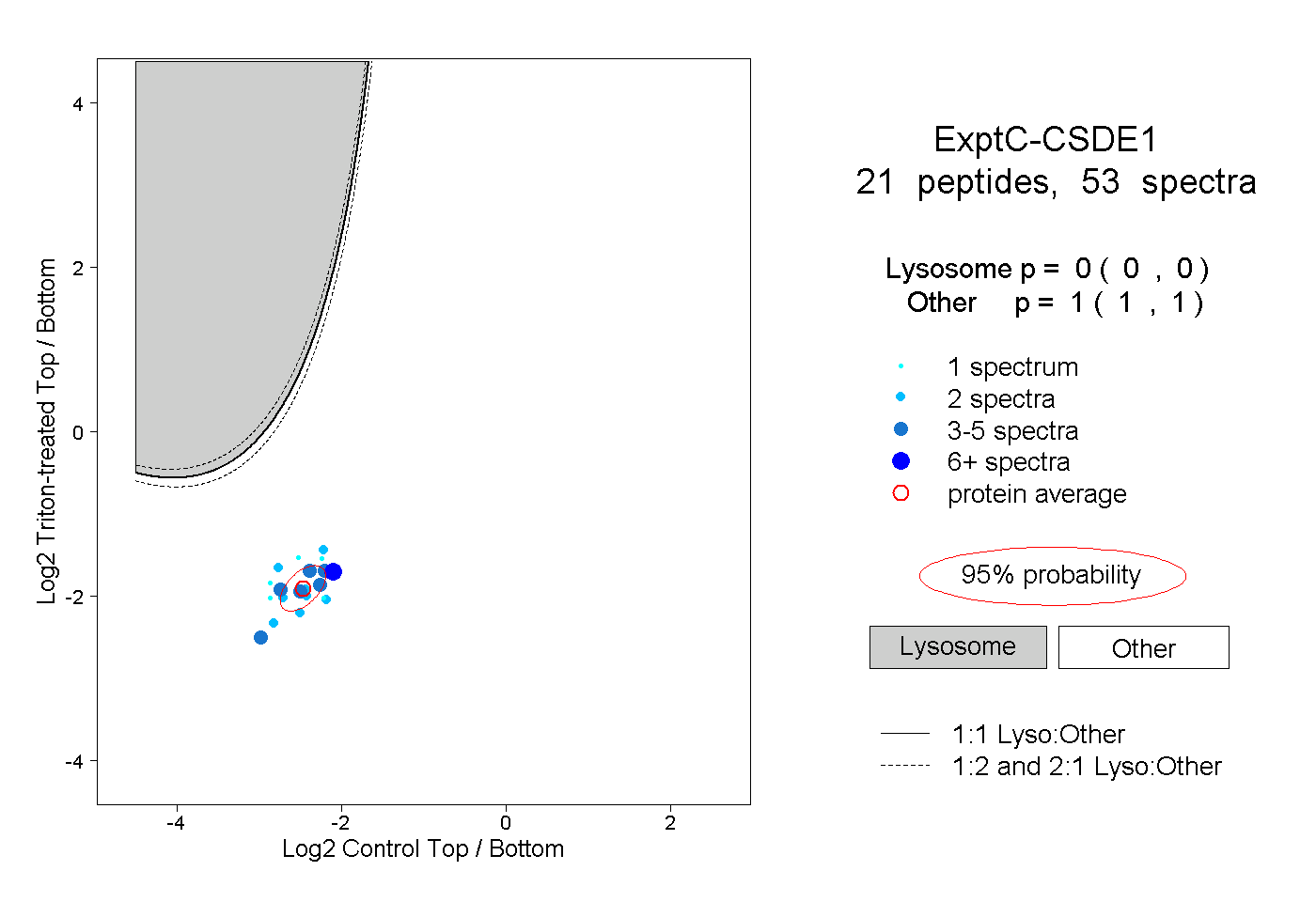
 21
21
peptides |
53
spectra |
 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 4 spectra, TGKPIAIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HTGAVSAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LLGYVATLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FNISTDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VCEGPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ETGVIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FLGTVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AVAAPRPDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GPDNSMGFGAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LFFHVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IKPEIHPEER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EMGVIAAMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VTLLEGDHVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EATFSNPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TTSPNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DVEGSTSPQIGDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ATVECVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QRPGQQIATCVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DGFGFIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GDCLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EAFGFIER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
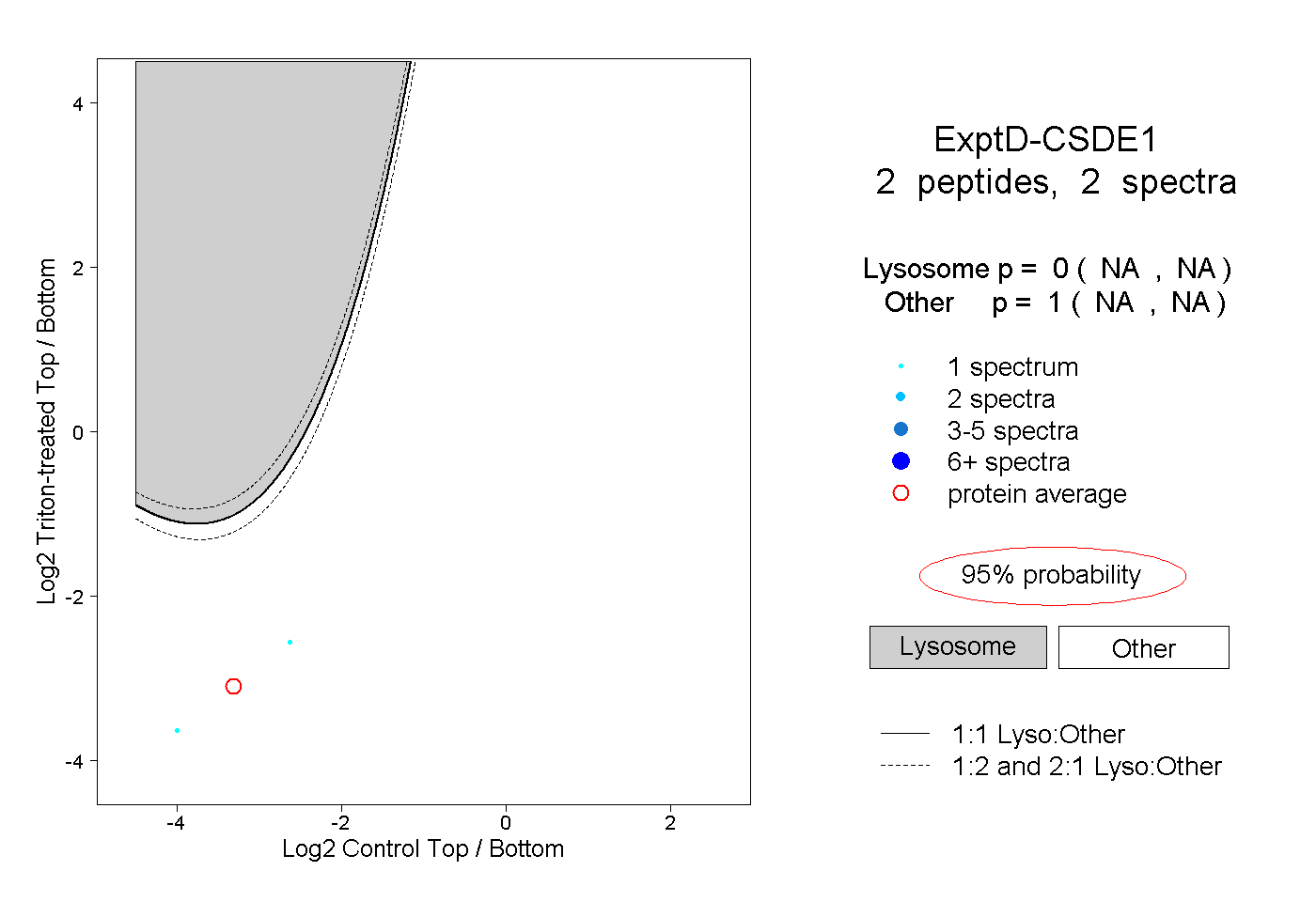
 2
2
peptides |
2
spectra |
 |
|
0.000
NA | NA |
|
|
|
|
|
|
|
1.000
NA | NA |



