peptides
spectra
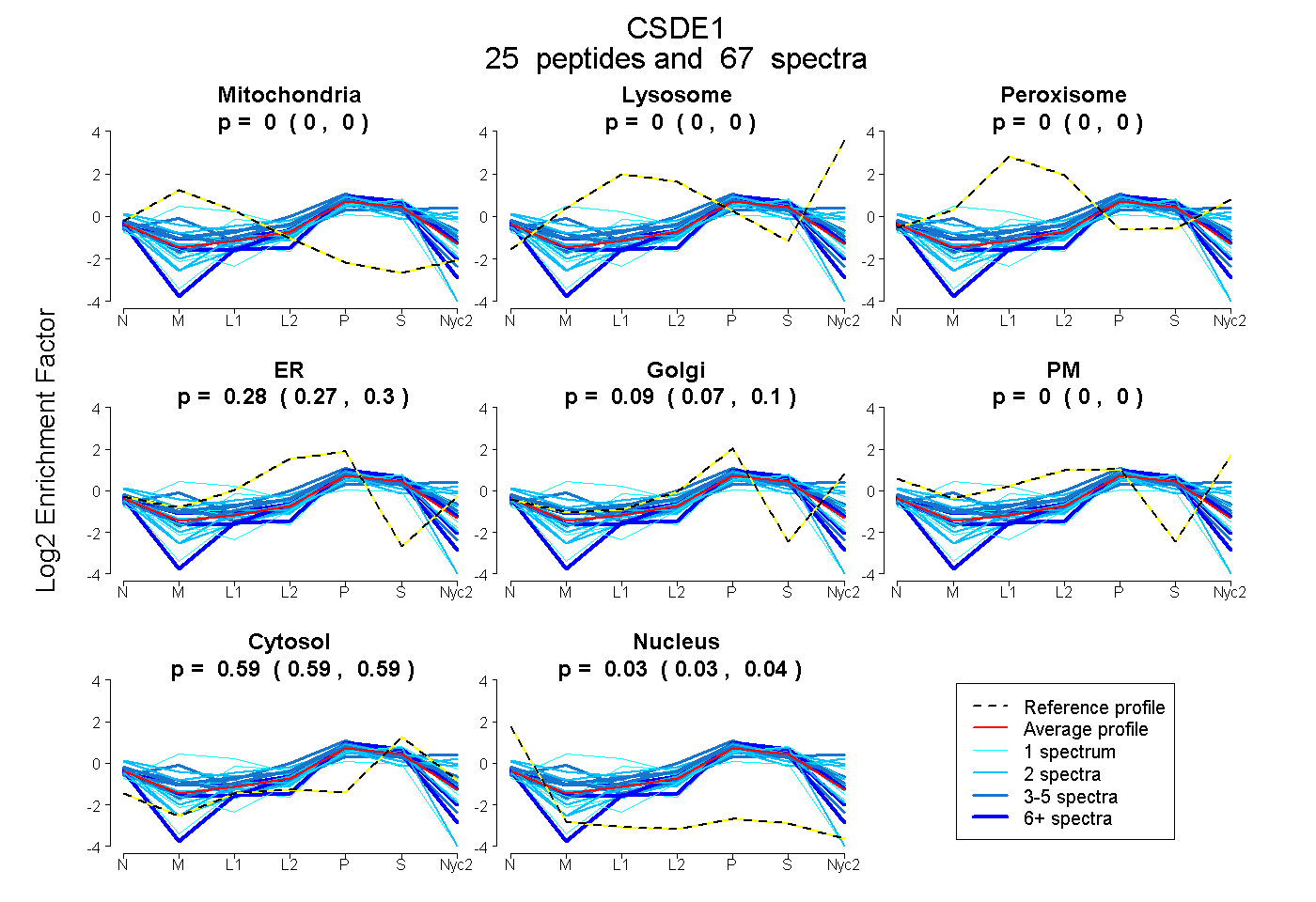
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.269 | 0.296
0.071 | 0.105
0.000 | 0.000
0.590 | 0.595
0.029 | 0.038
peptides
spectra
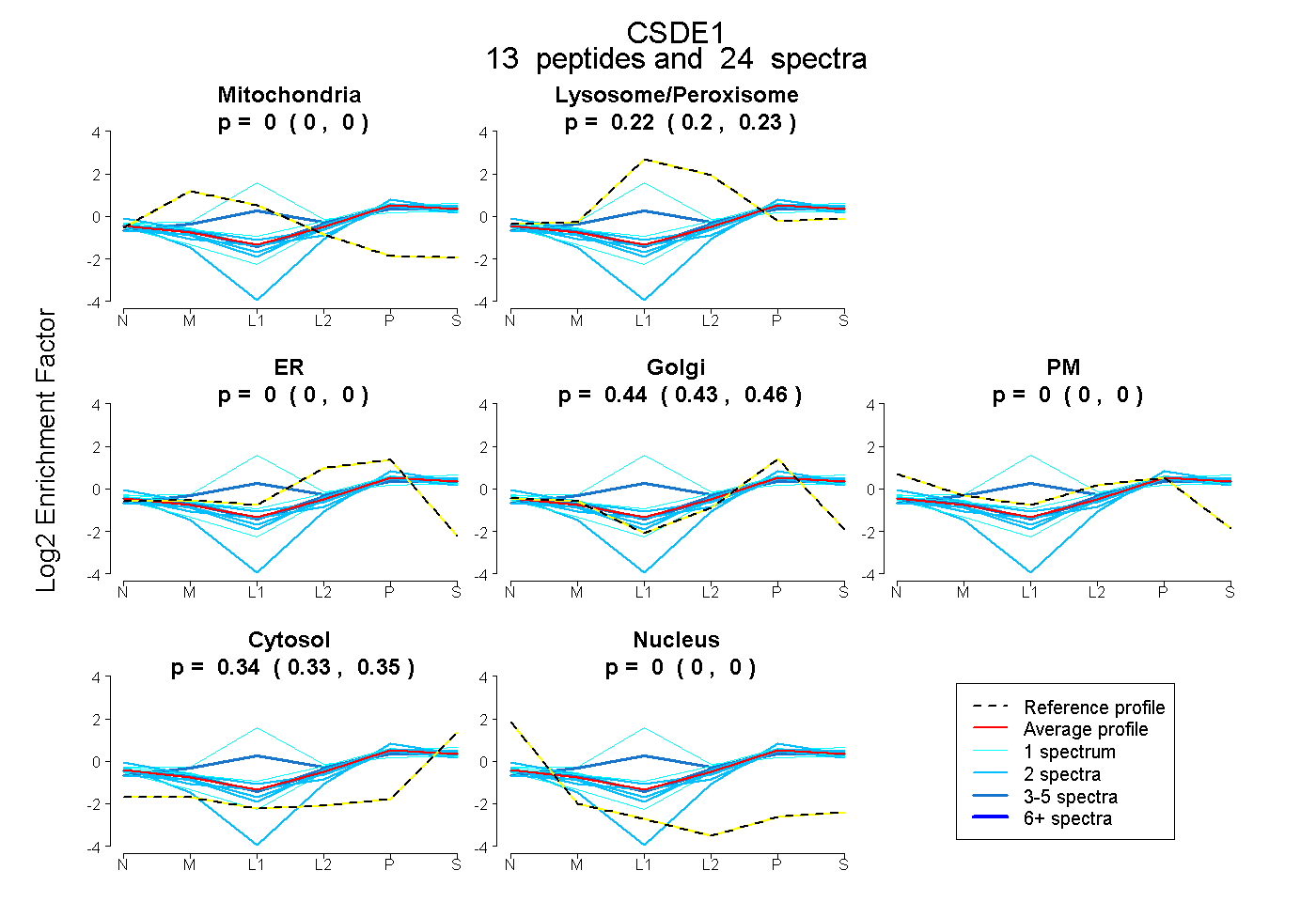
0.000 | 0.000
0.195 | 0.231
0.000 | 0.000
0.430 | 0.456
0.000 | 0.000
0.333 | 0.346
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
67 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.284 0.269 | 0.296 |
0.090 0.071 | 0.105 |
0.000 0.000 | 0.000 |
0.592 0.590 | 0.595 |
0.034 0.029 | 0.038 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.216 0.195 | 0.231 |
0.000 0.000 | 0.000 |
0.444 0.430 | 0.456 |
0.000 0.000 | 0.000 |
0.340 0.333 | 0.346 |
0.000 0.000 | 0.000 |
| 3 spectra, LFFHVK | 0.000 | 0.207 | 0.000 | 0.447 | 0.000 | 0.346 | 0.000 | |||
| 1 spectrum, DQFGFINYEVGDSK | 0.000 | 0.167 | 0.000 | 0.338 | 0.150 | 0.345 | 0.000 | |||
| 2 spectra, AVAAPRPDR | 0.000 | 0.000 | 0.000 | 0.579 | 0.000 | 0.421 | 0.000 | |||
| 3 spectra, IKPEIHPEER | 0.000 | 0.461 | 0.000 | 0.273 | 0.000 | 0.266 | 0.000 | |||
| 2 spectra, LLGYVATLK | 0.000 | 0.139 | 0.005 | 0.486 | 0.000 | 0.371 | 0.000 | |||
| 2 spectra, VTLLEGDHVR | 0.000 | 0.156 | 0.000 | 0.457 | 0.000 | 0.388 | 0.000 | |||
| 1 spectrum, LLTSYGFIQCSER | 0.000 | 0.016 | 0.191 | 0.306 | 0.000 | 0.487 | 0.000 | |||
| 1 spectrum, DVEGSTSPQIGDK | 0.039 | 0.641 | 0.000 | 0.133 | 0.000 | 0.185 | 0.002 | |||
| 2 spectra, NITLDDASAPR | 0.000 | 0.179 | 0.000 | 0.427 | 0.000 | 0.394 | 0.000 | |||
| 1 spectrum, VLRPLR | 0.000 | 0.290 | 0.000 | 0.446 | 0.000 | 0.264 | 0.000 | |||
| 2 spectra, QRPGQQIATCVR | 0.000 | 0.172 | 0.000 | 0.299 | 0.220 | 0.309 | 0.000 | |||
| 1 spectrum, DGFGFIK | 0.000 | 0.202 | 0.000 | 0.484 | 0.000 | 0.314 | 0.000 | |||
| 3 spectra, EAFGFIER | 0.000 | 0.218 | 0.000 | 0.458 | 0.000 | 0.324 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
53 spectra |
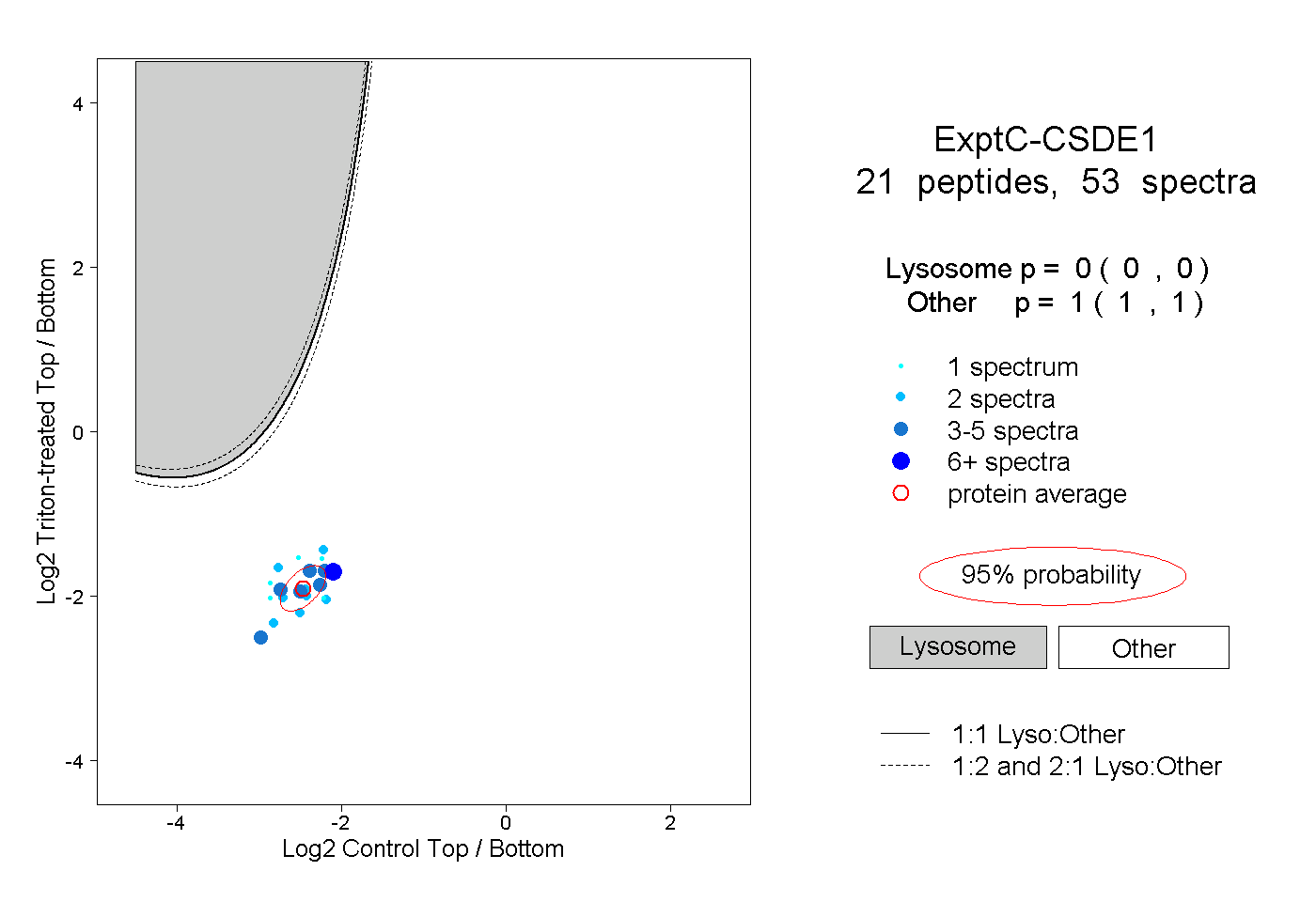 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
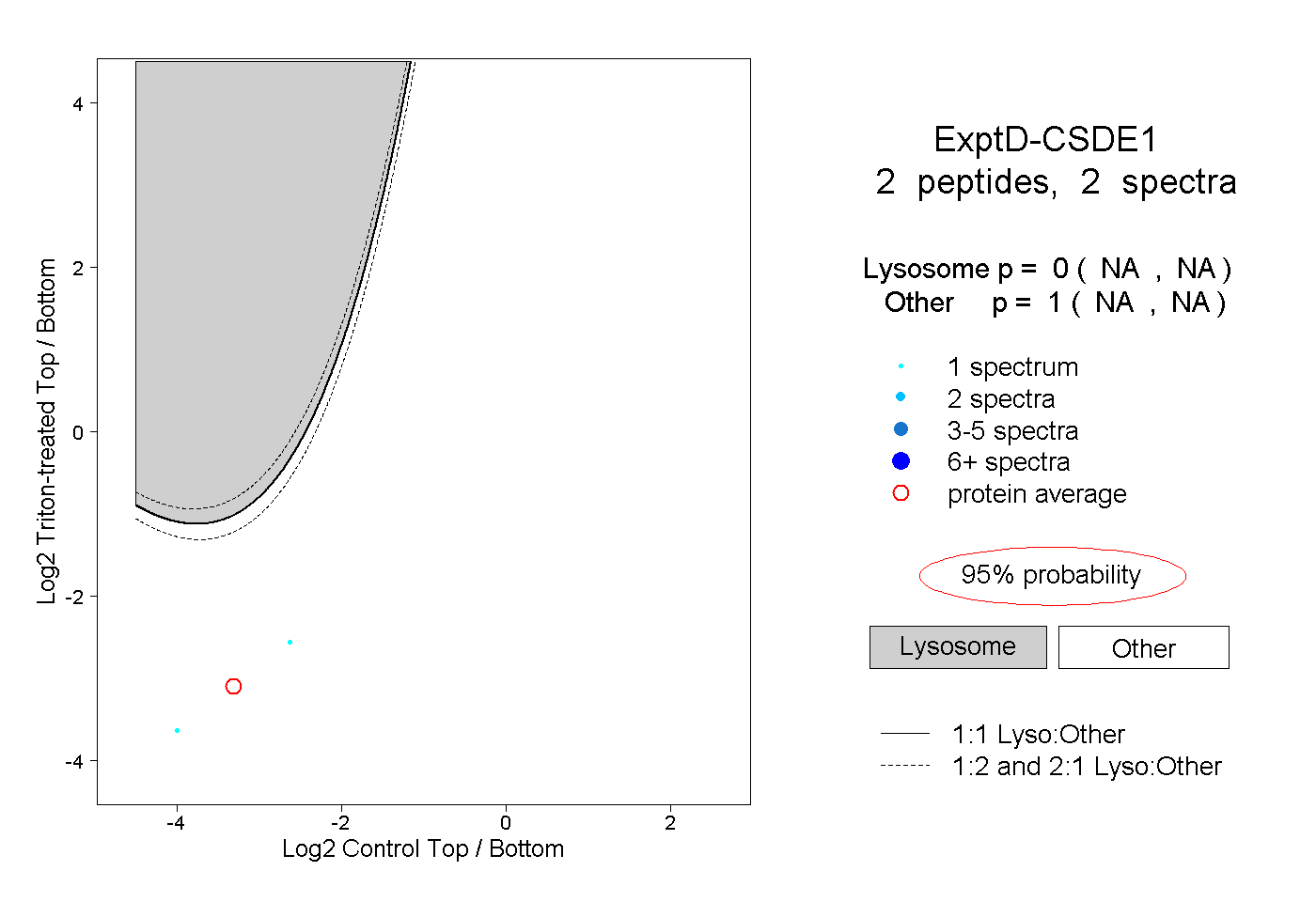 |
0.000 NA | NA |
1.000 NA | NA |