peptides
spectra
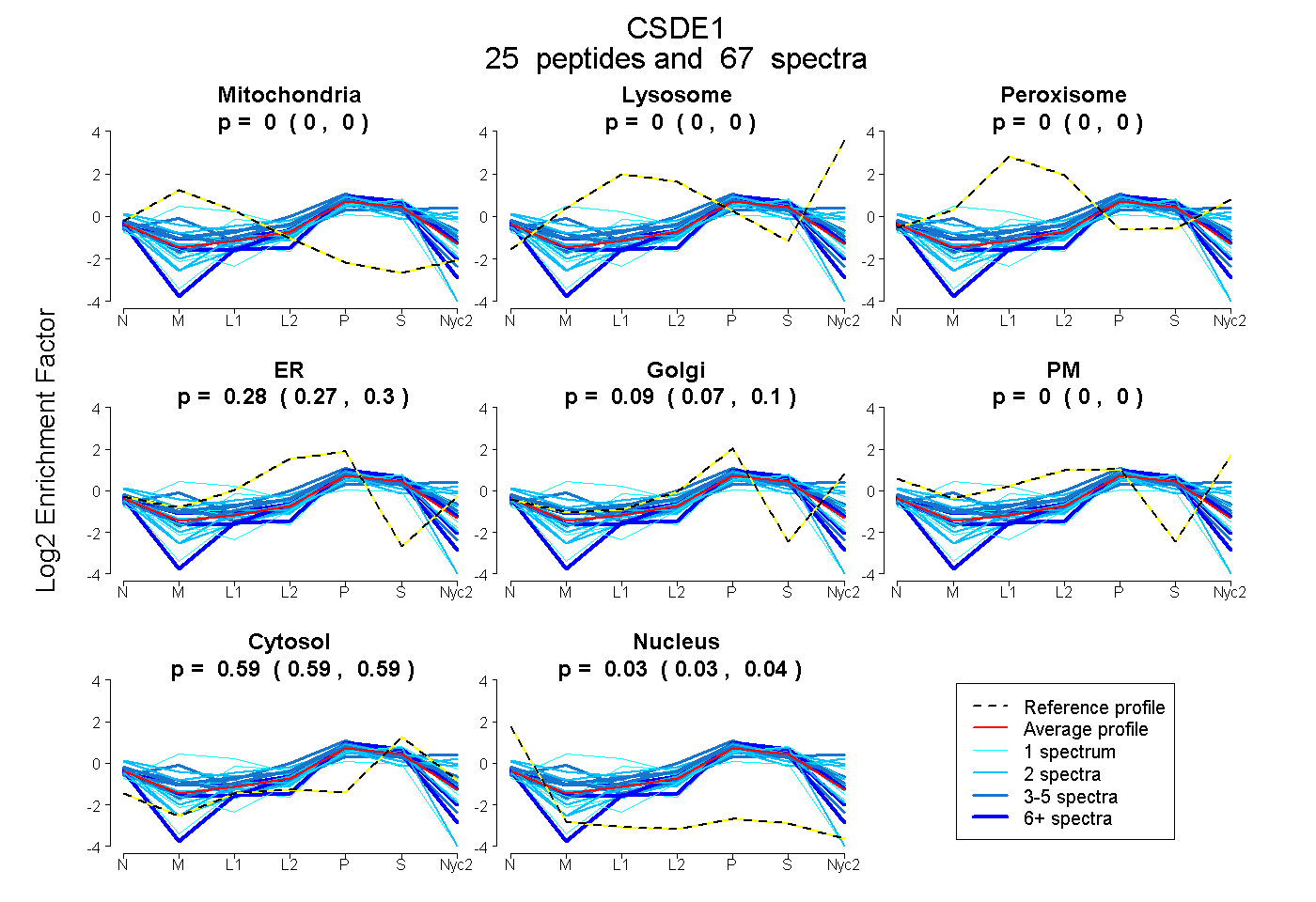
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.269 | 0.296
0.071 | 0.105
0.000 | 0.000
0.590 | 0.595
0.029 | 0.038
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
67 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.284 0.269 | 0.296 |
0.090 0.071 | 0.105 |
0.000 0.000 | 0.000 |
0.592 0.590 | 0.595 |
0.034 0.029 | 0.038 |
| 1 spectrum, DNFGFIETANHDK | 0.000 | 0.000 | 0.000 | 0.163 | 0.114 | 0.000 | 0.655 | 0.068 | ||
| 1 spectrum, LLGYVATLK | 0.535 | 0.000 | 0.000 | 0.158 | 0.000 | 0.000 | 0.307 | 0.000 | ||
| 1 spectrum, GDLETLQPGDDVEFTIK | 0.000 | 0.000 | 0.159 | 0.102 | 0.213 | 0.000 | 0.526 | 0.000 | ||
| 2 spectra, FNISTDR | 0.000 | 0.000 | 0.000 | 0.161 | 0.216 | 0.000 | 0.605 | 0.018 | ||
| 8 spectra, NITLDDASAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.244 | 0.000 | 0.679 | 0.077 | ||
| 4 spectra, VLRPLR | 0.000 | 0.000 | 0.074 | 0.228 | 0.208 | 0.000 | 0.490 | 0.000 | ||
| 3 spectra, FLGTVEK | 0.212 | 0.000 | 0.000 | 0.067 | 0.241 | 0.000 | 0.480 | 0.000 | ||
| 1 spectrum, AVAAPRPDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.231 | 0.000 | 0.672 | 0.098 | ||
| 5 spectra, LFFHVK | 0.000 | 0.000 | 0.000 | 0.084 | 0.291 | 0.000 | 0.622 | 0.002 | ||
| 2 spectra, SPAAPGQSPTGSVCYER | 0.000 | 0.000 | 0.000 | 0.188 | 0.000 | 0.000 | 0.603 | 0.209 | ||
| 3 spectra, ELPFGDK | 0.000 | 0.000 | 0.000 | 0.483 | 0.000 | 0.000 | 0.517 | 0.000 | ||
| 3 spectra, IKPEIHPEER | 0.063 | 0.000 | 0.000 | 0.319 | 0.000 | 0.000 | 0.502 | 0.117 | ||
| 3 spectra, EMGVIAAMR | 0.018 | 0.000 | 0.027 | 0.085 | 0.290 | 0.000 | 0.580 | 0.000 | ||
| 1 spectrum, VTLLEGDHVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.319 | 0.000 | 0.679 | 0.002 | ||
| 2 spectra, LLTSYGFIQCSER | 0.000 | 0.000 | 0.000 | 0.273 | 0.031 | 0.000 | 0.582 | 0.114 | ||
| 1 spectrum, EATFSNPK | 0.062 | 0.000 | 0.000 | 0.207 | 0.190 | 0.000 | 0.542 | 0.000 | ||
| 2 spectra, NQNDPLPGR | 0.000 | 0.000 | 0.126 | 0.080 | 0.206 | 0.172 | 0.417 | 0.000 | ||
| 3 spectra, TTSPNK | 0.000 | 0.006 | 0.000 | 0.000 | 0.343 | 0.163 | 0.488 | 0.000 | ||
| 1 spectrum, EVATDVR | 0.087 | 0.000 | 0.000 | 0.330 | 0.000 | 0.000 | 0.536 | 0.047 | ||
| 2 spectra, NIMLLK | 0.000 | 0.000 | 0.000 | 0.065 | 0.266 | 0.000 | 0.598 | 0.072 | ||
| 6 spectra, ATVECVK | 0.062 | 0.000 | 0.000 | 0.319 | 0.000 | 0.000 | 0.569 | 0.050 | ||
| 2 spectra, VEFSISDK | 0.000 | 0.000 | 0.018 | 0.000 | 0.460 | 0.009 | 0.513 | 0.000 | ||
| 6 spectra, QRPGQQIATCVR | 0.000 | 0.000 | 0.000 | 0.320 | 0.000 | 0.000 | 0.523 | 0.157 | ||
| 2 spectra, GDCLQK | 0.050 | 0.000 | 0.039 | 0.000 | 0.199 | 0.326 | 0.386 | 0.000 | ||
| 2 spectra, EAFGFIER | 0.000 | 0.000 | 0.000 | 0.071 | 0.329 | 0.000 | 0.599 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
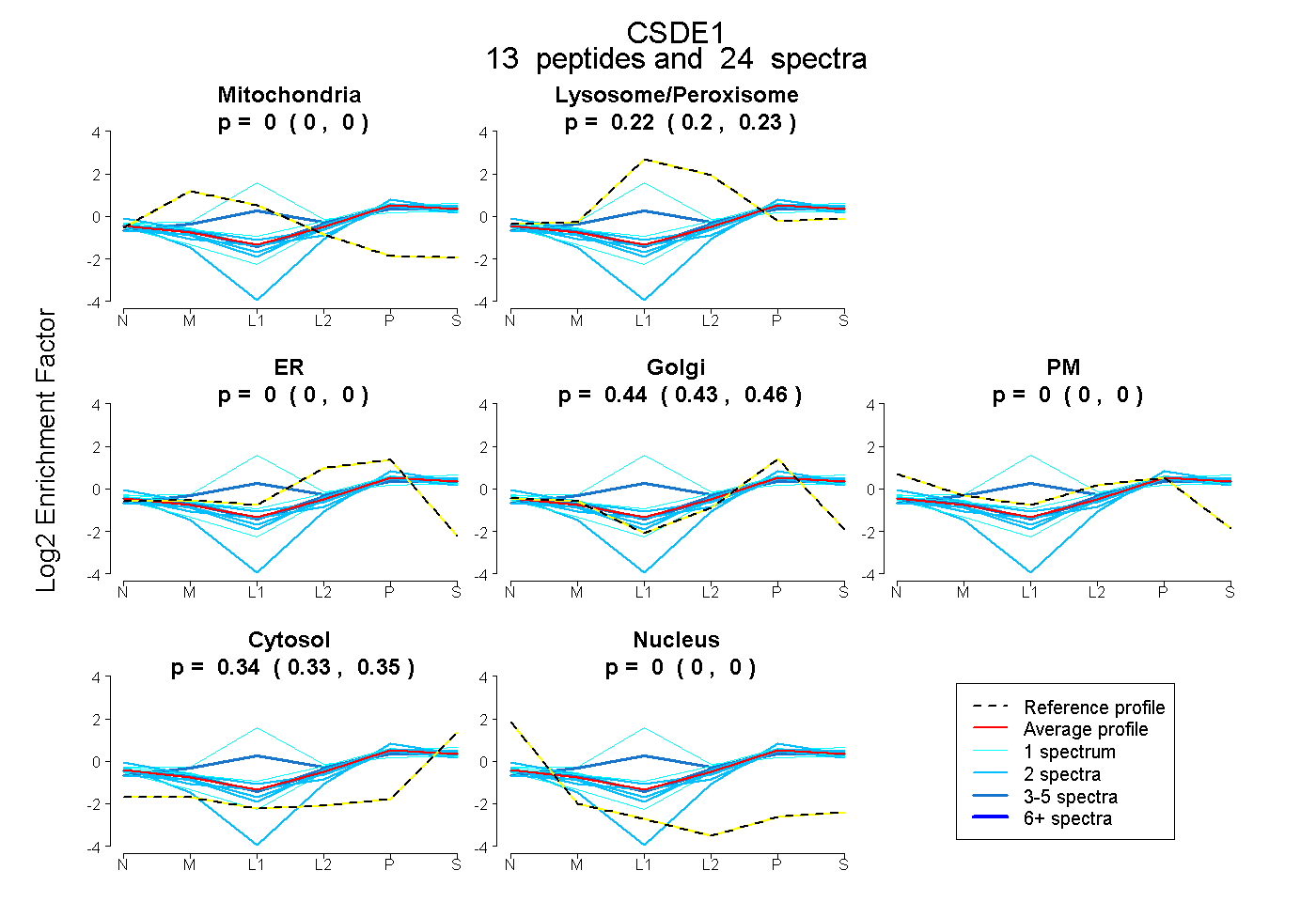 |
0.000 0.000 | 0.000 |
0.216 0.195 | 0.231 |
0.000 0.000 | 0.000 |
0.444 0.430 | 0.456 |
0.000 0.000 | 0.000 |
0.340 0.333 | 0.346 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
53 spectra |
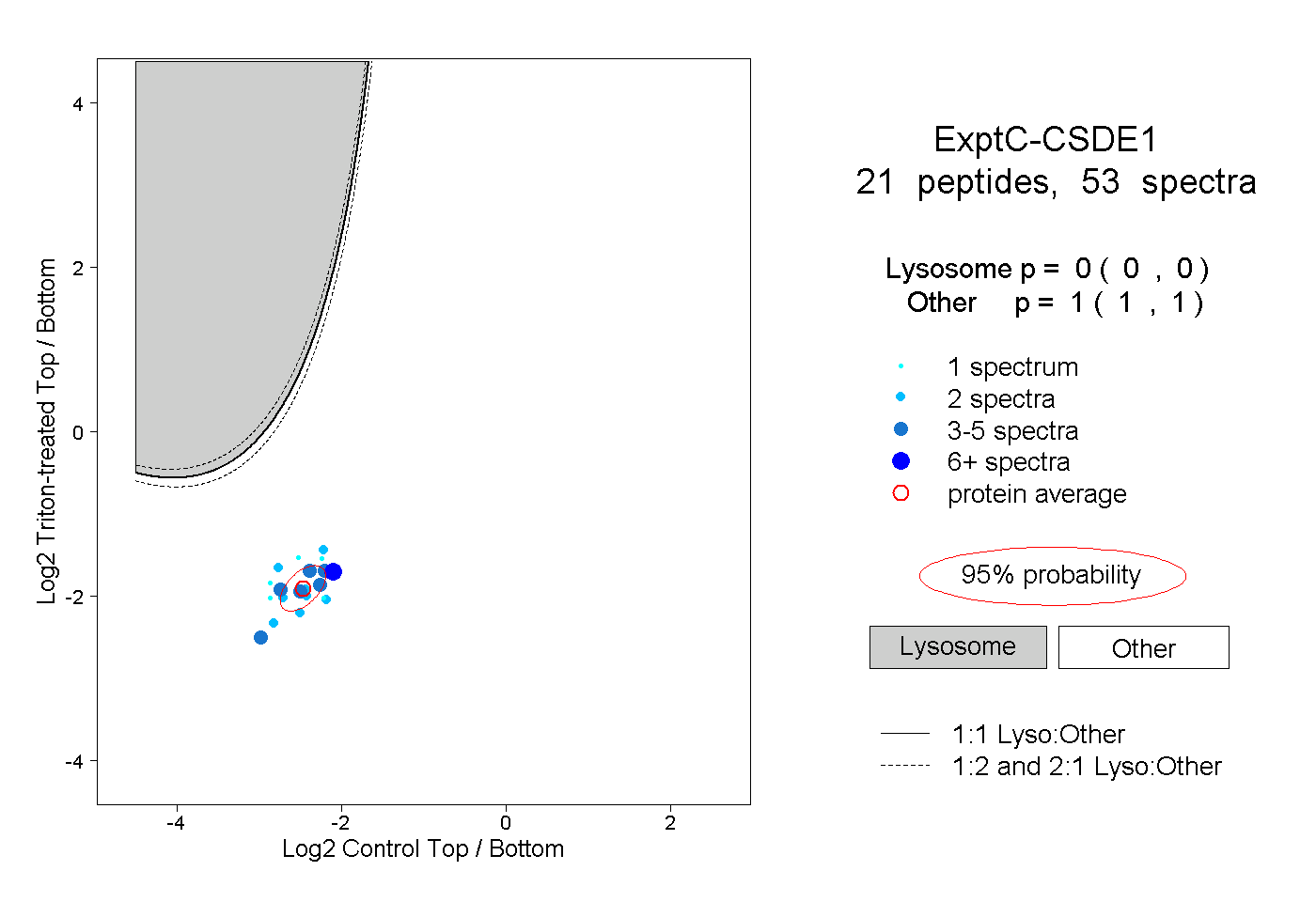 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
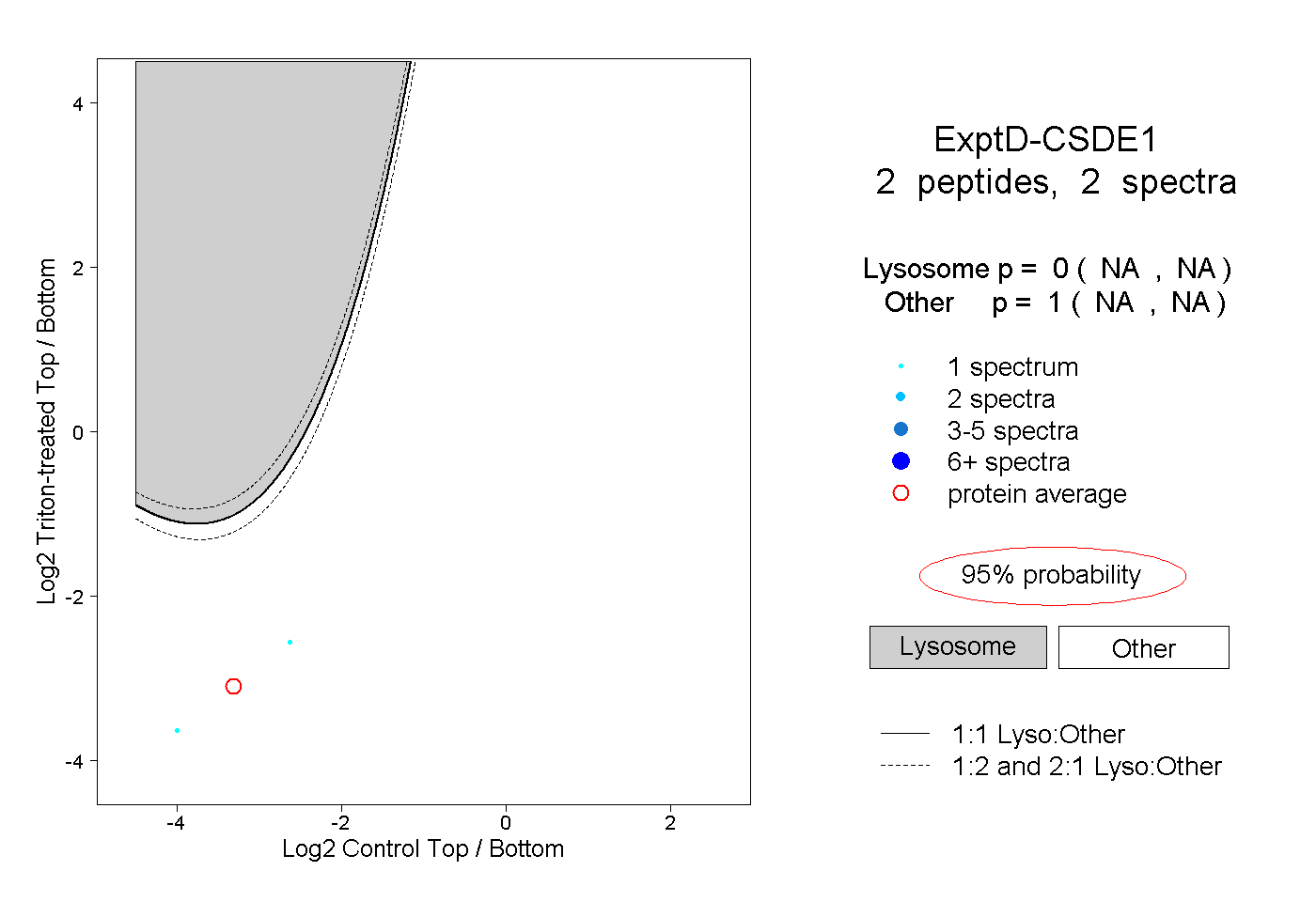 |
0.000 NA | NA |
1.000 NA | NA |