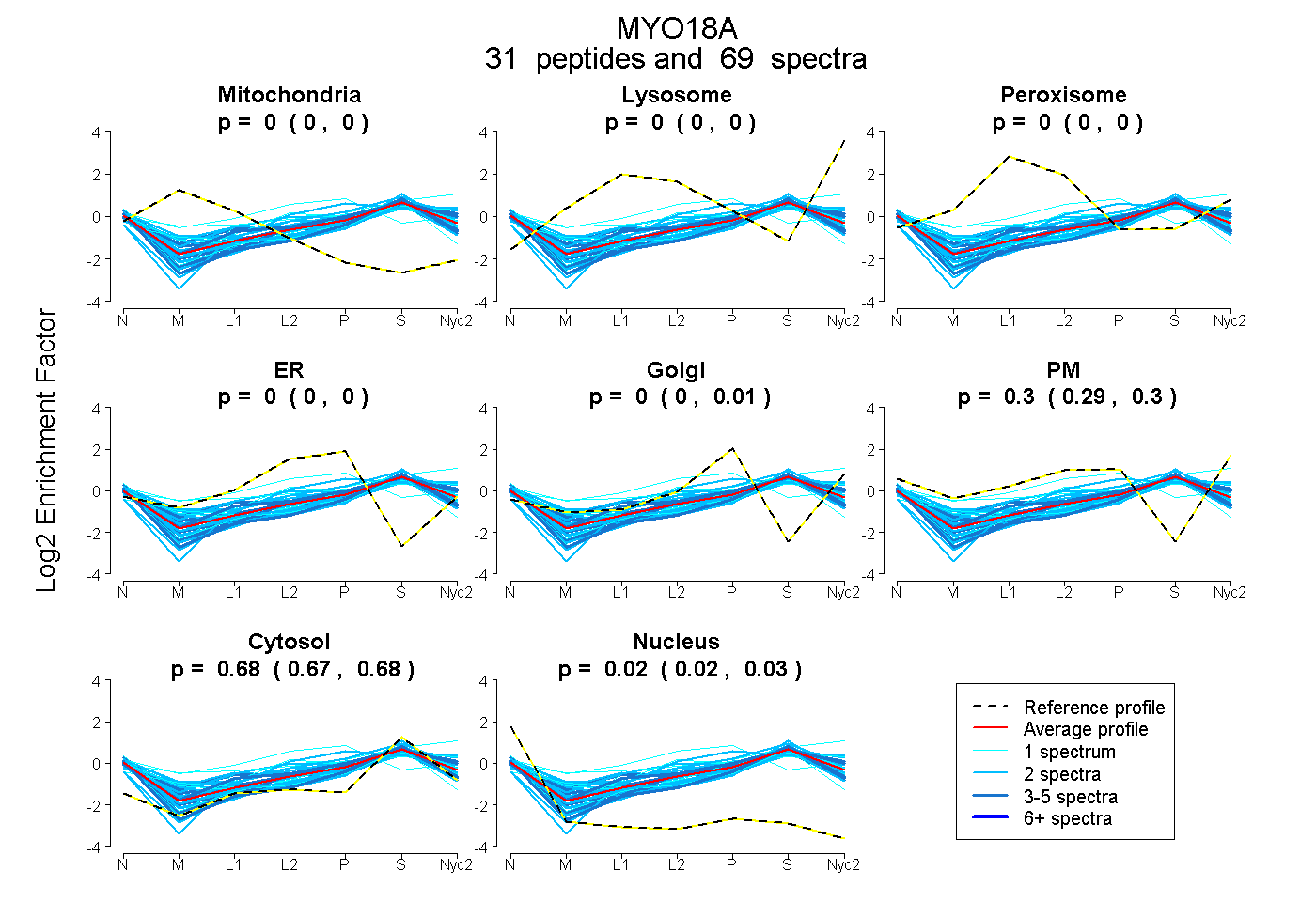
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.005
0.293 | 0.301
0.675 | 0.678
0.022 | 0.026
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
69 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.005 |
0.299 0.293 | 0.301 |
0.677 0.675 | 0.678 |
0.024 0.022 | 0.026 |
| 3 spectra, VVHFAEPGAGTK | 0.000 | 0.000 | 0.005 | 0.000 | 0.000 | 0.351 | 0.645 | 0.000 | ||
| 1 spectrum, QGYPDHMVFSEFR | 0.080 | 0.000 | 0.010 | 0.000 | 0.014 | 0.217 | 0.679 | 0.000 | ||
| 1 spectrum, SSCCMGLSR | 0.119 | 0.000 | 0.000 | 0.104 | 0.000 | 0.071 | 0.642 | 0.065 | ||
| 2 spectra, LHLEGQQVR | 0.000 | 0.000 | 0.051 | 0.000 | 0.000 | 0.349 | 0.600 | 0.000 | ||
| 2 spectra, IQDLAIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.032 | 0.183 | 0.704 | 0.082 | ||
| 1 spectrum, HLTLFQAACR | 0.000 | 0.000 | 0.146 | 0.279 | 0.000 | 0.268 | 0.307 | 0.000 | ||
| 2 spectra, VMHMFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.068 | 0.184 | 0.722 | 0.026 | ||
| 3 spectra, APEGQAYR | 0.000 | 0.000 | 0.070 | 0.000 | 0.000 | 0.237 | 0.588 | 0.105 | ||
| 2 spectra, FSFSQR | 0.000 | 0.037 | 0.077 | 0.000 | 0.000 | 0.305 | 0.582 | 0.000 | ||
| 1 spectrum, TFLQELER | 0.000 | 0.000 | 0.000 | 0.000 | 0.158 | 0.128 | 0.708 | 0.006 | ||
| 4 spectra, LTAELQDTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.336 | 0.658 | 0.000 | ||
| 4 spectra, DLALGLVPGDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 | 0.185 | 0.699 | 0.099 | ||
| 2 spectra, ANAPSCDR | 0.000 | 0.000 | 0.000 | 0.101 | 0.000 | 0.132 | 0.711 | 0.056 | ||
| 2 spectra, LGDLQADSDESQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.269 | 0.673 | 0.057 | ||
| 1 spectrum, NHELEK | 0.000 | 0.000 | 0.008 | 0.000 | 0.000 | 0.423 | 0.569 | 0.000 | ||
| 2 spectra, DLDIAGFTQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.113 | 0.017 | 0.835 | 0.035 | ||
| 2 spectra, FDSELSQAHEETQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.457 | 0.543 | 0.000 | ||
| 1 spectrum, GFFNLNR | 0.000 | 0.088 | 0.000 | 0.000 | 0.000 | 0.320 | 0.592 | 0.000 | ||
| 2 spectra, LEEDQEDMNELMK | 0.000 | 0.000 | 0.120 | 0.000 | 0.000 | 0.315 | 0.565 | 0.000 | ||
| 2 spectra, SEELSLPEGK | 0.063 | 0.000 | 0.000 | 0.000 | 0.027 | 0.175 | 0.643 | 0.093 | ||
| 3 spectra, GASFEELCHNYAQDR | 0.000 | 0.000 | 0.174 | 0.110 | 0.000 | 0.063 | 0.591 | 0.062 | ||
| 2 spectra, LSTLSDQVNQR | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | 0.353 | 0.599 | 0.030 | ||
| 2 spectra, QDQSIVLLGSSGSGK | 0.000 | 0.000 | 0.000 | 0.154 | 0.046 | 0.261 | 0.539 | 0.000 | ||
| 2 spectra, QNPATQNAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 | 0.183 | 0.716 | 0.088 | ||
| 2 spectra, EVDFTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | 0.266 | 0.627 | 0.044 | ||
| 4 spectra, AAVAQASR | 0.000 | 0.000 | 0.000 | 0.000 | 0.093 | 0.103 | 0.713 | 0.091 | ||
| 2 spectra, ISELTSELTDER | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | 0.196 | 0.714 | 0.088 | ||
| 2 spectra, SLEEMSMR | 0.000 | 0.000 | 0.000 | 0.145 | 0.044 | 0.083 | 0.728 | 0.000 | ||
| 1 spectrum, LQQELEDK | 0.026 | 0.000 | 0.152 | 0.000 | 0.014 | 0.346 | 0.462 | 0.000 | ||
| 5 spectra, VWLVHR | 0.000 | 0.000 | 0.000 | 0.000 | 0.104 | 0.073 | 0.729 | 0.094 | ||
| 4 spectra, RPTGDFGFSLR | 0.000 | 0.000 | 0.000 | 0.096 | 0.101 | 0.081 | 0.677 | 0.044 |
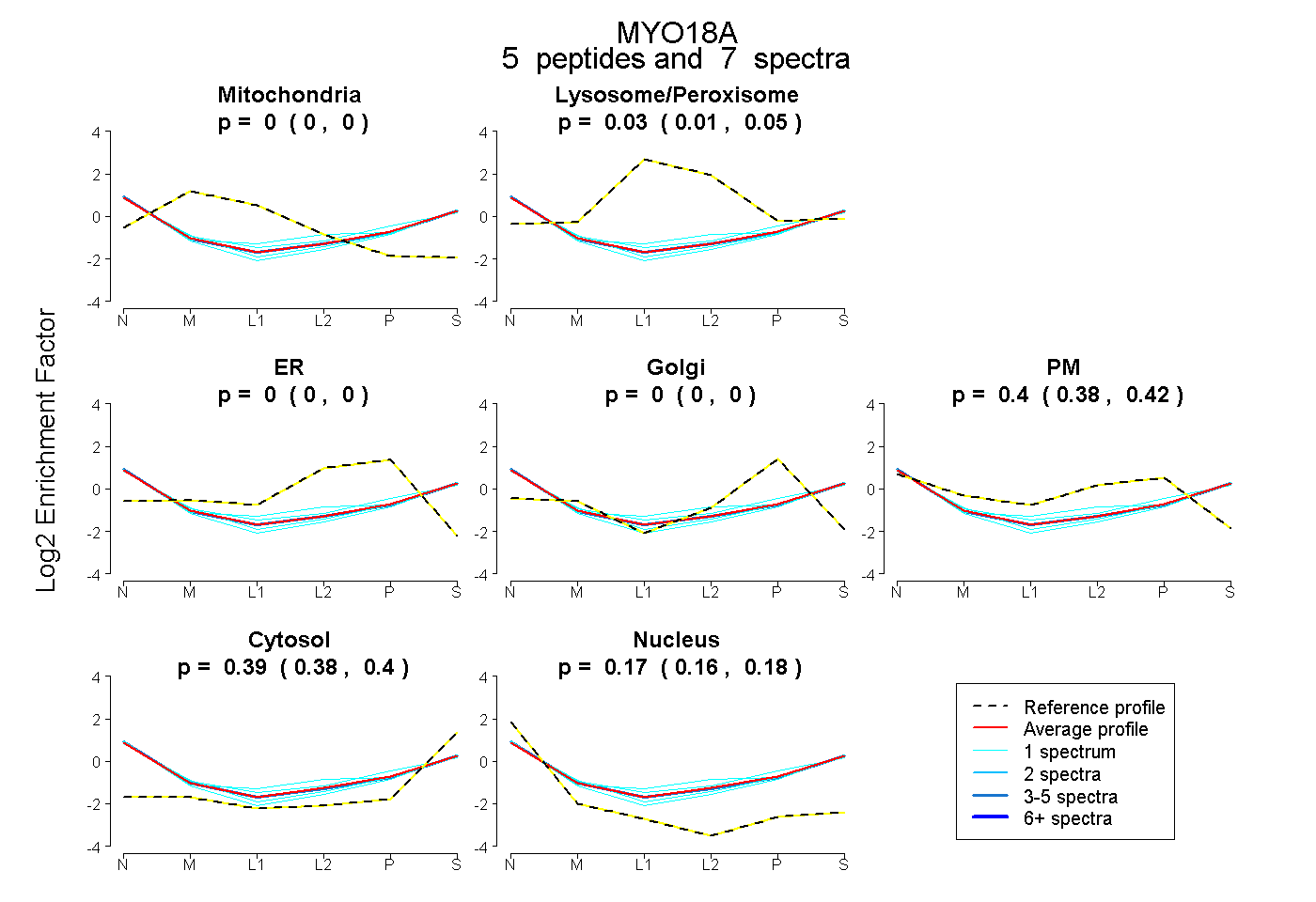
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
 |
0.000 0.000 | 0.000 |
0.033 0.011 | 0.051 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.403 0.379 | 0.424 |
0.393 0.383 | 0.402 |
0.172 0.158 | 0.183 |
|||
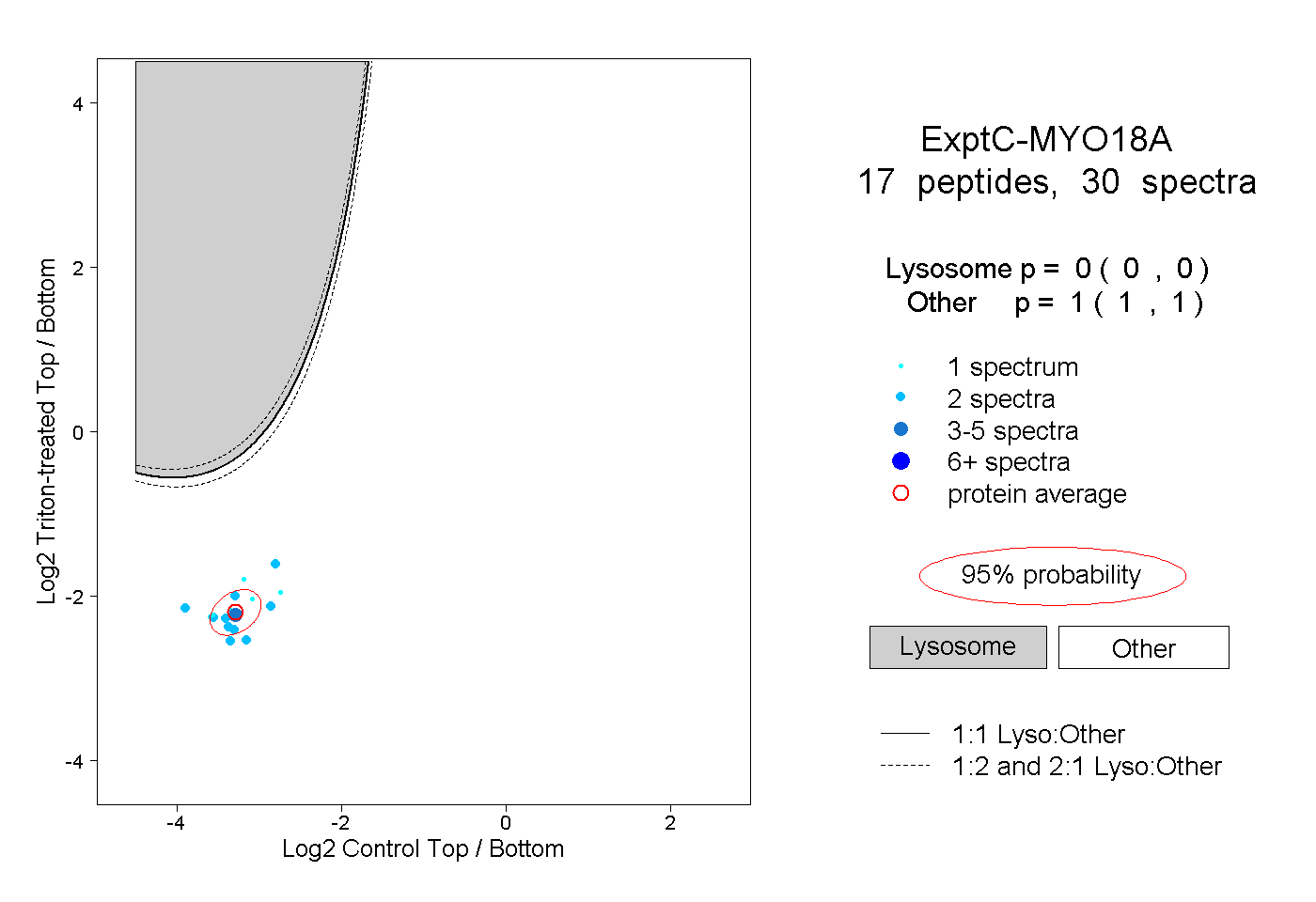
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
30 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
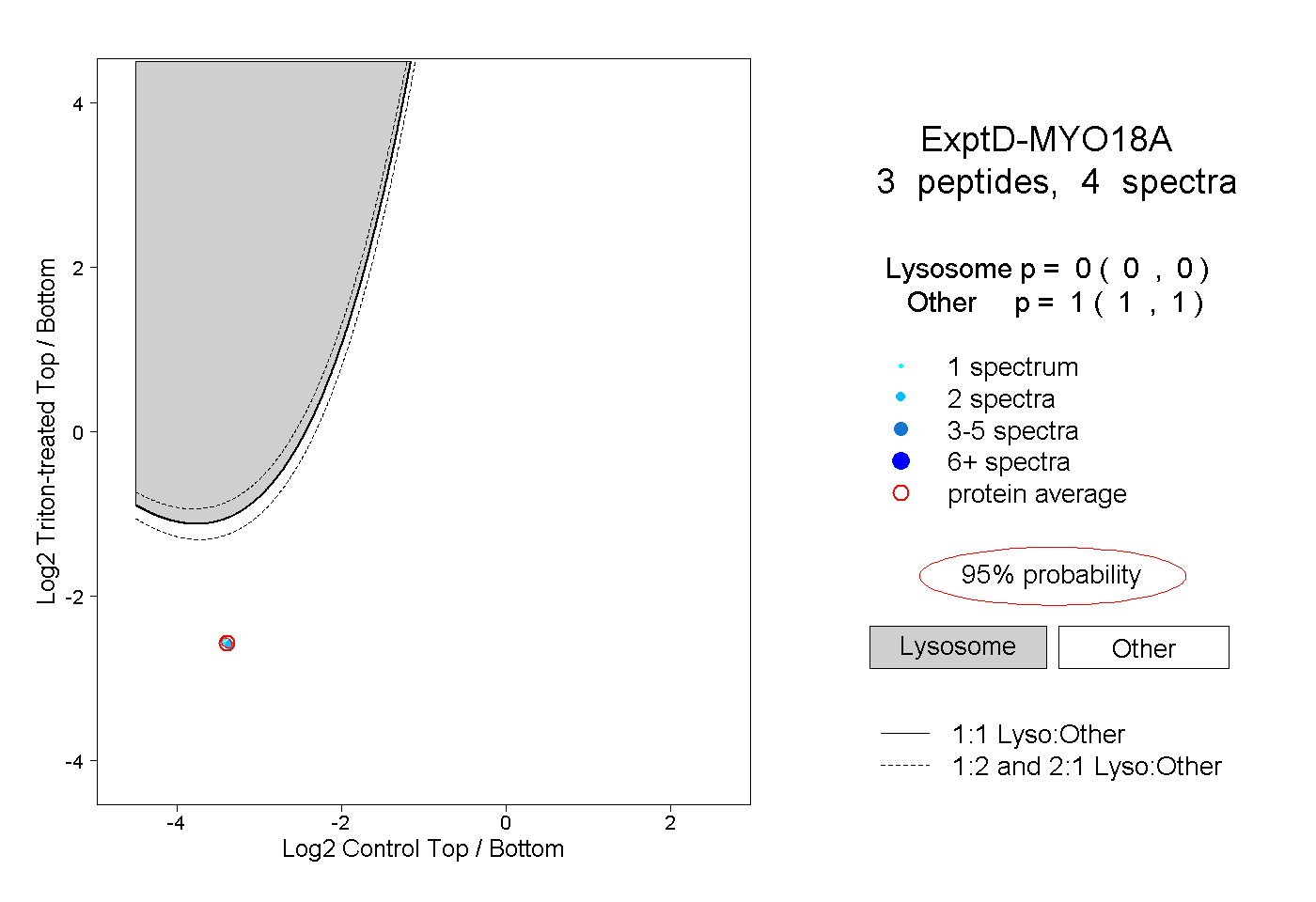
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |