peptides
spectra
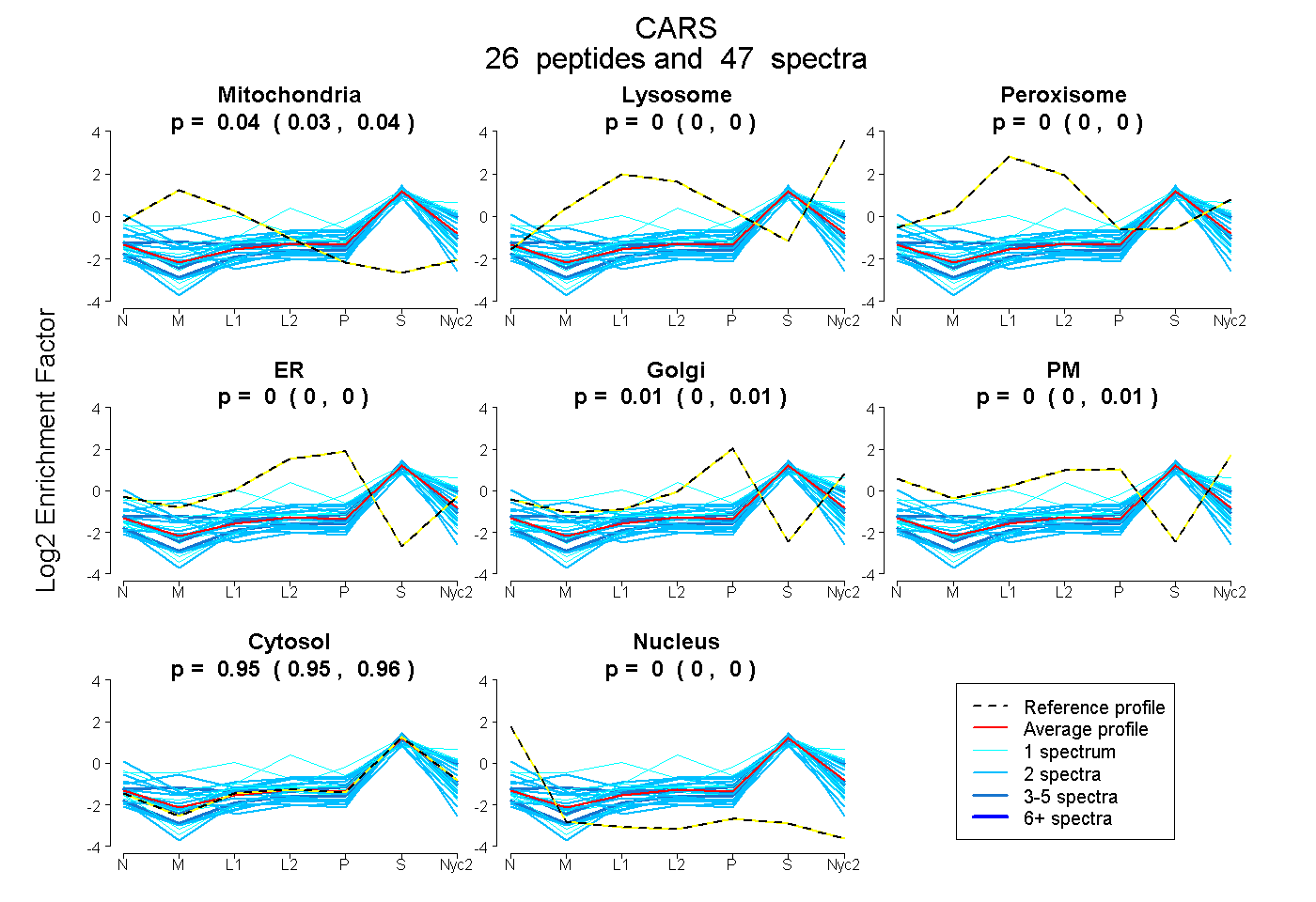
0.031 | 0.044
0.000 | 0.002
0.000 | 0.000
0.000 | 0.000
0.000 | 0.014
0.000 | 0.006
0.947 | 0.957
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
47 spectra |
 |
0.038 0.031 | 0.044 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.000 | 0.014 |
0.000 0.000 | 0.006 |
0.953 0.947 | 0.957 |
0.000 0.000 | 0.000 |
| 1 spectrum, VSEYVPEIVNFVQK | 0.000 | 0.120 | 0.000 | 0.000 | 0.000 | 0.000 | 0.880 | 0.000 | ||
| 2 spectra, SPNDFALWK | 0.000 | 0.136 | 0.000 | 0.000 | 0.042 | 0.000 | 0.822 | 0.000 | ||
| 2 spectra, WEAEEVELNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.978 | 0.022 | ||
| 1 spectrum, NFITIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | 0.930 | 0.006 | ||
| 2 spectra, TAVHEALCDNIDTR | 0.268 | 0.000 | 0.000 | 0.035 | 0.000 | 0.000 | 0.697 | 0.000 | ||
| 2 spectra, LATEPLEQAVHSNPSGEEVDSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.968 | 0.032 | ||
| 1 spectrum, FMNEFFLNVK | 0.000 | 0.098 | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | ||
| 1 spectrum, EYLQQLQNSSLQ | 0.121 | 0.239 | 0.106 | 0.000 | 0.000 | 0.000 | 0.534 | 0.000 | ||
| 4 spectra, LFEAQEK | 0.073 | 0.116 | 0.000 | 0.000 | 0.000 | 0.000 | 0.810 | 0.000 | ||
| 1 spectrum, DTLDYSSNTMESALQYEK | 0.000 | 0.101 | 0.000 | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 | ||
| 2 spectra, LYNSLTR | 0.000 | 0.025 | 0.000 | 0.000 | 0.000 | 0.229 | 0.746 | 0.000 | ||
| 2 spectra, DDILPELGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.026 | ||
| 2 spectra, FEDHEGLPTVVK | 0.017 | 0.011 | 0.126 | 0.000 | 0.000 | 0.072 | 0.774 | 0.000 | ||
| 2 spectra, LAFLMHSWK | 0.000 | 0.086 | 0.000 | 0.000 | 0.040 | 0.000 | 0.874 | 0.000 | ||
| 4 spectra, QNYLFEQYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.959 | 0.009 | ||
| 1 spectrum, TVMEEMR | 0.000 | 0.011 | 0.127 | 0.000 | 0.000 | 0.247 | 0.615 | 0.000 | ||
| 3 spectra, FWEEEFHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.987 | 0.013 | ||
| 2 spectra, LVPEAVGDQK | 0.129 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.854 | 0.017 | ||
| 1 spectrum, ALQEGEGDLSISADR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.920 | 0.080 | ||
| 1 spectrum, APVDITGQFEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.938 | 0.062 | ||
| 2 spectra, VLEVLQLSDALR | 0.001 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.999 | 0.000 | ||
| 2 spectra, SYISFDILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.012 | ||
| 2 spectra, VQVLLEEAK | 0.060 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.659 | 0.281 | ||
| 1 spectrum, FDENGLPTHDTEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.970 | 0.030 | ||
| 1 spectrum, YFLHTGHLTIAGCK | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.935 | 0.000 | ||
| 2 spectra, ALVSQCNLYMAAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.857 | 0.143 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
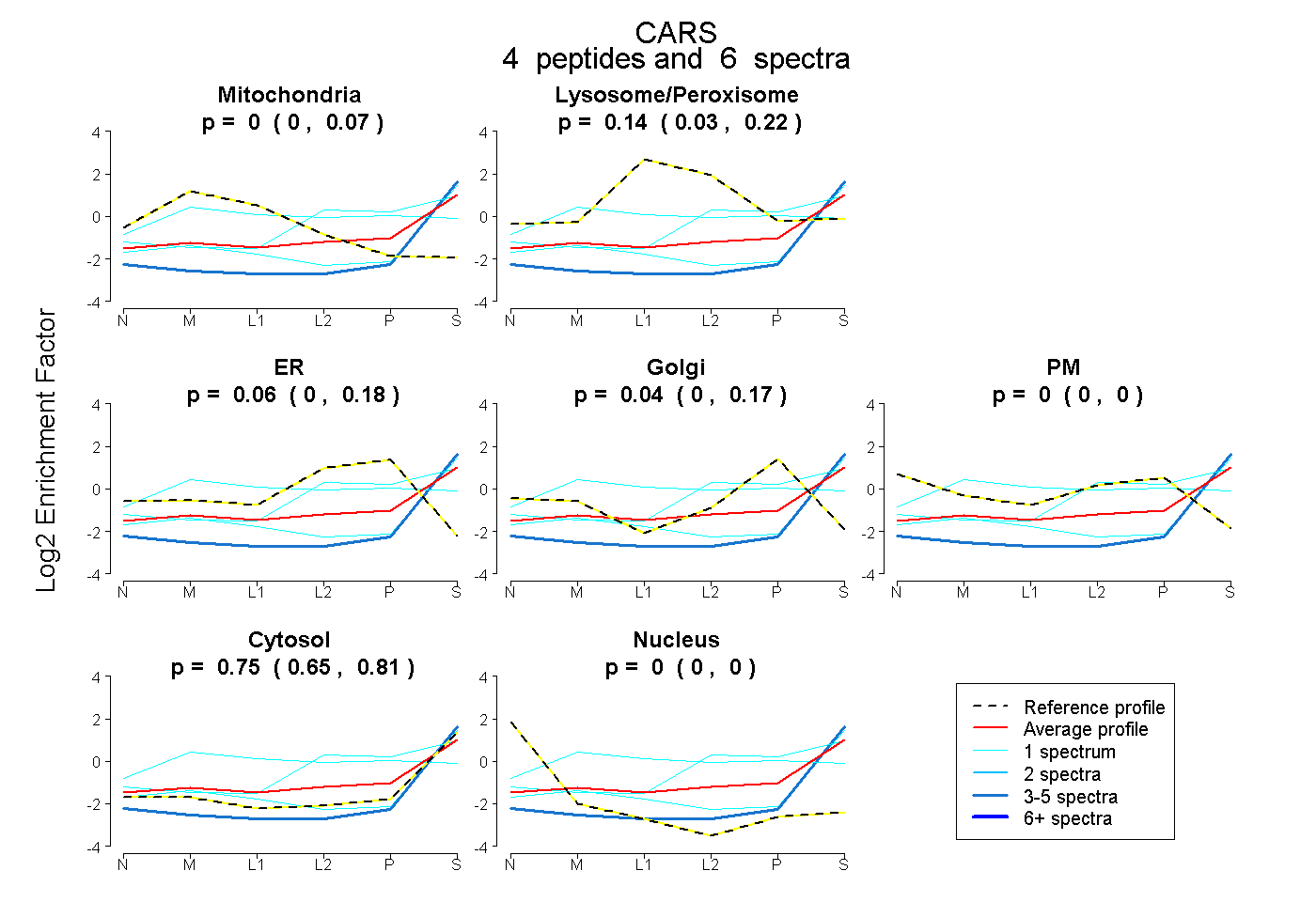 |
0.000 0.000 | 0.073 |
0.143 0.035 | 0.218 |
0.063 0.000 | 0.177 |
0.042 0.000 | 0.165 |
0.000 0.000 | 0.000 |
0.752 0.655 | 0.809 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
41 spectra |
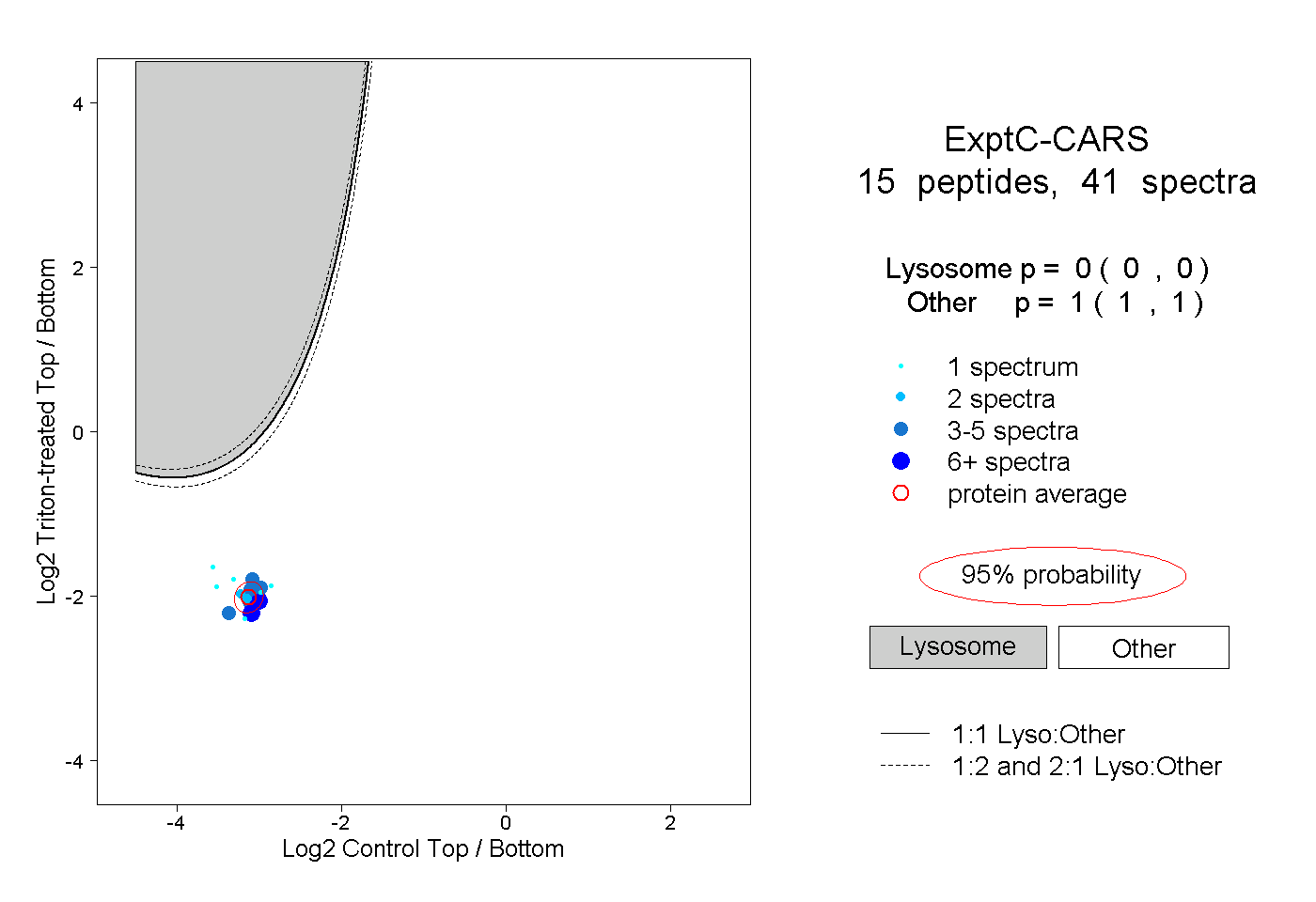 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
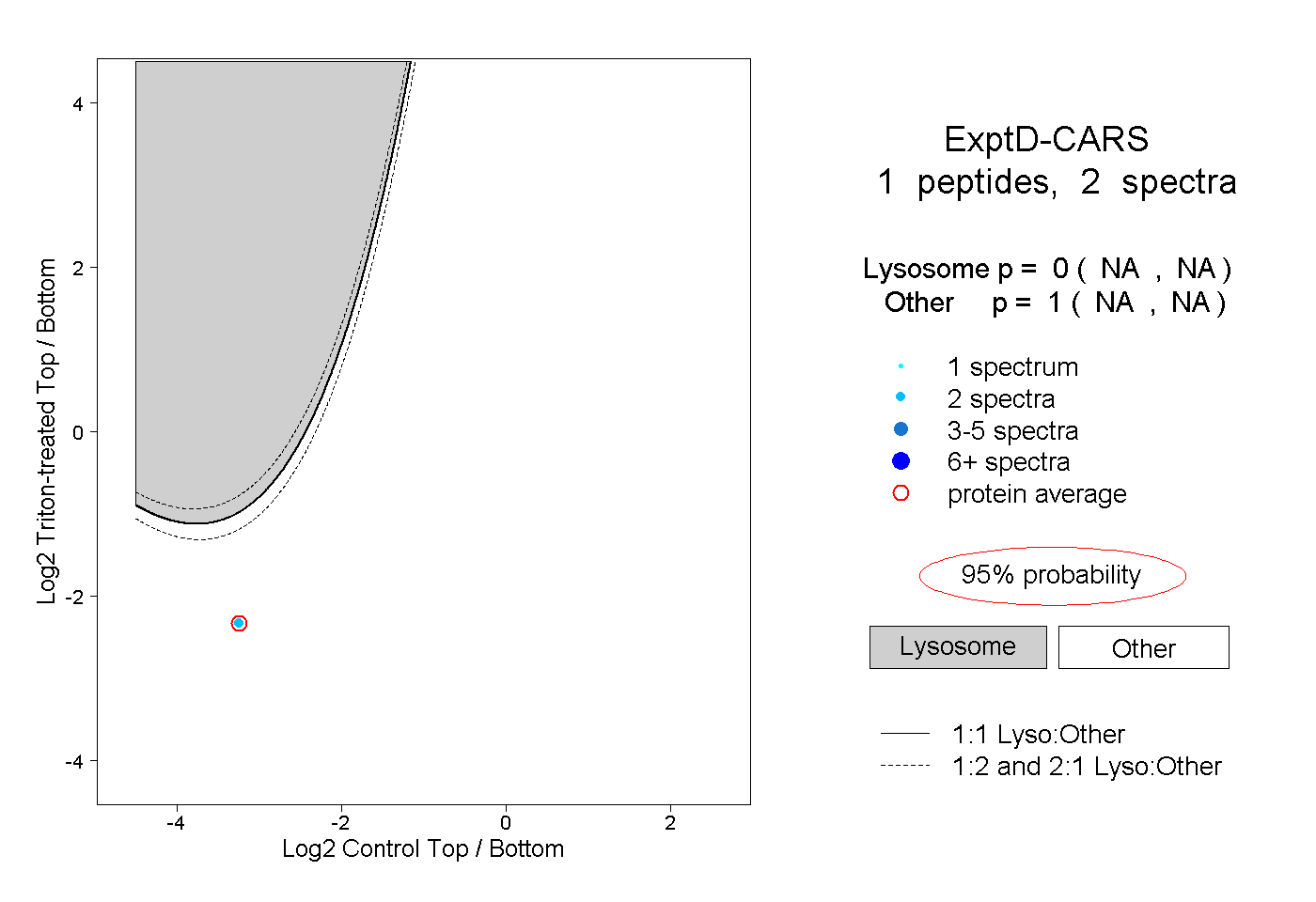 |
0.000 NA | NA |
1.000 NA | NA |