peptides
spectra
0.100 | 0.111
0.000 | 0.000
0.768 | 0.781
0.082 | 0.090
0.000 | 0.000
0.000 | 0.000
0.016 | 0.023
0.009 | 0.016
peptides
spectra
0.000 | 0.000
0.781 | 0.794
0.000 | 0.004
0.000 | 0.021
0.016 | 0.040
0.166 | 0.175
0.000 | 0.000
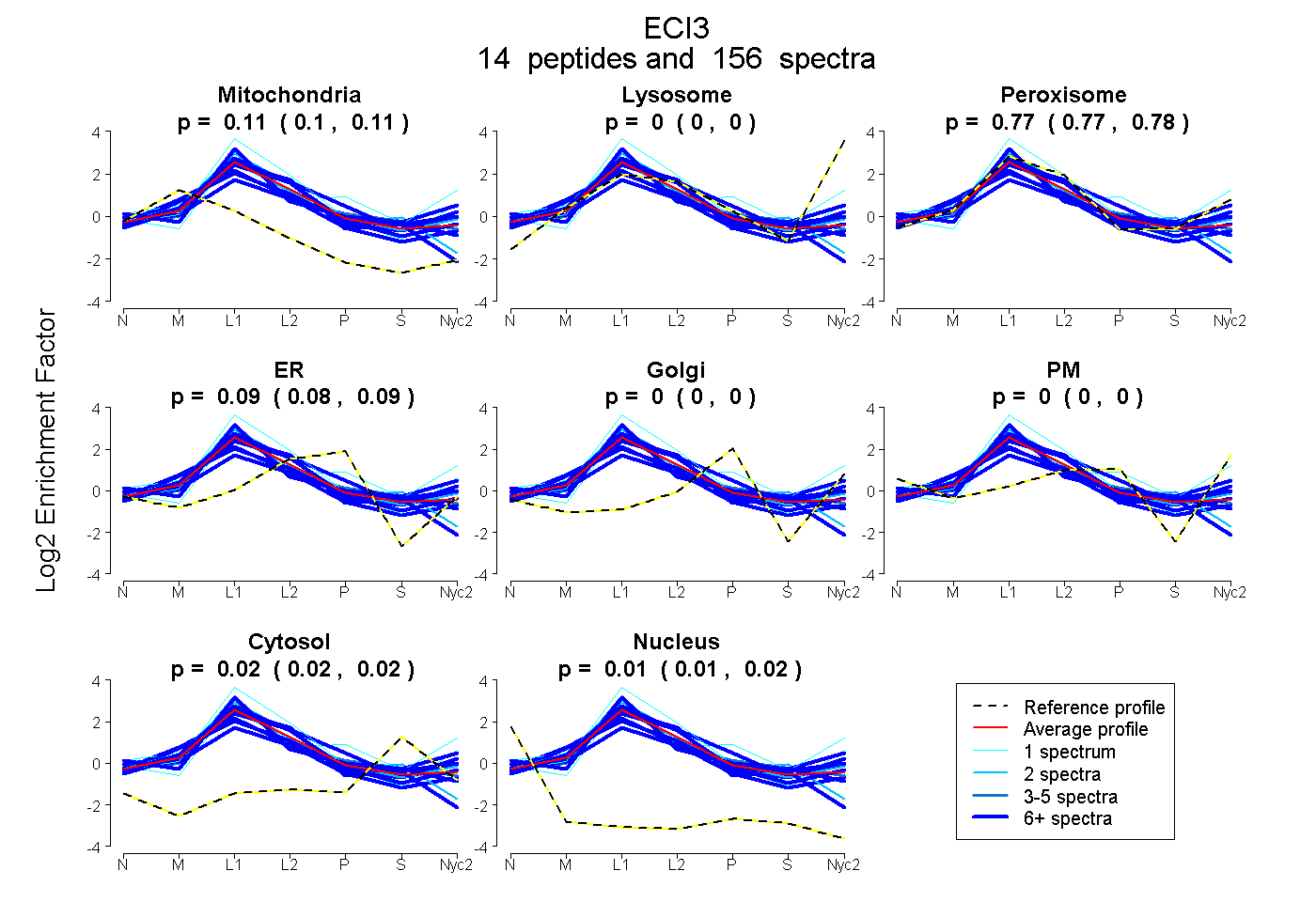
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
156 spectra |
 |
0.106 0.100 | 0.111 |
0.000 0.000 | 0.000 |
0.775 0.768 | 0.781 |
0.086 0.082 | 0.090 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.020 0.016 | 0.023 |
0.012 0.009 | 0.016 |
||
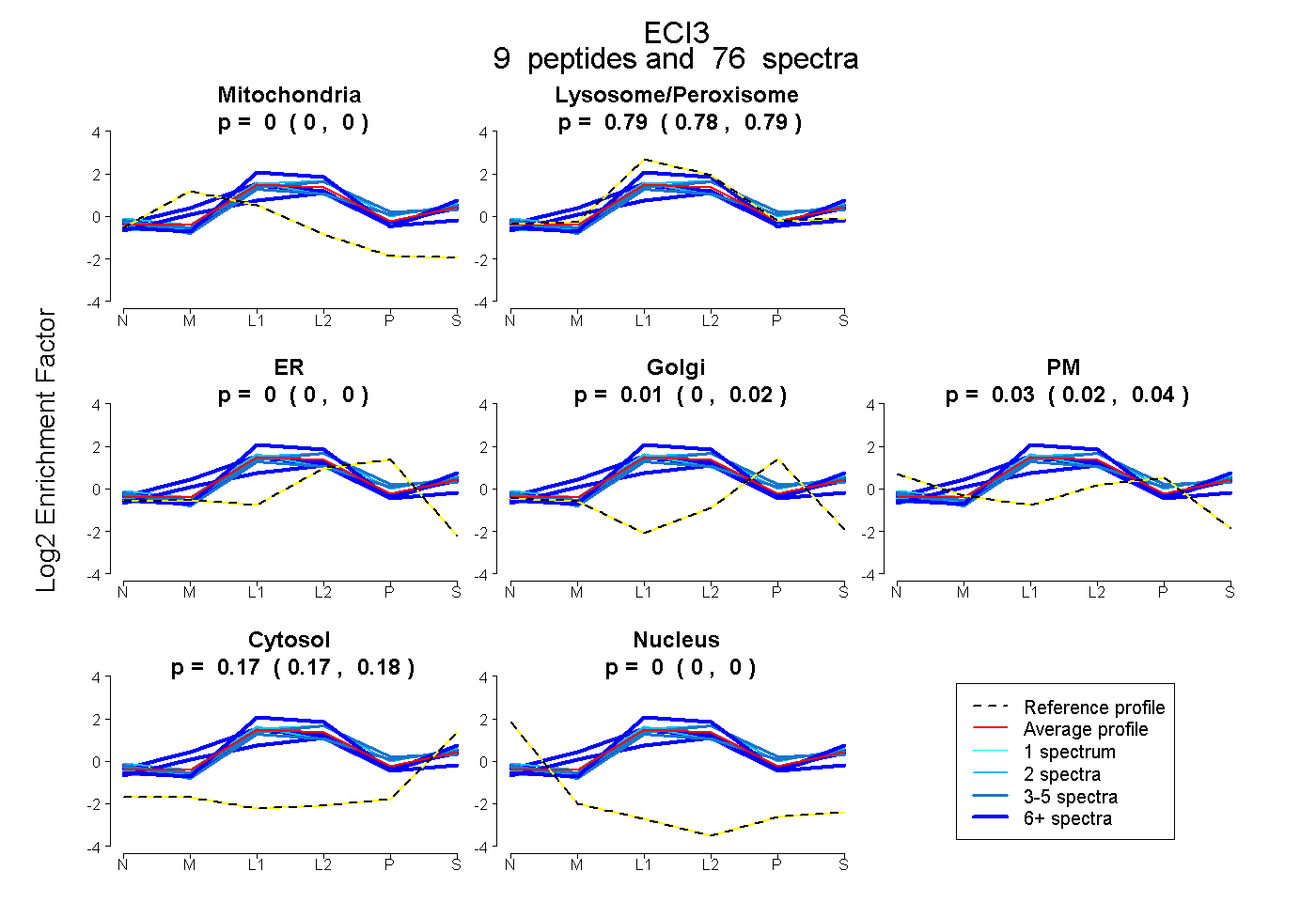
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
76 spectra |
 |
0.000 0.000 | 0.000 |
0.788 0.781 | 0.794 |
0.000 0.000 | 0.004 |
0.010 0.000 | 0.021 |
0.030 0.016 | 0.040 |
0.171 0.166 | 0.175 |
0.000 0.000 | 0.000 |
| 4 spectra, NFINDAGEIQDK | 0.000 | 0.724 | 0.000 | 0.091 | 0.008 | 0.176 | 0.000 | |||
| 12 spectra, DIMLALK | 0.000 | 0.767 | 0.000 | 0.000 | 0.023 | 0.210 | 0.000 | |||
| 6 spectra, MMGSAK | 0.010 | 0.643 | 0.075 | 0.043 | 0.000 | 0.229 | 0.000 | |||
| 5 spectra, NAISFQMYK | 0.000 | 0.738 | 0.149 | 0.000 | 0.000 | 0.114 | 0.000 | |||
| 21 spectra, AAEMLLFGK | 0.209 | 0.673 | 0.000 | 0.031 | 0.029 | 0.057 | 0.000 | |||
| 2 spectra, ETAMDLK | 0.000 | 0.804 | 0.033 | 0.000 | 0.000 | 0.163 | 0.000 | |||
| 2 spectra, LSPNGMR | 0.000 | 0.882 | 0.000 | 0.000 | 0.000 | 0.118 | 0.000 | |||
| 22 spectra, VTMCAVLLR | 0.000 | 0.878 | 0.000 | 0.000 | 0.000 | 0.122 | 0.000 | |||
| 2 spectra, LYTVNAEECAVGQER | 0.000 | 0.753 | 0.000 | 0.000 | 0.079 | 0.168 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
816 spectra |
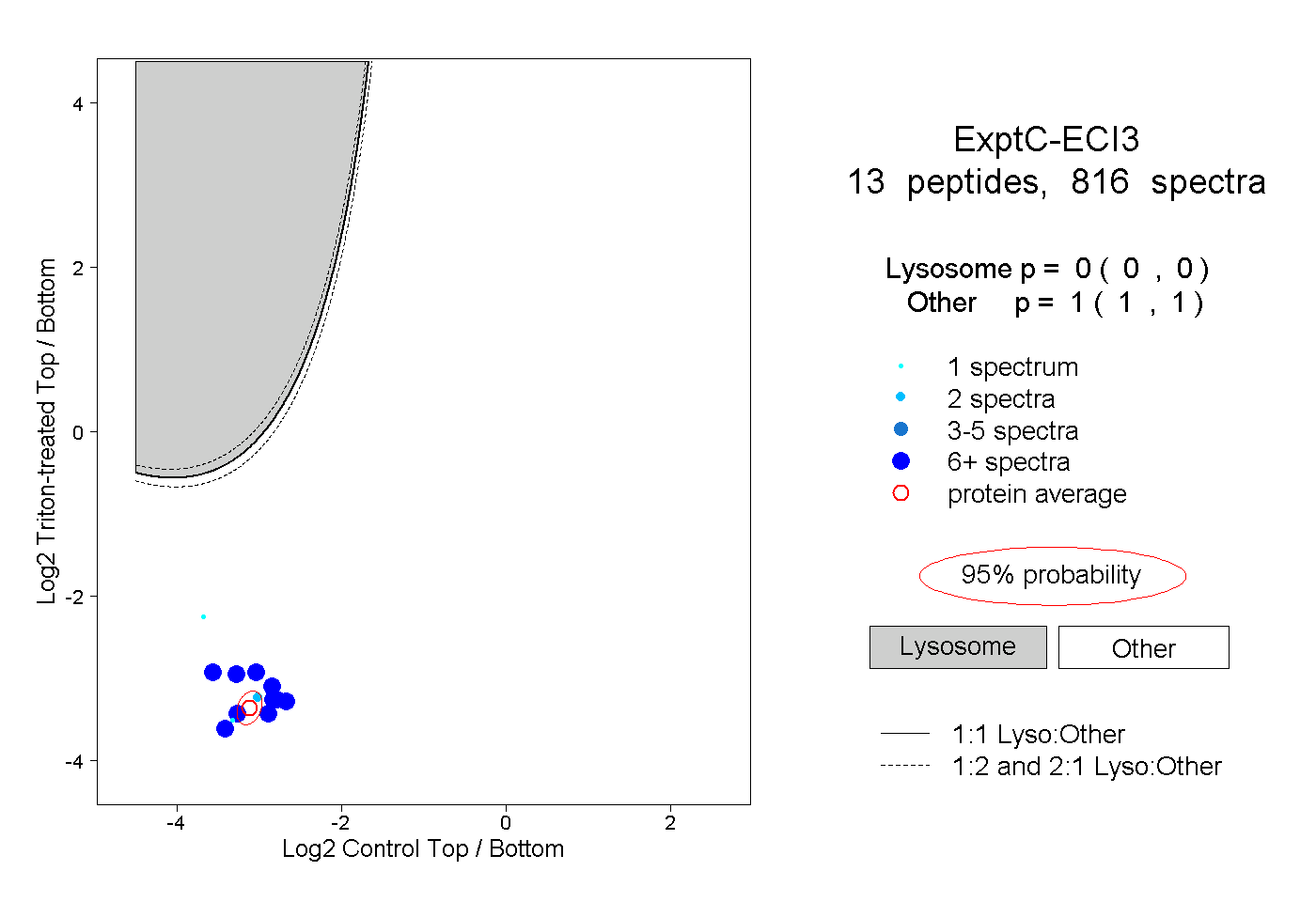 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
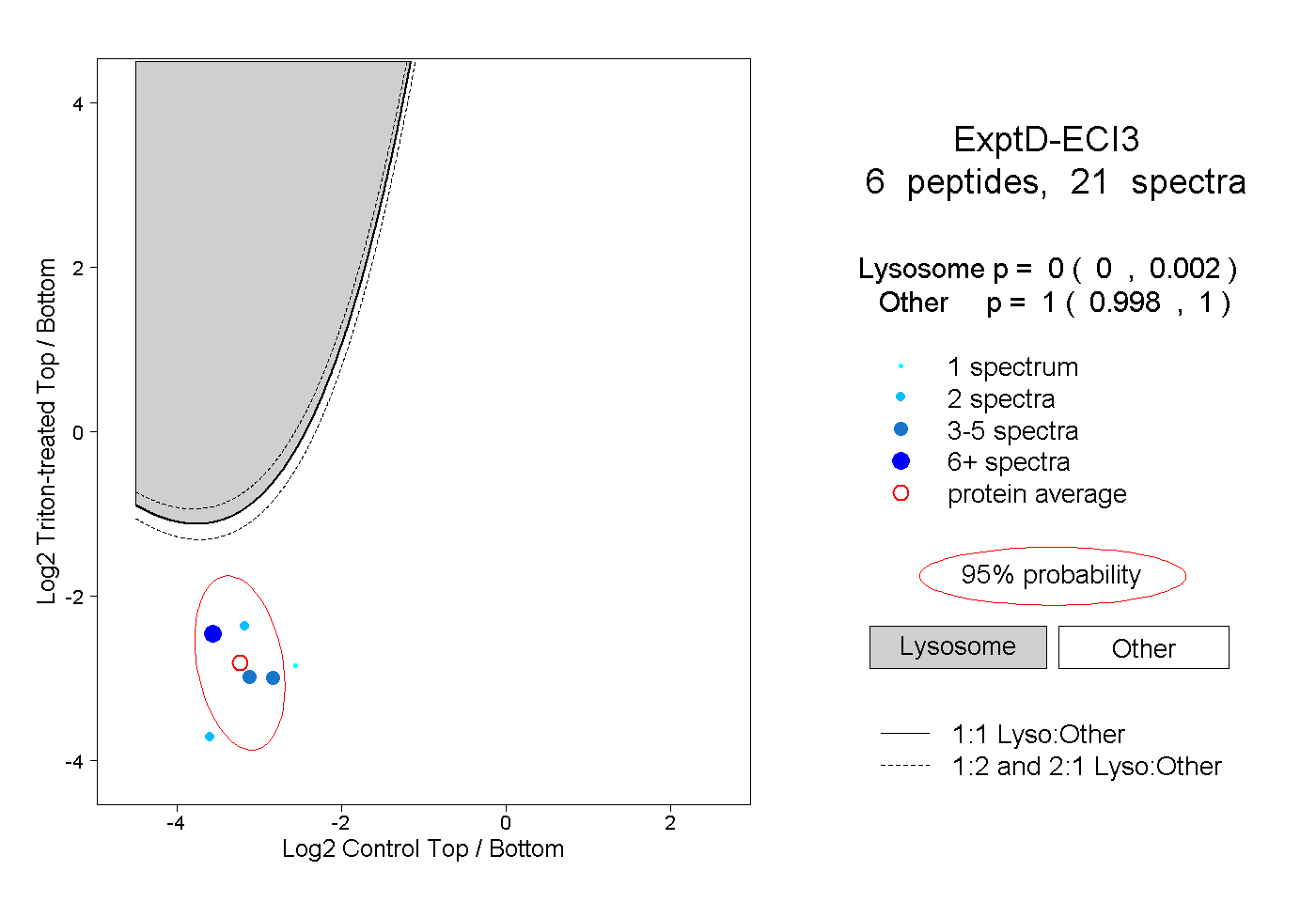 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |