peptides
spectra
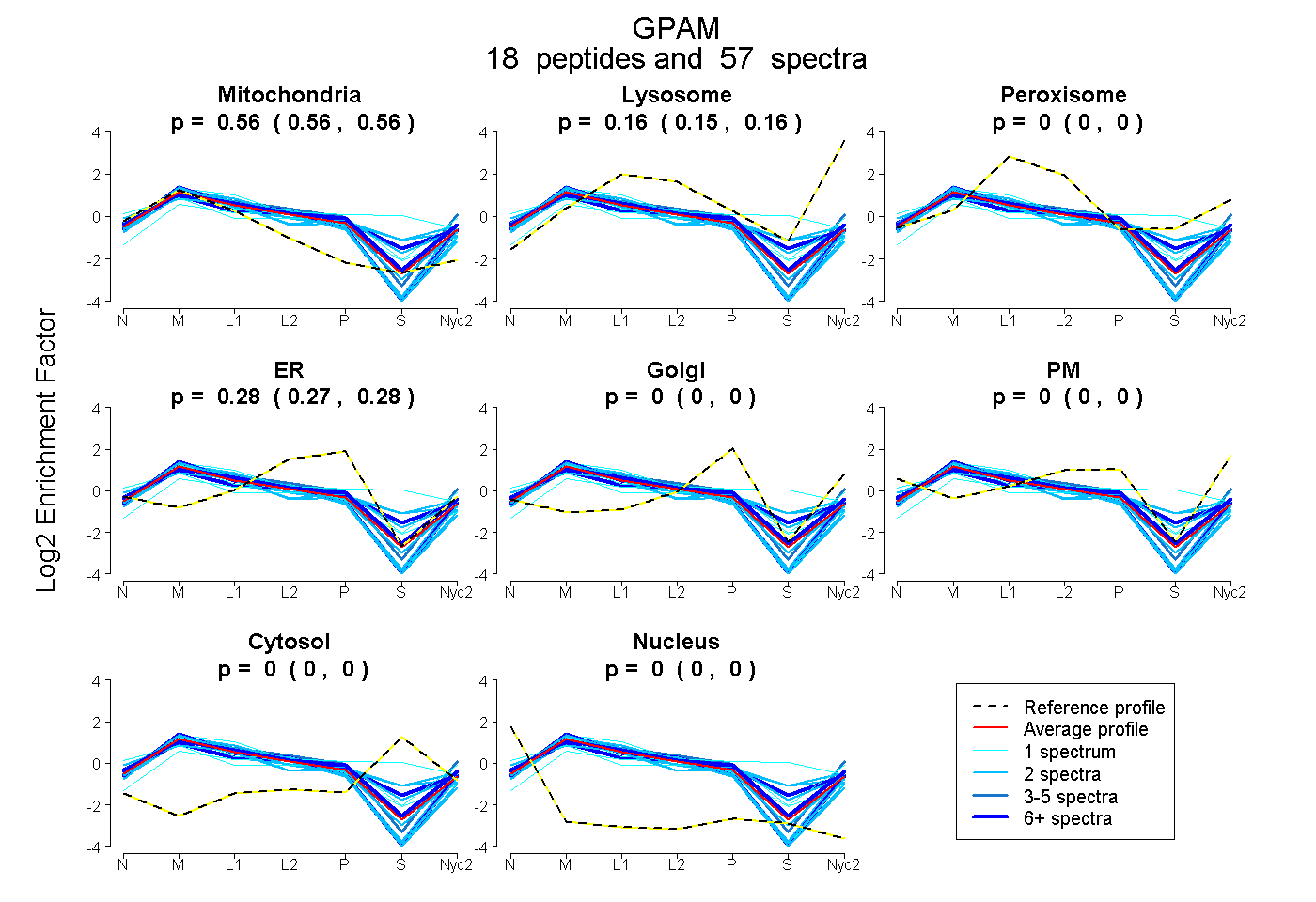
0.560 | 0.565
0.153 | 0.165
0.000 | 0.000
0.272 | 0.282
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
0.000 | 0.000
peptides
spectra
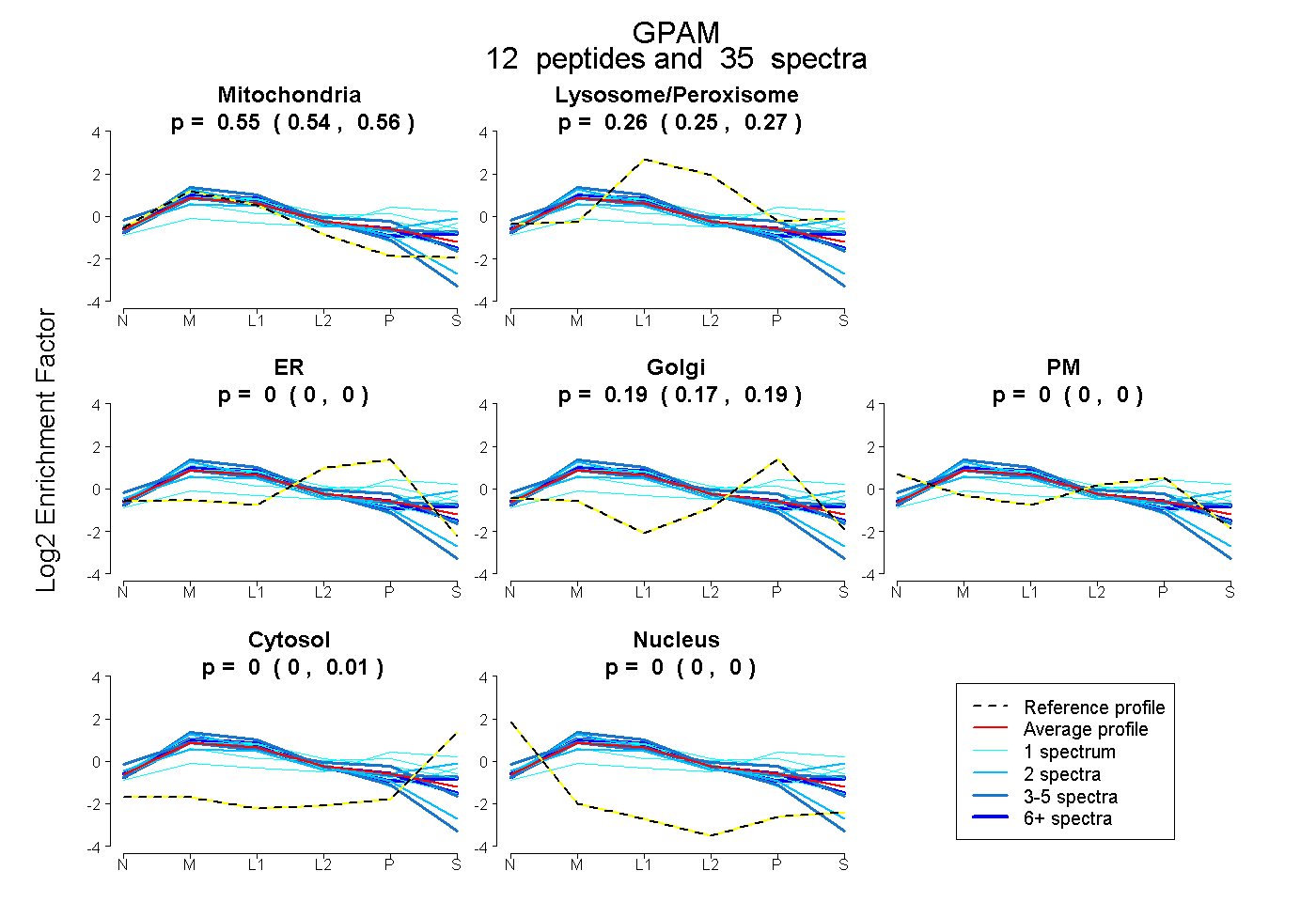
0.536 | 0.564
0.248 | 0.268
0.000 | 0.000
0.174 | 0.195
0.000 | 0.000
0.000 | 0.013
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
57 spectra |
 |
0.563 0.560 | 0.565 |
0.160 0.153 | 0.165 |
0.000 0.000 | 0.000 |
0.278 0.272 | 0.282 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.553 0.536 | 0.564 |
0.258 0.248 | 0.268 |
0.000 0.000 | 0.000 |
0.188 0.174 | 0.195 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.013 |
0.000 0.000 | 0.000 |
| 1 spectrum, GMFATSITDNVLNSSR | 0.246 | 0.352 | 0.000 | 0.334 | 0.000 | 0.069 | 0.000 | |||
| 5 spectra, EHQQFITFLQR | 0.499 | 0.294 | 0.000 | 0.115 | 0.000 | 0.091 | 0.000 | |||
| 8 spectra, ALLHGHIVELLR | 0.617 | 0.227 | 0.024 | 0.133 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LGGFFIR | 0.835 | 0.000 | 0.165 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DIGVFK | 0.514 | 0.335 | 0.000 | 0.000 | 0.000 | 0.151 | 0.000 | |||
| 2 spectra, NVIYINETHTR | 0.352 | 0.341 | 0.000 | 0.103 | 0.000 | 0.204 | 0.000 | |||
| 1 spectrum, LDETPDGR | 0.403 | 0.390 | 0.000 | 0.196 | 0.000 | 0.011 | 0.000 | |||
| 2 spectra, LSYILFVQER | 0.775 | 0.000 | 0.225 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, AATETNLPLLFLPVHR | 0.579 | 0.264 | 0.000 | 0.069 | 0.000 | 0.088 | 0.000 | |||
| 1 spectrum, NAADEAFR | 0.000 | 0.362 | 0.000 | 0.359 | 0.000 | 0.280 | 0.000 | |||
| 3 spectra, NVAVYAESATYCLVK | 0.481 | 0.161 | 0.131 | 0.027 | 0.200 | 0.000 | 0.000 | |||
| 1 spectrum, IIEGHYNGEQLGKPK | 0.663 | 0.213 | 0.000 | 0.124 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
141 spectra |
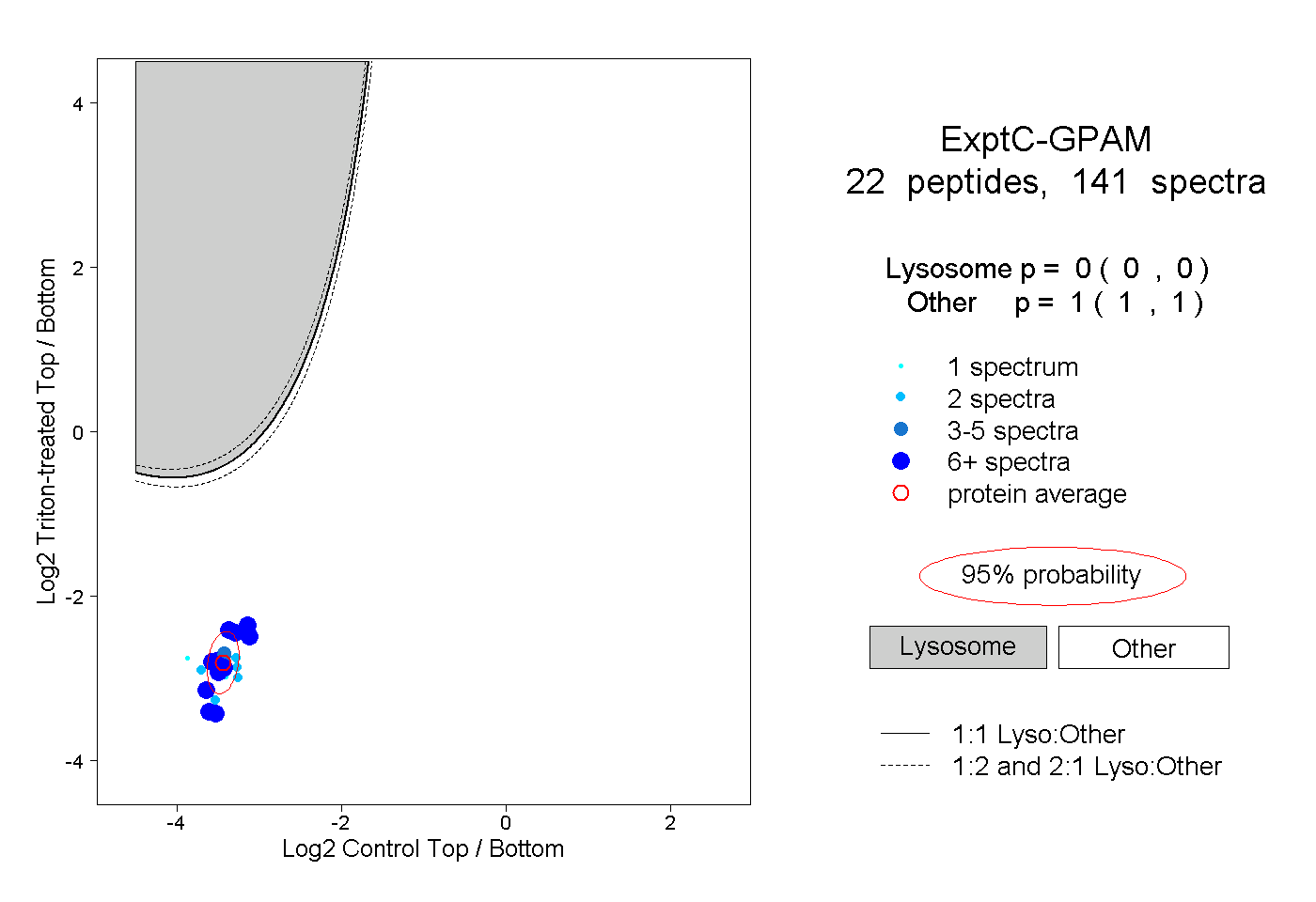 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
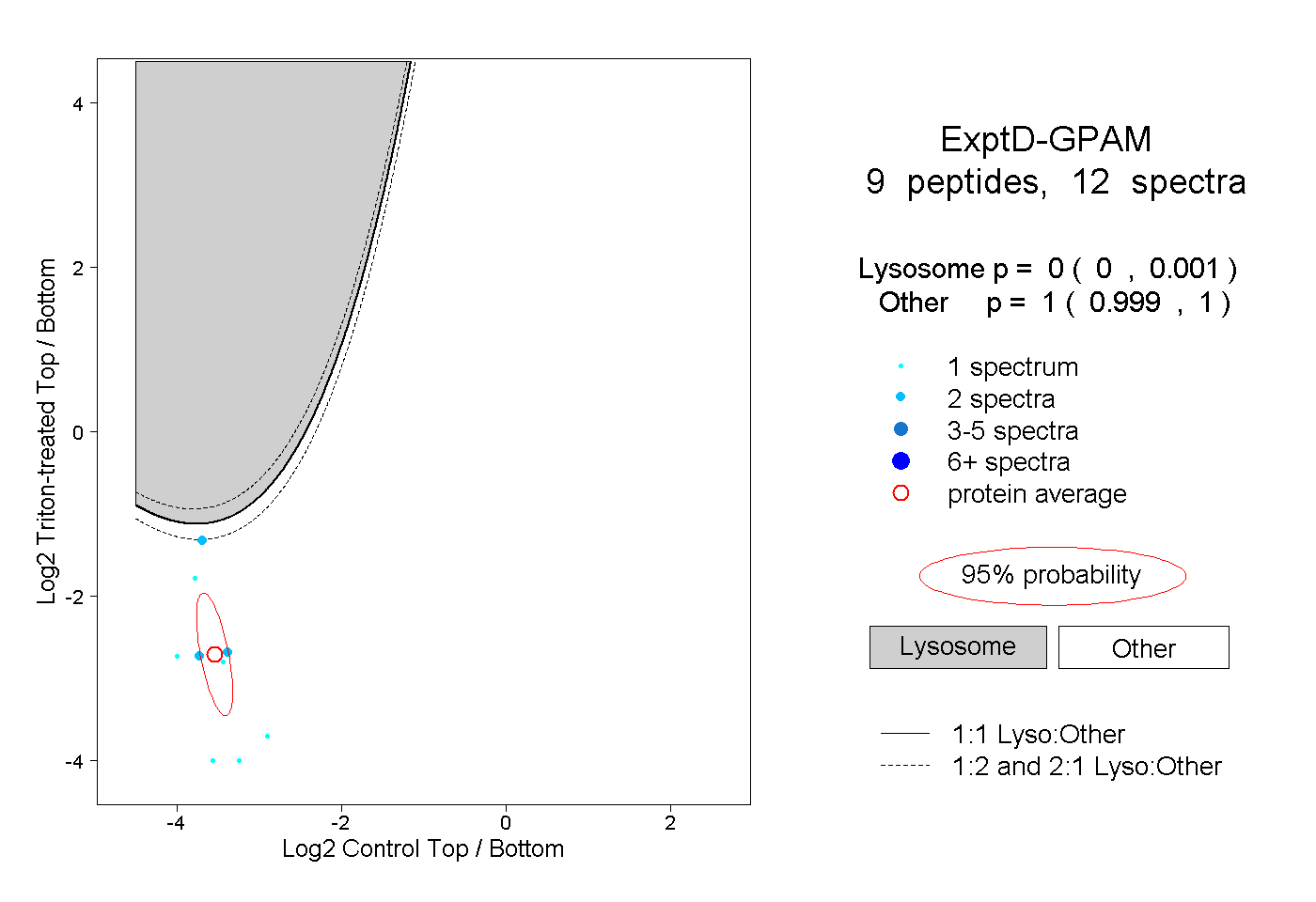 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |