peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.936 | 0.945
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.054 | 0.063
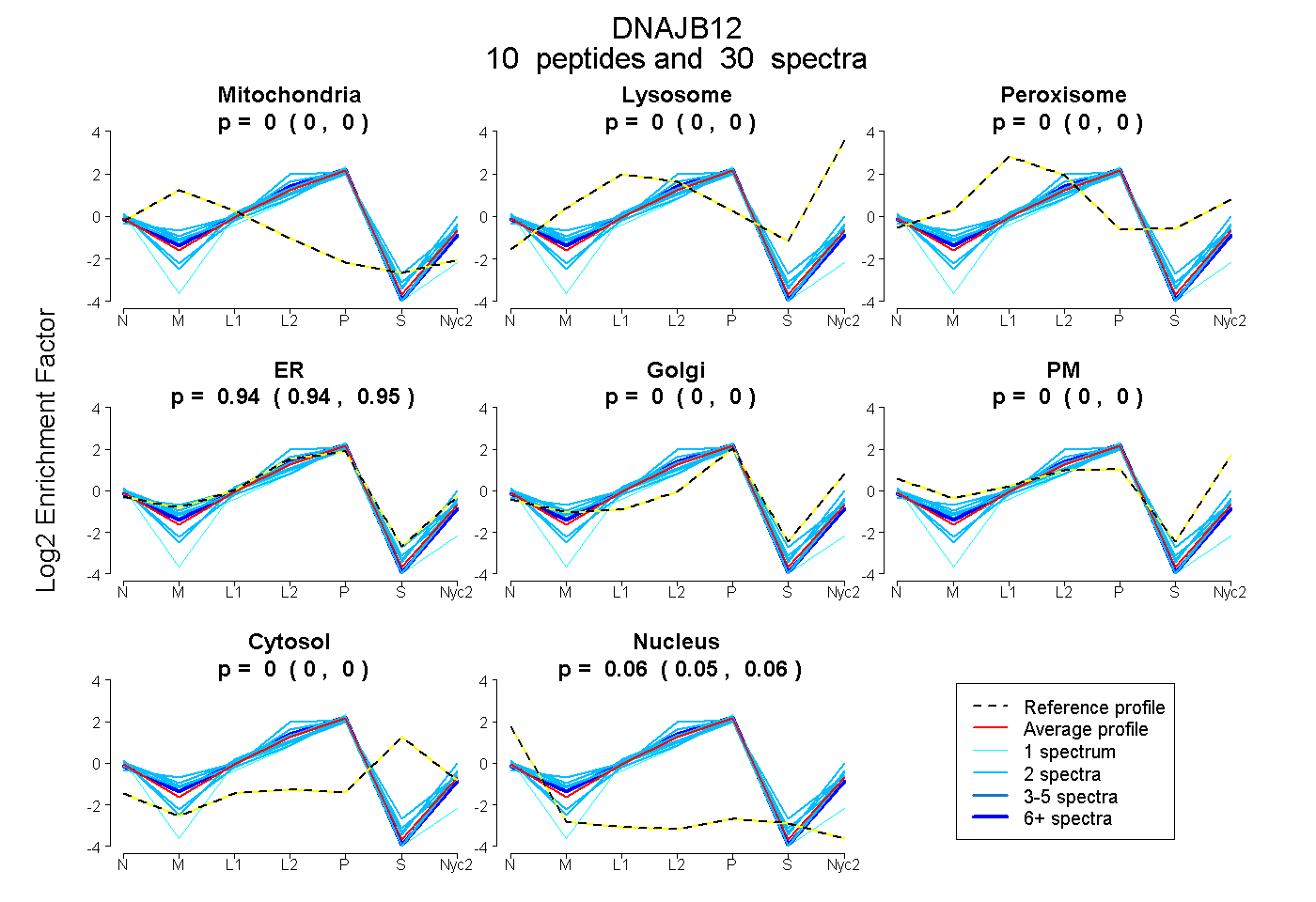
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
30 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.941 0.936 | 0.945 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.059 0.054 | 0.063 |
| 2 spectra, YFGDTDMYHR | 0.042 | 0.000 | 0.000 | 0.854 | 0.088 | 0.000 | 0.000 | 0.016 | ||
| 2 spectra, YTYQQR | 0.000 | 0.000 | 0.000 | 0.989 | 0.000 | 0.000 | 0.000 | 0.011 | ||
| 2 spectra, GYTSEQVAAVK | 0.000 | 0.000 | 0.000 | 0.931 | 0.000 | 0.000 | 0.000 | 0.069 | ||
| 2 spectra, SLENFW | 0.000 | 0.000 | 0.000 | 0.952 | 0.048 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, NVEDDYIANLR | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | 0.000 | 0.000 | 0.028 | ||
| 14 spectra, MSTPSCSR | 0.000 | 0.000 | 0.000 | 0.955 | 0.000 | 0.000 | 0.000 | 0.045 | ||
| 1 spectrum, AIQSNQPDR | 0.000 | 0.000 | 0.000 | 0.796 | 0.000 | 0.000 | 0.000 | 0.204 | ||
| 2 spectra, LYPTPR | 0.000 | 0.000 | 0.000 | 0.744 | 0.174 | 0.000 | 0.000 | 0.082 | ||
| 2 spectra, VTALIESLNQK | 0.000 | 0.000 | 0.000 | 0.942 | 0.000 | 0.000 | 0.000 | 0.058 | ||
| 1 spectrum, EGLLYR | 0.000 | 0.000 | 0.000 | 0.805 | 0.116 | 0.000 | 0.000 | 0.079 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
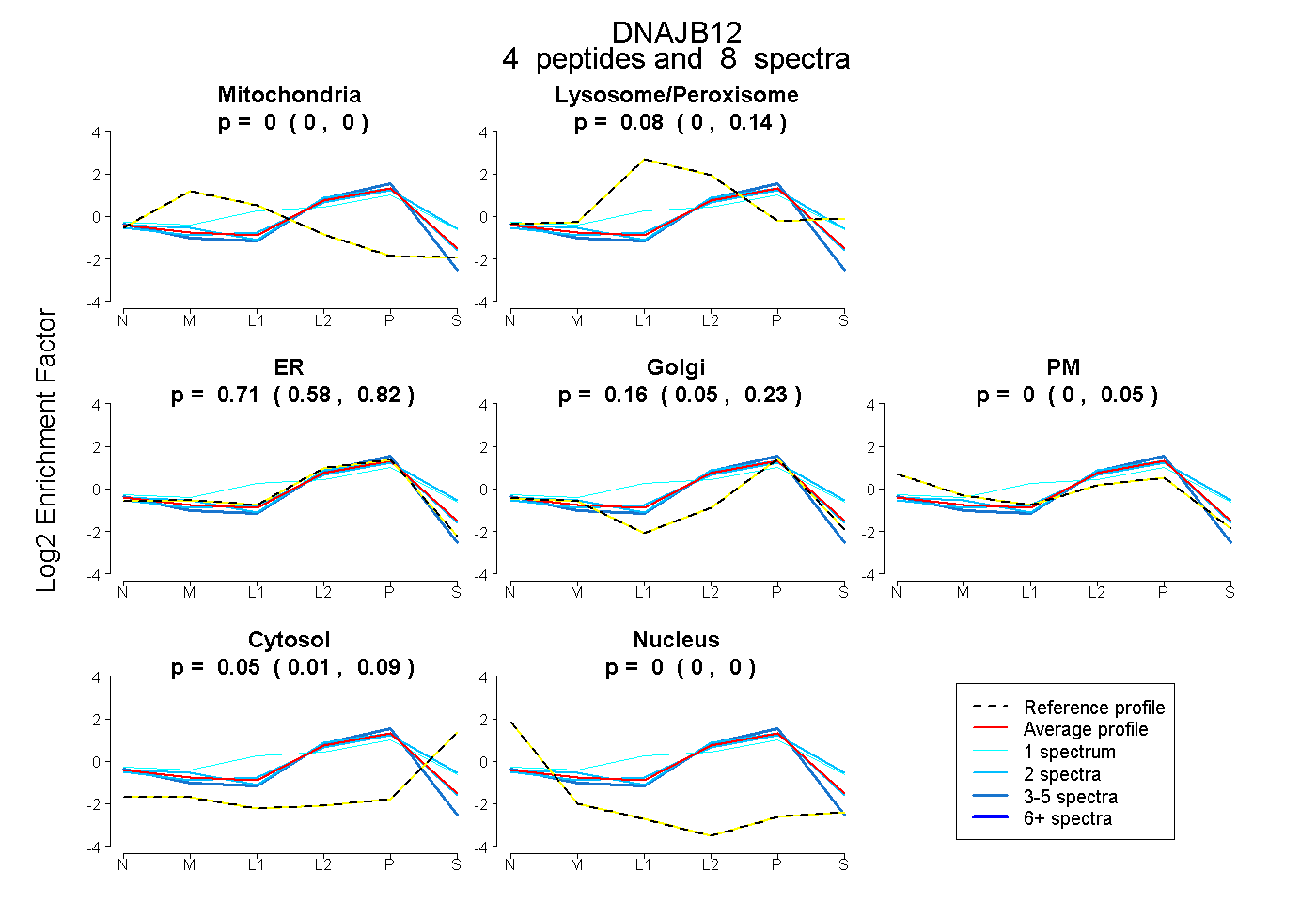 |
0.000 0.000 | 0.000 |
0.082 0.000 | 0.141 |
0.707 0.575 | 0.818 |
0.161 0.050 | 0.228 |
0.000 0.000 | 0.051 |
0.051 0.010 | 0.087 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
11 spectra |
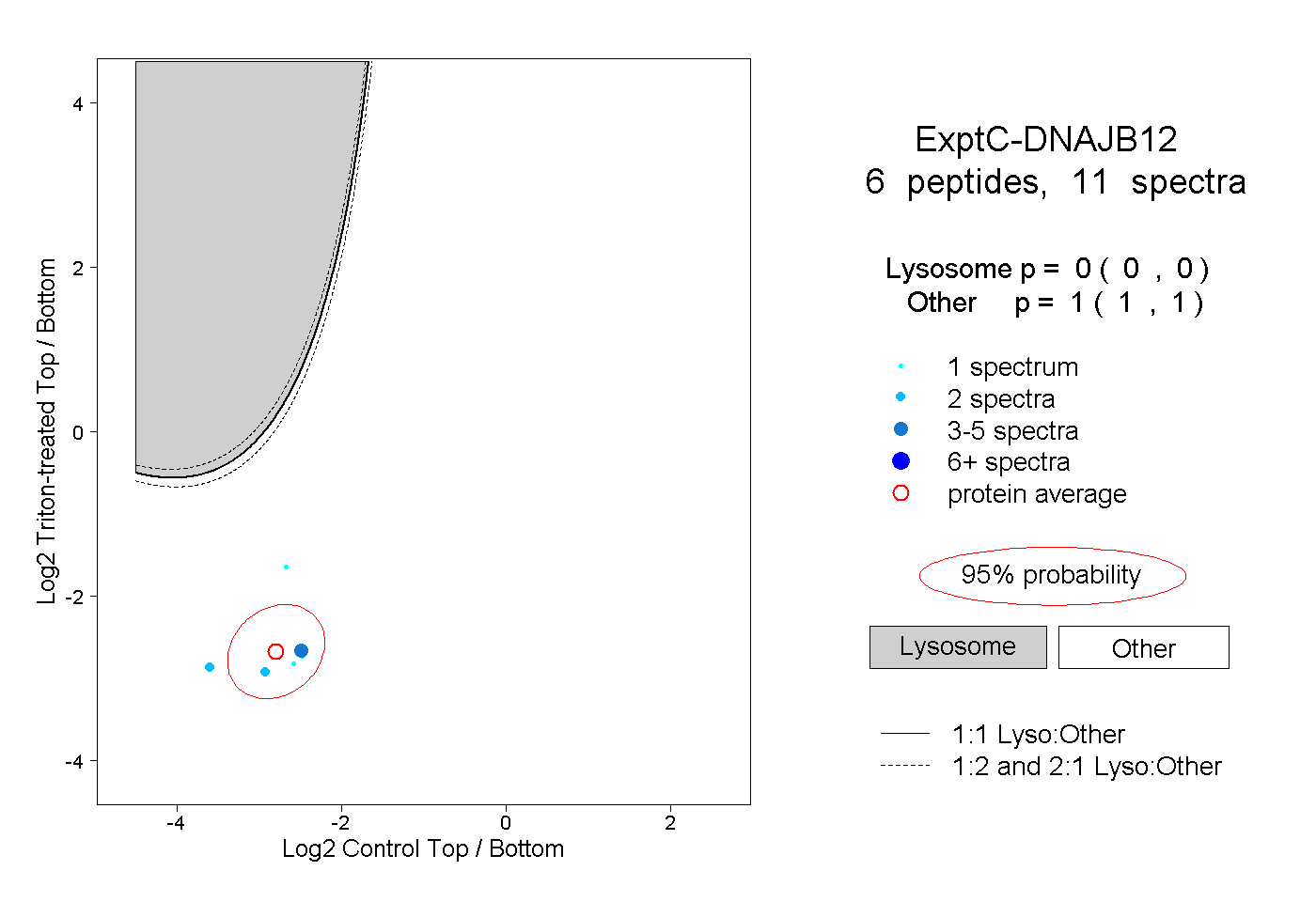 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
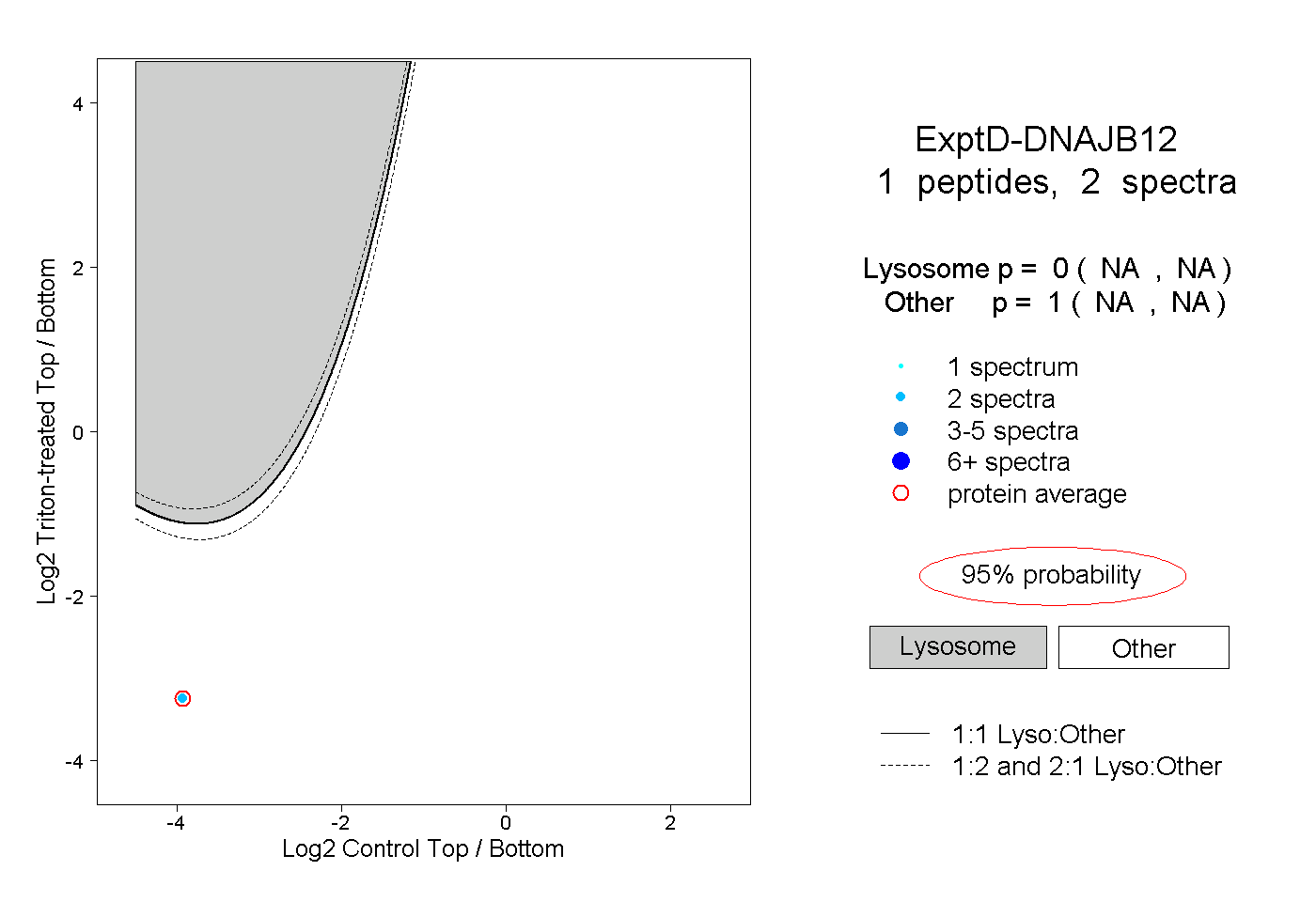 |
0.000 NA | NA |
1.000 NA | NA |