peptides
spectra
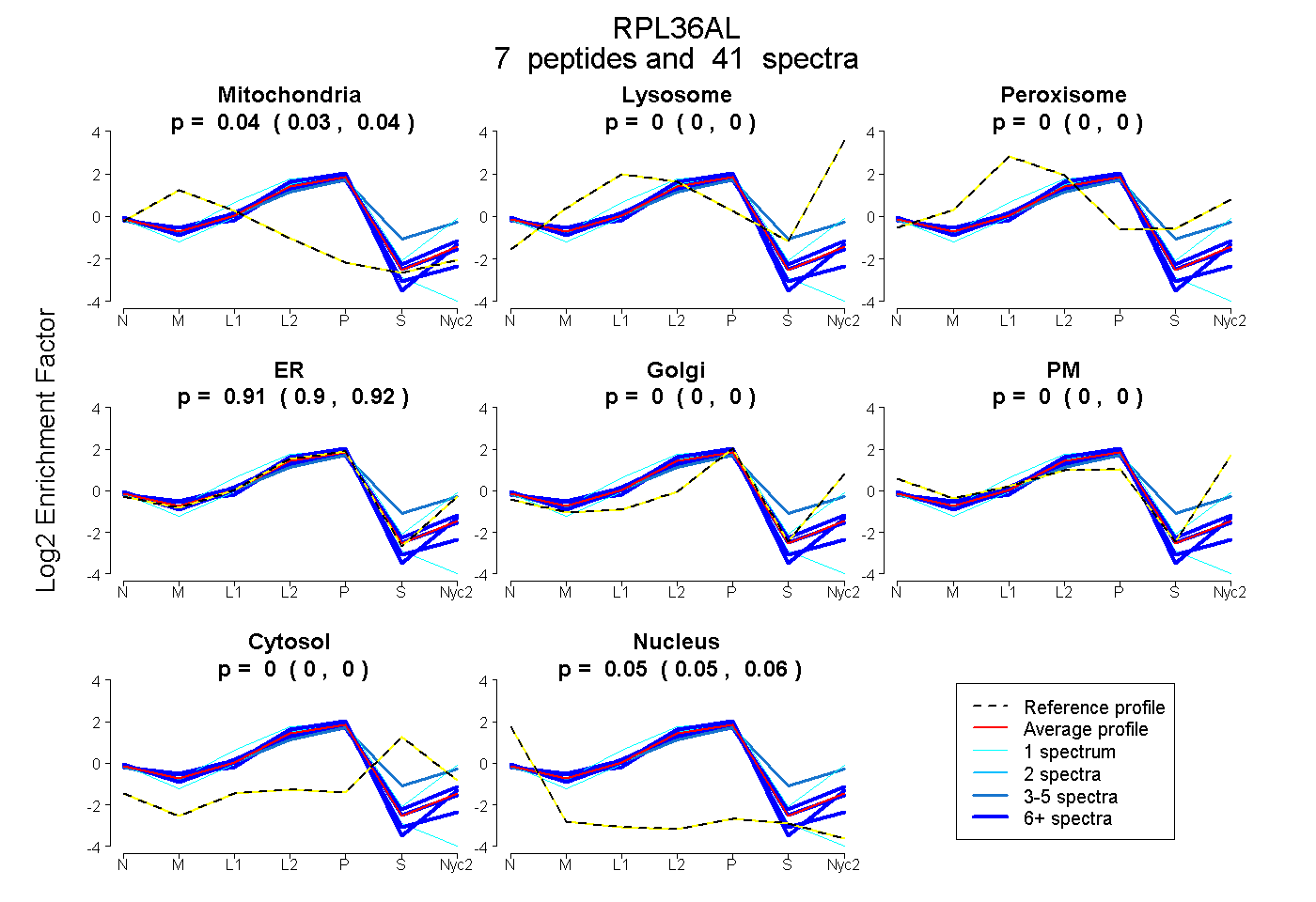
0.031 | 0.041
0.000 | 0.000
0.000 | 0.000
0.905 | 0.917
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.047 | 0.056
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
41 spectra |
 |
0.037 0.031 | 0.041 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.912 0.905 | 0.917 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.052 0.047 | 0.056 |
| 10 spectra, DSLYAQGK | 0.099 | 0.000 | 0.000 | 0.874 | 0.000 | 0.000 | 0.019 | 0.009 | ||
| 7 spectra, HFELGGDK | 0.062 | 0.000 | 0.000 | 0.853 | 0.000 | 0.000 | 0.000 | 0.085 | ||
| 6 spectra, LECVEPNCR | 0.040 | 0.000 | 0.000 | 0.905 | 0.000 | 0.000 | 0.000 | 0.055 | ||
| 12 spectra, VNVPK | 0.000 | 0.000 | 0.000 | 0.951 | 0.000 | 0.000 | 0.000 | 0.049 | ||
| 4 spectra, MLALK | 0.000 | 0.000 | 0.103 | 0.691 | 0.039 | 0.000 | 0.167 | 0.000 | ||
| 1 spectrum, QSGYGGQTKPIFR | 0.000 | 0.000 | 0.000 | 0.875 | 0.048 | 0.022 | 0.055 | 0.000 | ||
| 1 spectrum, GQVIQF | 0.104 | 0.000 | 0.000 | 0.804 | 0.000 | 0.000 | 0.000 | 0.092 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
11 spectra |
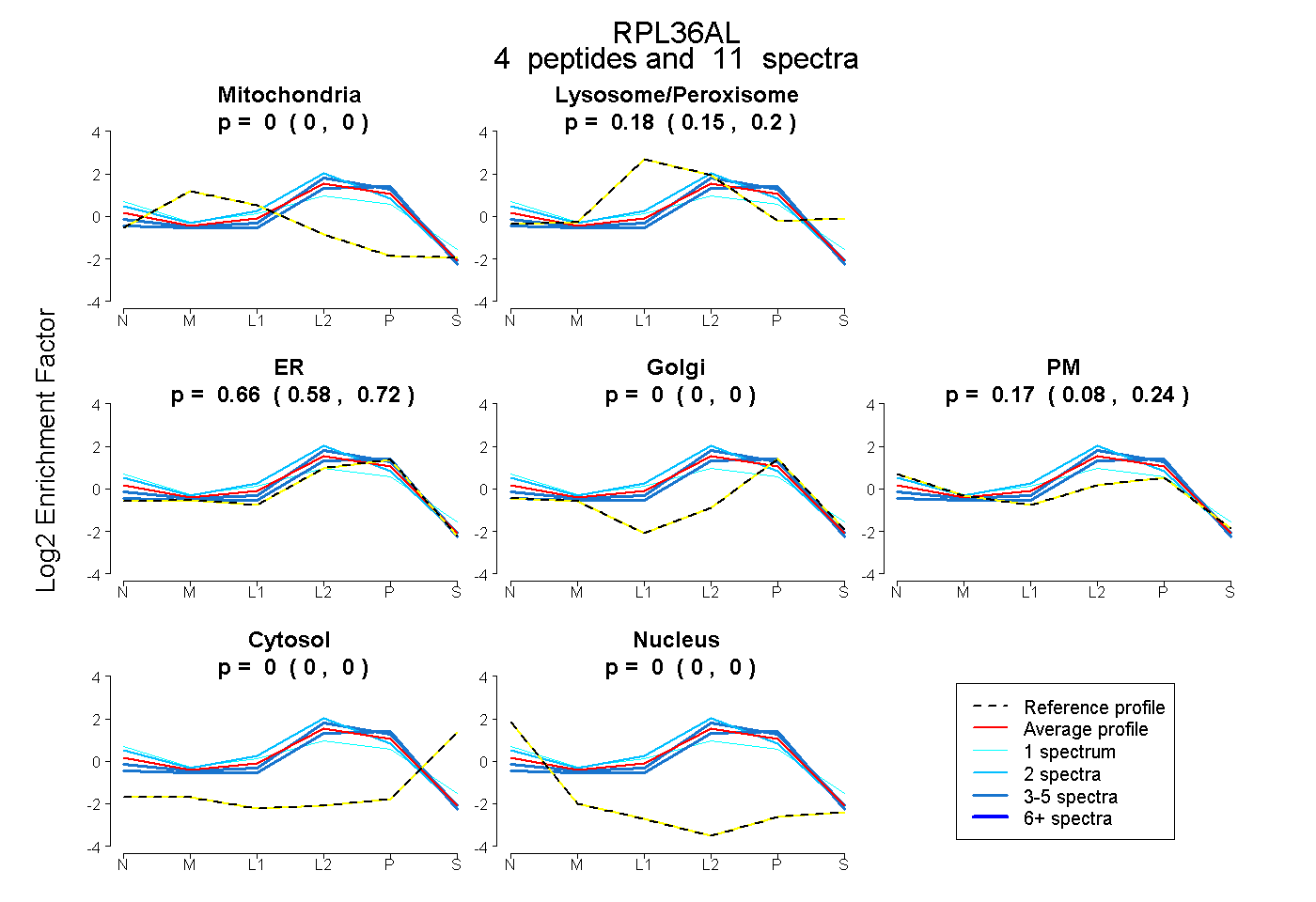 |
0.000 0.000 | 0.000 |
0.175 0.149 | 0.198 |
0.655 0.577 | 0.719 |
0.000 0.000 | 0.000 |
0.169 0.085 | 0.238 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
100 spectra |
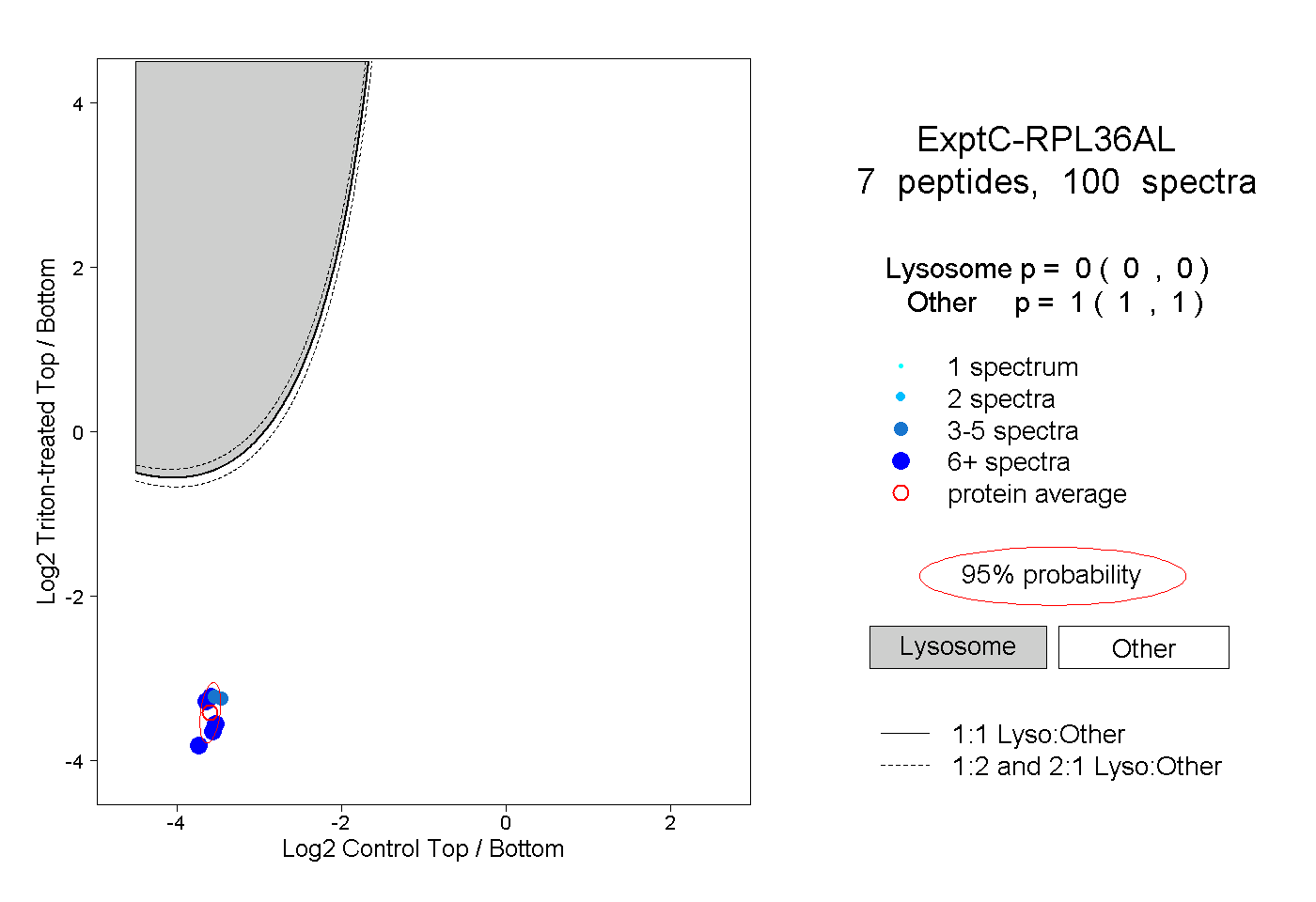 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
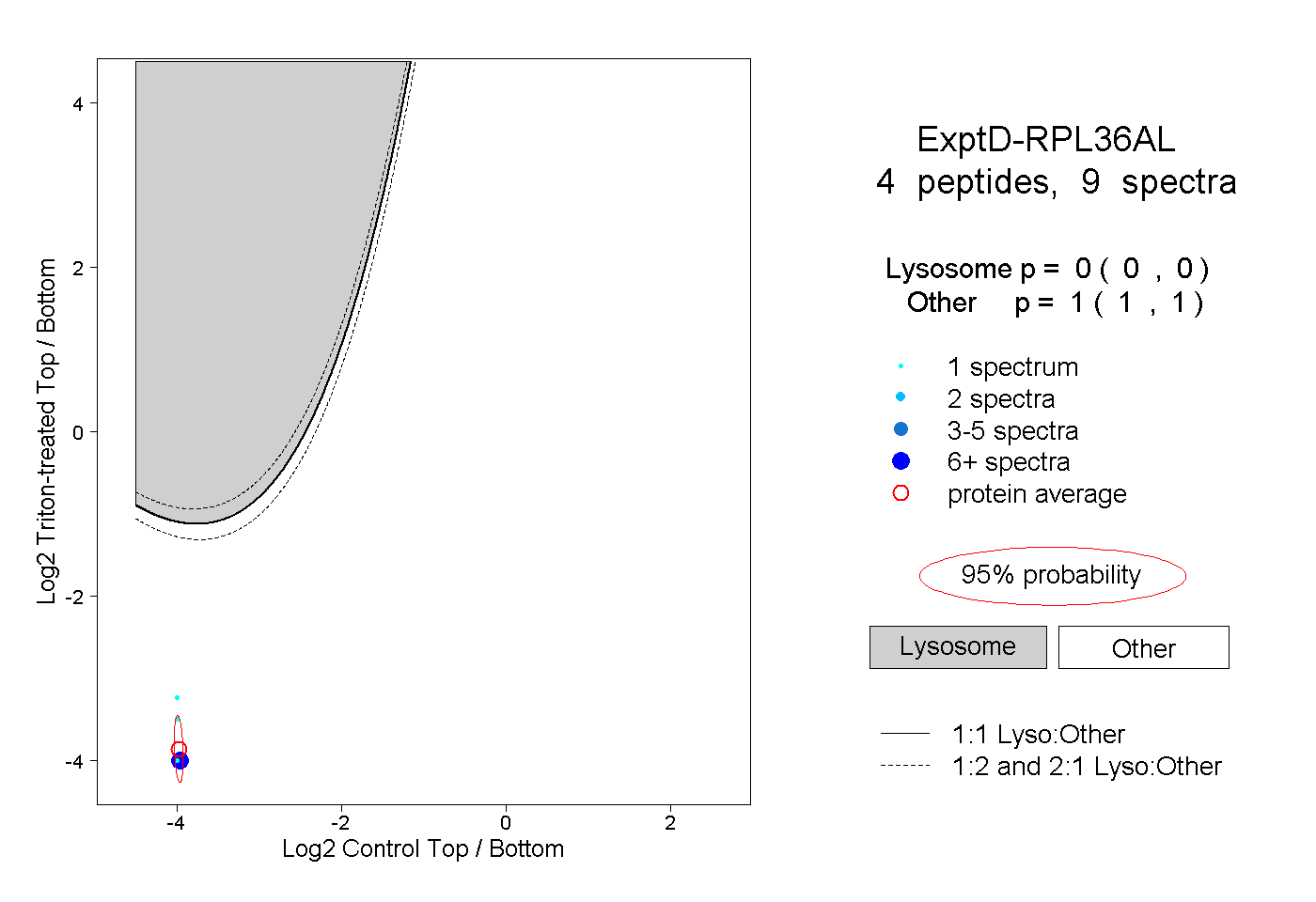 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |