peptides
spectra
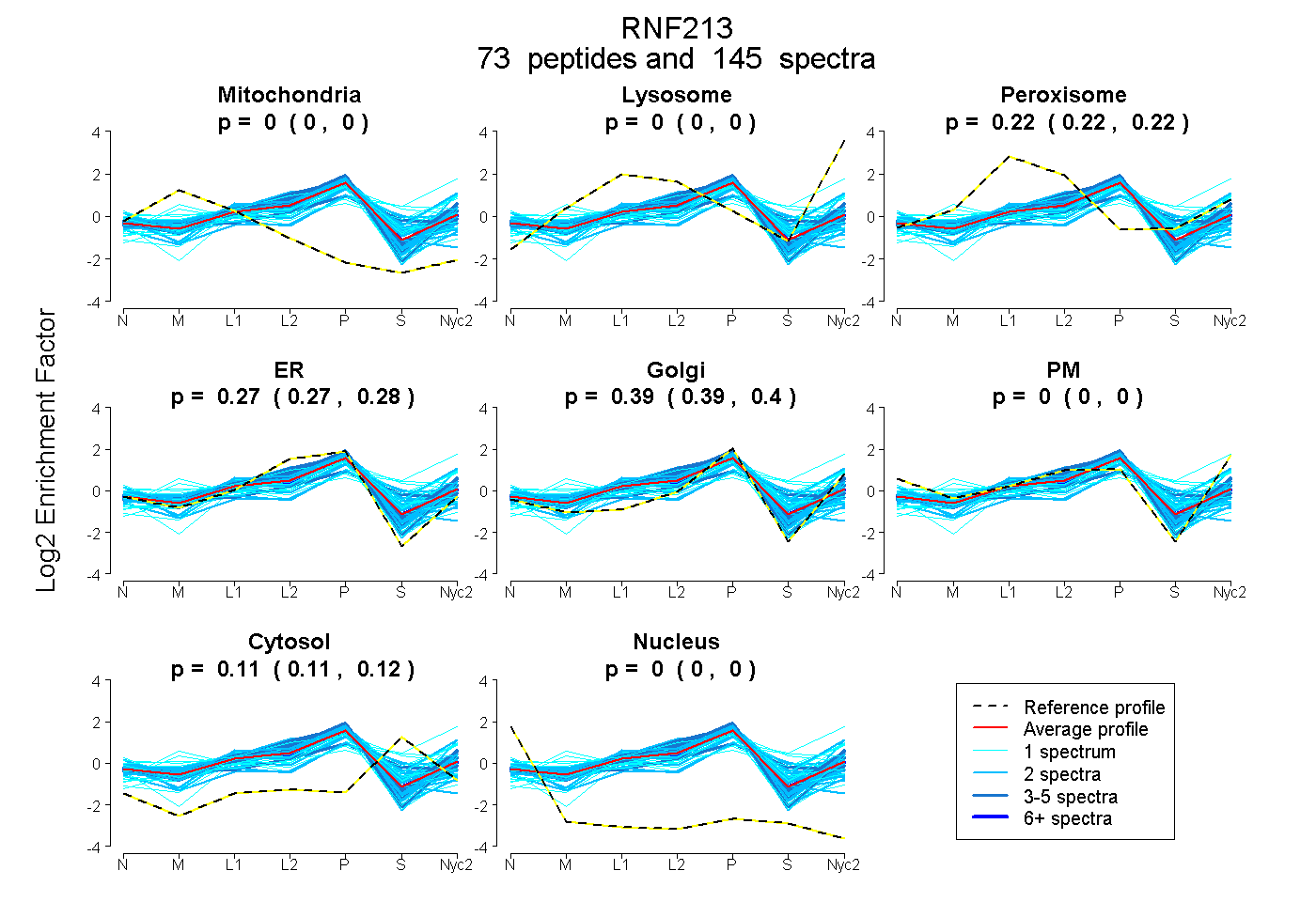
0.000 | 0.000
0.000 | 0.000
0.216 | 0.219
0.269 | 0.279
0.389 | 0.398
0.000 | 0.000
0.112 | 0.115
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
145 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.218 0.216 | 0.219 |
0.275 0.269 | 0.279 |
0.394 0.389 | 0.398 |
0.000 0.000 | 0.000 |
0.114 0.112 | 0.115 |
0.000 0.000 | 0.000 |
| 1 spectrum, LIVIEEK | 0.000 | 0.312 | 0.035 | 0.182 | 0.287 | 0.000 | 0.185 | 0.000 | ||
| 2 spectra, LVDSVTVDQR | 0.000 | 0.000 | 0.220 | 0.229 | 0.466 | 0.000 | 0.085 | 0.000 | ||
| 2 spectra, SDLDLDAK | 0.057 | 0.000 | 0.192 | 0.423 | 0.283 | 0.000 | 0.044 | 0.000 | ||
| 1 spectrum, LGGSPVERPLPK | 0.174 | 0.000 | 0.126 | 0.269 | 0.407 | 0.000 | 0.024 | 0.000 | ||
| 2 spectra, EVLCDR | 0.000 | 0.000 | 0.081 | 0.231 | 0.222 | 0.018 | 0.430 | 0.018 | ||
| 4 spectra, LSGSSLGSFAANR | 0.000 | 0.010 | 0.234 | 0.229 | 0.489 | 0.038 | 0.000 | 0.000 | ||
| 3 spectra, LHVLLNK | 0.000 | 0.000 | 0.242 | 0.368 | 0.368 | 0.000 | 0.022 | 0.000 | ||
| 2 spectra, EEVSTVELIK | 0.000 | 0.000 | 0.261 | 0.000 | 0.457 | 0.000 | 0.283 | 0.000 | ||
| 2 spectra, DIAHAVLR | 0.000 | 0.000 | 0.178 | 0.259 | 0.340 | 0.000 | 0.224 | 0.000 | ||
| 1 spectrum, HSATIDGVAEEDLAPFSLR | 0.000 | 0.000 | 0.245 | 0.000 | 0.088 | 0.418 | 0.248 | 0.000 | ||
| 1 spectrum, VACFHDAVQGYASLLYK | 0.000 | 0.156 | 0.117 | 0.000 | 0.536 | 0.004 | 0.187 | 0.000 | ||
| 2 spectra, SPGLLQQAK | 0.000 | 0.105 | 0.254 | 0.000 | 0.509 | 0.000 | 0.131 | 0.000 | ||
| 3 spectra, QFPVPLINR | 0.000 | 0.000 | 0.289 | 0.089 | 0.614 | 0.000 | 0.009 | 0.000 | ||
| 1 spectrum, GQSPVVFILTR | 0.050 | 0.000 | 0.109 | 0.508 | 0.206 | 0.000 | 0.126 | 0.000 | ||
| 2 spectra, FLPEILALQR | 0.000 | 0.000 | 0.261 | 0.246 | 0.384 | 0.000 | 0.109 | 0.000 | ||
| 1 spectrum, QFYSVVR | 0.000 | 0.092 | 0.256 | 0.000 | 0.181 | 0.215 | 0.256 | 0.000 | ||
| 5 spectra, VGAEETADR | 0.000 | 0.000 | 0.159 | 0.398 | 0.312 | 0.000 | 0.131 | 0.000 | ||
| 3 spectra, QGHPYQWVFPR | 0.000 | 0.000 | 0.311 | 0.173 | 0.497 | 0.000 | 0.019 | 0.000 | ||
| 2 spectra, FLNIPLALNNTR | 0.026 | 0.058 | 0.072 | 0.539 | 0.282 | 0.024 | 0.000 | 0.000 | ||
| 4 spectra, SQALQLMQNR | 0.000 | 0.000 | 0.163 | 0.431 | 0.406 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, SLYVNTLHK | 0.236 | 0.000 | 0.028 | 0.361 | 0.375 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, GLDSADSR | 0.000 | 0.000 | 0.223 | 0.299 | 0.315 | 0.000 | 0.163 | 0.000 | ||
| 1 spectrum, LSLPDVVDHLYYPCYEK | 0.000 | 0.174 | 0.019 | 0.391 | 0.000 | 0.000 | 0.417 | 0.000 | ||
| 1 spectrum, VWLQLVK | 0.075 | 0.000 | 0.125 | 0.400 | 0.125 | 0.275 | 0.000 | 0.000 | ||
| 4 spectra, TTFQEALNTTR | 0.000 | 0.000 | 0.155 | 0.418 | 0.308 | 0.000 | 0.119 | 0.000 | ||
| 2 spectra, QEENQVR | 0.000 | 0.000 | 0.195 | 0.348 | 0.456 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, MVNAFLPTMPEDLLVHAK | 0.000 | 0.000 | 0.133 | 0.649 | 0.090 | 0.000 | 0.127 | 0.000 | ||
| 1 spectrum, LYIQQIVQR | 0.000 | 0.000 | 0.206 | 0.199 | 0.465 | 0.000 | 0.129 | 0.000 | ||
| 1 spectrum, LGSIPLR | 0.000 | 0.000 | 0.213 | 0.195 | 0.337 | 0.000 | 0.255 | 0.000 | ||
| 1 spectrum, QVGFVGISNWALDPAK | 0.000 | 0.000 | 0.162 | 0.340 | 0.307 | 0.000 | 0.191 | 0.000 | ||
| 2 spectra, LSQEYYYK | 0.000 | 0.000 | 0.255 | 0.213 | 0.497 | 0.000 | 0.034 | 0.000 | ||
| 1 spectrum, LNQISPQFIK | 0.000 | 0.000 | 0.254 | 0.236 | 0.479 | 0.000 | 0.031 | 0.000 | ||
| 2 spectra, CLAHLAR | 0.000 | 0.000 | 0.265 | 0.447 | 0.202 | 0.020 | 0.067 | 0.000 | ||
| 1 spectrum, VTCRPPK | 0.020 | 0.000 | 0.103 | 0.544 | 0.156 | 0.000 | 0.177 | 0.000 | ||
| 2 spectra, NQQAAALEATK | 0.102 | 0.000 | 0.132 | 0.107 | 0.363 | 0.000 | 0.296 | 0.000 | ||
| 9 spectra, LMLMSGR | 0.000 | 0.000 | 0.216 | 0.277 | 0.394 | 0.000 | 0.114 | 0.000 | ||
| 2 spectra, EFFGLR | 0.000 | 0.000 | 0.329 | 0.000 | 0.586 | 0.000 | 0.085 | 0.000 | ||
| 1 spectrum, QFQNVSEVEFSSIR | 0.000 | 0.000 | 0.221 | 0.284 | 0.365 | 0.000 | 0.130 | 0.000 | ||
| 2 spectra, VTVCFHAIVSR | 0.050 | 0.000 | 0.011 | 0.727 | 0.000 | 0.000 | 0.212 | 0.000 | ||
| 1 spectrum, GIPTLVYR | 0.255 | 0.052 | 0.060 | 0.183 | 0.449 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ADQFIAR | 0.000 | 0.000 | 0.233 | 0.240 | 0.483 | 0.000 | 0.044 | 0.000 | ||
| 1 spectrum, FWEGLTNVR | 0.019 | 0.000 | 0.211 | 0.368 | 0.402 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, ELLQDISELR | 0.000 | 0.000 | 0.175 | 0.389 | 0.402 | 0.000 | 0.034 | 0.000 | ||
| 1 spectrum, DFLLLTMK | 0.000 | 0.000 | 0.191 | 0.452 | 0.152 | 0.000 | 0.205 | 0.000 | ||
| 3 spectra, LNLWEHVK | 0.000 | 0.000 | 0.174 | 0.398 | 0.311 | 0.000 | 0.118 | 0.000 | ||
| 2 spectra, SCVQGAVGMLR | 0.000 | 0.000 | 0.079 | 0.739 | 0.000 | 0.000 | 0.183 | 0.000 | ||
| 2 spectra, MGSGTPYVGFHGGLWR | 0.000 | 0.000 | 0.192 | 0.612 | 0.056 | 0.000 | 0.141 | 0.000 | ||
| 2 spectra, CLEEDSNLK | 0.000 | 0.000 | 0.282 | 0.054 | 0.531 | 0.000 | 0.134 | 0.000 | ||
| 2 spectra, TYSPGLR | 0.000 | 0.000 | 0.207 | 0.195 | 0.466 | 0.000 | 0.132 | 0.000 | ||
| 2 spectra, GMEFVQSFSR | 0.000 | 0.054 | 0.199 | 0.000 | 0.579 | 0.167 | 0.000 | 0.000 | ||
| 2 spectra, WAHEFADVK | 0.000 | 0.000 | 0.279 | 0.212 | 0.510 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, QIQSAATVFR | 0.062 | 0.000 | 0.031 | 0.691 | 0.161 | 0.000 | 0.056 | 0.000 | ||
| 2 spectra, ELFDGLK | 0.000 | 0.000 | 0.153 | 0.454 | 0.316 | 0.000 | 0.077 | 0.000 | ||
| 1 spectrum, GSIEAETMK | 0.000 | 0.000 | 0.346 | 0.028 | 0.553 | 0.000 | 0.073 | 0.000 | ||
| 2 spectra, TLDVGNALSTCR | 0.001 | 0.000 | 0.078 | 0.595 | 0.141 | 0.000 | 0.184 | 0.000 | ||
| 5 spectra, HFGTLLLR | 0.000 | 0.000 | 0.217 | 0.365 | 0.399 | 0.000 | 0.018 | 0.000 | ||
| 1 spectrum, DTLVSYMETK | 0.000 | 0.000 | 0.244 | 0.316 | 0.426 | 0.000 | 0.015 | 0.000 | ||
| 1 spectrum, ELFQEVDVK | 0.000 | 0.000 | 0.191 | 0.323 | 0.318 | 0.000 | 0.167 | 0.000 | ||
| 1 spectrum, VSPDTVLHLLLPDDHGYQEAFR | 0.000 | 0.000 | 0.178 | 0.405 | 0.195 | 0.000 | 0.222 | 0.000 | ||
| 1 spectrum, FILLDCATPDAVVR | 0.097 | 0.000 | 0.007 | 0.785 | 0.000 | 0.000 | 0.112 | 0.000 | ||
| 2 spectra, SGESLPADCPVR | 0.009 | 0.000 | 0.234 | 0.352 | 0.406 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, YSAINEINK | 0.000 | 0.026 | 0.260 | 0.000 | 0.582 | 0.043 | 0.089 | 0.000 | ||
| 1 spectrum, TELPDK | 0.000 | 0.078 | 0.209 | 0.000 | 0.315 | 0.000 | 0.398 | 0.000 | ||
| 4 spectra, QMEDFLHEWK | 0.000 | 0.000 | 0.273 | 0.149 | 0.537 | 0.000 | 0.042 | 0.000 | ||
| 2 spectra, DACNAVPFSWR | 0.017 | 0.000 | 0.165 | 0.559 | 0.175 | 0.000 | 0.080 | 0.003 | ||
| 2 spectra, YLLVLTR | 0.000 | 0.000 | 0.216 | 0.260 | 0.473 | 0.000 | 0.051 | 0.000 | ||
| 1 spectrum, EEVVLLSSTDSGK | 0.000 | 0.302 | 0.000 | 0.000 | 0.288 | 0.000 | 0.410 | 0.000 | ||
| 2 spectra, LMVTAESVFQK | 0.000 | 0.000 | 0.089 | 0.483 | 0.131 | 0.000 | 0.267 | 0.030 | ||
| 2 spectra, LADFLR | 0.065 | 0.000 | 0.000 | 0.773 | 0.081 | 0.000 | 0.081 | 0.000 | ||
| 2 spectra, LLTSHDCDVLESELR | 0.000 | 0.000 | 0.170 | 0.473 | 0.252 | 0.000 | 0.106 | 0.000 | ||
| 2 spectra, EEGHFLR | 0.000 | 0.000 | 0.210 | 0.153 | 0.471 | 0.000 | 0.167 | 0.000 | ||
| 3 spectra, MALLHVDEYLFR | 0.022 | 0.000 | 0.198 | 0.205 | 0.269 | 0.000 | 0.306 | 0.000 | ||
| 2 spectra, VPFNINFDSLPR | 0.000 | 0.000 | 0.173 | 0.388 | 0.366 | 0.000 | 0.074 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
30 spectra |
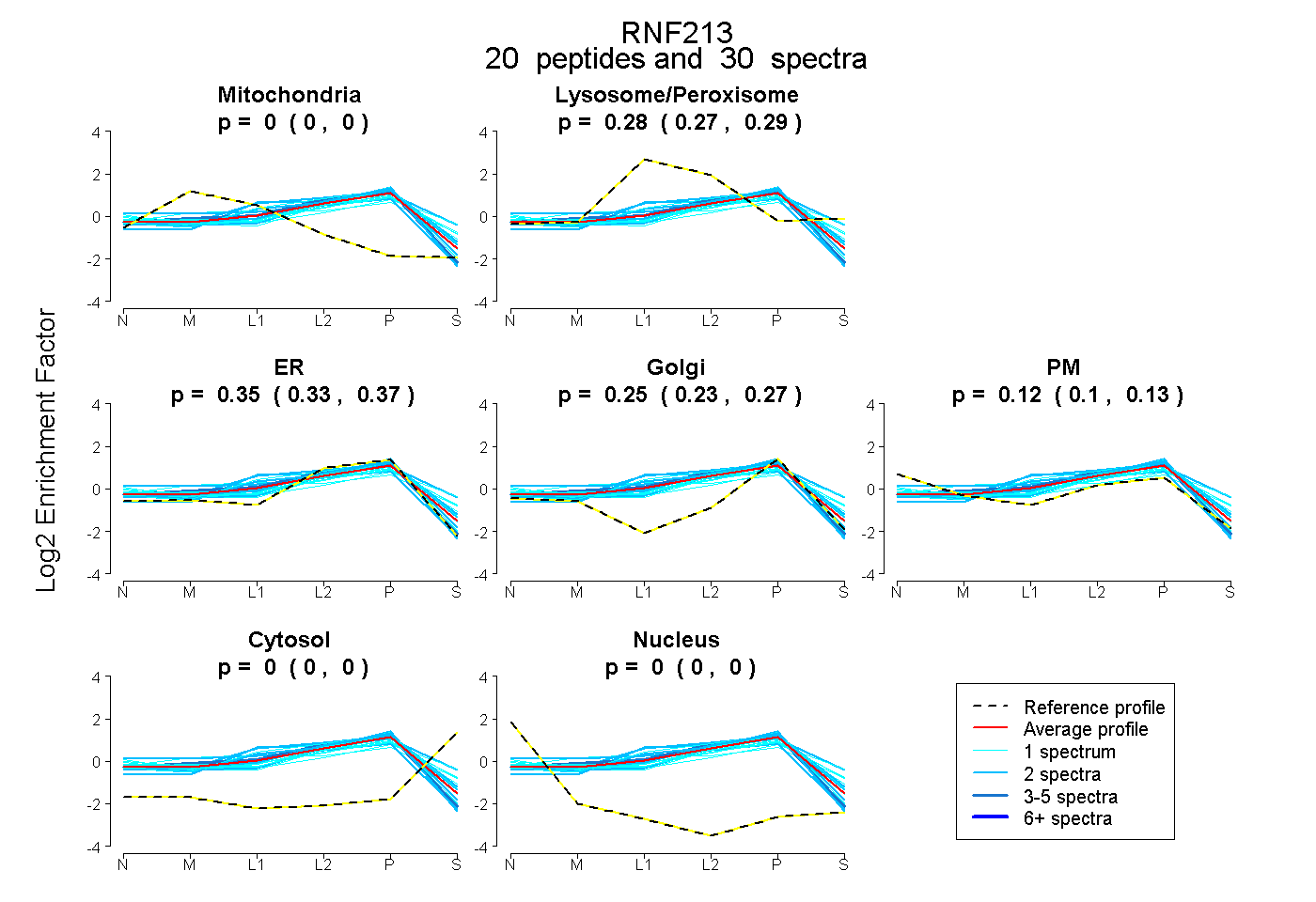 |
0.000 0.000 | 0.000 |
0.283 0.269 | 0.294 |
0.349 0.326 | 0.369 |
0.252 0.228 | 0.270 |
0.117 0.101 | 0.131 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
286 spectra |
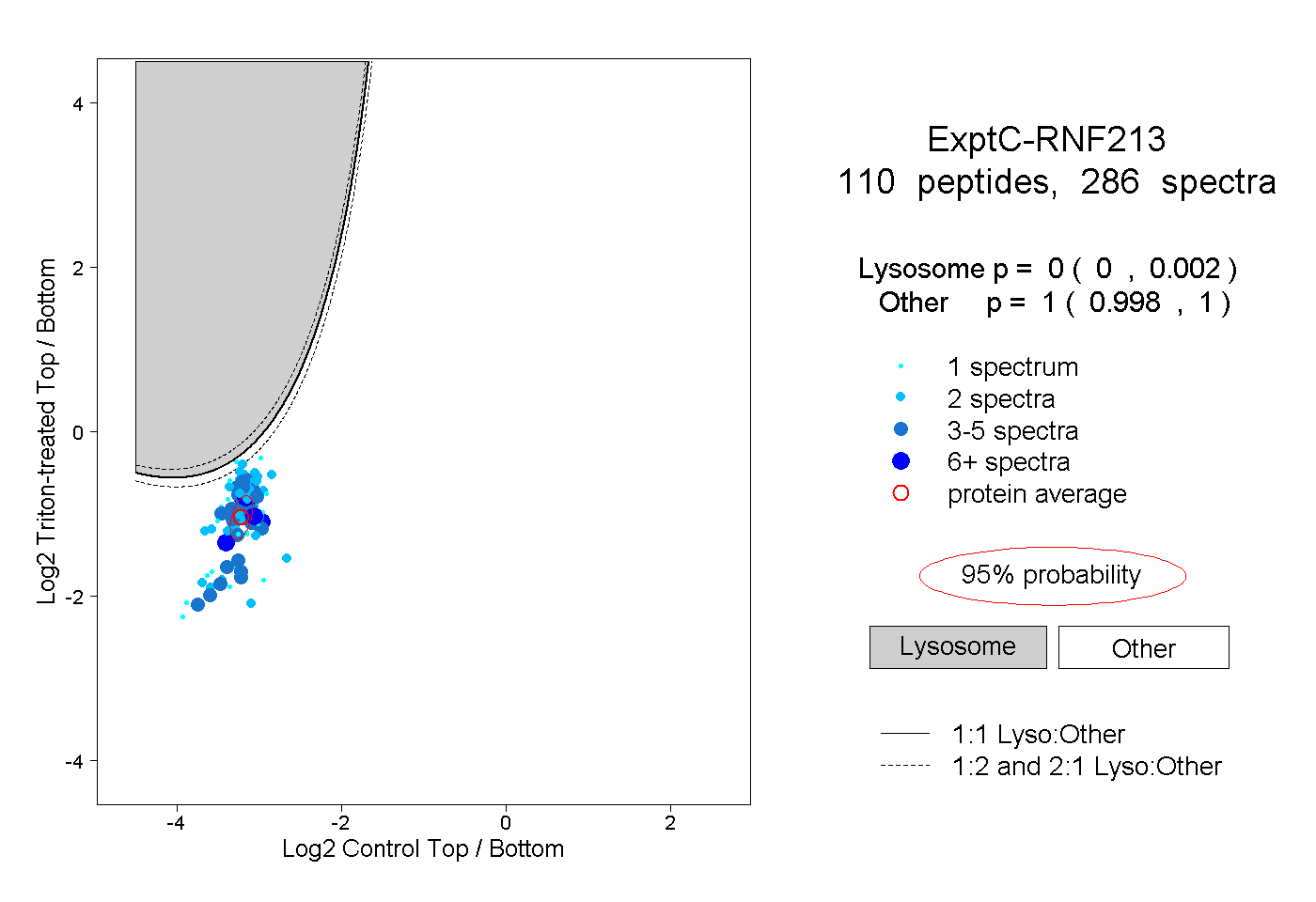 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
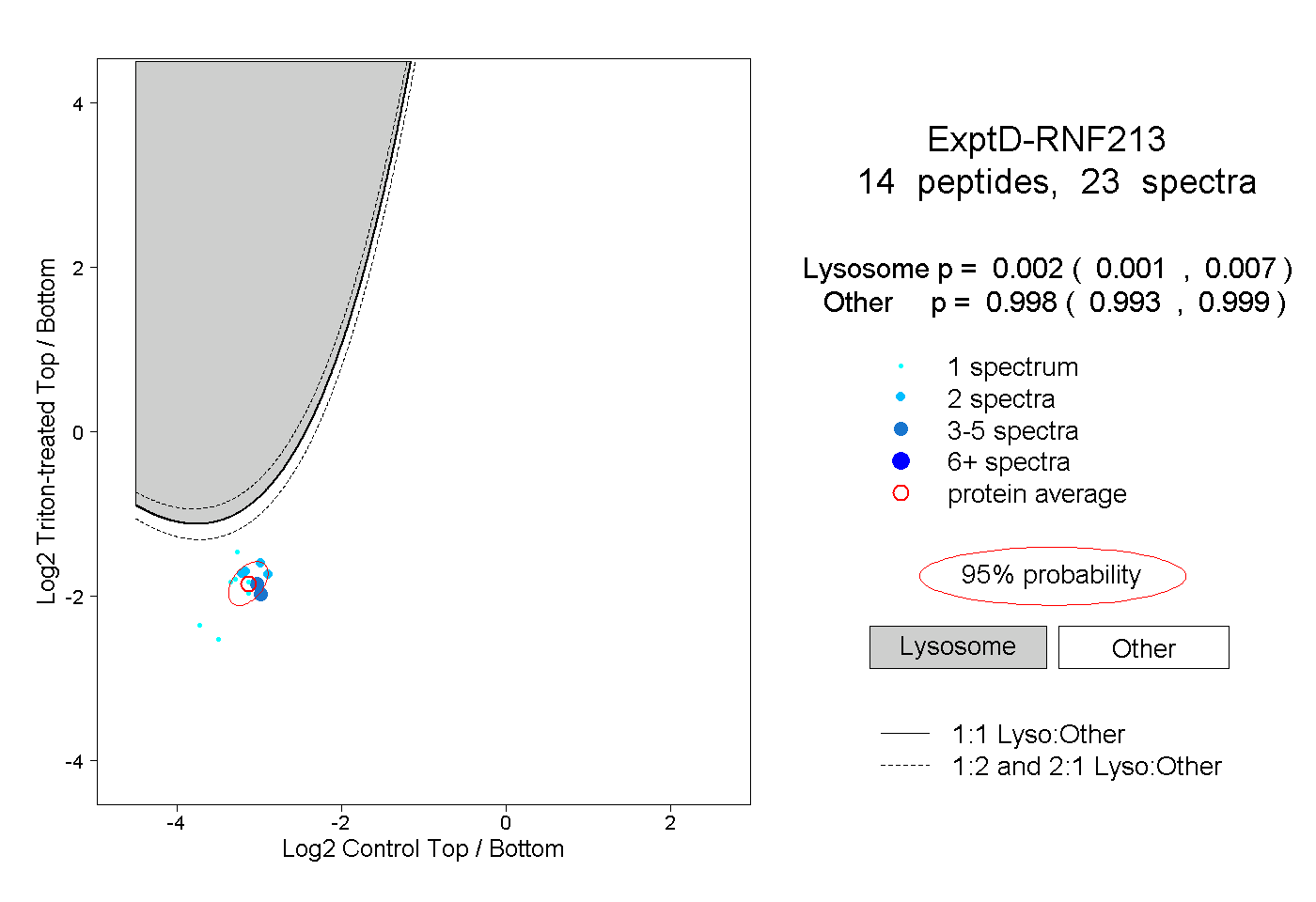 |
0.002 0.001 | 0.007 |
0.998 0.993 | 0.999 |