peptides
spectra
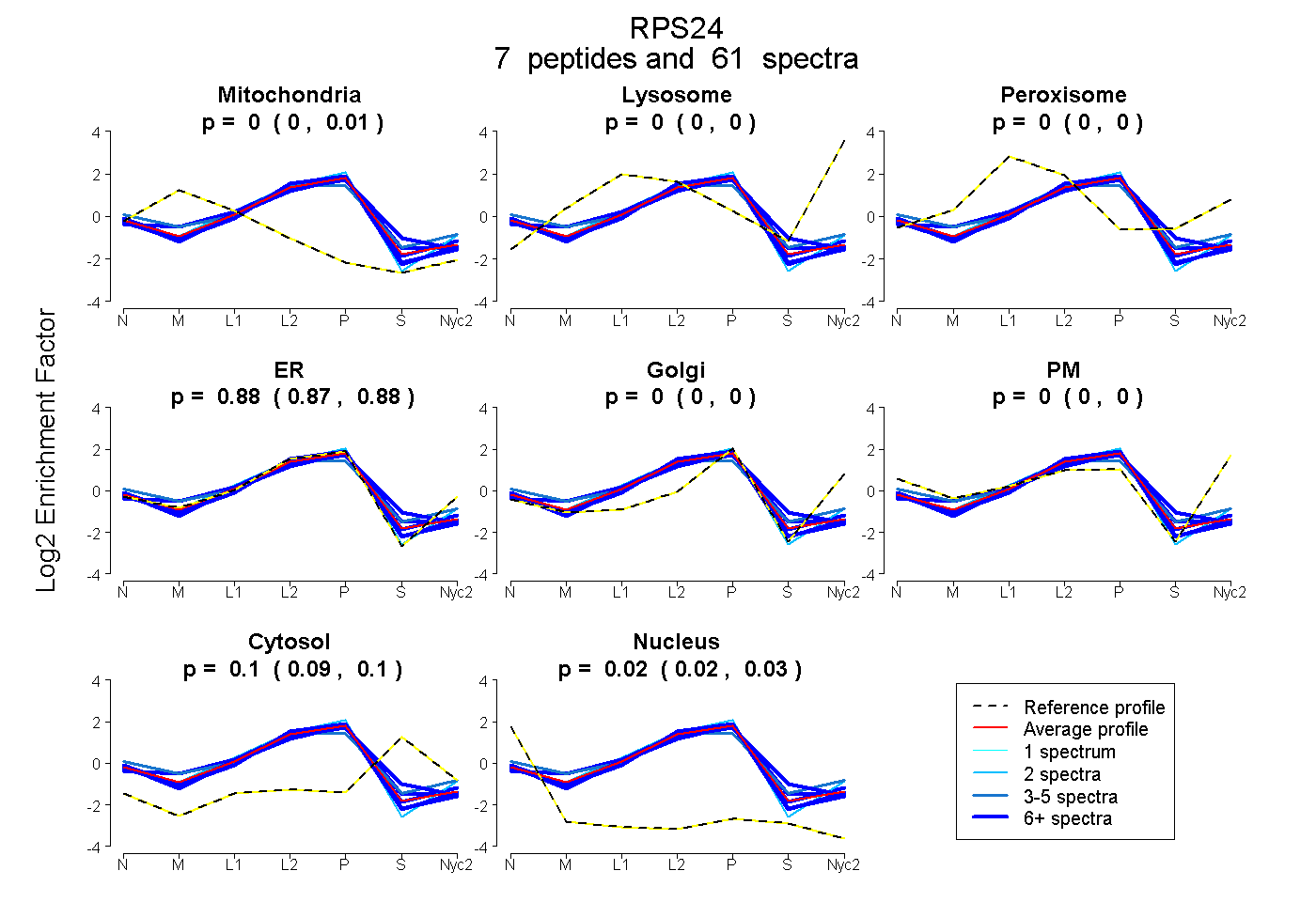
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.872 | 0.880
0.000 | 0.000
0.000 | 0.000
0.090 | 0.104
0.018 | 0.027
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
61 spectra |
 |
0.002 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.877 0.872 | 0.880 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.098 0.090 | 0.104 |
0.023 0.018 | 0.027 |
| 7 spectra, TTGFGMIYDSLDYAK | 0.000 | 0.000 | 0.017 | 0.773 | 0.000 | 0.000 | 0.211 | 0.000 | ||
| 3 spectra, THFGGGK | 0.014 | 0.000 | 0.109 | 0.769 | 0.000 | 0.000 | 0.095 | 0.013 | ||
| 13 spectra, HGLYEK | 0.000 | 0.000 | 0.000 | 0.852 | 0.000 | 0.000 | 0.135 | 0.013 | ||
| 2 spectra, MNDTVTIR | 0.000 | 0.000 | 0.000 | 0.982 | 0.000 | 0.000 | 0.000 | 0.018 | ||
| 8 spectra, TTPDVIFVFGFR | 0.000 | 0.000 | 0.000 | 0.912 | 0.000 | 0.000 | 0.018 | 0.071 | ||
| 10 spectra, QMVIDVLHPGK | 0.109 | 0.000 | 0.000 | 0.880 | 0.000 | 0.000 | 0.011 | 0.000 | ||
| 18 spectra, ANVGAGK | 0.000 | 0.000 | 0.000 | 0.861 | 0.000 | 0.000 | 0.105 | 0.035 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
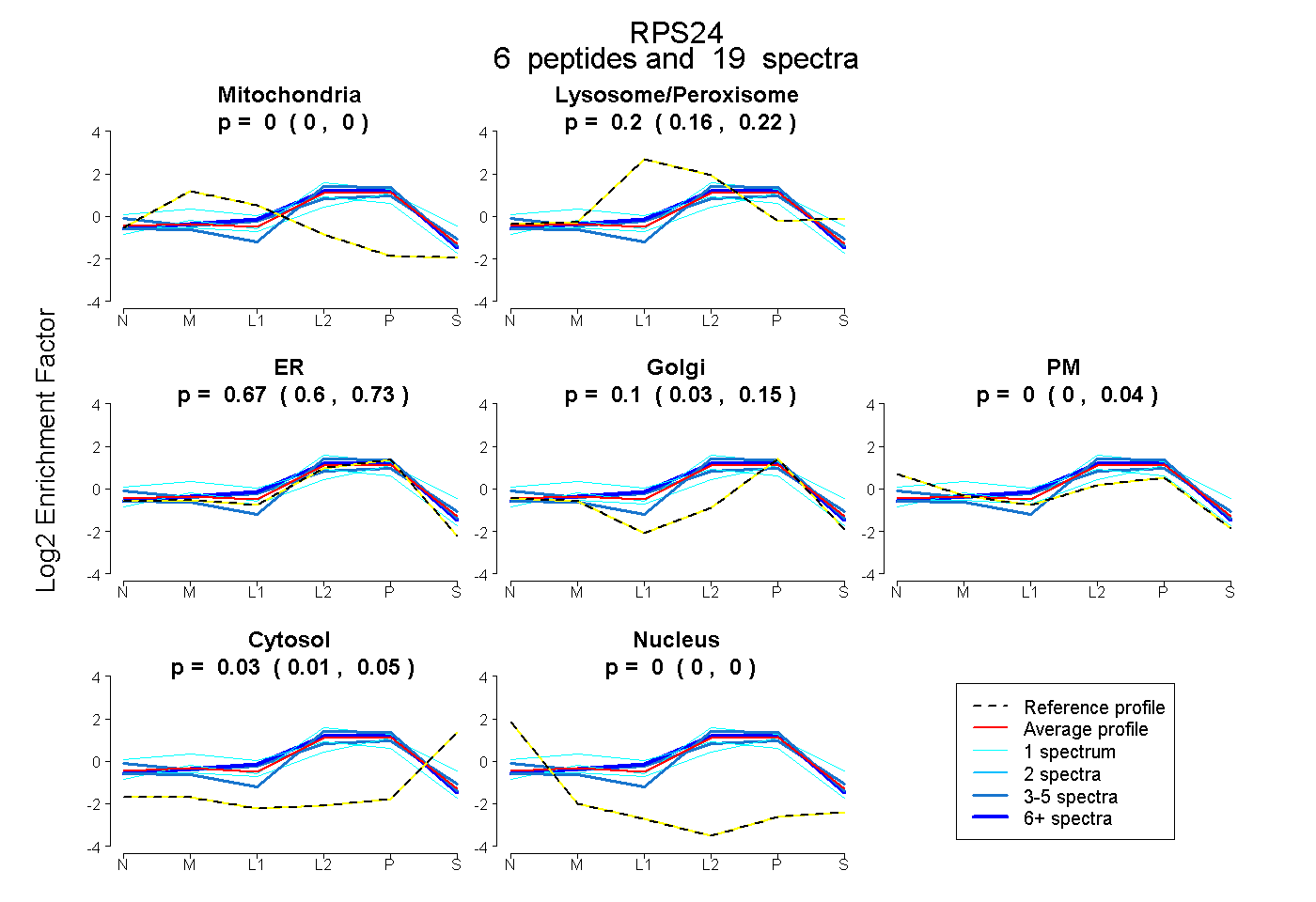 |
0.000 0.000 | 0.000 |
0.197 0.159 | 0.221 |
0.667 0.598 | 0.726 |
0.103 0.027 | 0.147 |
0.000 0.000 | 0.041 |
0.033 0.014 | 0.051 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
122 spectra |
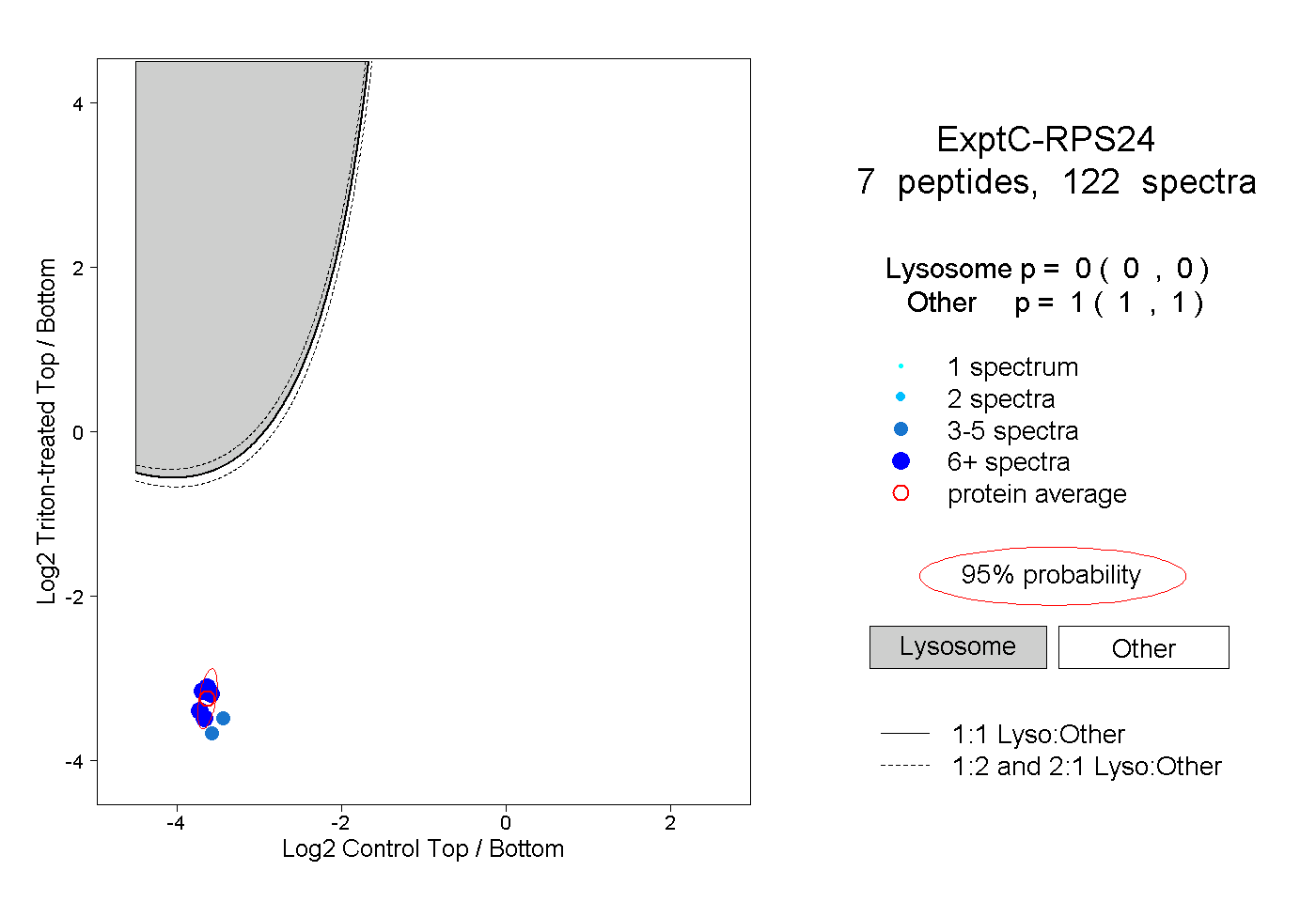 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
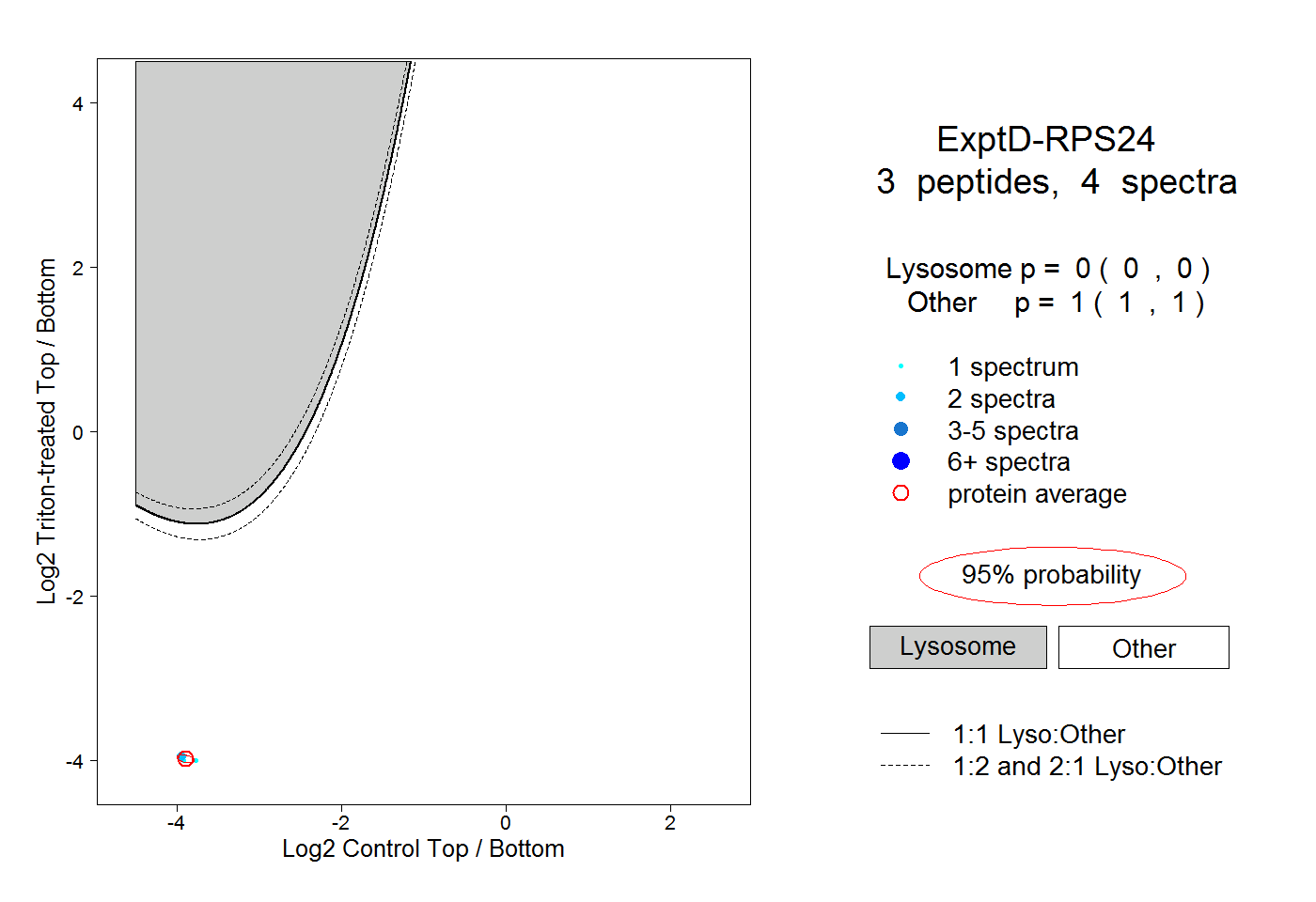 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |