peptides
spectra
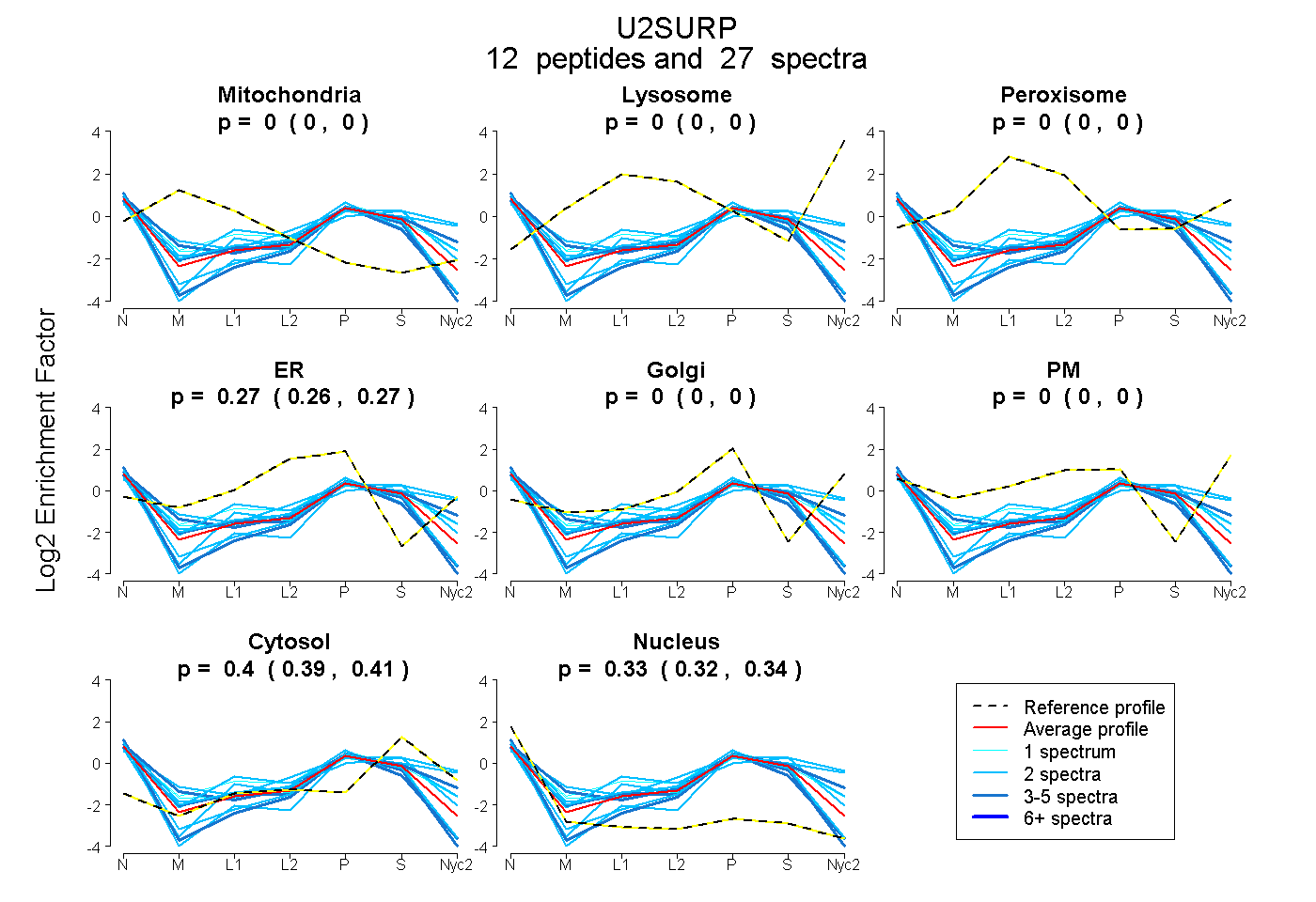
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.258 | 0.273
0.000 | 0.000
0.000 | 0.000
0.394 | 0.412
0.318 | 0.340
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.266 0.258 | 0.273 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.403 0.394 | 0.412 |
0.331 0.318 | 0.340 |
| 2 spectra, TIQGHLQSENFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.054 | 0.345 | 0.477 | 0.124 | ||
| 2 spectra, AWEDWAIYPEPFLIK | 0.000 | 0.000 | 0.000 | 0.200 | 0.000 | 0.000 | 0.550 | 0.250 | ||
| 2 spectra, NCGFVAFMNR | 0.000 | 0.000 | 0.000 | 0.341 | 0.000 | 0.000 | 0.231 | 0.428 | ||
| 2 spectra, FLFENQTPAHVYYR | 0.000 | 0.000 | 0.000 | 0.362 | 0.011 | 0.000 | 0.439 | 0.188 | ||
| 2 spectra, VVIPTER | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | 0.000 | 0.353 | 0.467 | ||
| 2 spectra, VMTCFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.094 | 0.237 | 0.542 | 0.127 | ||
| 1 spectrum, FGPLASVK | 0.000 | 0.000 | 0.000 | 0.232 | 0.000 | 0.000 | 0.353 | 0.415 | ||
| 3 spectra, VANASYYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.361 | 0.000 | 0.422 | 0.217 | ||
| 2 spectra, FEPPQSDSDGQR | 0.000 | 0.000 | 0.000 | 0.083 | 0.000 | 0.000 | 0.390 | 0.528 | ||
| 4 spectra, NLLALIHR | 0.000 | 0.000 | 0.000 | 0.332 | 0.000 | 0.000 | 0.232 | 0.436 | ||
| 4 spectra, FQDELESGK | 0.000 | 0.000 | 0.000 | 0.135 | 0.000 | 0.000 | 0.331 | 0.534 | ||
| 1 spectrum, EINNPMFR | 0.000 | 0.000 | 0.000 | 0.388 | 0.011 | 0.000 | 0.410 | 0.191 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
4 spectra |
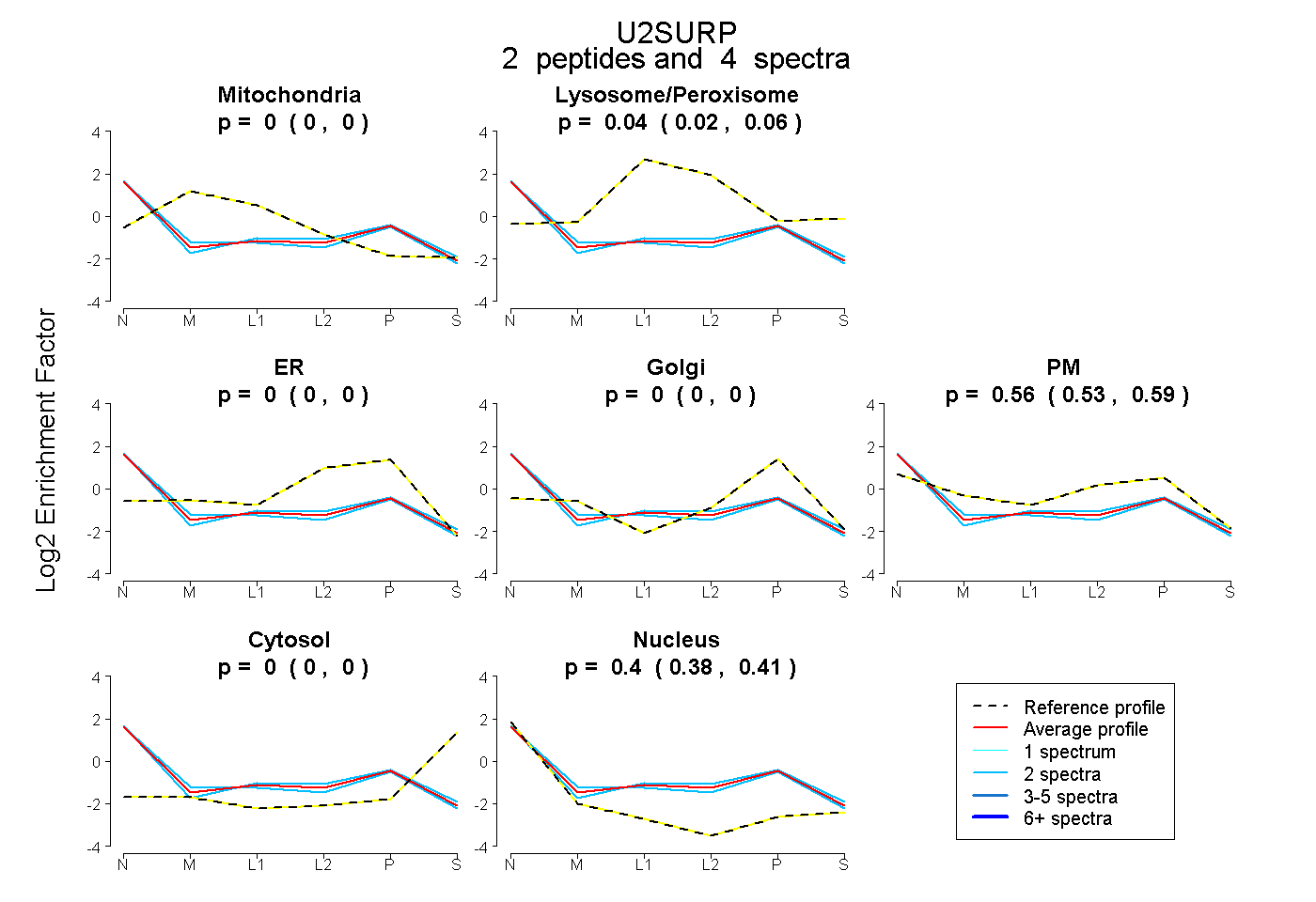 |
0.000 0.000 | 0.000 |
0.039 0.018 | 0.056 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.562 0.528 | 0.590 |
0.000 0.000 | 0.000 |
0.399 0.378 | 0.414 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
4 spectra |
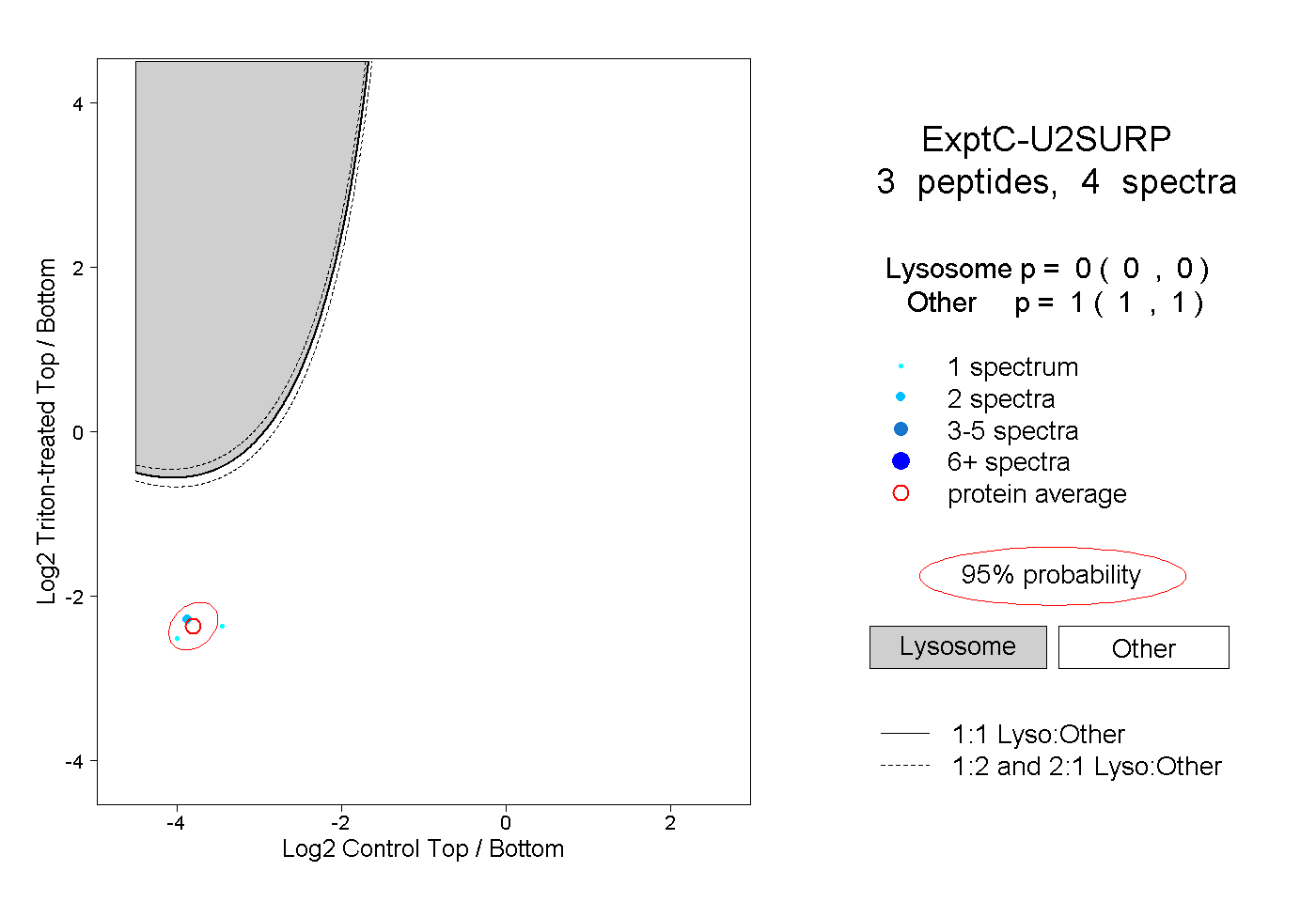 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |