peptides
spectra
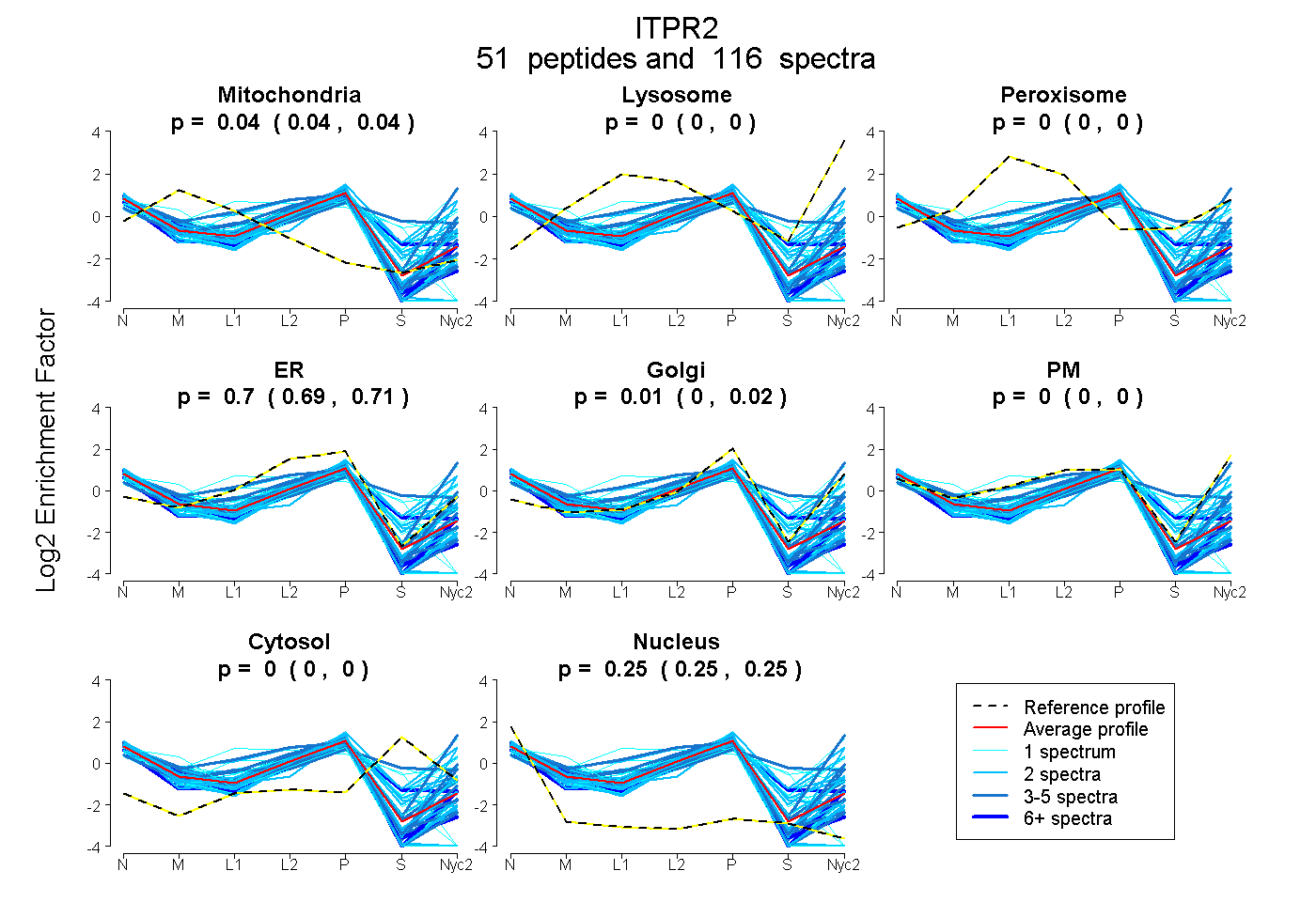
0.037 | 0.041
0.000 | 0.000
0.000 | 0.000
0.693 | 0.708
0.000 | 0.015
0.000 | 0.000
0.000 | 0.000
0.248 | 0.254
peptides
spectra
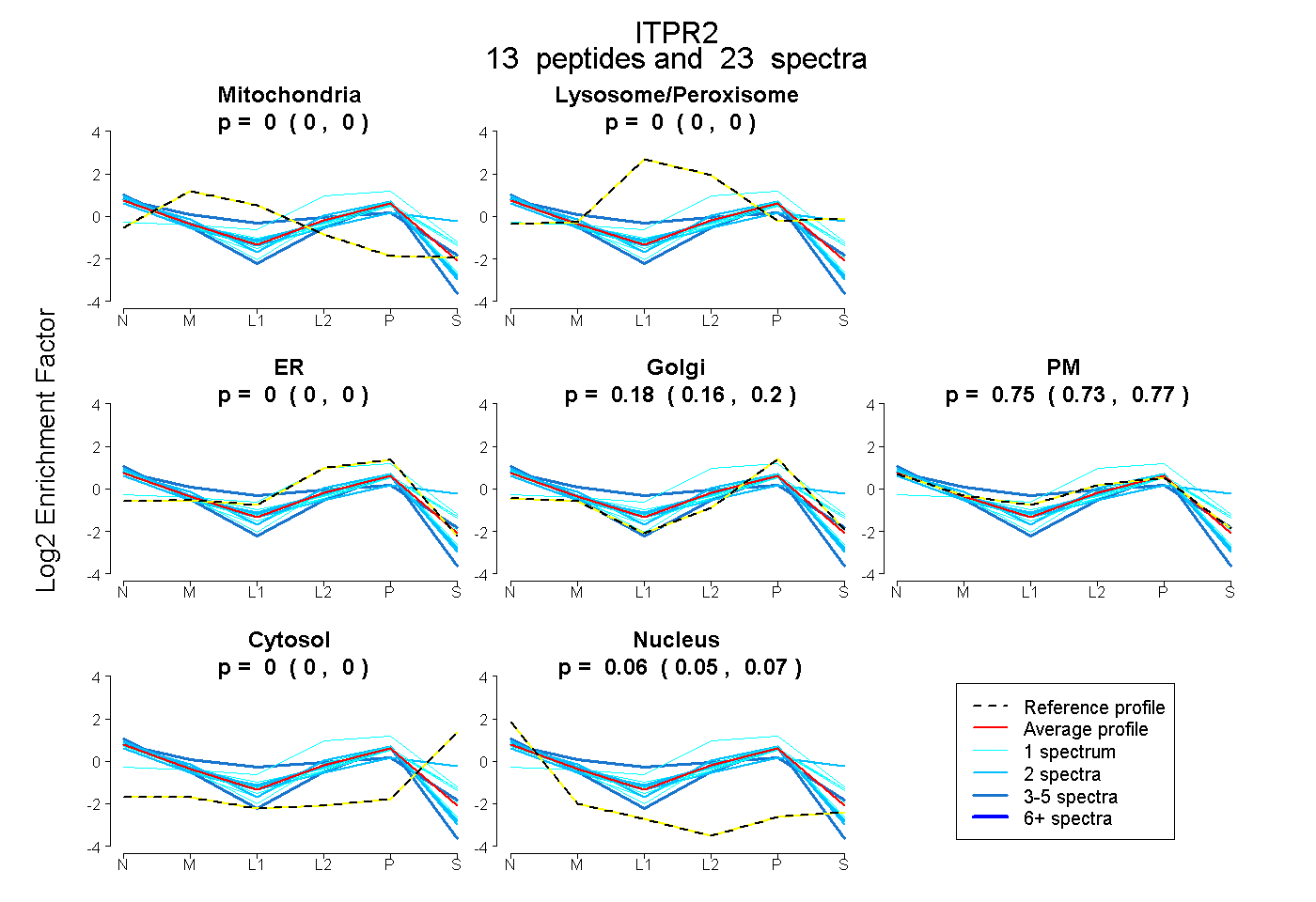
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.164 | 0.202
0.731 | 0.773
0.000 | 0.000
0.054 | 0.066
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
116 spectra |
 |
0.039 0.037 | 0.041 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.704 0.693 | 0.708 |
0.006 0.000 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.252 0.248 | 0.254 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.185 0.164 | 0.202 |
0.755 0.731 | 0.773 |
0.000 0.000 | 0.000 |
0.060 0.054 | 0.066 |
| 1 spectrum, GQLTEASSATSK | 0.000 | 0.000 | 0.000 | 0.048 | 0.841 | 0.092 | 0.020 | |||
| 2 spectra, ILFNMRPK | 0.000 | 0.000 | 0.121 | 0.210 | 0.600 | 0.000 | 0.068 | |||
| 1 spectrum, SELWVEK | 0.000 | 0.000 | 0.000 | 0.143 | 0.755 | 0.083 | 0.018 | |||
| 1 spectrum, LLLALMESR | 0.000 | 0.000 | 0.027 | 0.314 | 0.564 | 0.000 | 0.095 | |||
| 1 spectrum, LLETLR | 0.000 | 0.182 | 0.557 | 0.160 | 0.069 | 0.032 | 0.000 | |||
| 1 spectrum, ELQNFLR | 0.000 | 0.000 | 0.000 | 0.132 | 0.763 | 0.000 | 0.105 | |||
| 2 spectra, LLGEIVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.700 | 0.300 | 0.000 | |||
| 1 spectrum, YQLNLFAR | 0.000 | 0.000 | 0.000 | 0.191 | 0.680 | 0.057 | 0.072 | |||
| 2 spectra, LTFEVVHLAR | 0.000 | 0.000 | 0.091 | 0.094 | 0.713 | 0.000 | 0.102 | |||
| 1 spectrum, AEVLQAFK | 0.000 | 0.000 | 0.056 | 0.215 | 0.620 | 0.000 | 0.110 | |||
| 4 spectra, EIETFVSLLR | 0.000 | 0.000 | 0.282 | 0.275 | 0.204 | 0.000 | 0.239 | |||
| 4 spectra, FLQLLCENHNR | 0.164 | 0.033 | 0.000 | 0.000 | 0.799 | 0.000 | 0.004 | |||
| 2 spectra, HVEYLR | 0.000 | 0.000 | 0.213 | 0.035 | 0.623 | 0.000 | 0.129 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
72 spectra |
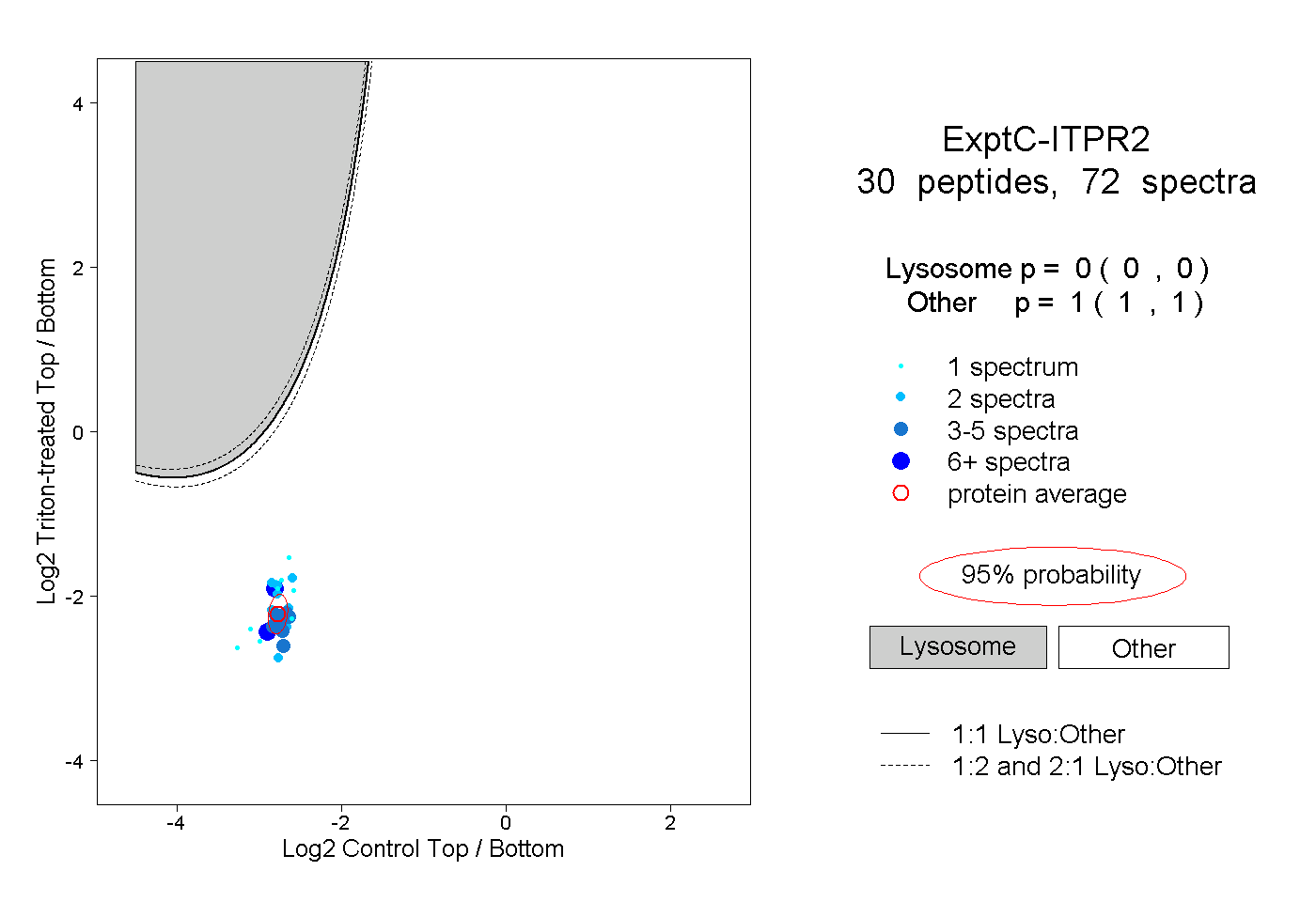 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
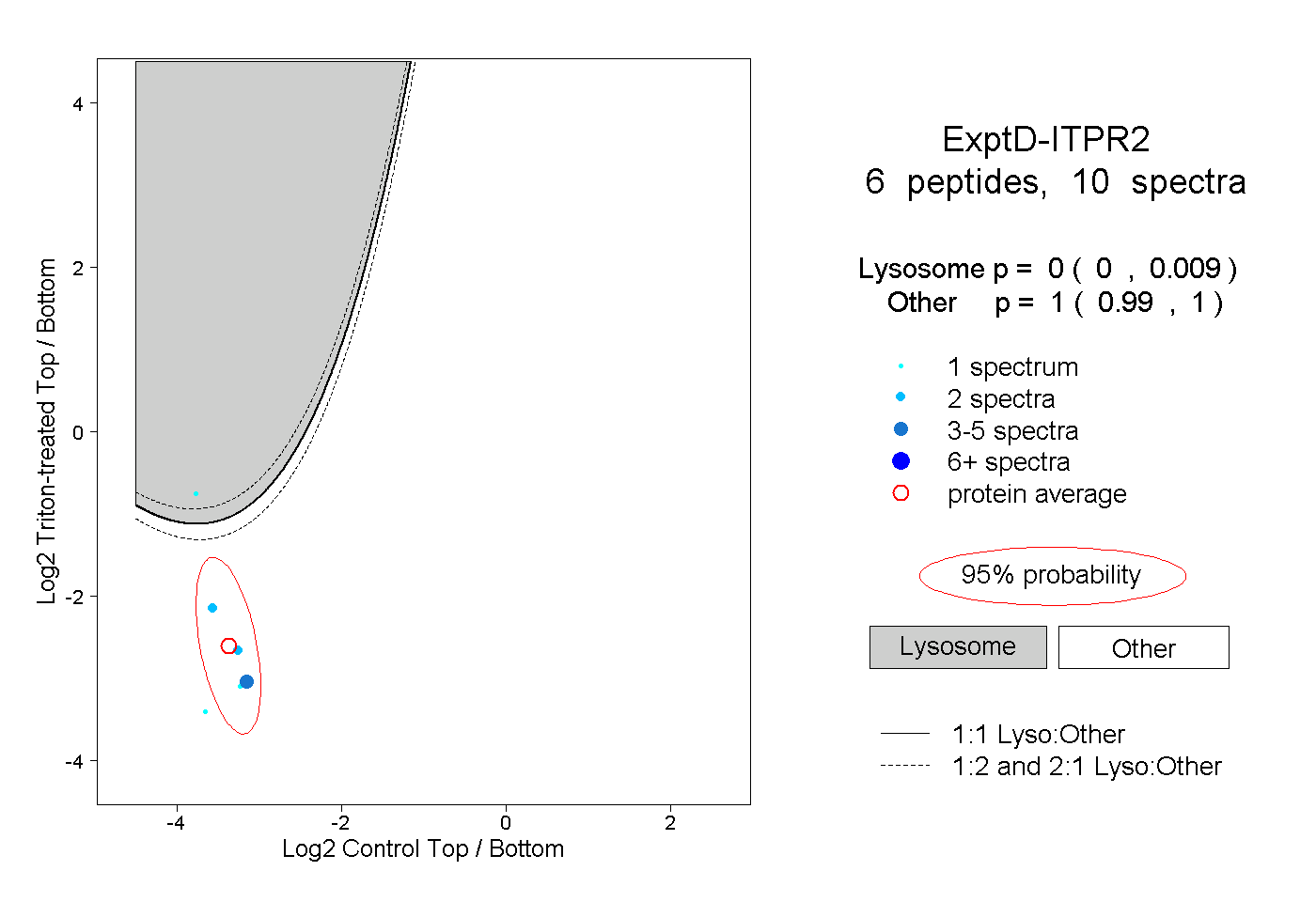 |
0.000 0.000 | 0.009 |
1.000 0.990 | 1.000 |