peptides
spectra
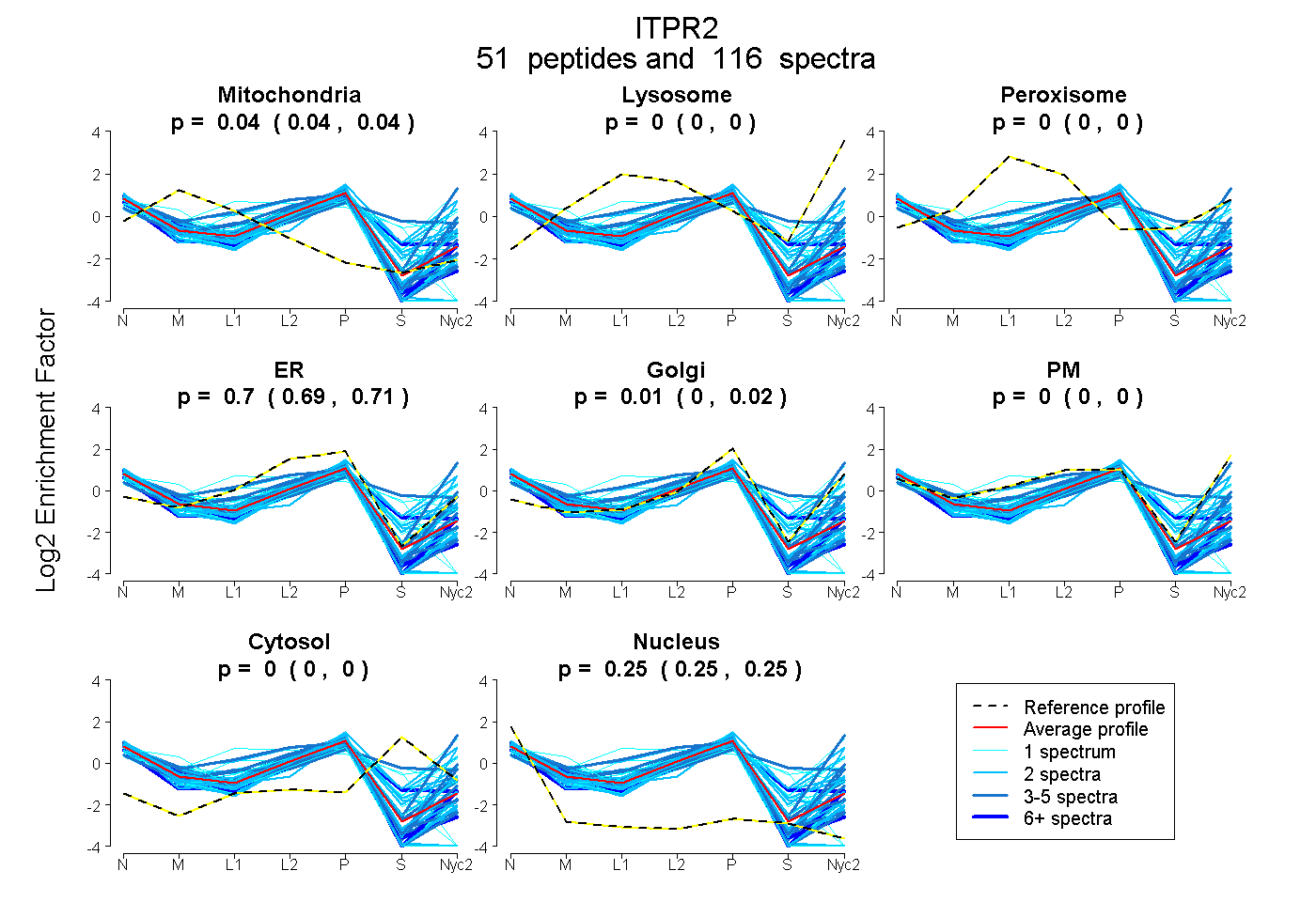
0.037 | 0.041
0.000 | 0.000
0.000 | 0.000
0.693 | 0.708
0.000 | 0.015
0.000 | 0.000
0.000 | 0.000
0.248 | 0.254
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
116 spectra |
 |
0.039 0.037 | 0.041 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.704 0.693 | 0.708 |
0.006 0.000 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.252 0.248 | 0.254 |
| 2 spectra, TAQVGGGFTGQDADK | 0.000 | 0.000 | 0.000 | 0.672 | 0.000 | 0.000 | 0.000 | 0.328 | ||
| 8 spectra, ILFNMRPK | 0.000 | 0.000 | 0.000 | 0.727 | 0.000 | 0.000 | 0.000 | 0.273 | ||
| 2 spectra, NVYTEIK | 0.033 | 0.000 | 0.000 | 0.403 | 0.107 | 0.203 | 0.082 | 0.173 | ||
| 2 spectra, ELVDVMK | 0.132 | 0.000 | 0.000 | 0.640 | 0.000 | 0.000 | 0.036 | 0.192 | ||
| 3 spectra, VCNTTTDR | 0.119 | 0.000 | 0.000 | 0.424 | 0.000 | 0.402 | 0.000 | 0.055 | ||
| 1 spectrum, ALWEIEVVHHDPCR | 0.166 | 0.000 | 0.000 | 0.497 | 0.000 | 0.000 | 0.000 | 0.337 | ||
| 4 spectra, QSATSATSSK | 0.000 | 0.000 | 0.000 | 0.692 | 0.000 | 0.000 | 0.000 | 0.308 | ||
| 3 spectra, EIETFVSLLR | 0.000 | 0.000 | 0.000 | 0.689 | 0.000 | 0.000 | 0.000 | 0.311 | ||
| 3 spectra, DLDFANDANK | 0.000 | 0.000 | 0.000 | 0.688 | 0.000 | 0.000 | 0.000 | 0.312 | ||
| 2 spectra, ITLFMK | 0.000 | 0.000 | 0.000 | 0.678 | 0.000 | 0.000 | 0.000 | 0.322 | ||
| 3 spectra, LFENFLVDMAR | 0.000 | 0.000 | 0.000 | 0.436 | 0.140 | 0.239 | 0.000 | 0.185 | ||
| 2 spectra, AYCVYR | 0.000 | 0.000 | 0.000 | 0.137 | 0.133 | 0.494 | 0.160 | 0.076 | ||
| 1 spectrum, LINHTK | 0.000 | 0.000 | 0.000 | 0.704 | 0.000 | 0.000 | 0.000 | 0.296 | ||
| 2 spectra, QHIFLR | 0.155 | 0.000 | 0.000 | 0.506 | 0.000 | 0.000 | 0.000 | 0.340 | ||
| 1 spectrum, NMGAHSVVLDLLQIPYEK | 0.000 | 0.000 | 0.407 | 0.237 | 0.110 | 0.048 | 0.143 | 0.055 | ||
| 1 spectrum, ADCLVPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.133 | 0.648 | 0.176 | 0.043 | ||
| 2 spectra, EALGGPAWDYR | 0.000 | 0.000 | 0.000 | 0.624 | 0.000 | 0.000 | 0.000 | 0.376 | ||
| 1 spectrum, TGISMSDIQCLLDK | 0.000 | 0.000 | 0.000 | 0.488 | 0.133 | 0.140 | 0.000 | 0.238 | ||
| 4 spectra, SAEEVTMSPAITIMRPILR | 0.016 | 0.000 | 0.000 | 0.686 | 0.000 | 0.000 | 0.000 | 0.298 | ||
| 1 spectrum, HIFMNNYHLCNEISER | 0.265 | 0.000 | 0.000 | 0.392 | 0.000 | 0.000 | 0.186 | 0.157 | ||
| 1 spectrum, ELQNFLR | 0.000 | 0.000 | 0.000 | 0.650 | 0.021 | 0.000 | 0.041 | 0.288 | ||
| 2 spectra, YQLNLFAR | 0.040 | 0.000 | 0.000 | 0.688 | 0.000 | 0.000 | 0.000 | 0.271 | ||
| 1 spectrum, HLAQEAR | 0.116 | 0.000 | 0.000 | 0.064 | 0.180 | 0.486 | 0.113 | 0.041 | ||
| 7 spectra, DSFMEEGSTLR | 0.000 | 0.000 | 0.000 | 0.516 | 0.084 | 0.000 | 0.186 | 0.215 | ||
| 4 spectra, NQEYIAK | 0.000 | 0.000 | 0.154 | 0.091 | 0.199 | 0.168 | 0.325 | 0.063 | ||
| 2 spectra, SEGDNIVVGDK | 0.000 | 0.000 | 0.000 | 0.425 | 0.039 | 0.289 | 0.000 | 0.248 | ||
| 2 spectra, ASVESCIR | 0.000 | 0.000 | 0.000 | 0.689 | 0.008 | 0.048 | 0.000 | 0.254 | ||
| 2 spectra, CVSDESLPFDLR | 0.065 | 0.000 | 0.000 | 0.550 | 0.000 | 0.000 | 0.000 | 0.384 | ||
| 2 spectra, LFHAEQEK | 0.000 | 0.000 | 0.000 | 0.309 | 0.131 | 0.364 | 0.037 | 0.159 | ||
| 4 spectra, LLGEIVK | 0.153 | 0.000 | 0.000 | 0.574 | 0.000 | 0.000 | 0.000 | 0.274 | ||
| 2 spectra, TPVQLDDEGGR | 0.000 | 0.000 | 0.000 | 0.002 | 0.409 | 0.456 | 0.000 | 0.133 | ||
| 1 spectrum, QGNHTEAALLK | 0.000 | 0.000 | 0.000 | 0.150 | 0.172 | 0.484 | 0.112 | 0.081 | ||
| 2 spectra, AGEGSMLR | 0.001 | 0.000 | 0.000 | 0.382 | 0.349 | 0.000 | 0.168 | 0.099 | ||
| 2 spectra, GGAGQWNSLFR | 0.008 | 0.000 | 0.000 | 0.649 | 0.000 | 0.000 | 0.000 | 0.343 | ||
| 2 spectra, CNSLLPLDDIVR | 0.121 | 0.000 | 0.000 | 0.522 | 0.083 | 0.109 | 0.000 | 0.164 | ||
| 1 spectrum, ASFPILLNMMCSER | 0.000 | 0.000 | 0.000 | 0.604 | 0.000 | 0.000 | 0.000 | 0.396 | ||
| 2 spectra, HVEYLR | 0.000 | 0.000 | 0.000 | 0.659 | 0.000 | 0.000 | 0.000 | 0.341 | ||
| 1 spectrum, LCVQNK | 0.007 | 0.000 | 0.000 | 0.355 | 0.000 | 0.149 | 0.387 | 0.101 | ||
| 4 spectra, SELWVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.791 | 0.000 | 0.083 | ||
| 1 spectrum, ADLDQLR | 0.000 | 0.000 | 0.108 | 0.584 | 0.086 | 0.032 | 0.000 | 0.190 | ||
| 1 spectrum, EVNAVNCNTSWK | 0.008 | 0.000 | 0.000 | 0.568 | 0.000 | 0.000 | 0.000 | 0.425 | ||
| 1 spectrum, GIAIPVDLDSQVNTLFMK | 0.000 | 0.000 | 0.000 | 0.699 | 0.000 | 0.000 | 0.000 | 0.301 | ||
| 2 spectra, YSNVIQLLHIK | 0.001 | 0.000 | 0.000 | 0.724 | 0.006 | 0.000 | 0.000 | 0.269 | ||
| 3 spectra, LLLALMESR | 0.000 | 0.000 | 0.000 | 0.710 | 0.001 | 0.049 | 0.000 | 0.239 | ||
| 1 spectrum, CVVHPEAGDLTNPPK | 0.000 | 0.000 | 0.127 | 0.600 | 0.000 | 0.000 | 0.022 | 0.251 | ||
| 1 spectrum, VVTHDDCIPEVK | 0.268 | 0.000 | 0.000 | 0.431 | 0.000 | 0.000 | 0.000 | 0.300 | ||
| 6 spectra, LTFEVVHLAR | 0.040 | 0.000 | 0.000 | 0.640 | 0.000 | 0.000 | 0.000 | 0.320 | ||
| 1 spectrum, AEVLQAFK | 0.065 | 0.000 | 0.000 | 0.583 | 0.081 | 0.000 | 0.000 | 0.270 | ||
| 3 spectra, FLQLLCENHNR | 0.062 | 0.000 | 0.000 | 0.578 | 0.009 | 0.172 | 0.000 | 0.179 | ||
| 2 spectra, GGDVVR | 0.002 | 0.000 | 0.149 | 0.108 | 0.119 | 0.497 | 0.126 | 0.000 | ||
| 2 spectra, HADTFLER | 0.000 | 0.000 | 0.000 | 0.717 | 0.000 | 0.000 | 0.000 | 0.283 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
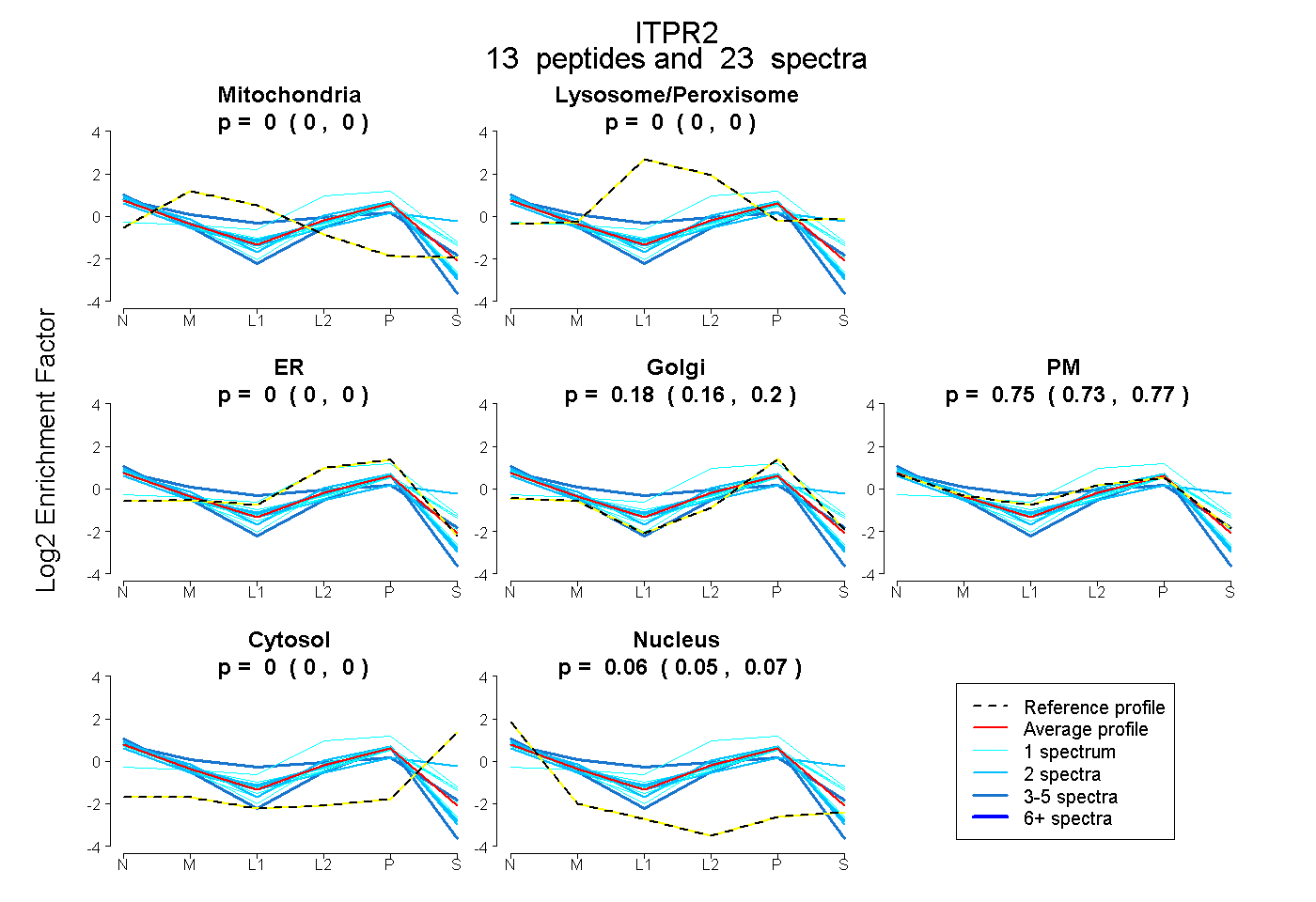 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.185 0.164 | 0.202 |
0.755 0.731 | 0.773 |
0.000 0.000 | 0.000 |
0.060 0.054 | 0.066 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
72 spectra |
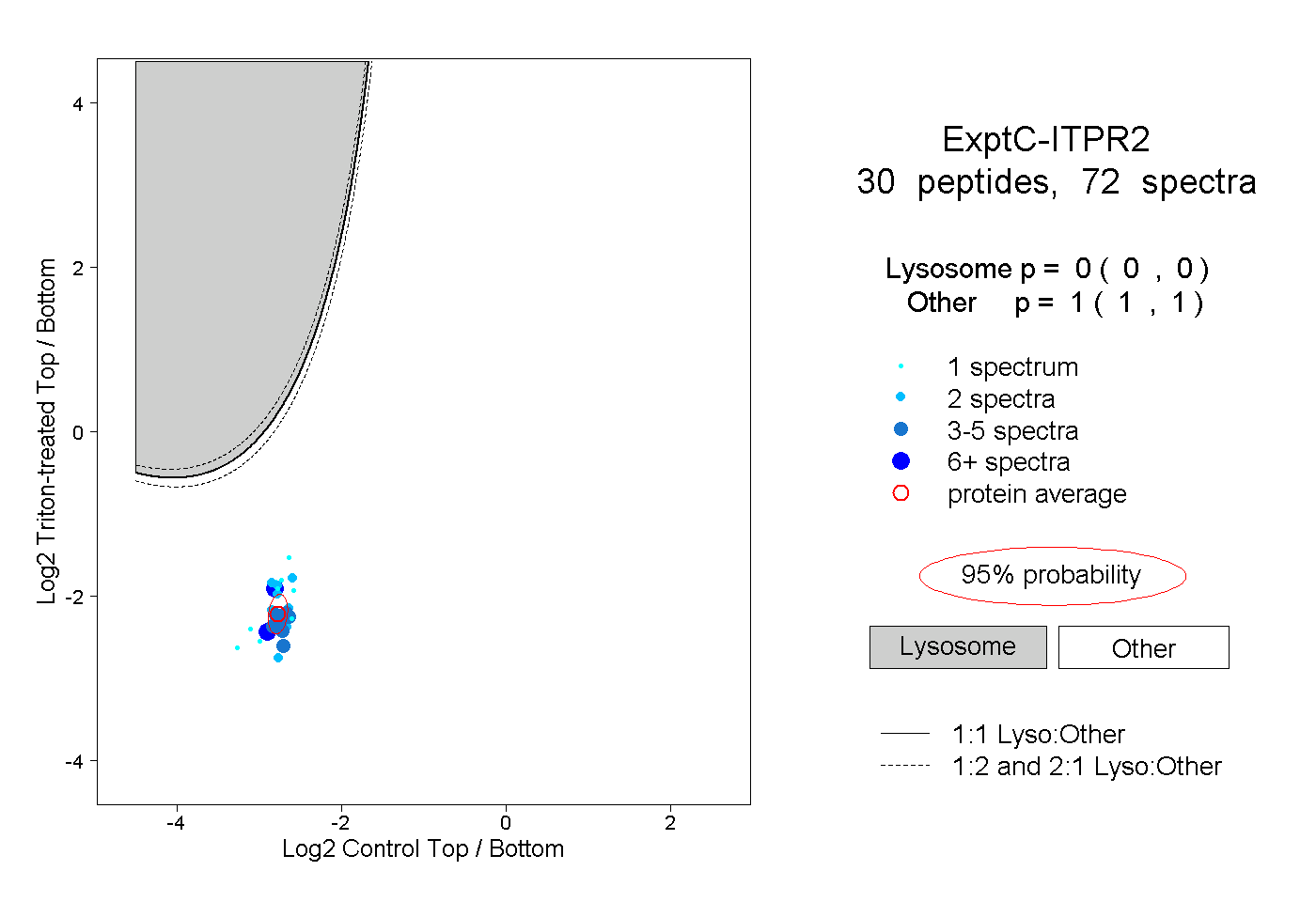 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
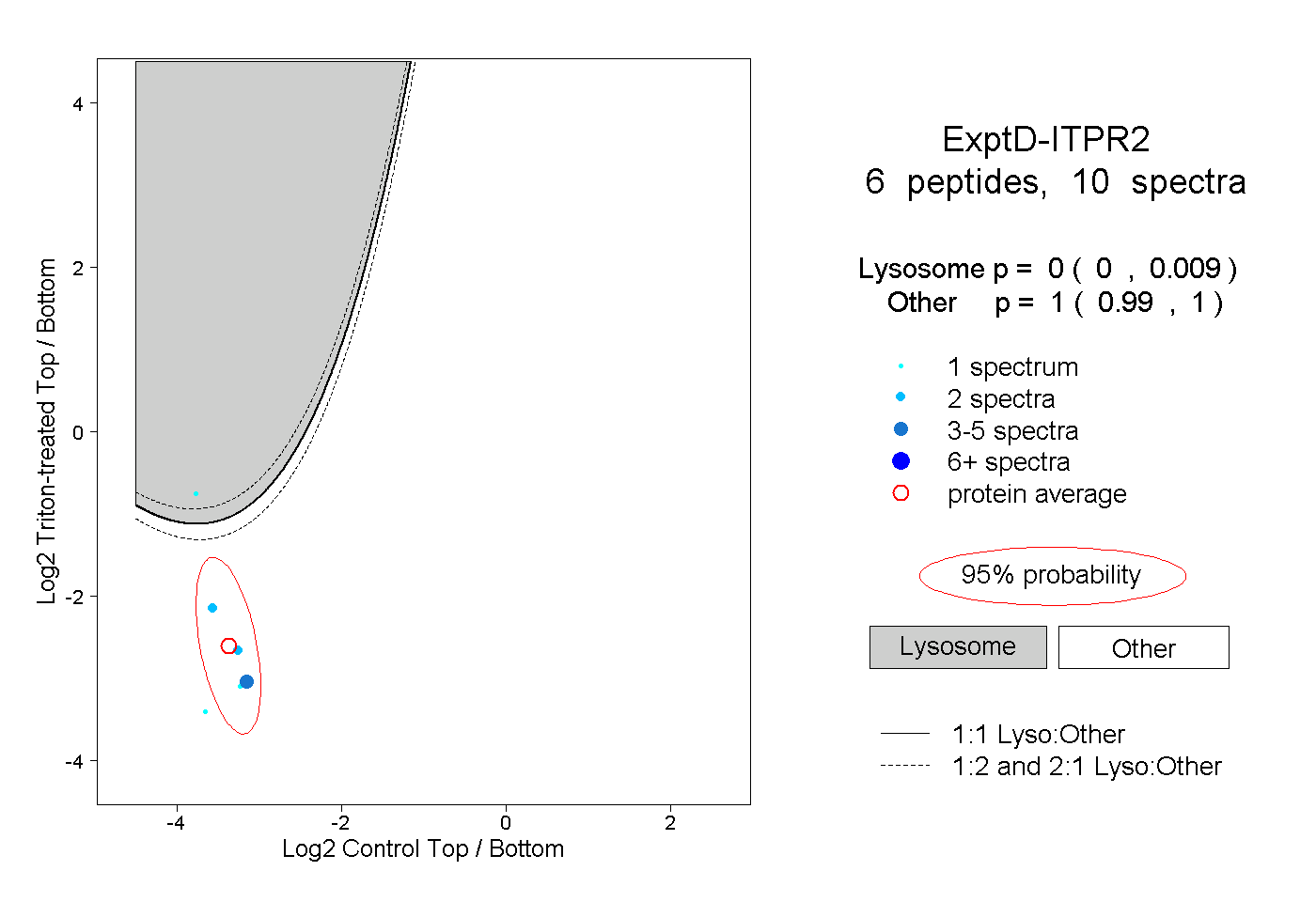 |
0.000 0.000 | 0.009 |
1.000 0.990 | 1.000 |