peptides
spectra
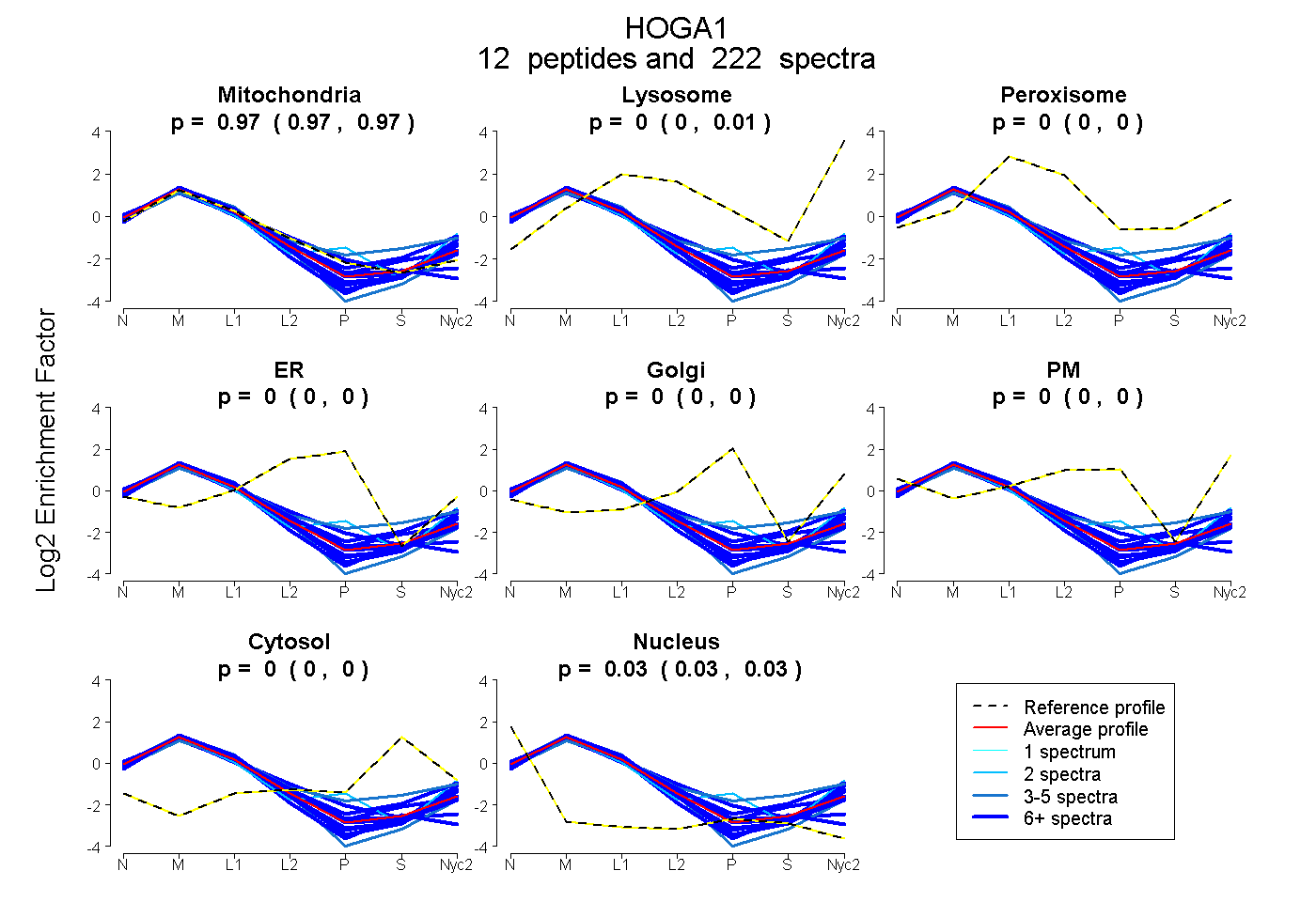
0.966 | 0.972
0.000 | 0.005
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.027 | 0.029
peptides
spectra
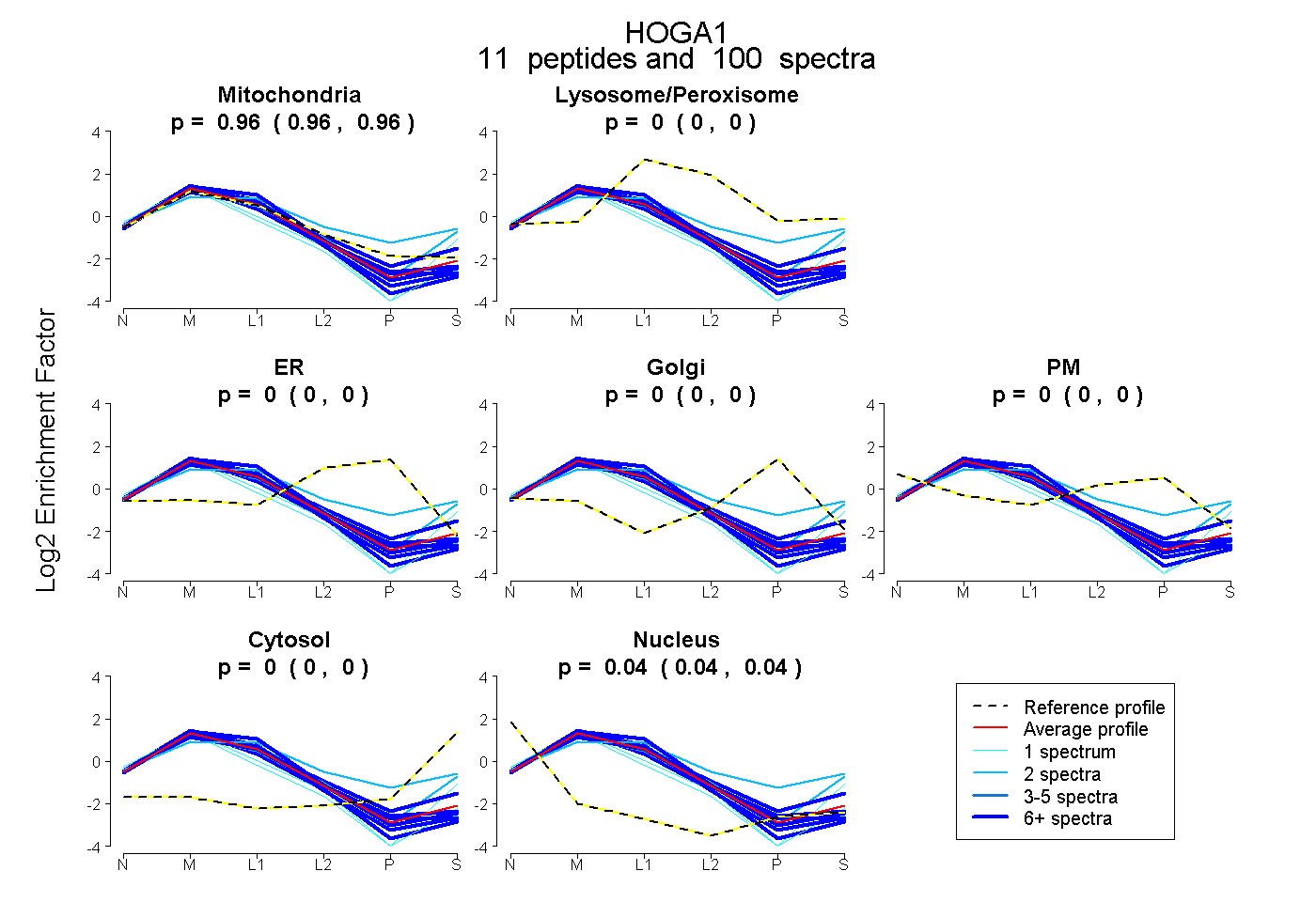
0.959 | 0.963
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.036 | 0.041
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
222 spectra |
 |
0.970 0.966 | 0.972 |
0.003 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.027 | 0.029 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
100 spectra |
 |
0.961 0.959 | 0.963 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.039 0.036 | 0.041 |
| 2 spectra, FGIPGLK | 0.840 | 0.000 | 0.000 | 0.000 | 0.000 | 0.160 | 0.000 | |||
| 2 spectra, MNSAALIHHYTK | 0.616 | 0.262 | 0.000 | 0.000 | 0.000 | 0.122 | 0.000 | |||
| 16 spectra, LAAFPFR | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | |||
| 15 spectra, LEVVSR | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.036 | |||
| 1 spectrum, APLQELSPSEEEALR | 0.785 | 0.000 | 0.000 | 0.000 | 0.000 | 0.132 | 0.082 | |||
| 8 spectra, DSGGDVTR | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | |||
| 33 spectra, LIEPNTAVTR | 0.979 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.021 | |||
| 1 spectrum, LEENLNK | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | |||
| 7 spectra, TGLIVHK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, LCLTGQGEAAQR | 0.950 | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | |||
| 1 spectrum, GFVVQGSTGEFPFLTSLER | 0.858 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.142 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
551 spectra |
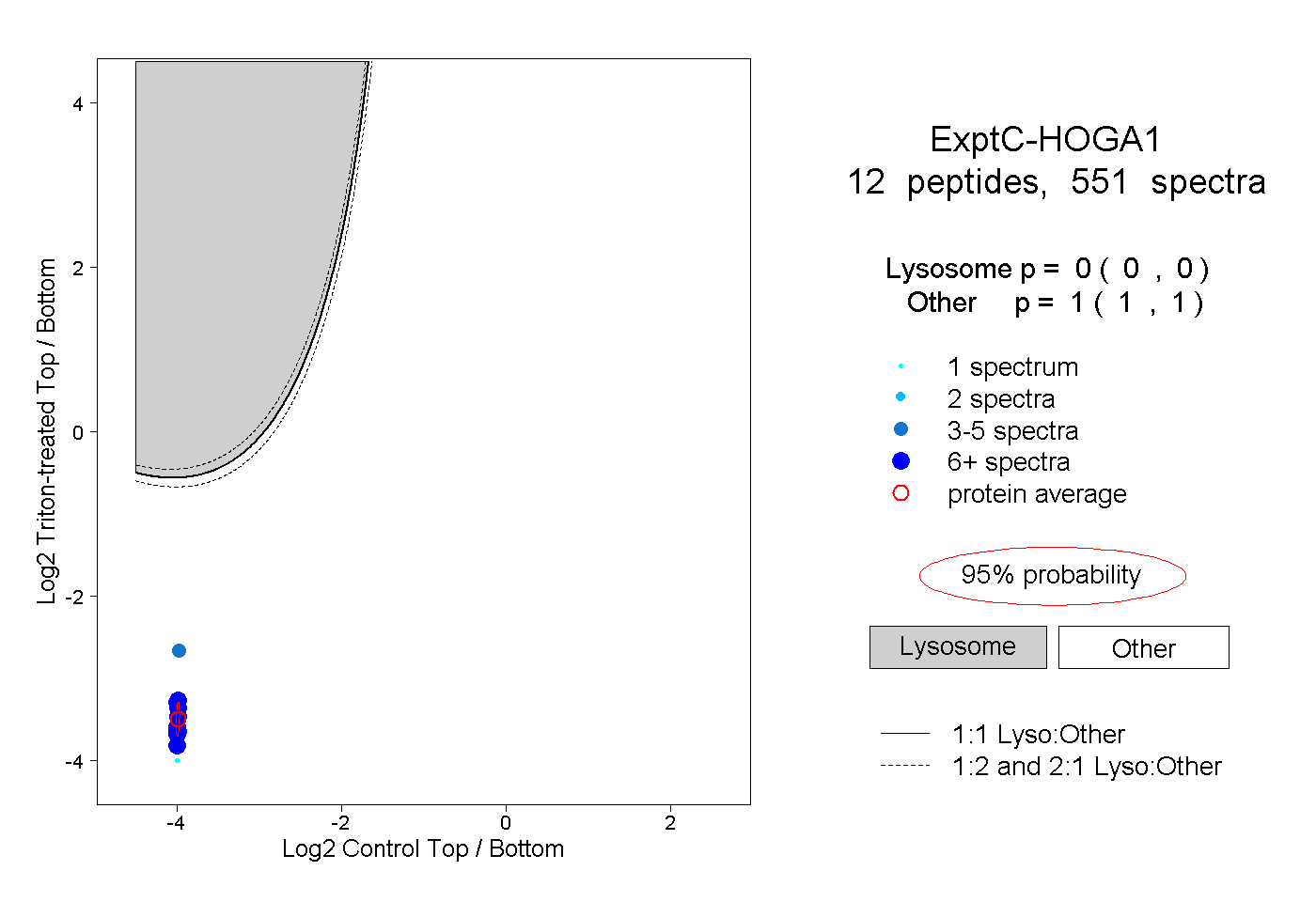 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
45 spectra |
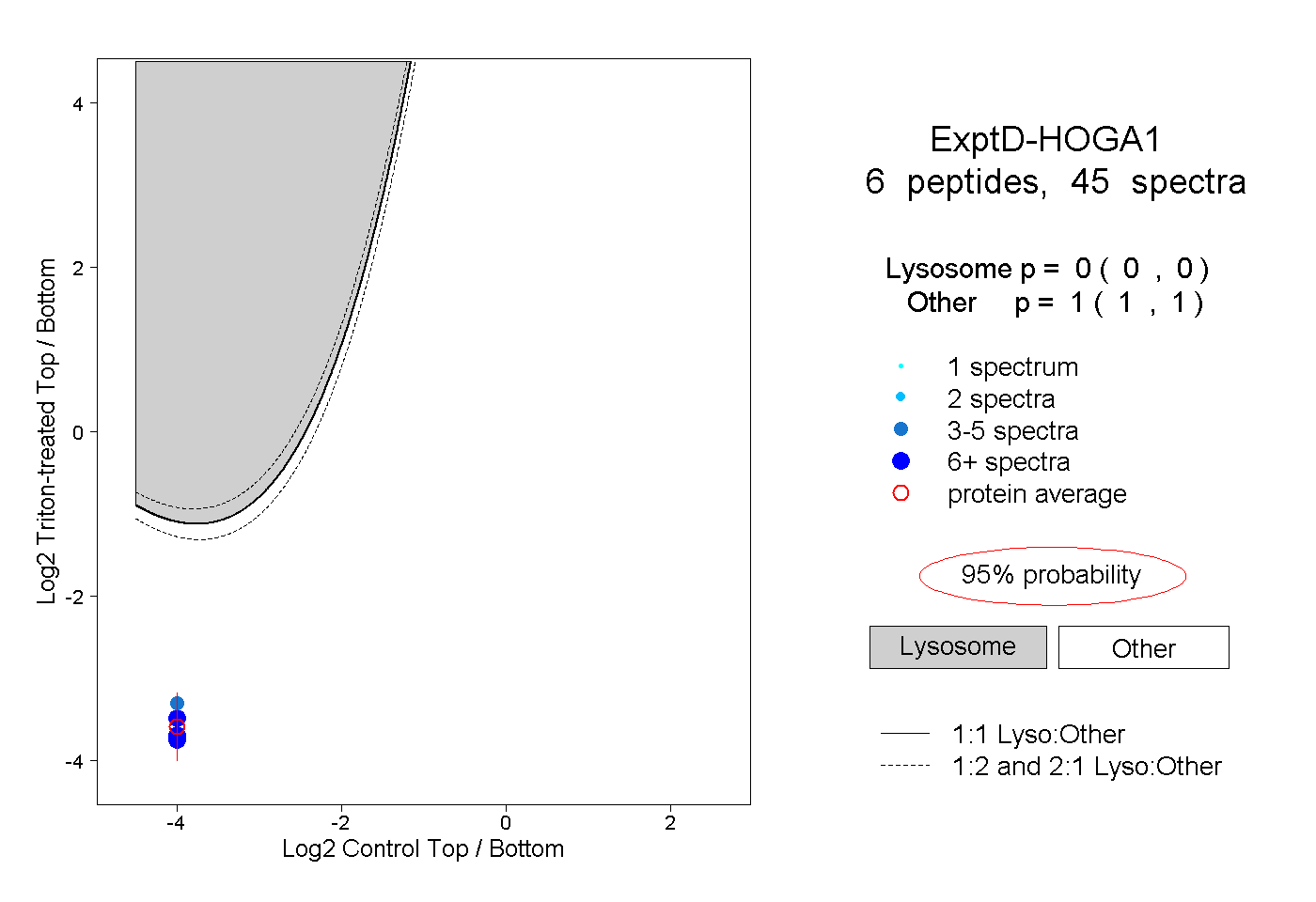 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |