peptides
spectra
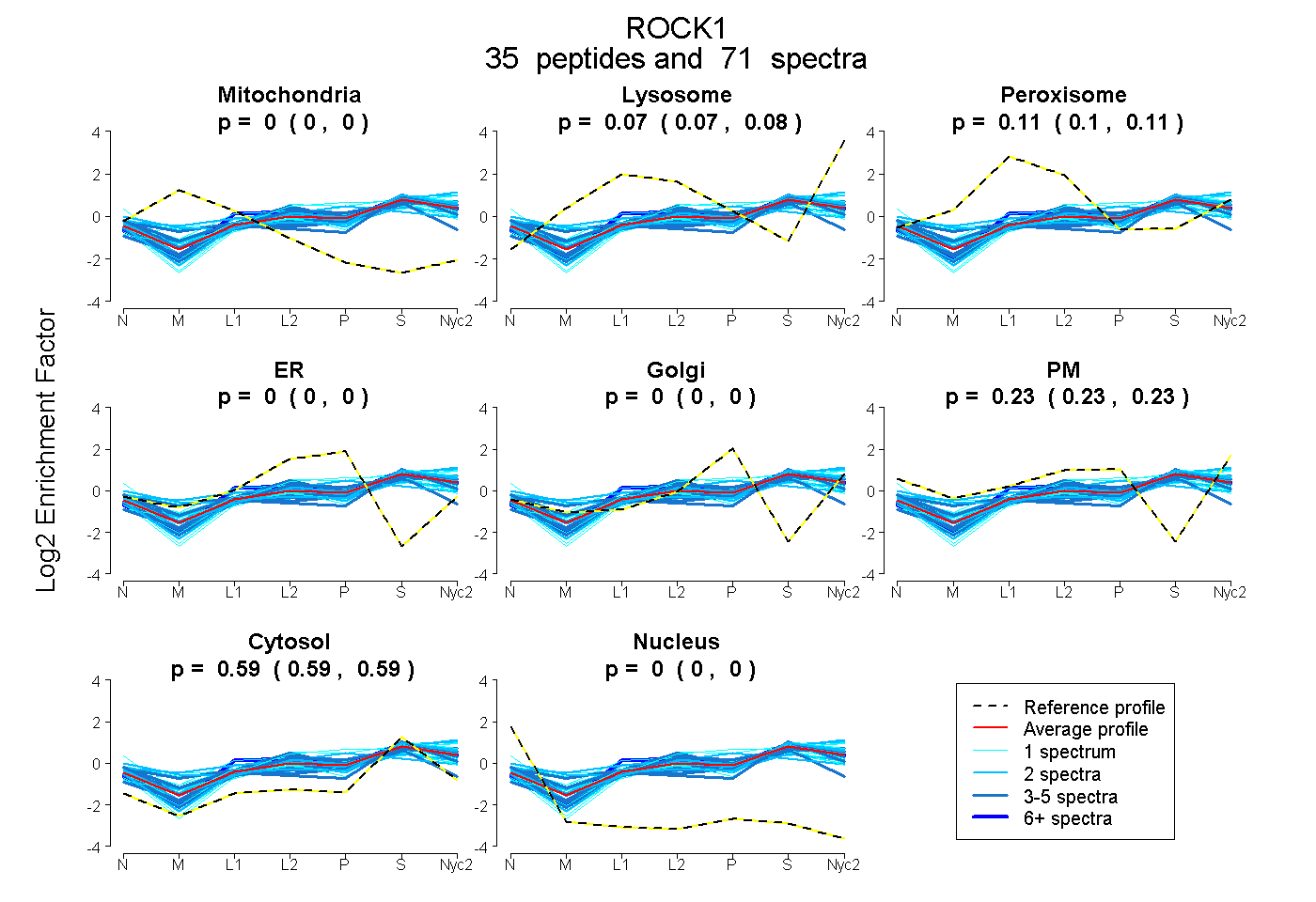
0.000 | 0.000
0.069 | 0.078
0.101 | 0.109
0.000 | 0.000
0.000 | 0.000
0.229 | 0.235
0.587 | 0.590
0.000 | 0.000
peptides
spectra
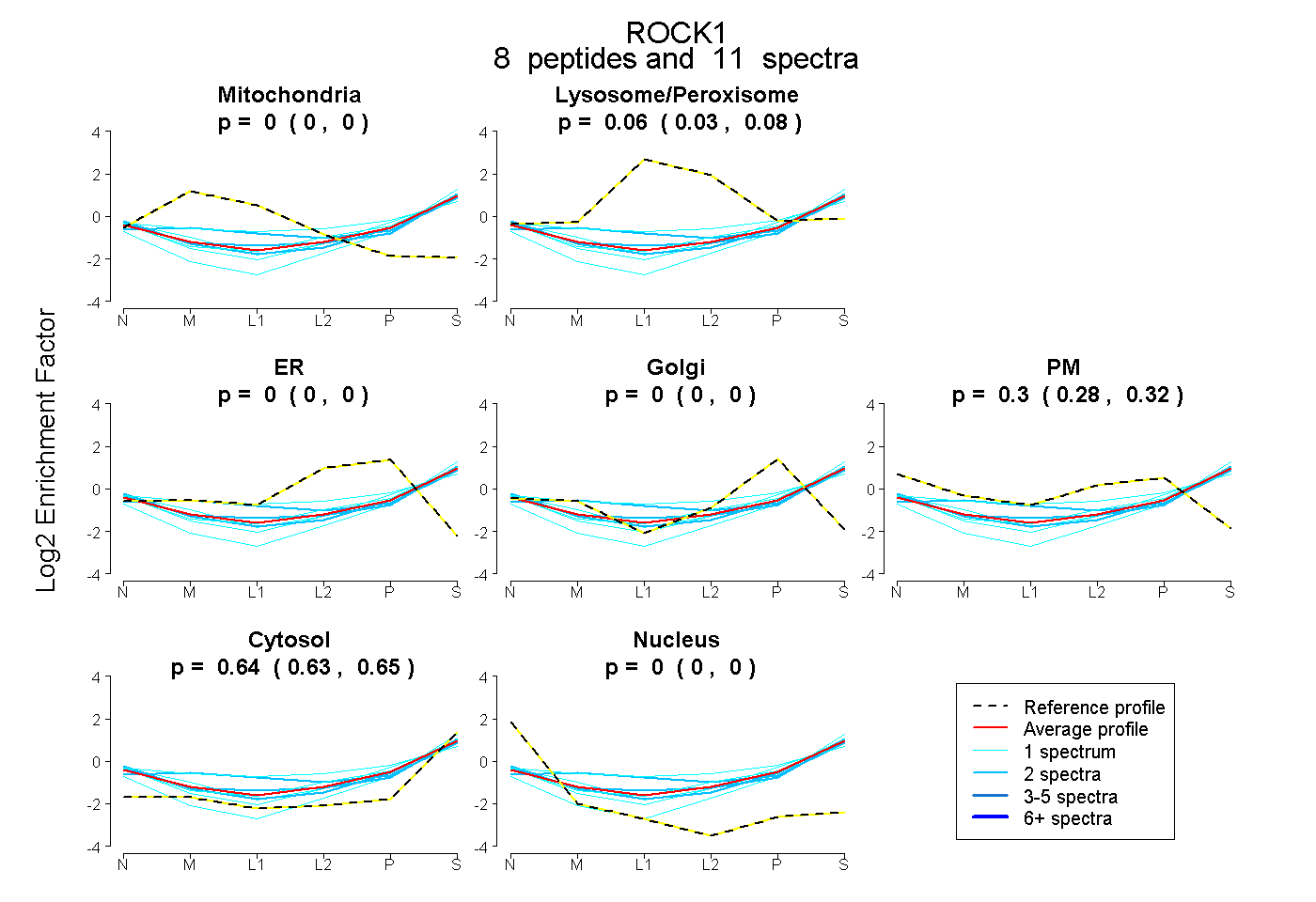
0.000 | 0.000
0.032 | 0.078
0.000 | 0.000
0.000 | 0.000
0.281 | 0.315
0.631 | 0.652
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
71 spectra |
 |
0.000 0.000 | 0.000 |
0.074 0.069 | 0.078 |
0.105 0.101 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.232 0.229 | 0.235 |
0.589 0.587 | 0.590 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
11 spectra |
 |
0.000 0.000 | 0.000 |
0.057 0.032 | 0.078 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.300 0.281 | 0.315 |
0.643 0.631 | 0.652 |
0.000 0.000 | 0.000 |
| 1 spectrum, TNFQNHK | 0.000 | 0.253 | 0.000 | 0.077 | 0.218 | 0.452 | 0.000 | |||
| 2 spectra, LLEFELAQLTK | 0.000 | 0.101 | 0.000 | 0.000 | 0.237 | 0.662 | 0.000 | |||
| 2 spectra, LFHVRPVTQGDVYR | 0.010 | 0.222 | 0.000 | 0.000 | 0.196 | 0.572 | 0.000 | |||
| 1 spectrum, YLPSANPSENR | 0.000 | 0.066 | 0.000 | 0.000 | 0.297 | 0.637 | 0.000 | |||
| 2 spectra, NLICAFLTDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.330 | 0.670 | 0.000 | |||
| 1 spectrum, ELDEEGNQR | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | 0.797 | 0.023 | |||
| 1 spectrum, ESDIEQLR | 0.000 | 0.000 | 0.000 | 0.019 | 0.301 | 0.680 | 0.000 | |||
| 1 spectrum, GAFGEVQLVR | 0.000 | 0.000 | 0.000 | 0.045 | 0.349 | 0.606 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
121 spectra |
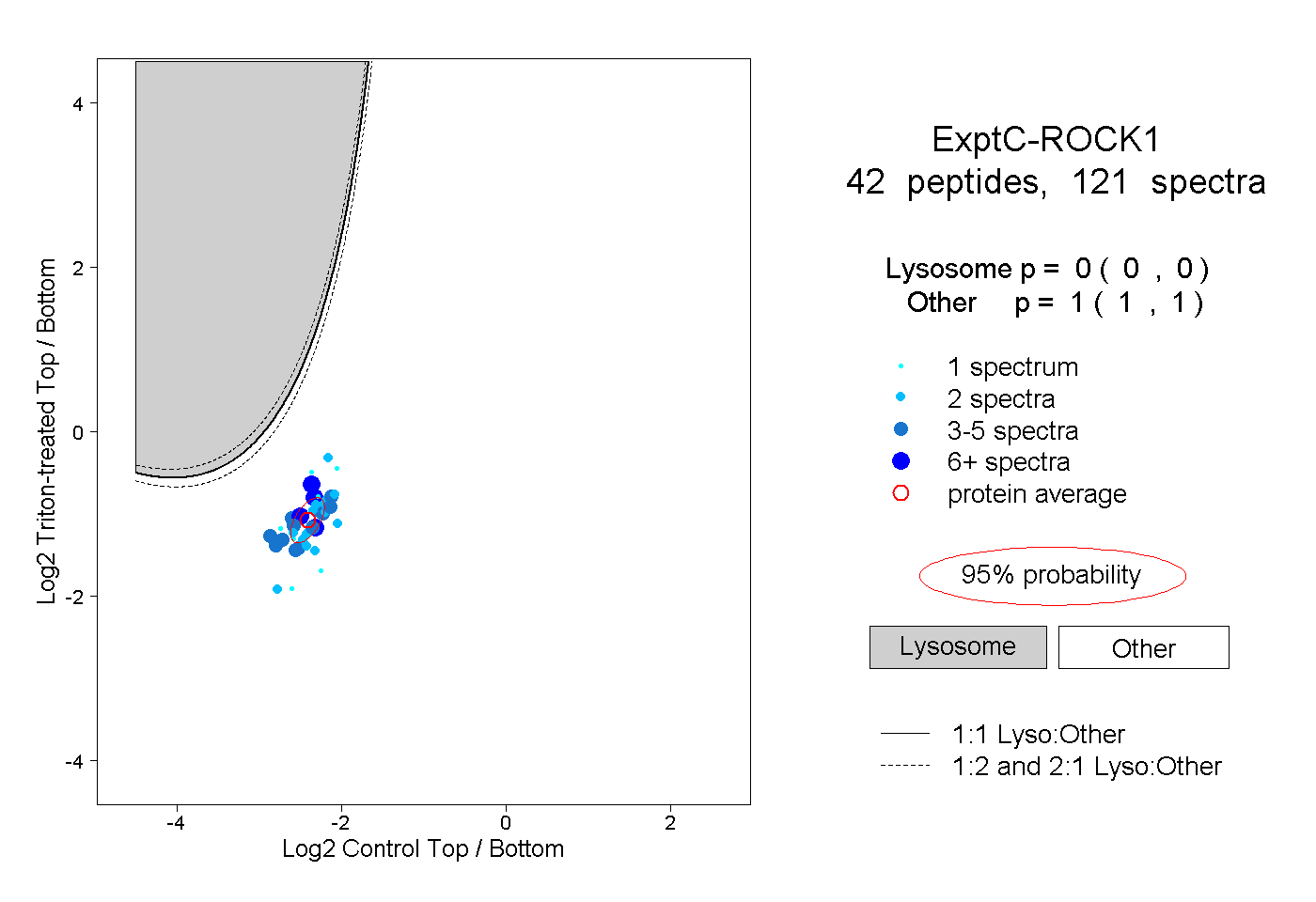 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
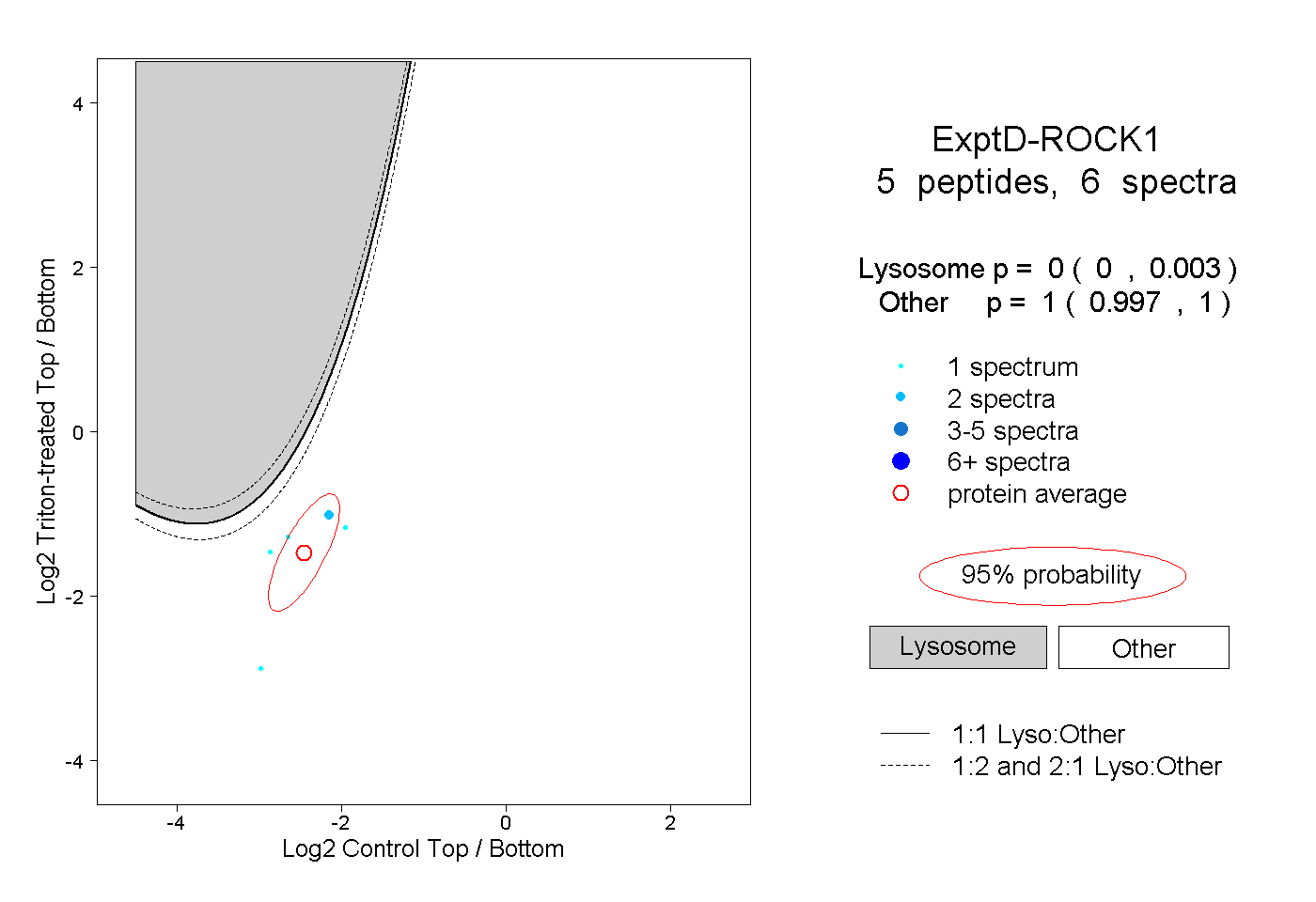 |
0.000 0.000 | 0.003 |
1.000 0.997 | 1.000 |