peptides
spectra
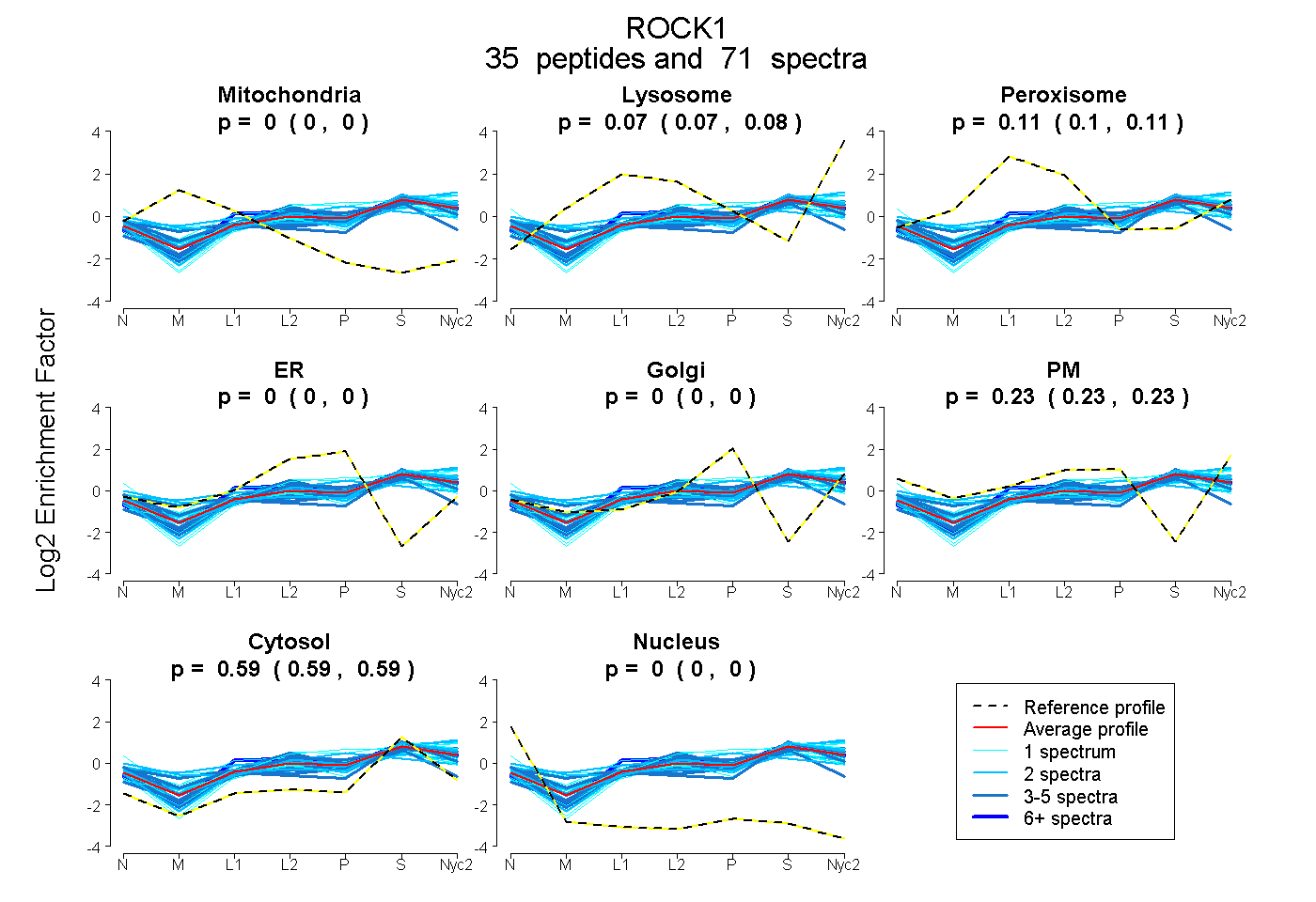
0.000 | 0.000
0.069 | 0.078
0.101 | 0.109
0.000 | 0.000
0.000 | 0.000
0.229 | 0.235
0.587 | 0.590
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
71 spectra |
 |
0.000 0.000 | 0.000 |
0.074 0.069 | 0.078 |
0.105 0.101 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.232 0.229 | 0.235 |
0.589 0.587 | 0.590 |
0.000 0.000 | 0.000 |
| 3 spectra, VVETEK | 0.000 | 0.108 | 0.108 | 0.000 | 0.000 | 0.051 | 0.733 | 0.000 | ||
| 1 spectrum, DVKPDNMLLDK | 0.000 | 0.002 | 0.163 | 0.000 | 0.002 | 0.281 | 0.552 | 0.000 | ||
| 1 spectrum, LEEANNALTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.482 | 0.518 | 0.000 | ||
| 2 spectra, YLPSANPSENR | 0.000 | 0.145 | 0.009 | 0.000 | 0.000 | 0.163 | 0.682 | 0.000 | ||
| 1 spectrum, TAEEEYK | 0.000 | 0.043 | 0.214 | 0.000 | 0.000 | 0.115 | 0.628 | 0.000 | ||
| 2 spectra, SDSAFFWEER | 0.000 | 0.246 | 0.000 | 0.000 | 0.000 | 0.212 | 0.542 | 0.000 | ||
| 3 spectra, NIDNFLSR | 0.000 | 0.101 | 0.154 | 0.000 | 0.000 | 0.259 | 0.486 | 0.000 | ||
| 1 spectrum, ESDIEQLR | 0.000 | 0.066 | 0.029 | 0.000 | 0.000 | 0.211 | 0.694 | 0.000 | ||
| 1 spectrum, LAEIMNR | 0.000 | 0.207 | 0.000 | 0.059 | 0.000 | 0.094 | 0.639 | 0.000 | ||
| 2 spectra, GAFGEVQLVR | 0.000 | 0.157 | 0.125 | 0.000 | 0.000 | 0.160 | 0.558 | 0.000 | ||
| 2 spectra, WVTHLVK | 0.000 | 0.063 | 0.082 | 0.000 | 0.000 | 0.259 | 0.595 | 0.000 | ||
| 1 spectrum, GNEGQMR | 0.000 | 0.000 | 0.213 | 0.040 | 0.138 | 0.162 | 0.448 | 0.000 | ||
| 2 spectra, QLEEANDLLR | 0.000 | 0.112 | 0.026 | 0.000 | 0.000 | 0.257 | 0.605 | 0.000 | ||
| 1 spectrum, ELNDMQAQLVEECTHR | 0.000 | 0.348 | 0.000 | 0.000 | 0.000 | 0.103 | 0.549 | 0.000 | ||
| 1 spectrum, SVAMCEMEK | 0.000 | 0.094 | 0.079 | 0.309 | 0.000 | 0.000 | 0.518 | 0.000 | ||
| 1 spectrum, DIEVEPVQQGEK | 0.000 | 0.038 | 0.259 | 0.000 | 0.107 | 0.000 | 0.596 | 0.000 | ||
| 4 spectra, TESDTAVR | 0.000 | 0.046 | 0.085 | 0.000 | 0.000 | 0.336 | 0.533 | 0.000 | ||
| 4 spectra, SQGGDGYYGR | 0.000 | 0.091 | 0.034 | 0.000 | 0.000 | 0.174 | 0.702 | 0.000 | ||
| 1 spectrum, SVSQLESLNR | 0.000 | 0.221 | 0.007 | 0.000 | 0.000 | 0.103 | 0.670 | 0.000 | ||
| 2 spectra, ASQSSQLANEK | 0.000 | 0.063 | 0.071 | 0.000 | 0.000 | 0.187 | 0.680 | 0.000 | ||
| 1 spectrum, LEQEVNEHK | 0.000 | 0.005 | 0.095 | 0.000 | 0.000 | 0.196 | 0.704 | 0.000 | ||
| 1 spectrum, LLEFELAQLTK | 0.000 | 0.124 | 0.000 | 0.202 | 0.000 | 0.073 | 0.602 | 0.000 | ||
| 2 spectra, LTQLQK | 0.000 | 0.294 | 0.025 | 0.000 | 0.000 | 0.092 | 0.589 | 0.000 | ||
| 4 spectra, NLICAFLTDR | 0.000 | 0.000 | 0.238 | 0.231 | 0.000 | 0.000 | 0.531 | 0.000 | ||
| 3 spectra, IQELQSEK | 0.000 | 0.140 | 0.087 | 0.004 | 0.000 | 0.226 | 0.543 | 0.000 | ||
| 2 spectra, AESEQLAR | 0.000 | 0.128 | 0.000 | 0.000 | 0.000 | 0.250 | 0.621 | 0.000 | ||
| 4 spectra, EEEISNLK | 0.000 | 0.098 | 0.048 | 0.000 | 0.000 | 0.192 | 0.662 | 0.000 | ||
| 1 spectrum, EAQDMLNHSEK | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.316 | 0.578 | 0.000 | ||
| 2 spectra, NISTER | 0.045 | 0.000 | 0.129 | 0.000 | 0.000 | 0.316 | 0.510 | 0.000 | ||
| 1 spectrum, AETEEIPK | 0.004 | 0.000 | 0.165 | 0.024 | 0.014 | 0.292 | 0.501 | 0.000 | ||
| 1 spectrum, ILLQSELK | 0.000 | 0.150 | 0.000 | 0.000 | 0.000 | 0.258 | 0.592 | 0.000 | ||
| 4 spectra, NPPSGFVR | 0.000 | 0.080 | 0.042 | 0.000 | 0.000 | 0.216 | 0.661 | 0.000 | ||
| 1 spectrum, NELQMQLASK | 0.000 | 0.196 | 0.154 | 0.000 | 0.000 | 0.175 | 0.475 | 0.000 | ||
| 2 spectra, SHTEMSK | 0.000 | 0.000 | 0.323 | 0.020 | 0.305 | 0.000 | 0.352 | 0.000 | ||
| 6 spectra, MLLQHR | 0.000 | 0.114 | 0.194 | 0.028 | 0.000 | 0.080 | 0.583 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
11 spectra |
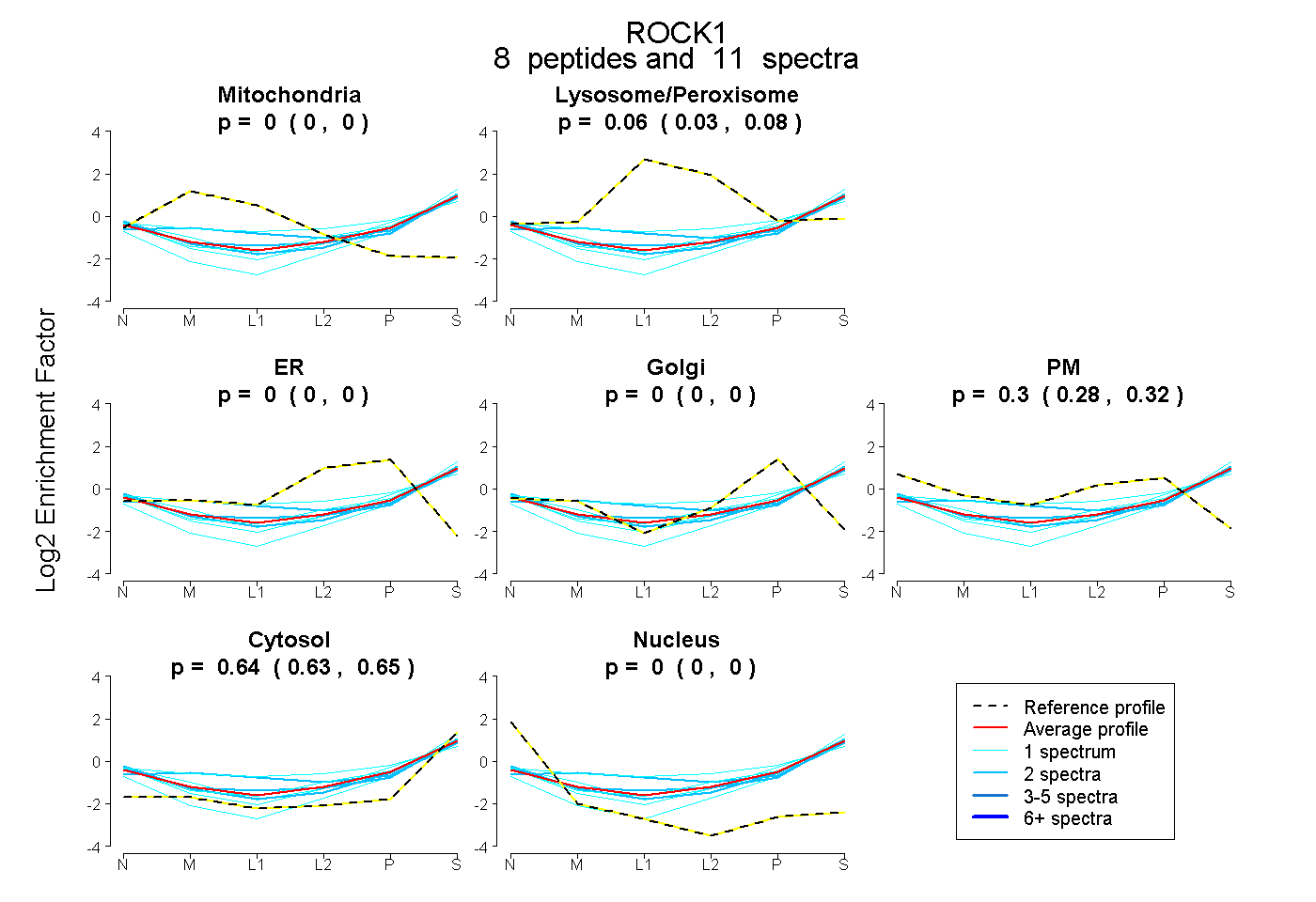 |
0.000 0.000 | 0.000 |
0.057 0.032 | 0.078 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.300 0.281 | 0.315 |
0.643 0.631 | 0.652 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
121 spectra |
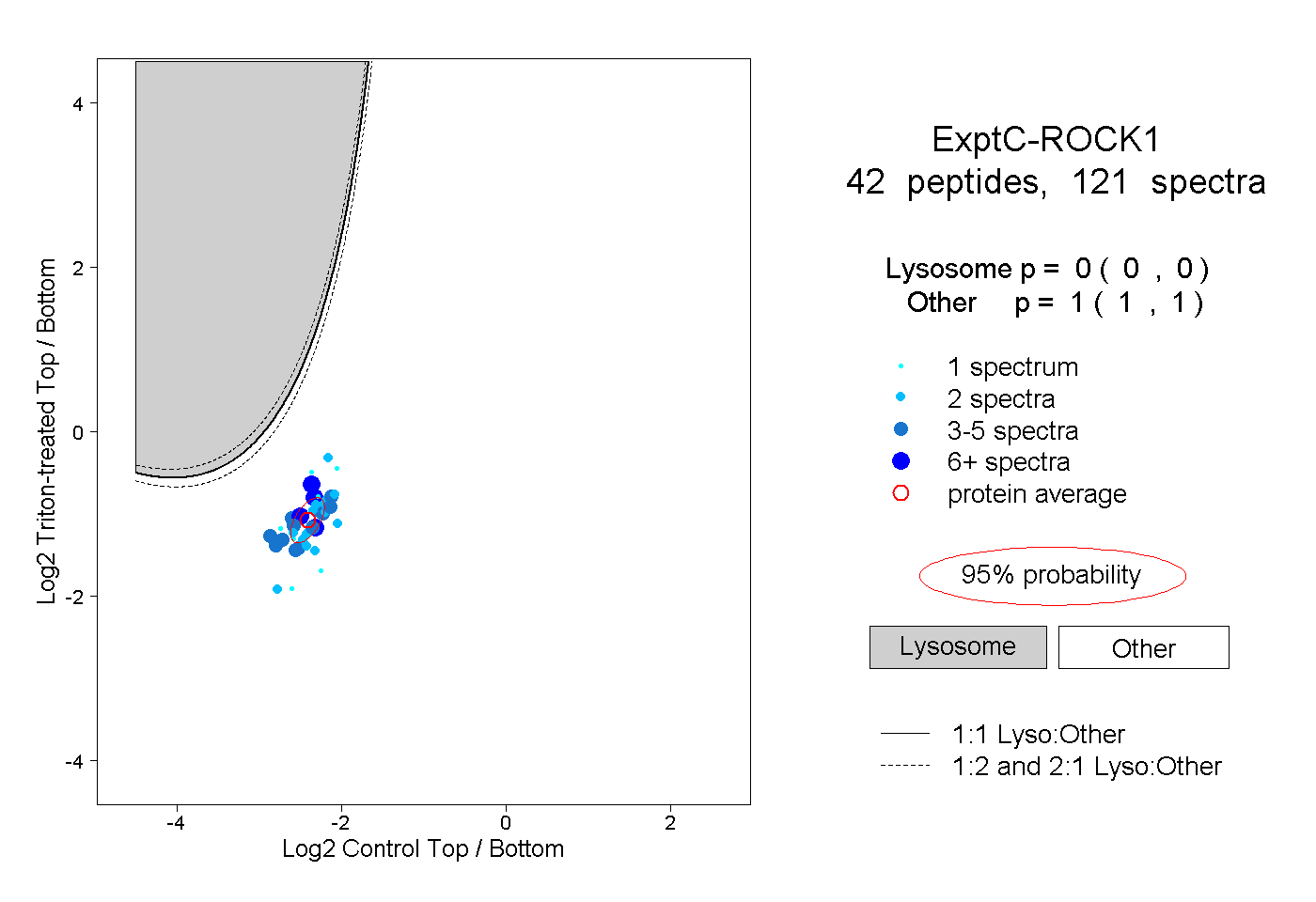 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
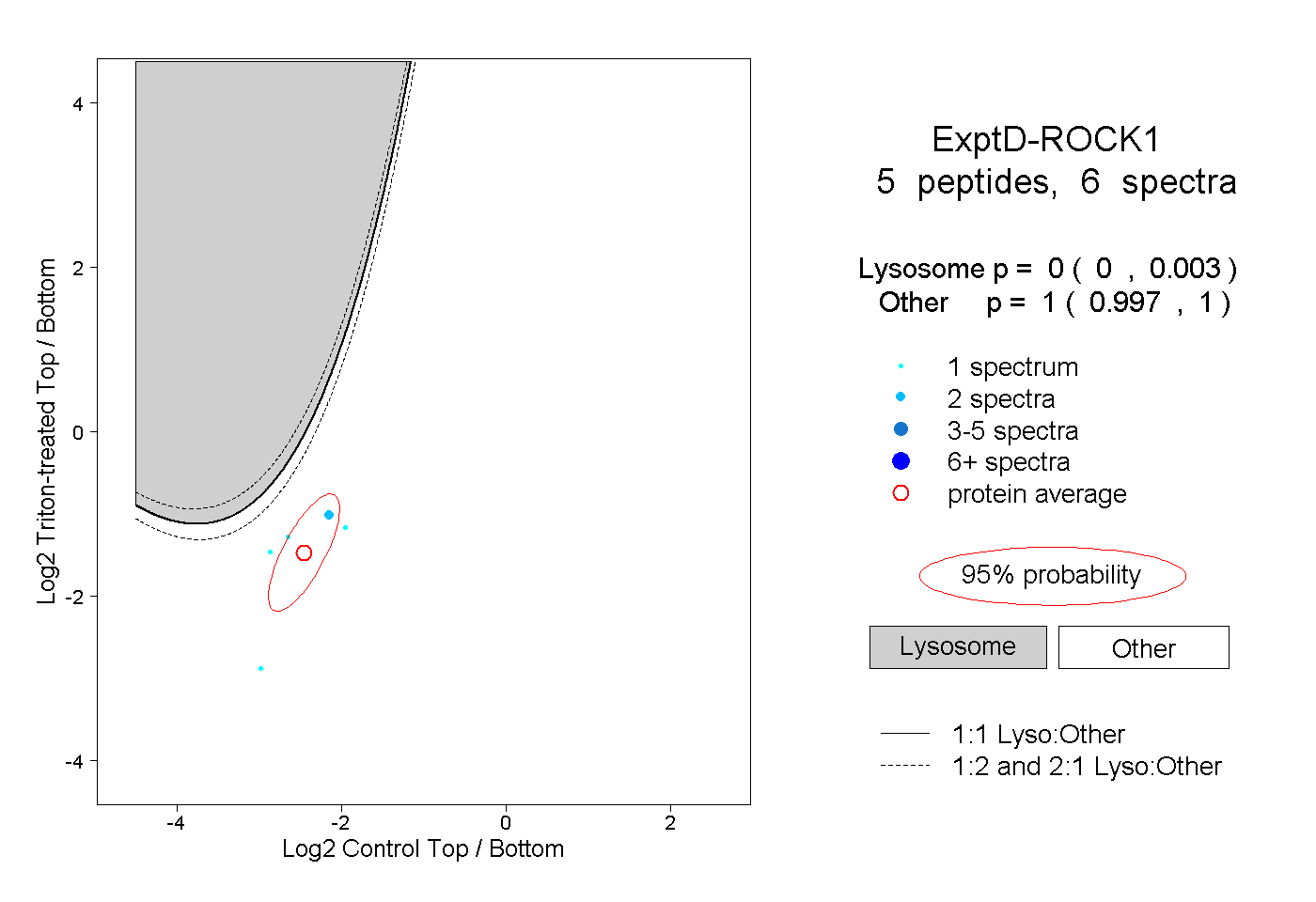 |
0.000 0.000 | 0.003 |
1.000 0.997 | 1.000 |