peptides
spectra
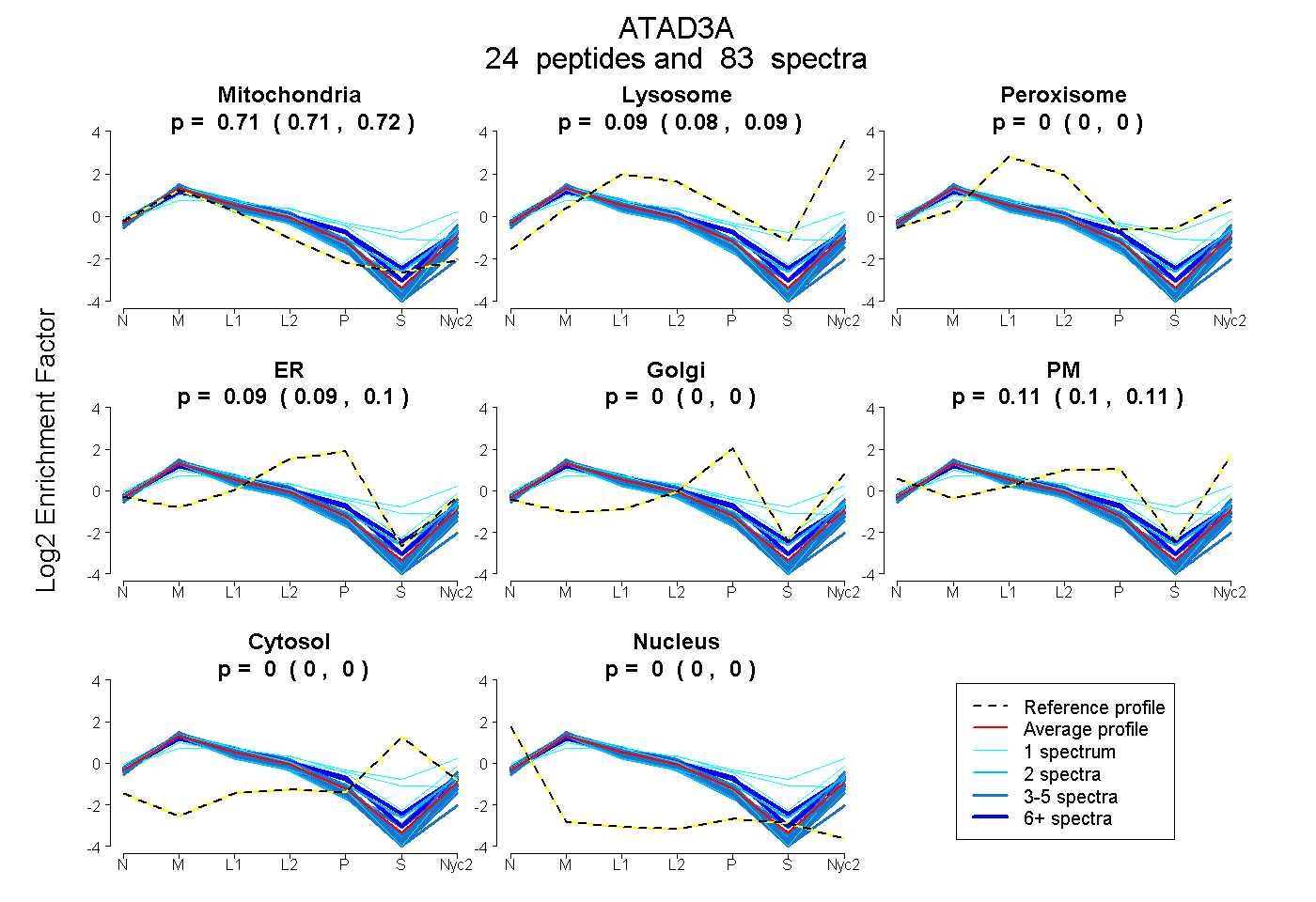
0.710 | 0.715
0.082 | 0.088
0.000 | 0.000
0.088 | 0.099
0.000 | 0.000
0.101 | 0.113
0.000 | 0.000
0.000 | 0.000
peptides
spectra
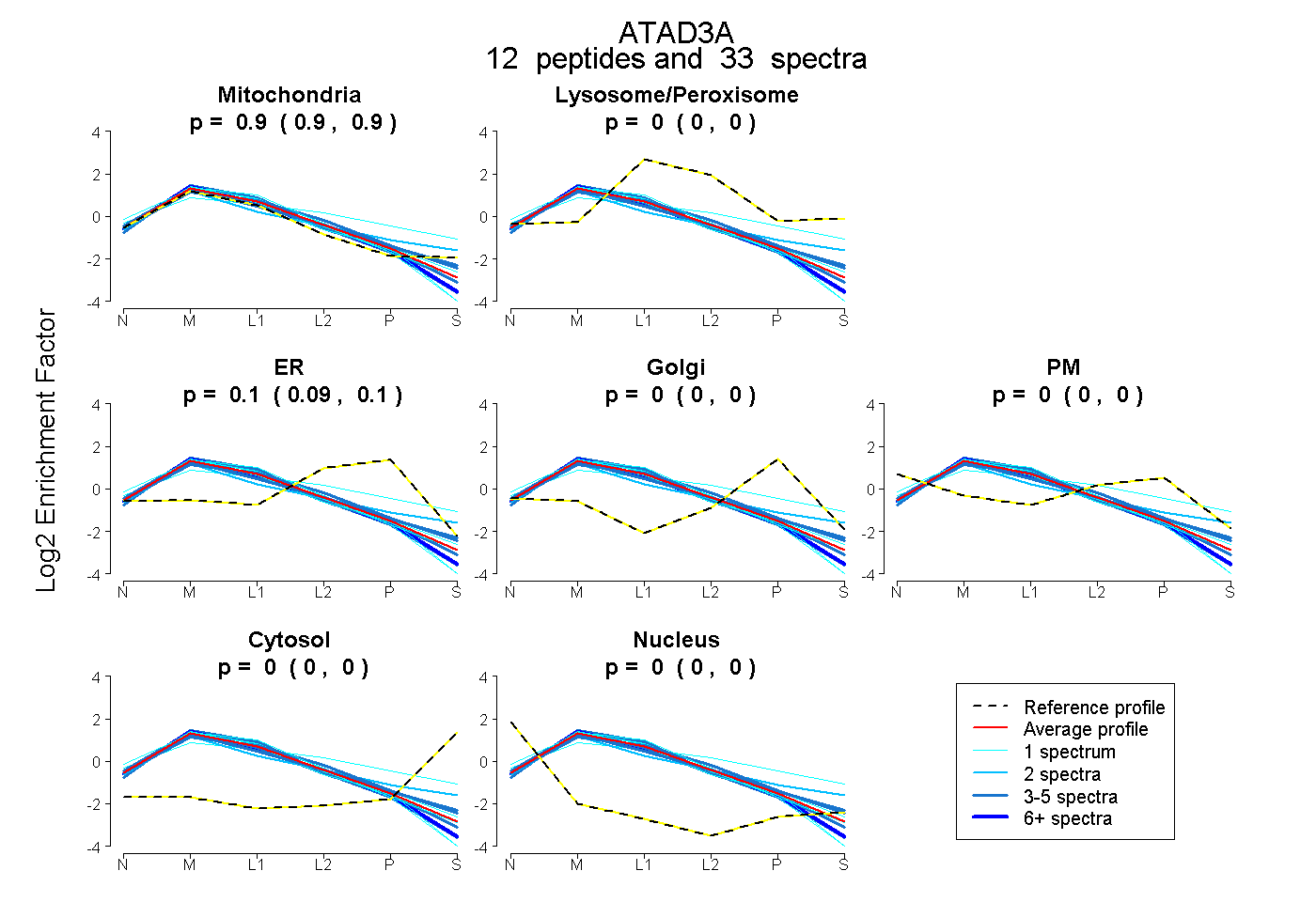
0.895 | 0.905
0.000 | 0.000
0.095 | 0.104
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
83 spectra |
 |
0.713 0.710 | 0.715 |
0.085 0.082 | 0.088 |
0.000 0.000 | 0.000 |
0.094 0.088 | 0.099 |
0.000 0.000 | 0.000 |
0.108 0.101 | 0.113 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.900 0.895 | 0.905 |
0.000 0.000 | 0.000 |
0.100 0.095 | 0.104 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, TLNEETR | 0.906 | 0.000 | 0.094 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QQQLLNEENLR | 0.940 | 0.000 | 0.060 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VFDWASTSR | 0.879 | 0.000 | 0.121 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NATSVAGR | 0.947 | 0.000 | 0.053 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LVSRPQDALEGVILSPSLEAR | 0.765 | 0.078 | 0.049 | 0.109 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QTILESIR | 0.895 | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TLFAK | 0.935 | 0.020 | 0.044 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AQYQDK | 0.452 | 0.315 | 0.000 | 0.175 | 0.058 | 0.000 | 0.000 | |||
| 3 spectra, LGKPSLVR | 0.924 | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, TAGTLFGEGFR | 0.828 | 0.055 | 0.117 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, ATLNAFLHR | 0.964 | 0.000 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, ISVLEALR | 0.926 | 0.000 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
415 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
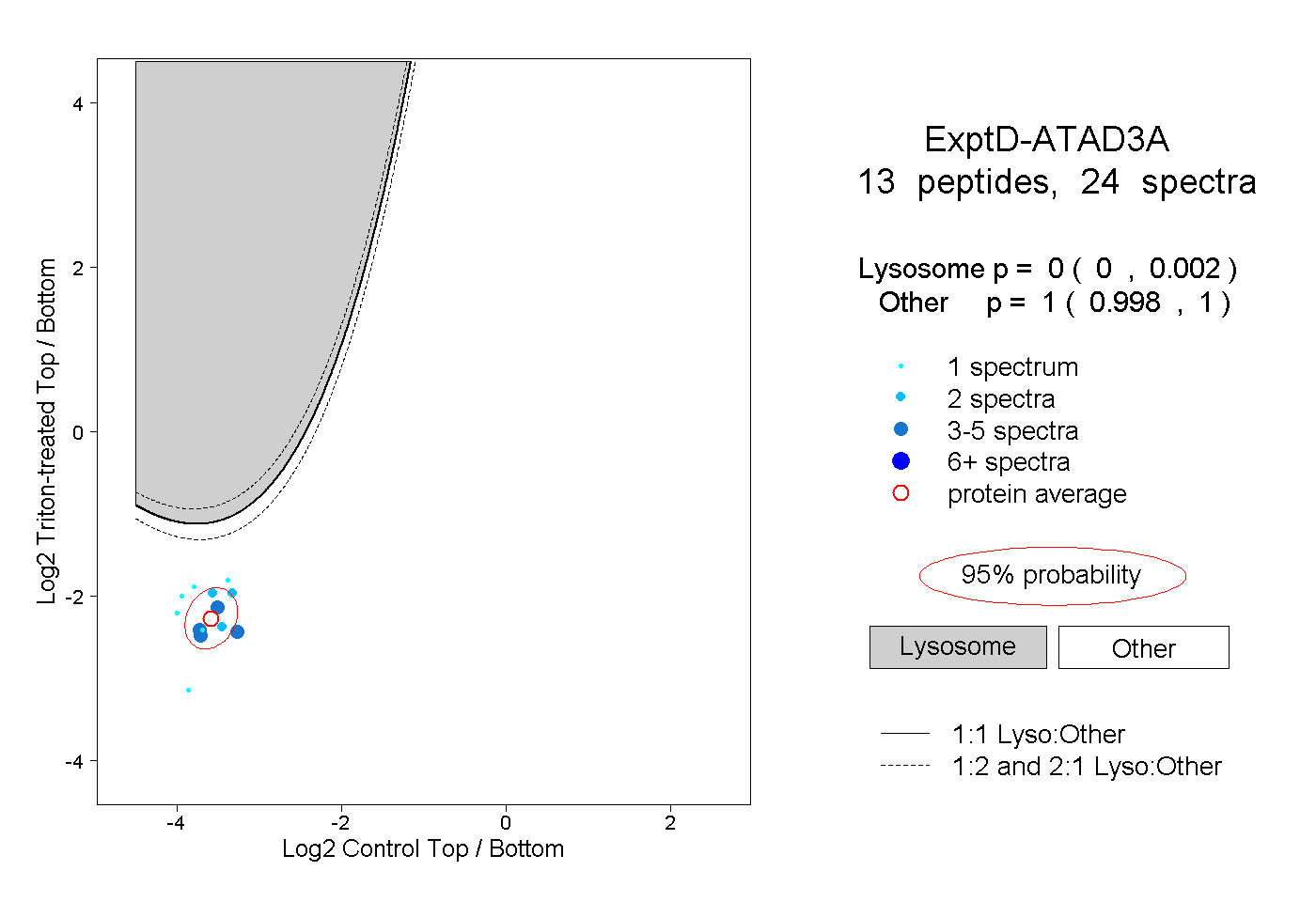 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |