peptides
spectra
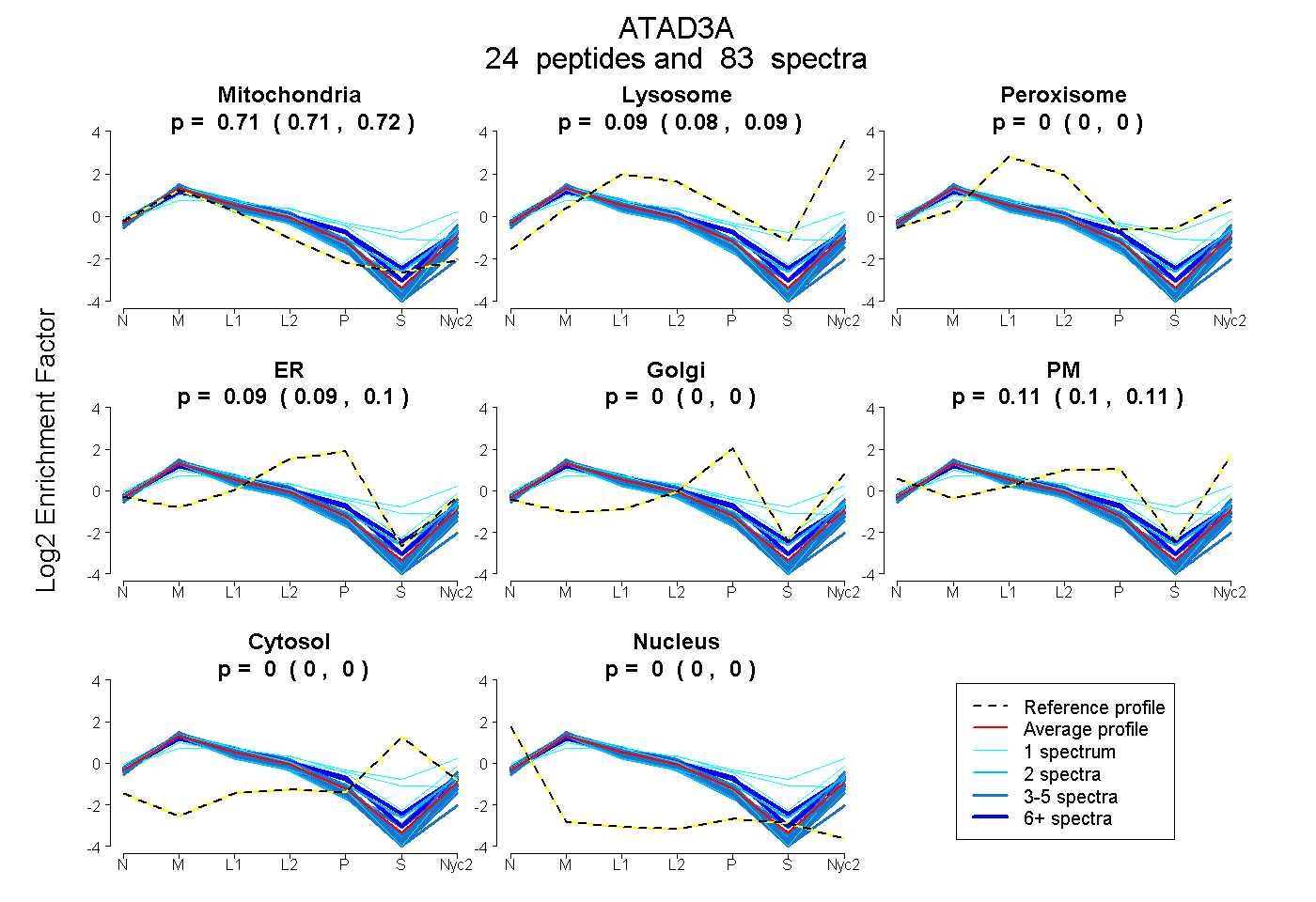
0.710 | 0.715
0.082 | 0.088
0.000 | 0.000
0.088 | 0.099
0.000 | 0.000
0.101 | 0.113
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
83 spectra |
 |
0.713 0.710 | 0.715 |
0.085 0.082 | 0.088 |
0.000 0.000 | 0.000 |
0.094 0.088 | 0.099 |
0.000 0.000 | 0.000 |
0.108 0.101 | 0.113 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, TLNEETR | 0.685 | 0.037 | 0.000 | 0.087 | 0.000 | 0.190 | 0.000 | 0.000 | ||
| 4 spectra, QQQLLNEENLR | 0.765 | 0.006 | 0.000 | 0.000 | 0.000 | 0.229 | 0.000 | 0.000 | ||
| 3 spectra, NATSVAGR | 0.720 | 0.048 | 0.000 | 0.055 | 0.000 | 0.176 | 0.000 | 0.000 | ||
| 1 spectrum, GAGDRPSPK | 0.745 | 0.000 | 0.000 | 0.129 | 0.000 | 0.125 | 0.000 | 0.000 | ||
| 4 spectra, AFVTDWDK | 0.760 | 0.192 | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | 0.000 | ||
| 3 spectra, LGKPSLVR | 0.765 | 0.014 | 0.000 | 0.116 | 0.000 | 0.106 | 0.000 | 0.000 | ||
| 9 spectra, HPIQVSR | 0.611 | 0.127 | 0.050 | 0.144 | 0.000 | 0.069 | 0.000 | 0.000 | ||
| 1 spectrum, AQYQDK | 0.508 | 0.159 | 0.000 | 0.119 | 0.000 | 0.213 | 0.000 | 0.000 | ||
| 2 spectra, VAQFDYGK | 0.683 | 0.123 | 0.000 | 0.000 | 0.060 | 0.134 | 0.000 | 0.000 | ||
| 5 spectra, TAGTLFGEGFR | 0.654 | 0.098 | 0.000 | 0.027 | 0.000 | 0.222 | 0.000 | 0.000 | ||
| 8 spectra, ENADIIR | 0.622 | 0.104 | 0.000 | 0.180 | 0.000 | 0.093 | 0.000 | 0.000 | ||
| 2 spectra, ISEDLR | 0.808 | 0.003 | 0.000 | 0.090 | 0.000 | 0.099 | 0.000 | 0.000 | ||
| 3 spectra, ATLNAFLHR | 0.735 | 0.015 | 0.000 | 0.250 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, CSEVAQLTAGMSGR | 0.730 | 0.121 | 0.000 | 0.144 | 0.000 | 0.005 | 0.000 | 0.000 | ||
| 1 spectrum, VEAEAR | 0.708 | 0.059 | 0.000 | 0.052 | 0.000 | 0.181 | 0.000 | 0.000 | ||
| 4 spectra, IDEMVCFALPQR | 0.863 | 0.000 | 0.000 | 0.137 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EALNLAQMQEQTLQLEQQSK | 0.458 | 0.000 | 0.256 | 0.178 | 0.004 | 0.000 | 0.105 | 0.000 | ||
| 4 spectra, VFDWASTSR | 0.733 | 0.050 | 0.000 | 0.155 | 0.000 | 0.061 | 0.000 | 0.000 | ||
| 2 spectra, GLLLFVDEADAFLR | 0.780 | 0.069 | 0.000 | 0.000 | 0.000 | 0.151 | 0.000 | 0.000 | ||
| 3 spectra, LVSRPQDALEGVILSPSLEAR | 0.725 | 0.071 | 0.000 | 0.000 | 0.000 | 0.204 | 0.000 | 0.000 | ||
| 2 spectra, QTILESIR | 0.687 | 0.085 | 0.000 | 0.000 | 0.000 | 0.228 | 0.000 | 0.000 | ||
| 1 spectrum, LALHSGMDYAIMTGGDVAPMGR | 0.267 | 0.081 | 0.311 | 0.000 | 0.042 | 0.178 | 0.122 | 0.000 | ||
| 2 spectra, DIAIATR | 0.789 | 0.183 | 0.000 | 0.000 | 0.000 | 0.028 | 0.000 | 0.000 | ||
| 10 spectra, ISVLEALR | 0.755 | 0.065 | 0.000 | 0.057 | 0.000 | 0.124 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
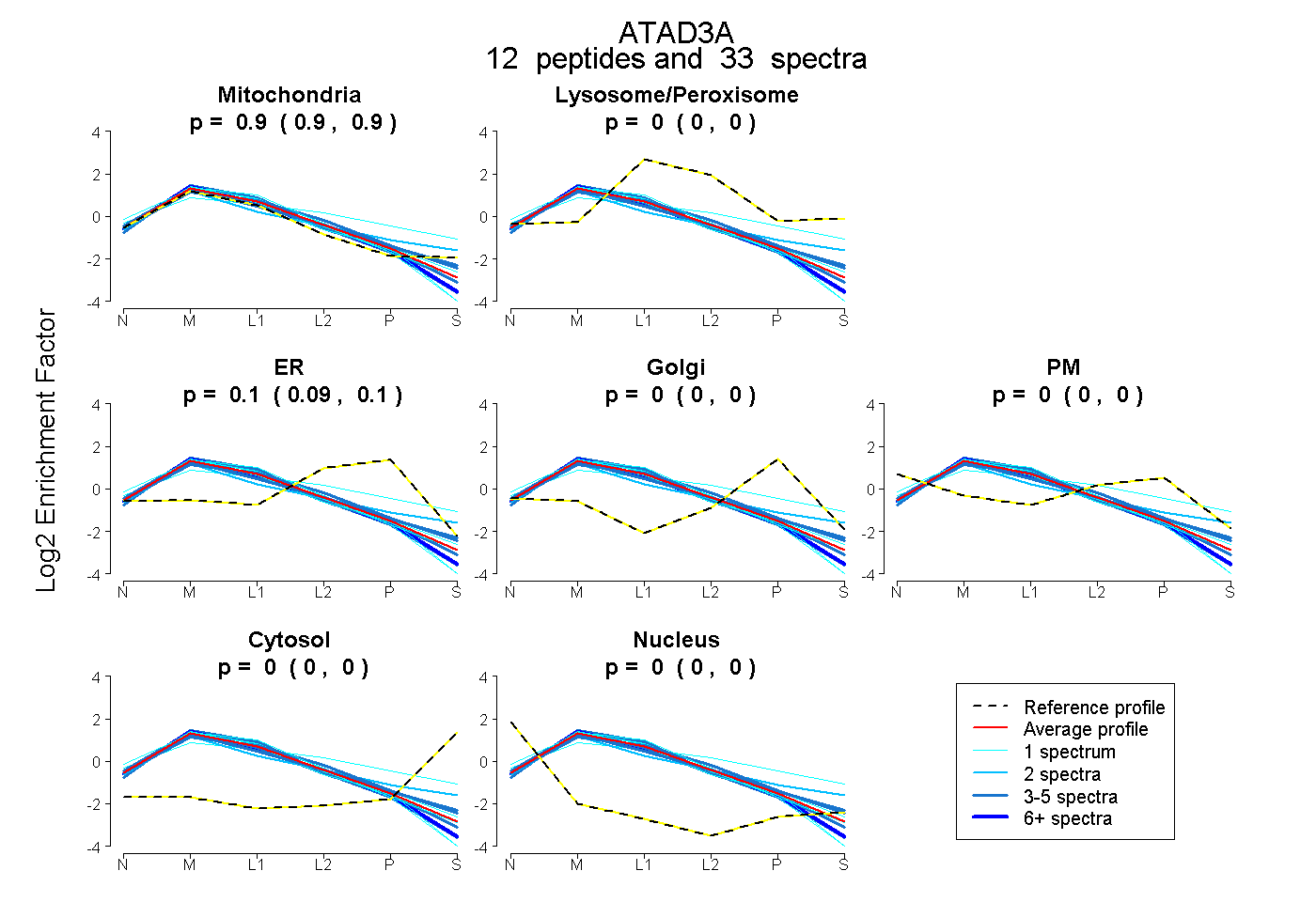 |
0.900 0.895 | 0.905 |
0.000 0.000 | 0.000 |
0.100 0.095 | 0.104 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
415 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
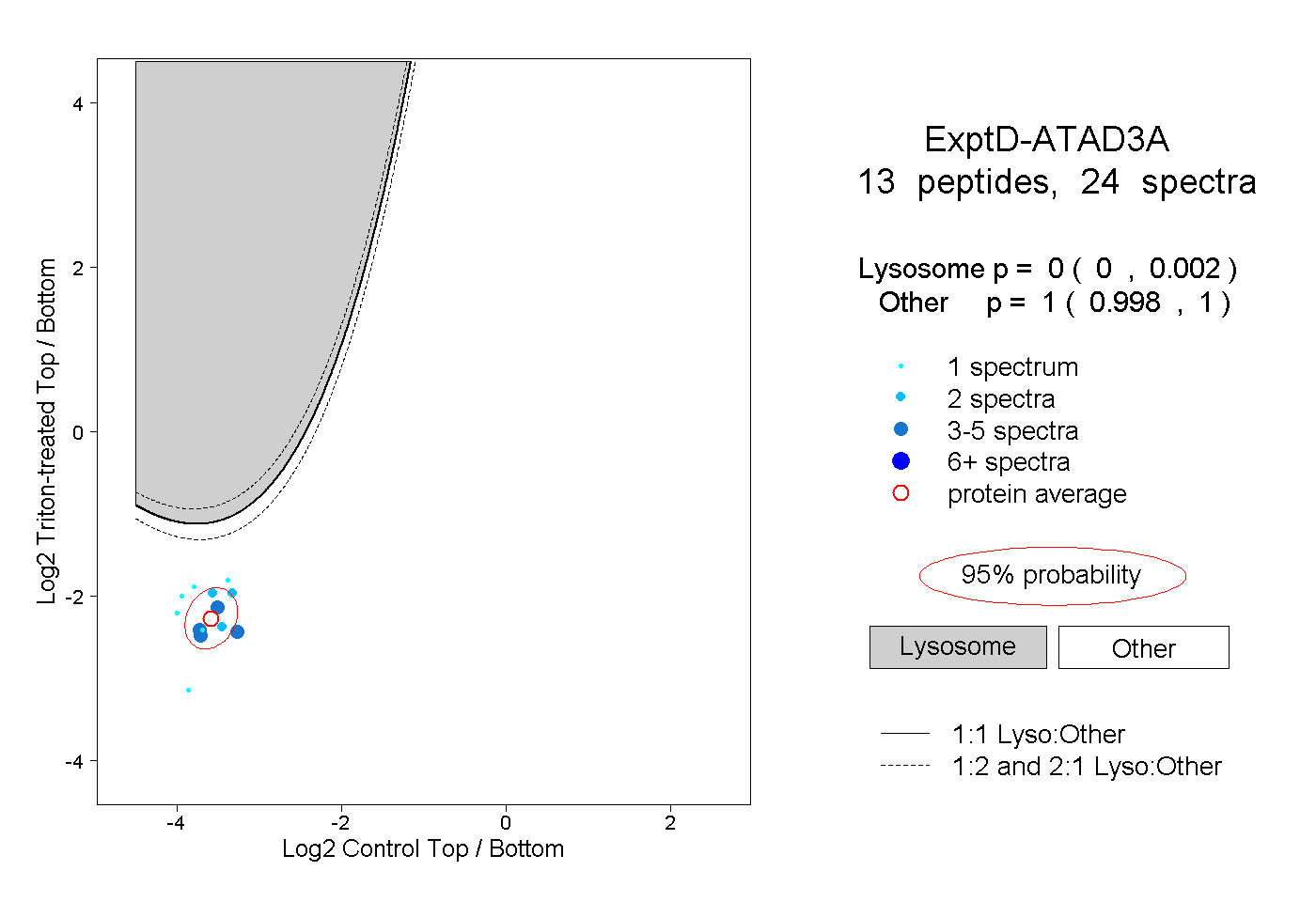 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |