STAT2
[ENSRNOP00000046028]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 22
22
peptides |
62
spectra |
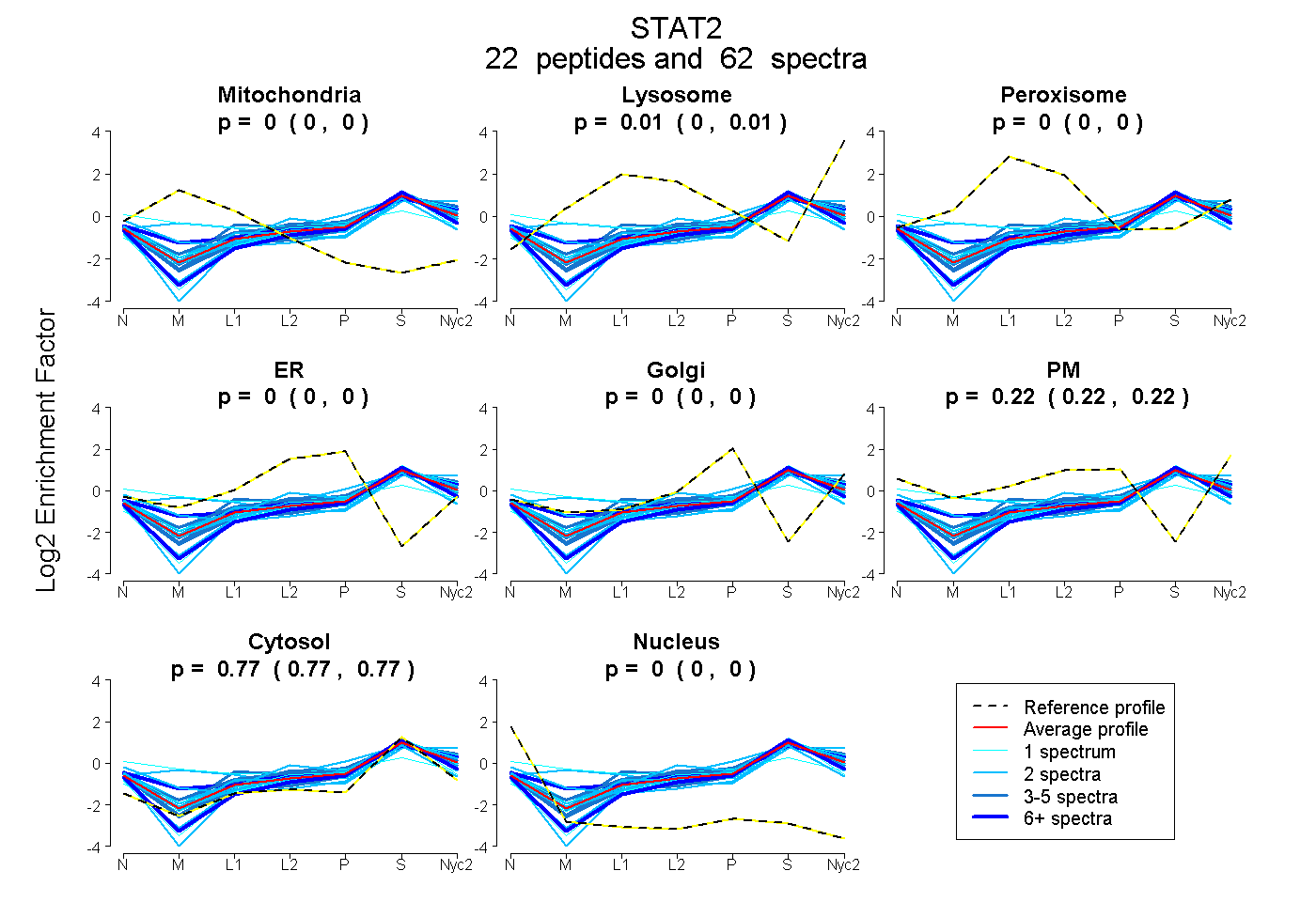 |
0.000
0.000 | 0.000 |
0.009
0.005 | 0.013 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.220
0.217 | 0.222 |
0.771
0.768 | 0.774 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 9
9
peptides |
19
spectra |
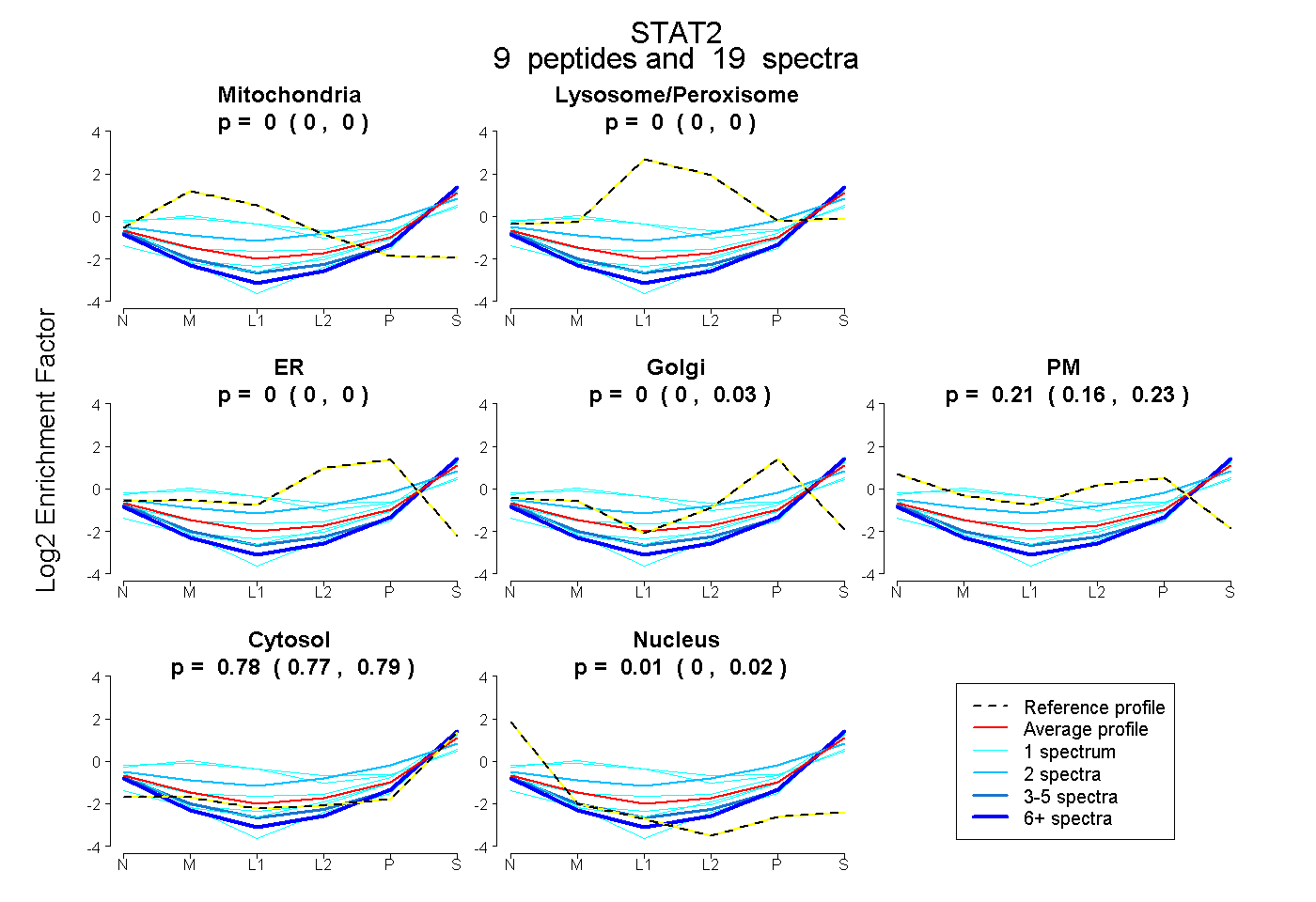 |
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.031 |
0.213
0.162 | 0.228 |
0.779
0.766 | 0.789 |
0.008
0.000 | 0.023 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 18
18
peptides |
54
spectra |
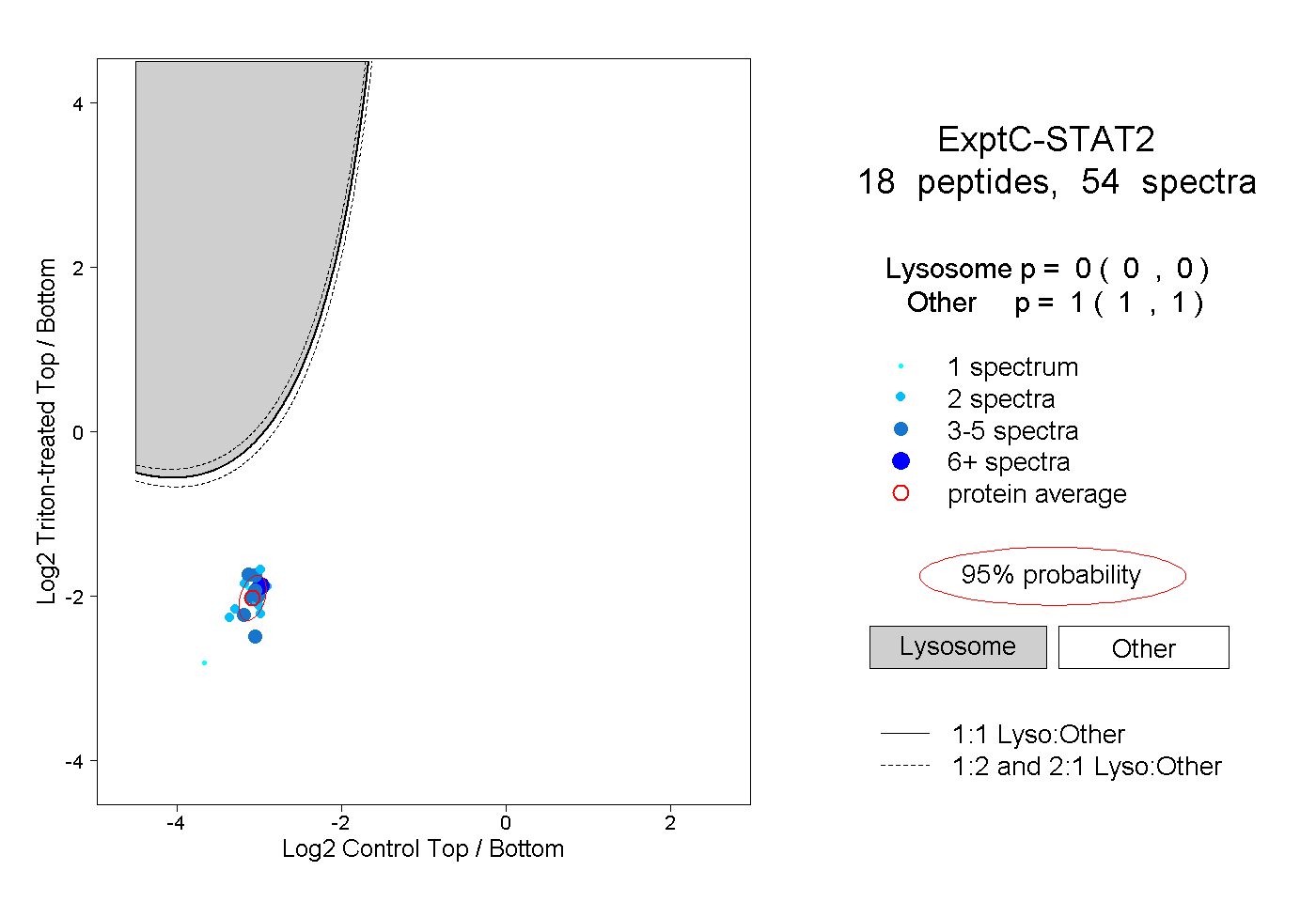 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 4 spectra, SLTPEEGQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IMGFVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VNLEER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VLFHLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DEAFGCYYQEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LQEGNESLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FNILTSNQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EVLDISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ESPPGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AEVSIDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DVQDVFSFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ILNQAQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LIVISNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GLDPEQLGMLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QLVQTTANELDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EVLQSLPLTEIIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SVGAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ILDLQTAVEALVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 4
4
peptides |
11
spectra |
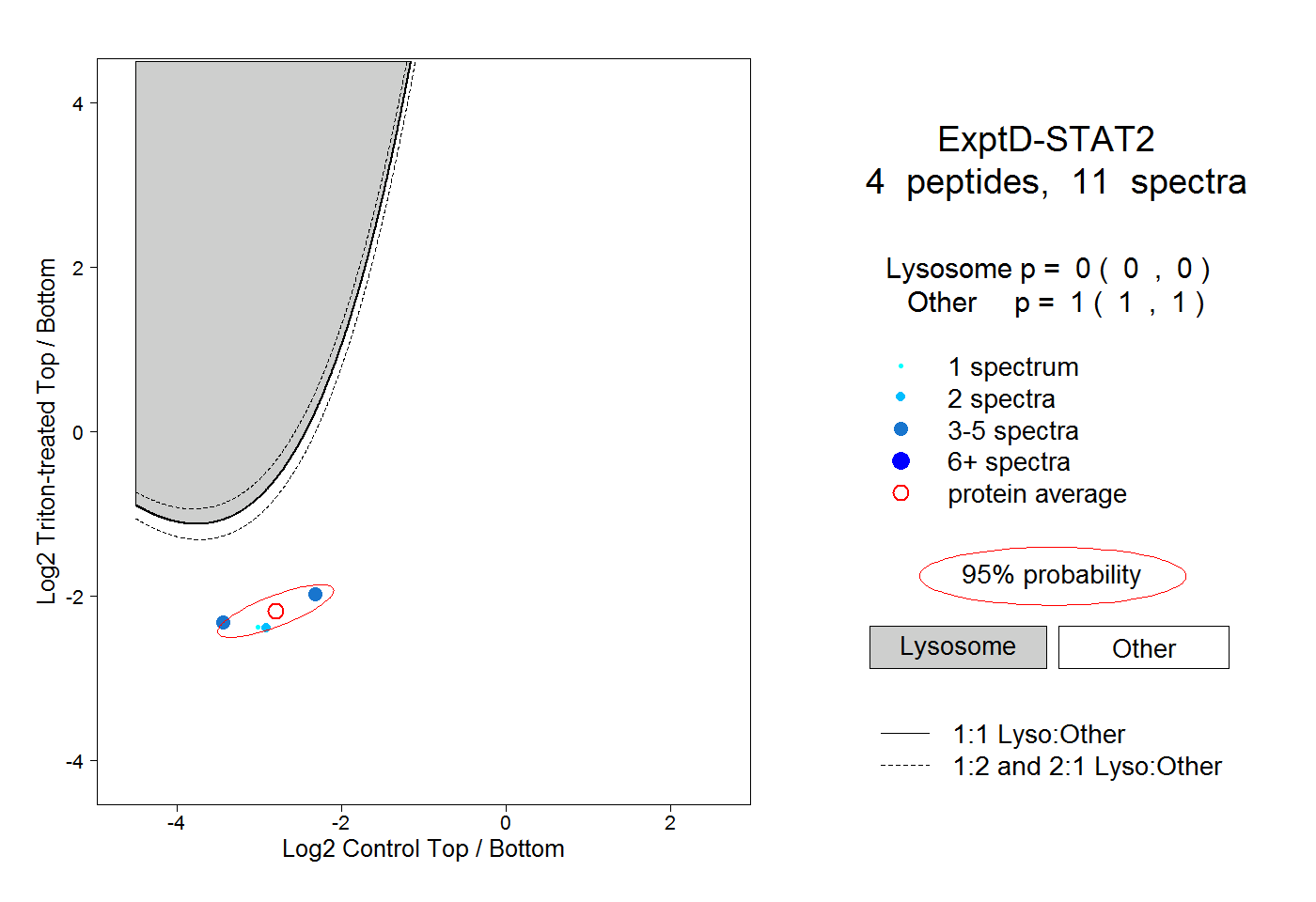 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |



