peptides
spectra
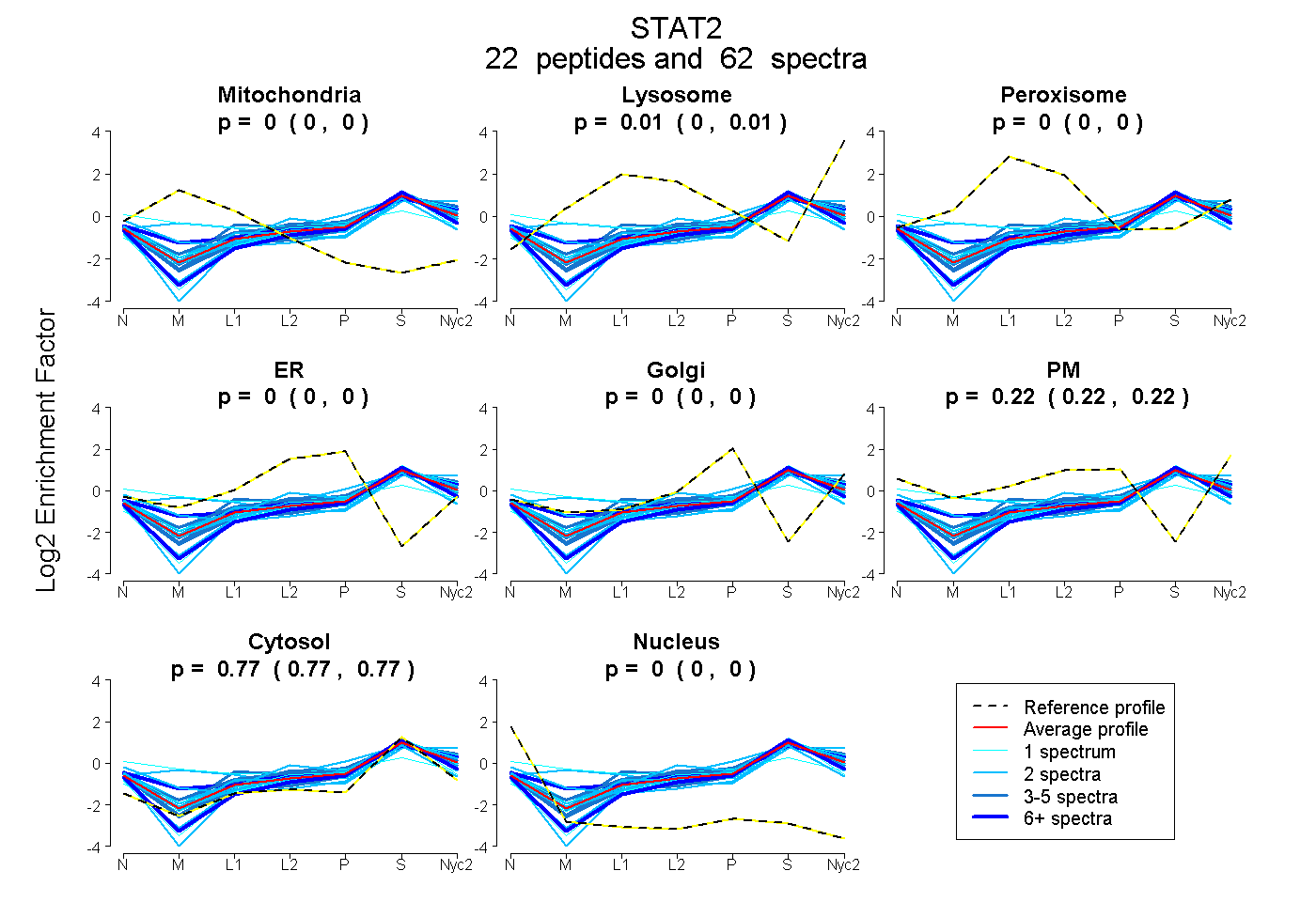
0.000 | 0.000
0.005 | 0.013
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.217 | 0.222
0.768 | 0.774
0.000 | 0.000
peptides
spectra
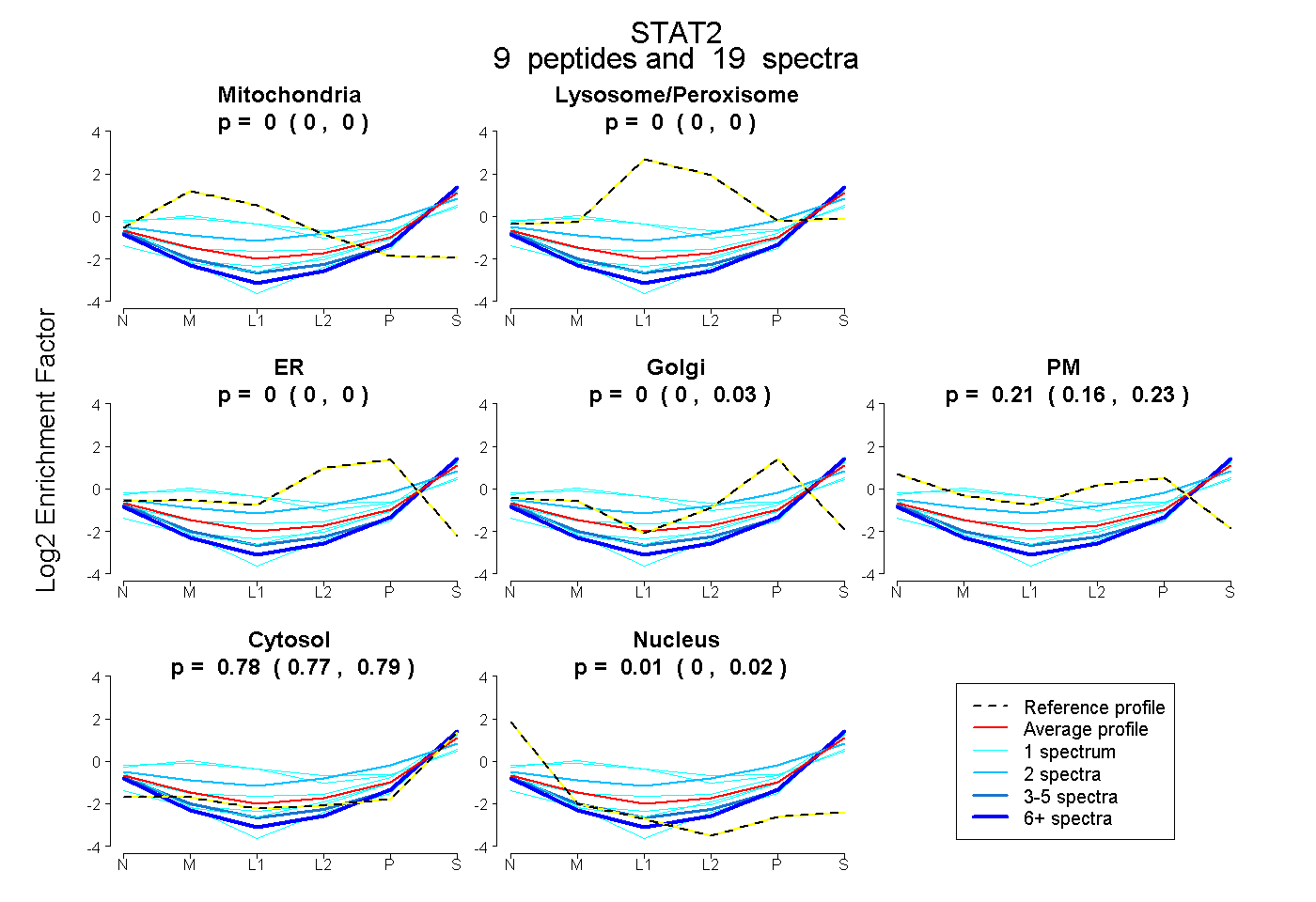
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.031
0.162 | 0.228
0.766 | 0.789
0.000 | 0.023
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
62 spectra |
 |
0.000 0.000 | 0.000 |
0.009 0.005 | 0.013 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.220 0.217 | 0.222 |
0.771 0.768 | 0.774 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.031 |
0.213 0.162 | 0.228 |
0.779 0.766 | 0.789 |
0.008 0.000 | 0.023 |
| 1 spectrum, IMGFVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.940 | 0.060 | |||
| 2 spectra, VNLEER | 0.000 | 0.196 | 0.000 | 0.151 | 0.134 | 0.519 | 0.000 | |||
| 7 spectra, VLFHLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.866 | 0.134 | |||
| 1 spectrum, HYQVLAEENAPENPLR | 0.149 | 0.208 | 0.000 | 0.000 | 0.204 | 0.439 | 0.000 | |||
| 1 spectrum, DVQDVFSFR | 0.000 | 0.000 | 0.000 | 0.099 | 0.000 | 0.840 | 0.062 | |||
| 4 spectra, ILNQAQR | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.867 | 0.114 | |||
| 1 spectrum, LIVISNR | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | 0.807 | 0.093 | |||
| 1 spectrum, GLDPEQLGMLR | 0.000 | 0.073 | 0.000 | 0.034 | 0.140 | 0.754 | 0.000 | |||
| 1 spectrum, QLVQTTANELDR | 0.140 | 0.240 | 0.000 | 0.000 | 0.221 | 0.399 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
54 spectra |
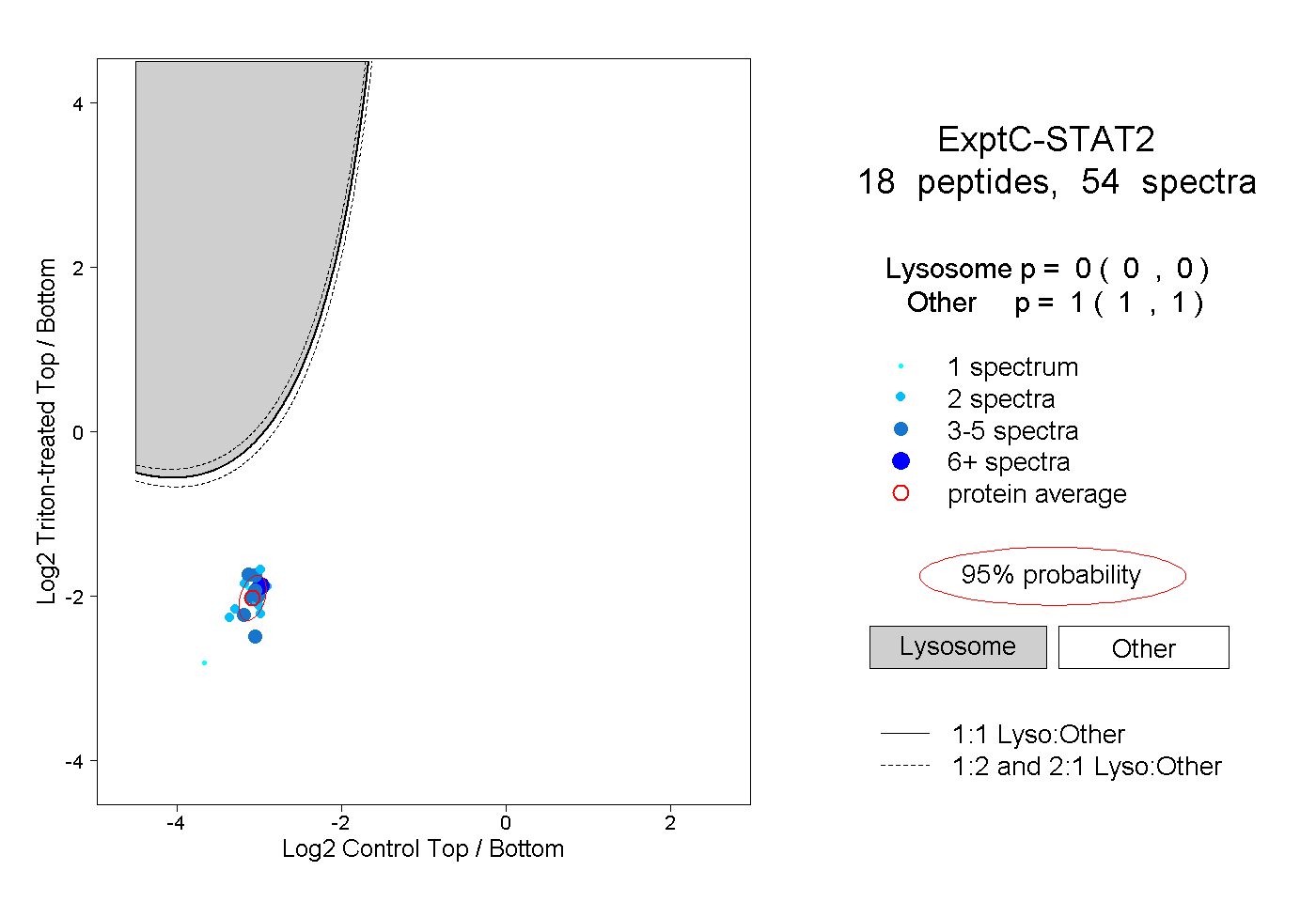 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
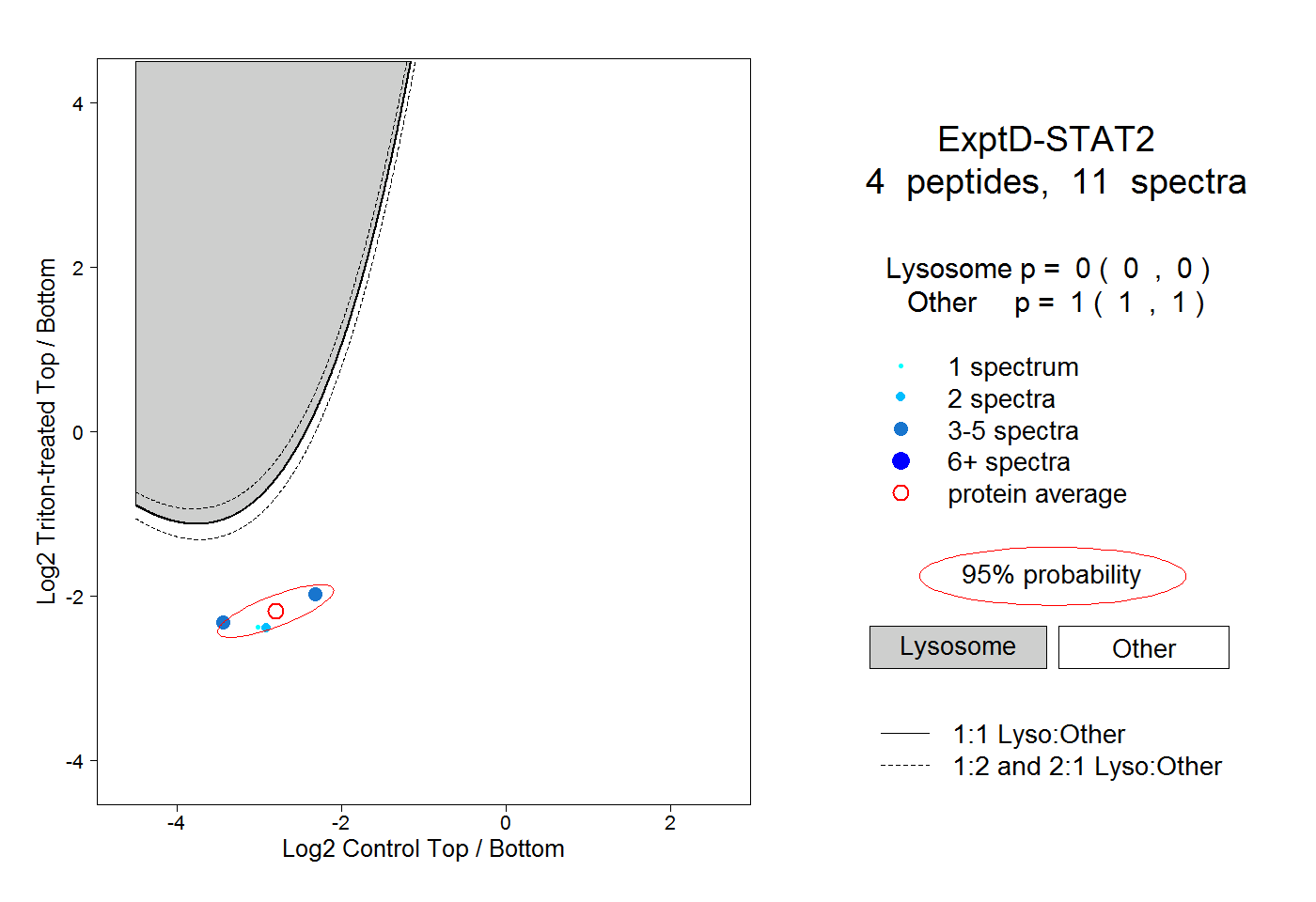 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |