peptides
spectra
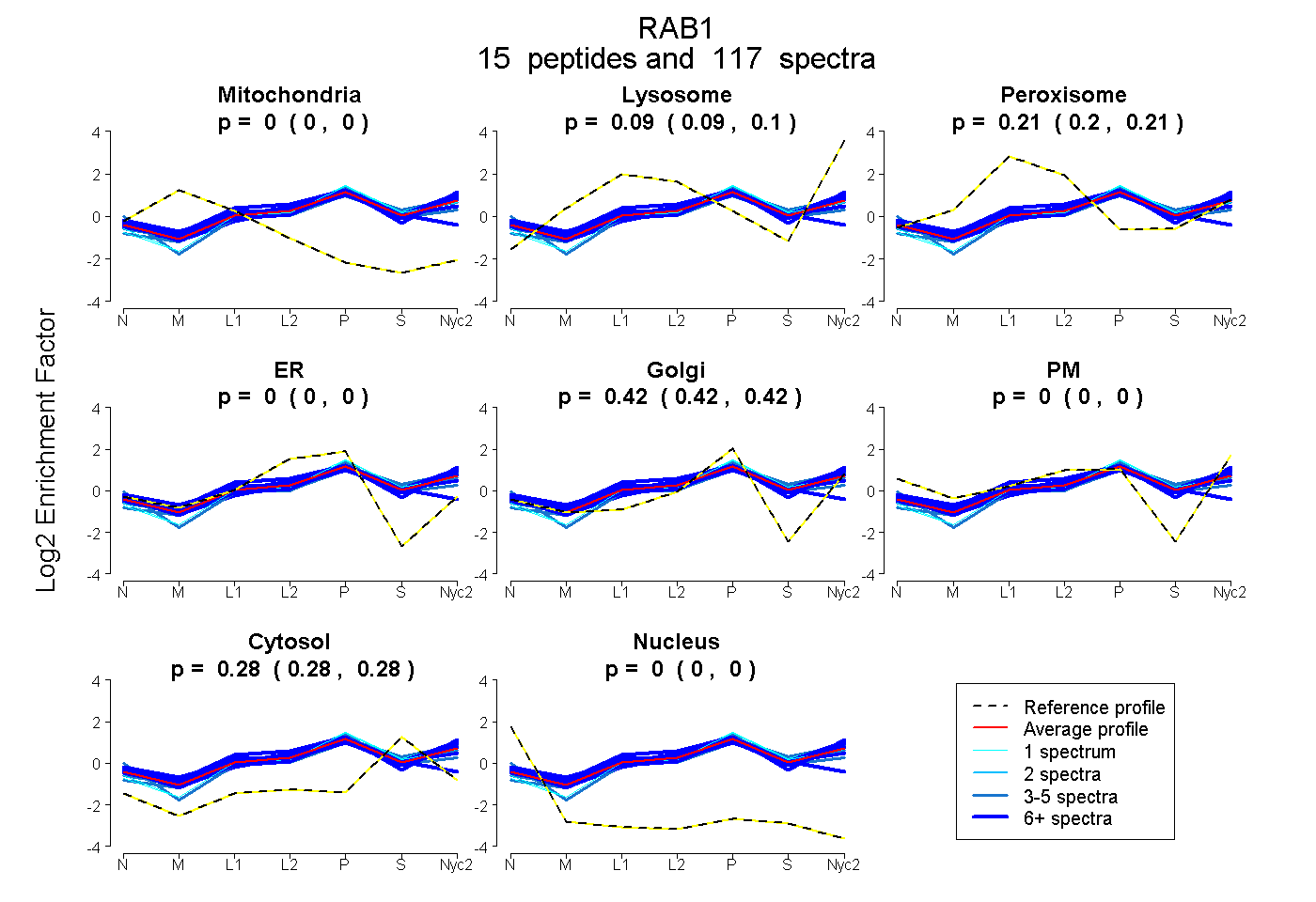
0.000 | 0.000
0.088 | 0.100
0.201 | 0.211
0.000 | 0.000
0.417 | 0.421
0.000 | 0.000
0.278 | 0.281
0.000 | 0.000
peptides
spectra
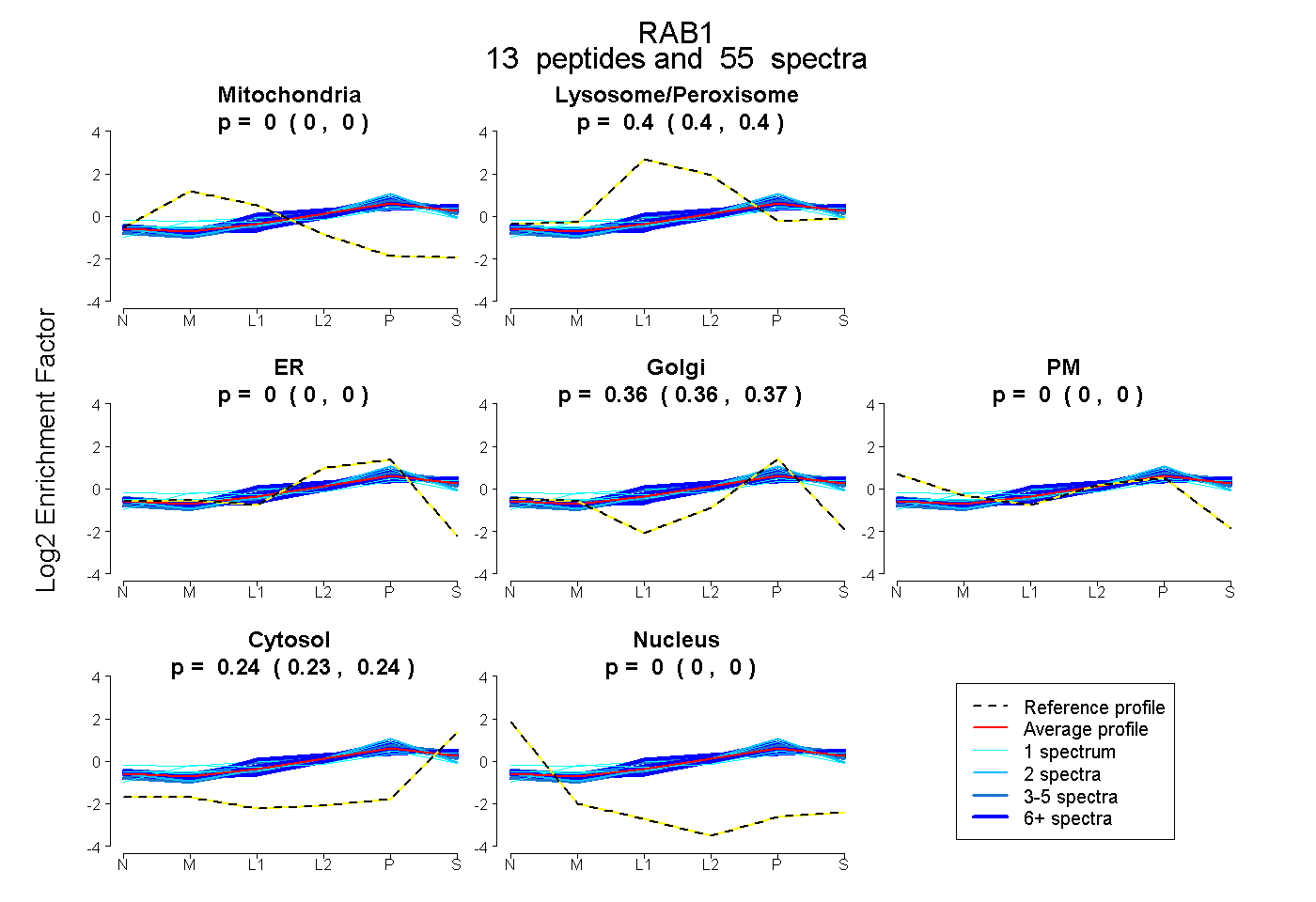
0.000 | 0.000
0.397 | 0.403
0.000 | 0.000
0.359 | 0.365
0.000 | 0.000
0.235 | 0.240
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
117 spectra |
 |
0.000 0.000 | 0.000 |
0.094 0.088 | 0.100 |
0.207 0.201 | 0.211 |
0.000 0.000 | 0.000 |
0.419 0.417 | 0.421 |
0.000 0.000 | 0.000 |
0.280 0.278 | 0.281 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
55 spectra |
 |
0.000 0.000 | 0.000 |
0.400 0.397 | 0.403 |
0.000 0.000 | 0.000 |
0.362 0.359 | 0.365 |
0.000 0.000 | 0.000 |
0.238 0.235 | 0.240 |
0.000 0.000 | 0.000 |
| 1 spectrum, YASENVNK | 0.000 | 0.399 | 0.000 | 0.302 | 0.000 | 0.300 | 0.000 | |||
| 9 spectra, TITSSYYR | 0.000 | 0.348 | 0.000 | 0.387 | 0.000 | 0.264 | 0.000 | |||
| 2 spectra, VVDYTTAK | 0.000 | 0.373 | 0.000 | 0.471 | 0.000 | 0.157 | 0.000 | |||
| 1 spectrum, MNPEYDYLFK | 0.000 | 0.406 | 0.000 | 0.455 | 0.000 | 0.139 | 0.000 | |||
| 5 spectra, LLLIGDSGVGK | 0.000 | 0.413 | 0.000 | 0.339 | 0.000 | 0.248 | 0.000 | |||
| 6 spectra, EFADSLGIPFLETSAK | 0.000 | 0.318 | 0.114 | 0.333 | 0.000 | 0.236 | 0.000 | |||
| 8 spectra, LQIWDTAGQER | 0.000 | 0.488 | 0.000 | 0.249 | 0.000 | 0.262 | 0.000 | |||
| 4 spectra, QWLQEIDR | 0.000 | 0.369 | 0.000 | 0.357 | 0.000 | 0.273 | 0.000 | |||
| 5 spectra, MGPGATAGGAEK | 0.000 | 0.357 | 0.000 | 0.389 | 0.000 | 0.253 | 0.000 | |||
| 1 spectrum, TIELDGK | 0.000 | 0.378 | 0.000 | 0.359 | 0.000 | 0.262 | 0.000 | |||
| 8 spectra, SCLLLR | 0.000 | 0.432 | 0.000 | 0.273 | 0.000 | 0.295 | 0.000 | |||
| 1 spectrum, IQSTPVK | 0.000 | 0.410 | 0.000 | 0.345 | 0.079 | 0.167 | 0.000 | |||
| 4 spectra, ILVGNK | 0.000 | 0.446 | 0.000 | 0.369 | 0.000 | 0.185 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
220 spectra |
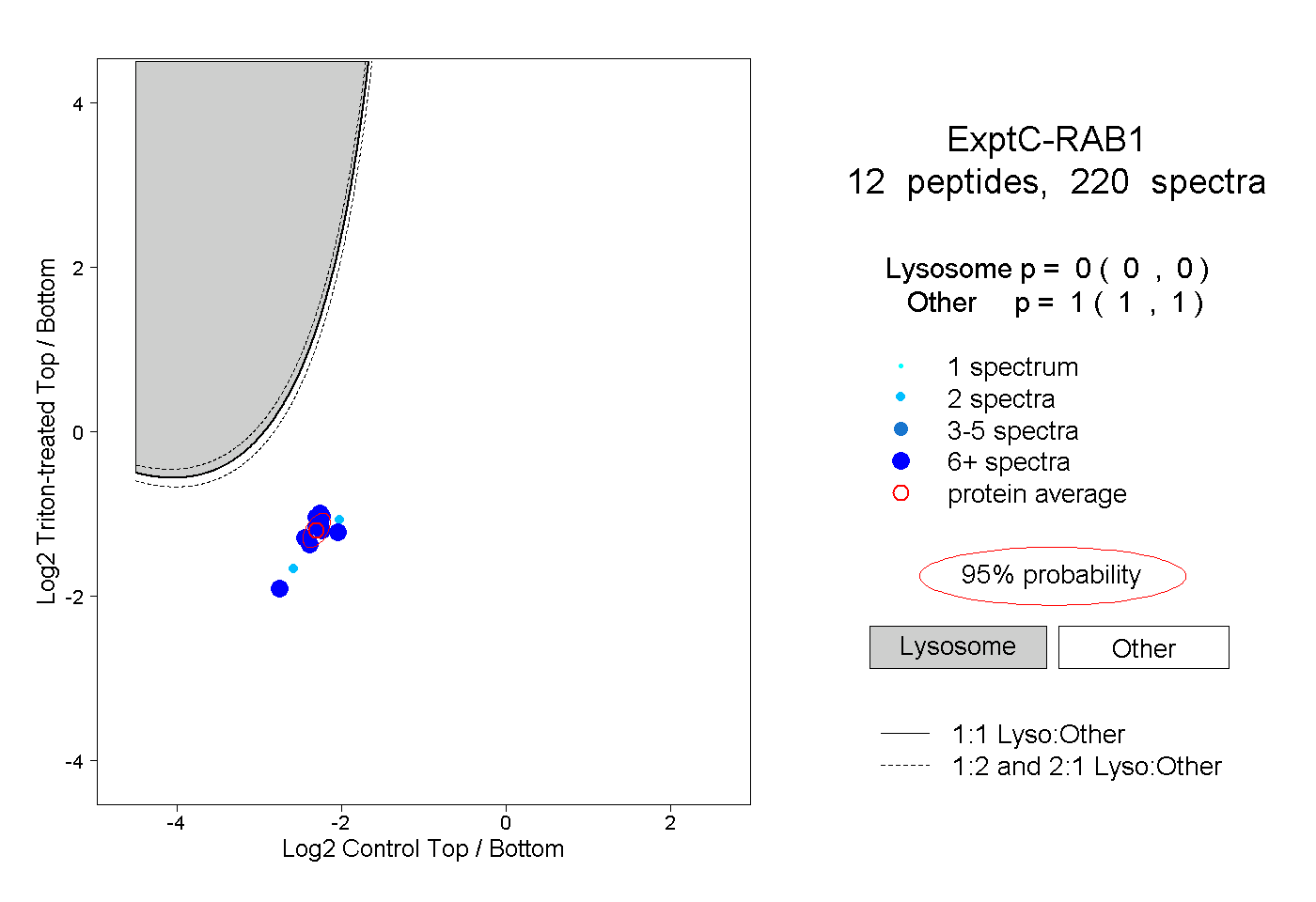 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
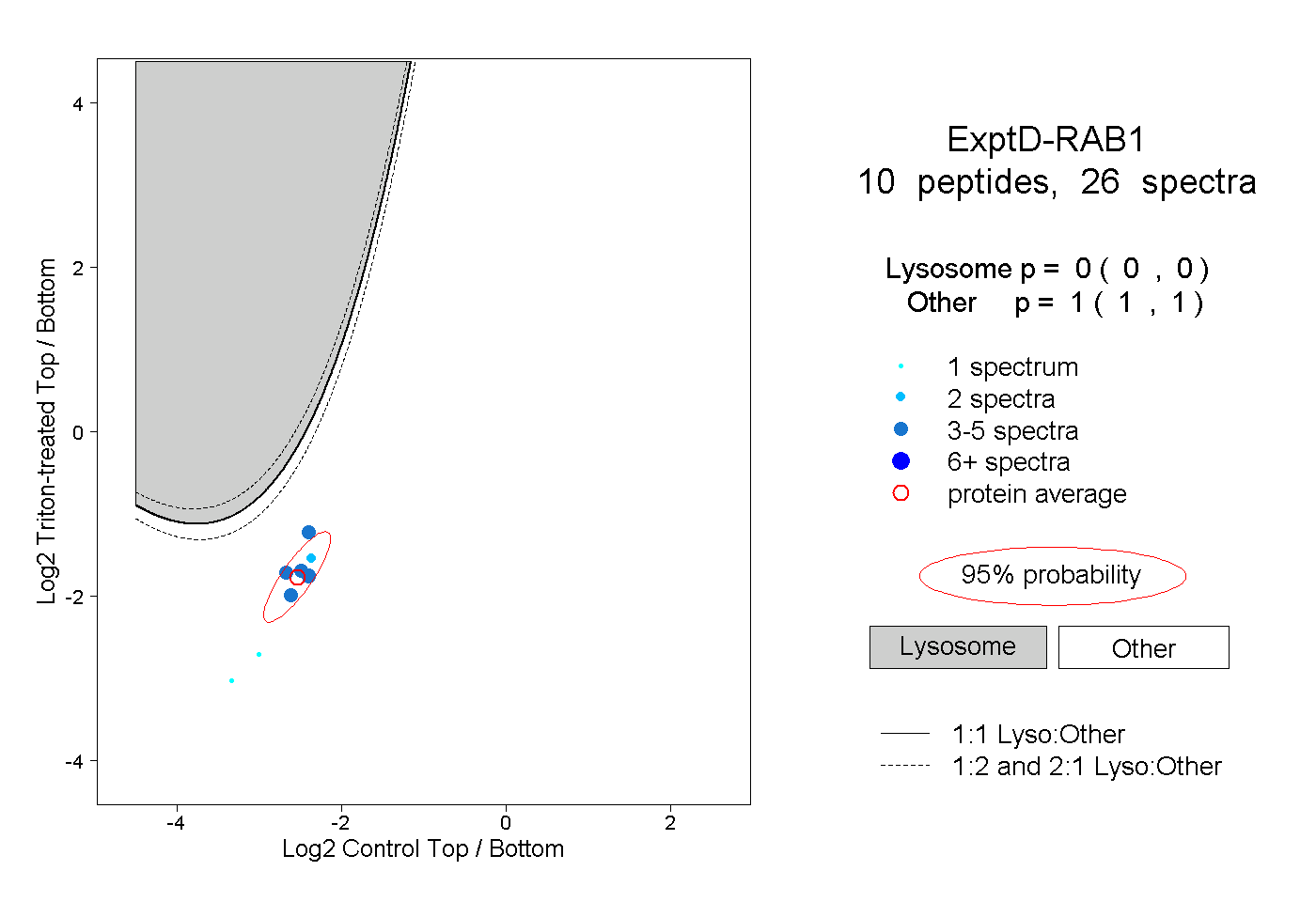 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |