peptides
spectra
0.000 | 0.000
0.121 | 0.144
0.000 | 0.000
0.000 | 0.010
0.033 | 0.058
0.000 | 0.000
0.809 | 0.822
0.000 | 0.000
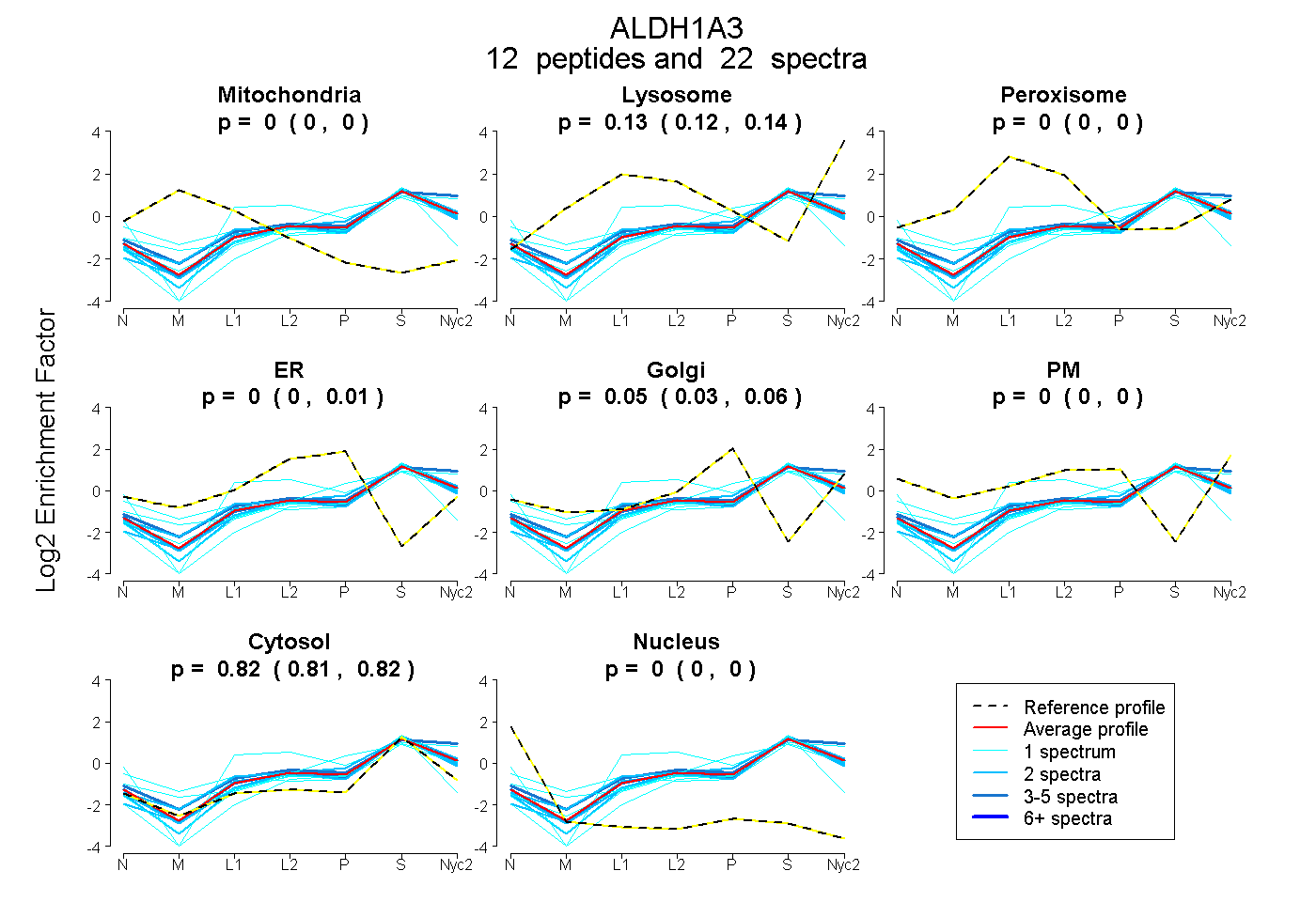
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.134 0.121 | 0.144 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.010 |
0.050 0.033 | 0.058 |
0.000 0.000 | 0.000 |
0.816 0.809 | 0.822 |
0.000 0.000 | 0.000 |
| 1 spectrum, IAFTGSTEVGK | 0.000 | 0.081 | 0.000 | 0.000 | 0.011 | 0.000 | 0.908 | 0.000 | ||
| 2 spectra, AVEAAQAAFQR | 0.000 | 0.075 | 0.000 | 0.000 | 0.046 | 0.000 | 0.879 | 0.000 | ||
| 1 spectrum, TIPTDDNVMCFTR | 0.000 | 0.131 | 0.000 | 0.000 | 0.026 | 0.000 | 0.843 | 0.000 | ||
| 3 spectra, TEQGPQIDQK | 0.000 | 0.273 | 0.000 | 0.000 | 0.010 | 0.000 | 0.718 | 0.000 | ||
| 1 spectrum, VFVEEQVYGEFVR | 0.000 | 0.071 | 0.000 | 0.000 | 0.282 | 0.000 | 0.647 | 0.000 | ||
| 5 spectra, GQLLHQLADLIER | 0.000 | 0.138 | 0.000 | 0.000 | 0.024 | 0.000 | 0.838 | 0.000 | ||
| 1 spectrum, ICEVEEGDKPDVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, VTLELGGR | 0.000 | 0.152 | 0.045 | 0.000 | 0.000 | 0.000 | 0.803 | 0.000 | ||
| 1 spectrum, FATYNPSTLEK | 0.000 | 0.073 | 0.067 | 0.000 | 0.000 | 0.152 | 0.707 | 0.000 | ||
| 2 spectra, LECGGSAMEDR | 0.000 | 0.061 | 0.000 | 0.024 | 0.094 | 0.000 | 0.821 | 0.000 | ||
| 1 spectrum, ILELIESGK | 0.000 | 0.085 | 0.126 | 0.000 | 0.000 | 0.160 | 0.629 | 0.000 | ||
| 2 spectra, GLFIKPTVFSDVTDNMR | 0.000 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | 0.843 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
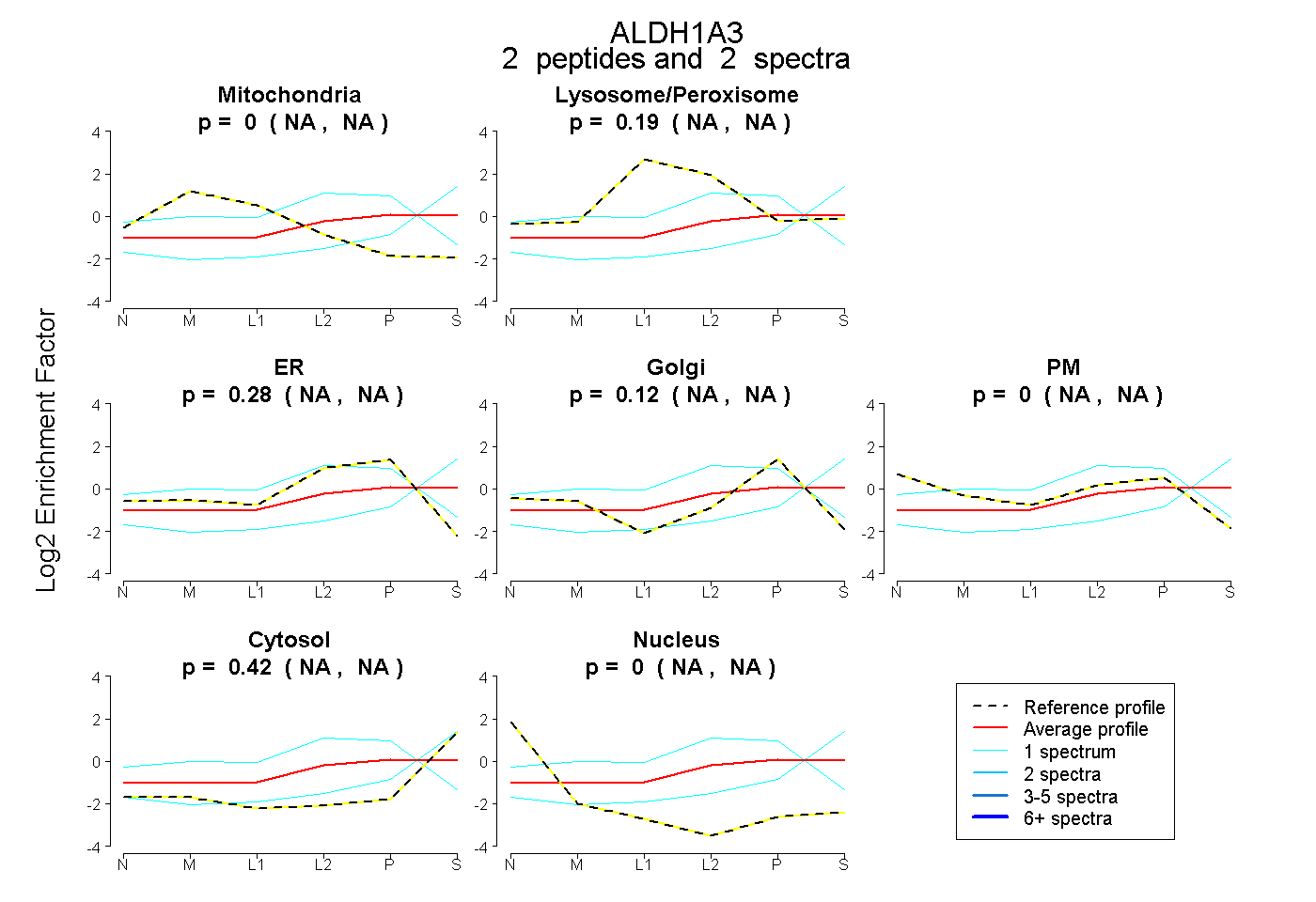 |
0.000 NA | NA |
0.188 NA | NA |
0.275 NA | NA |
0.122 NA | NA |
0.000 NA | NA |
0.416 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
15 spectra |
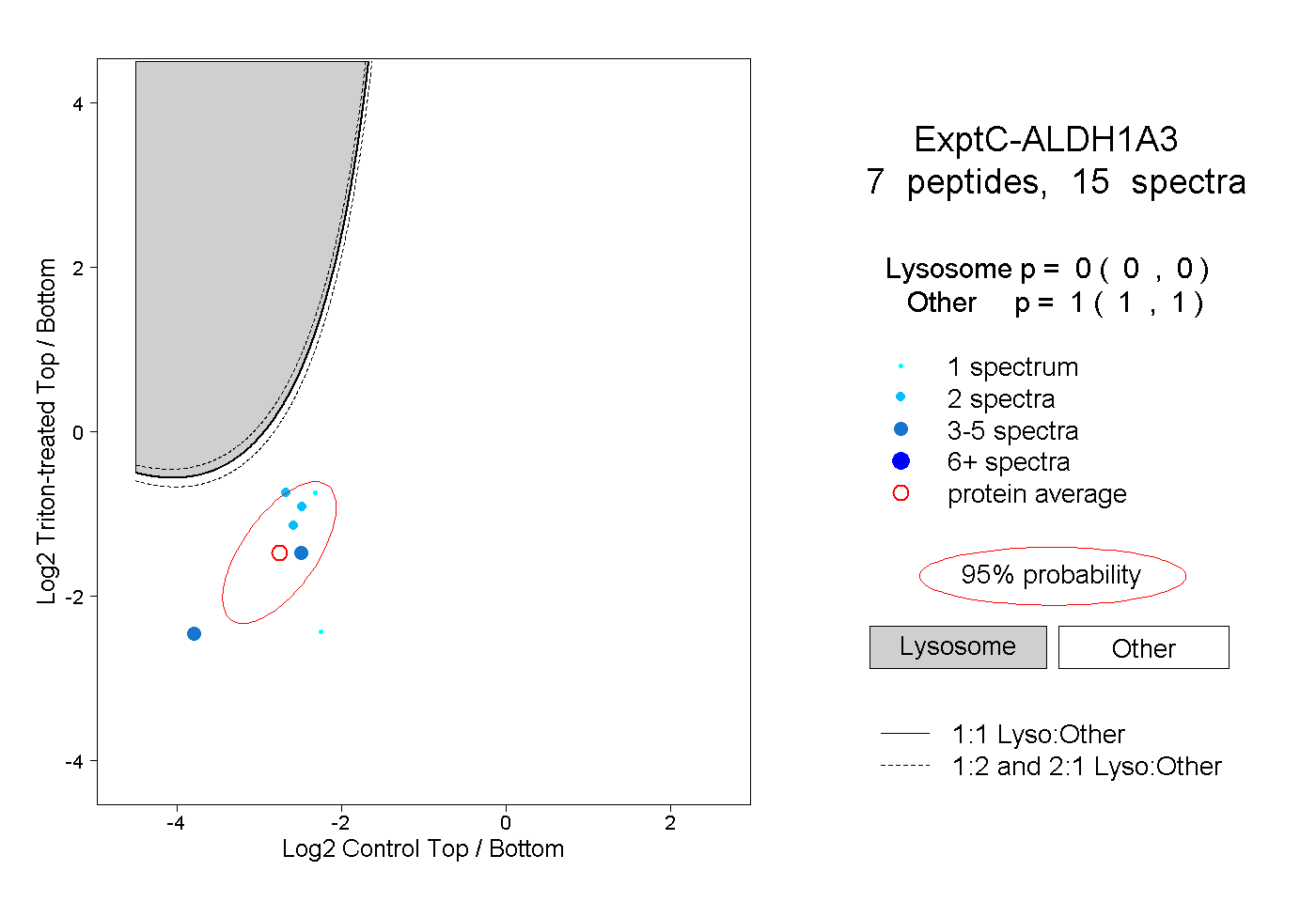 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |