peptides
spectra
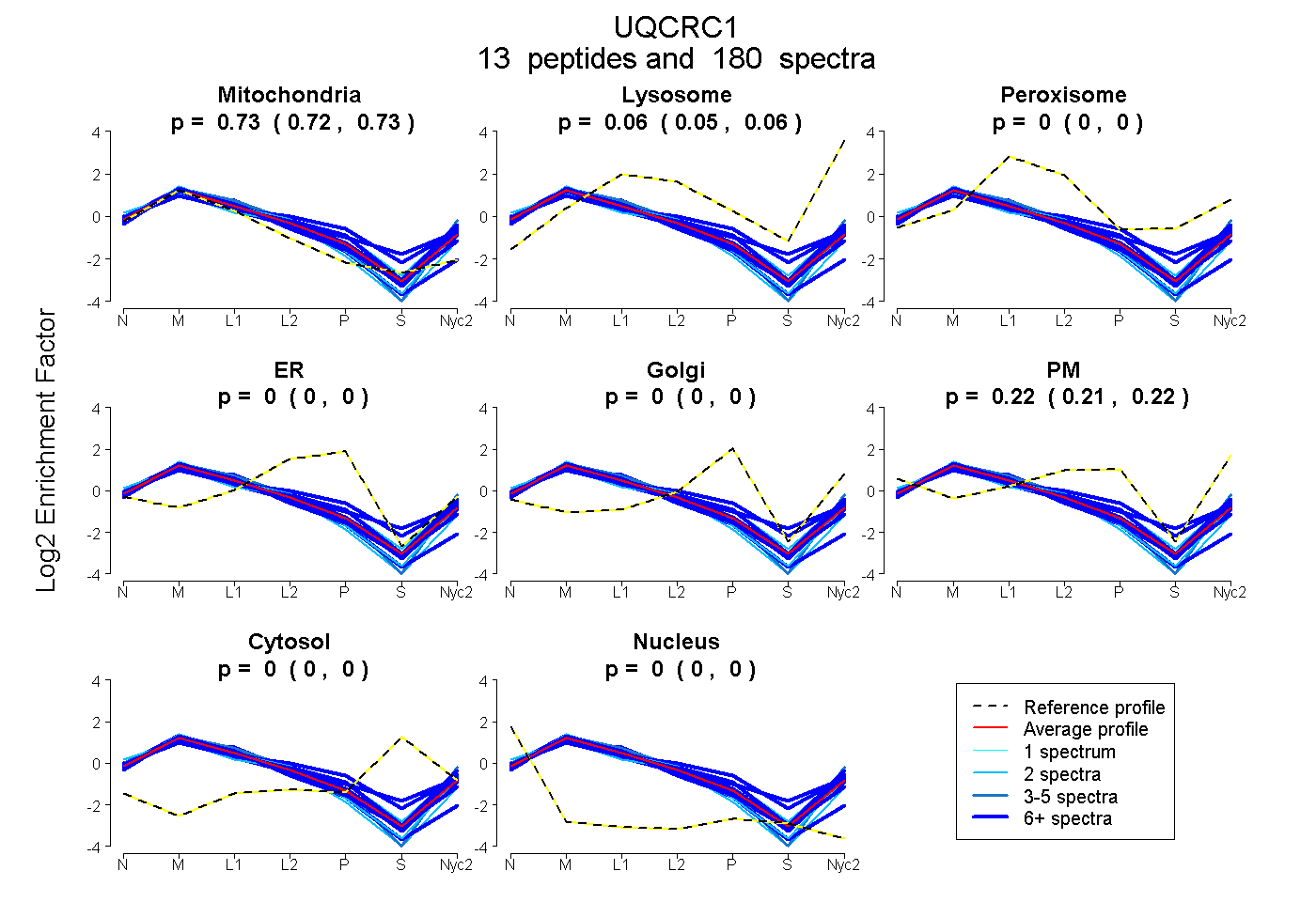
0.724 | 0.729
0.055 | 0.061
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.211 | 0.218
0.000 | 0.000
0.000 | 0.000
peptides
spectra
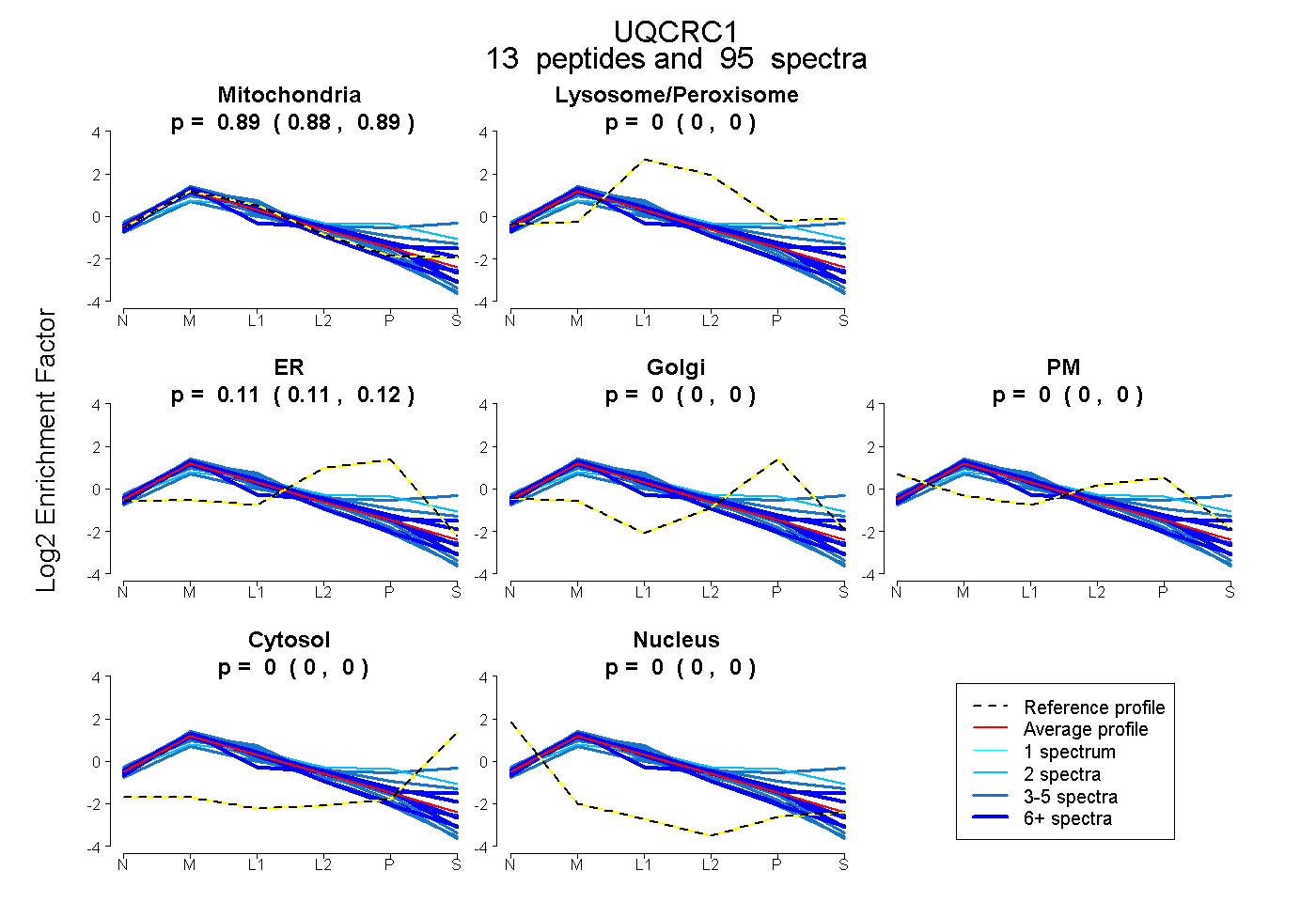
0.881 | 0.890
0.000 | 0.000
0.110 | 0.118
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
180 spectra |
 |
0.727 0.724 | 0.729 |
0.058 0.055 | 0.061 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.215 0.211 | 0.218 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
95 spectra |
 |
0.886 0.881 | 0.890 |
0.000 0.000 | 0.000 |
0.114 0.110 | 0.118 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 11 spectra, NALISHLDGTTPVCEDIGR | 0.812 | 0.080 | 0.000 | 0.054 | 0.022 | 0.032 | 0.000 | |||
| 5 spectra, MVLAAAGGVK | 0.916 | 0.000 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, FTGSEIR | 0.972 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.028 | |||
| 18 spectra, SLLTYGR | 0.974 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.026 | |||
| 5 spectra, EVESIGAHLNAYSTR | 0.645 | 0.172 | 0.000 | 0.092 | 0.076 | 0.014 | 0.000 | |||
| 3 spectra, NRPGNALEK | 0.923 | 0.000 | 0.052 | 0.000 | 0.025 | 0.000 | 0.000 | |||
| 2 spectra, NNGAGYFLEHLAFK | 0.476 | 0.267 | 0.000 | 0.246 | 0.000 | 0.011 | 0.000 | |||
| 13 spectra, TDLTDYLSR | 0.876 | 0.000 | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, SGMFWLR | 0.836 | 0.000 | 0.064 | 0.100 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, IEEVDAQMVR | 0.827 | 0.000 | 0.160 | 0.013 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, EHTAYLIK | 0.379 | 0.253 | 0.000 | 0.174 | 0.000 | 0.194 | 0.000 | |||
| 4 spectra, IPLAEWESR | 0.968 | 0.000 | 0.032 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, LCTSATESEVTR | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
677 spectra |
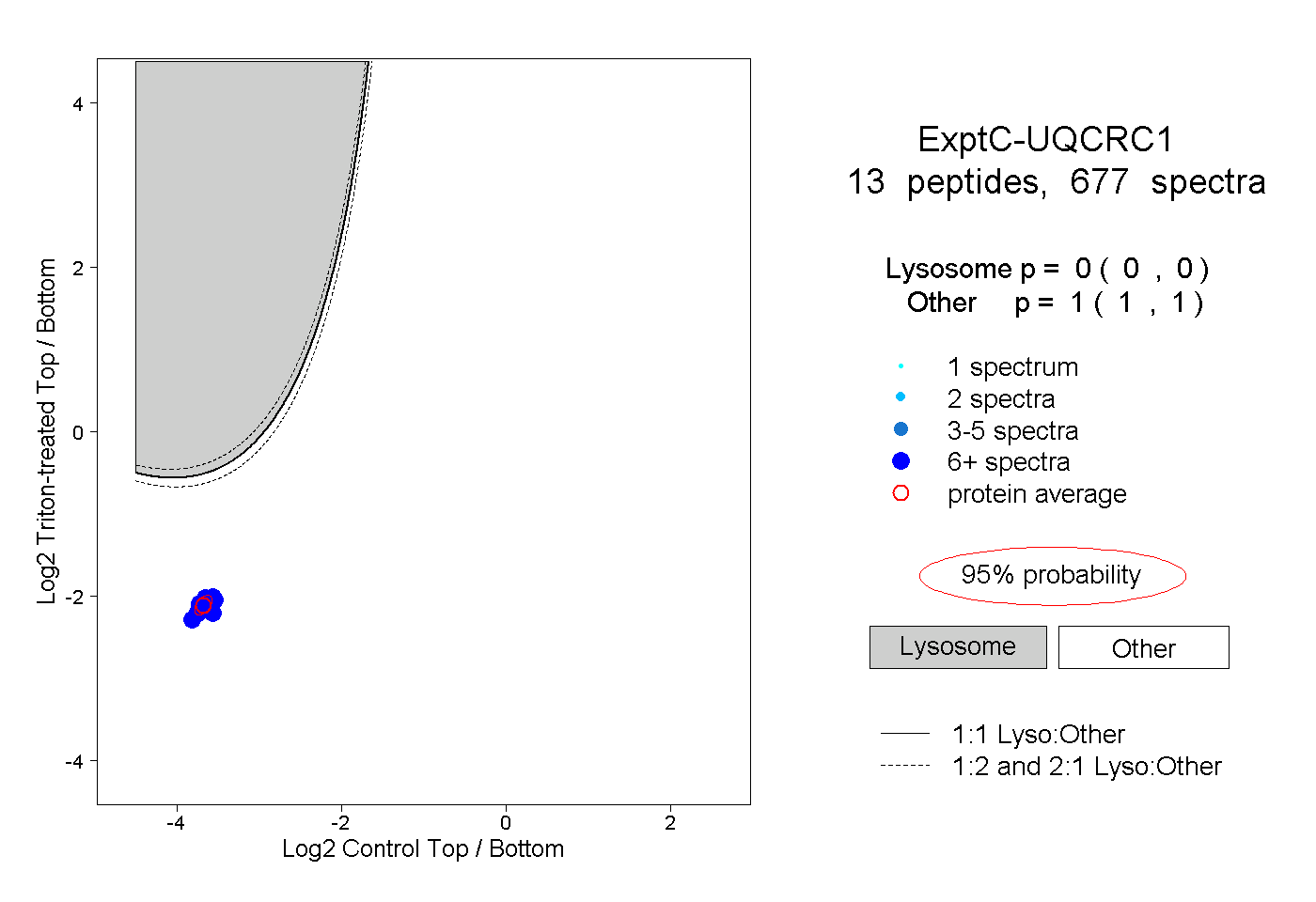 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
67 spectra |
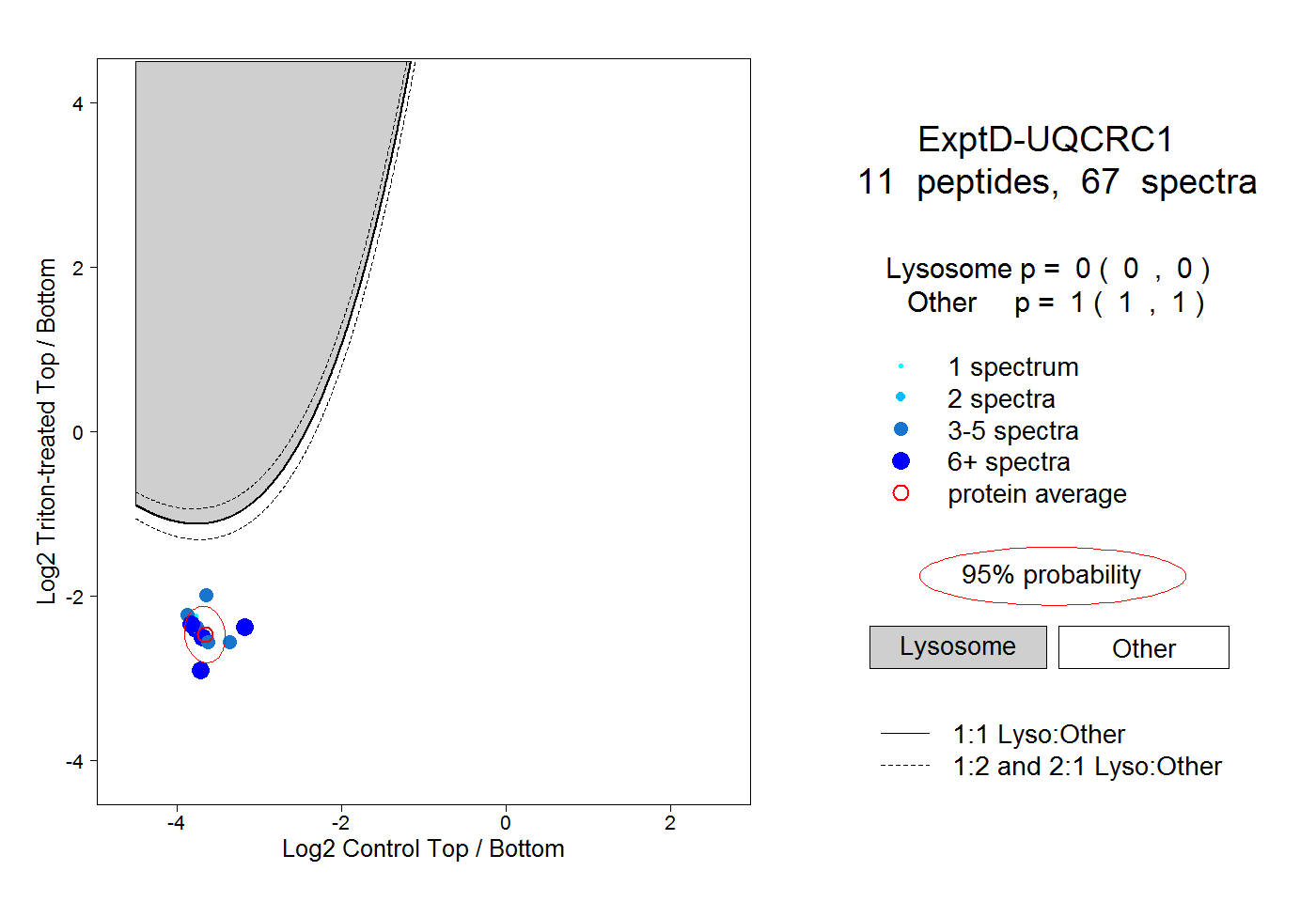 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |