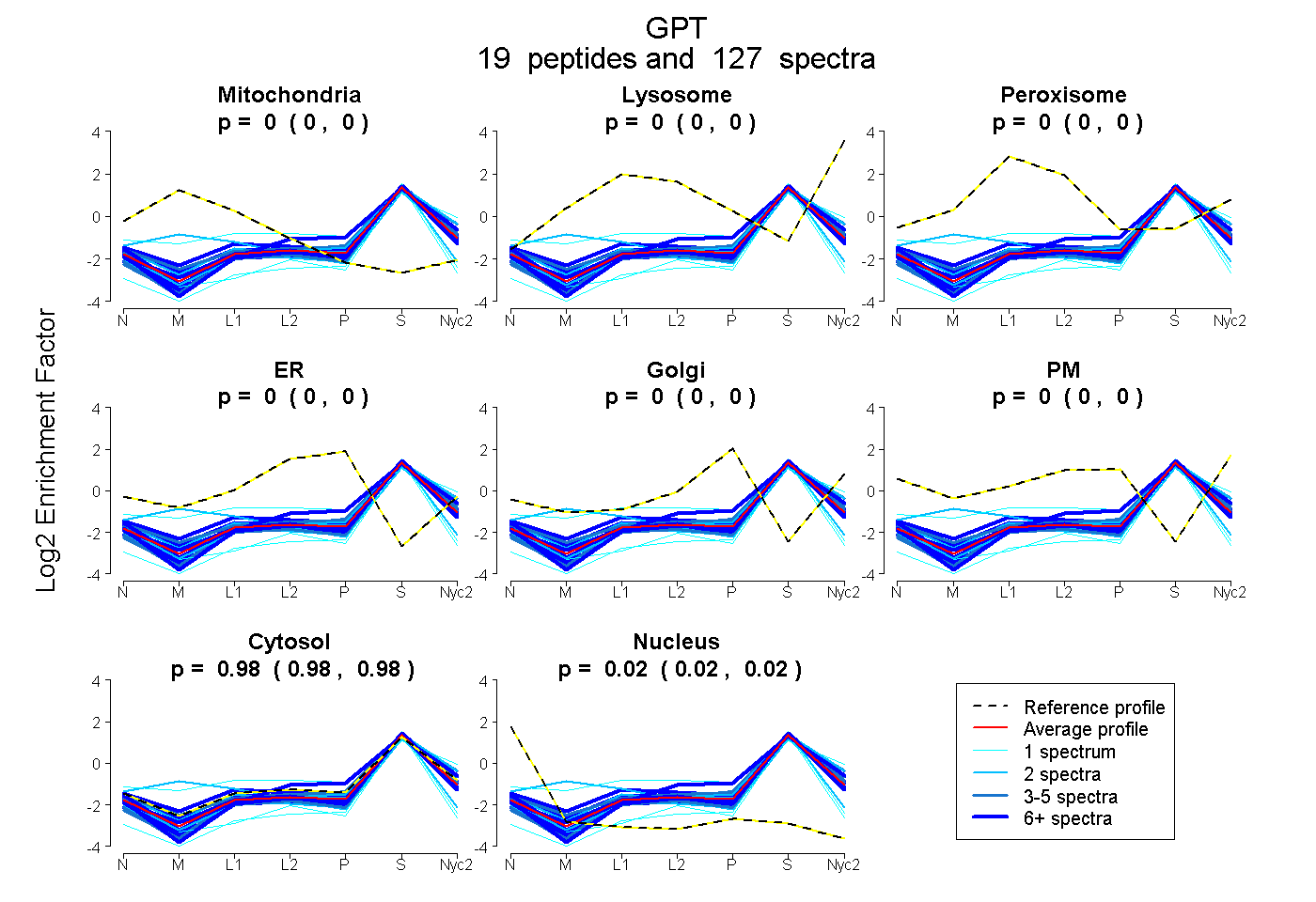
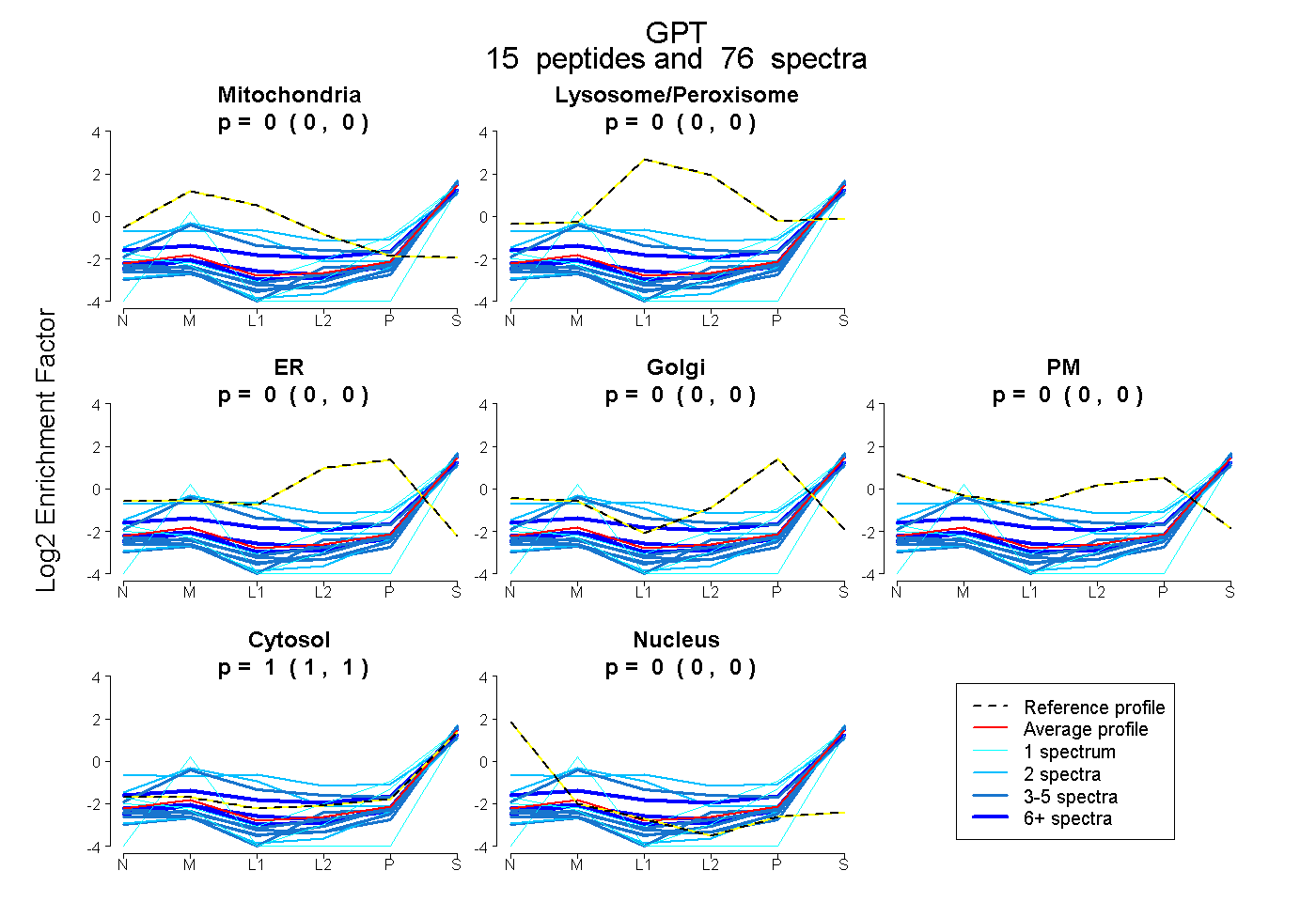
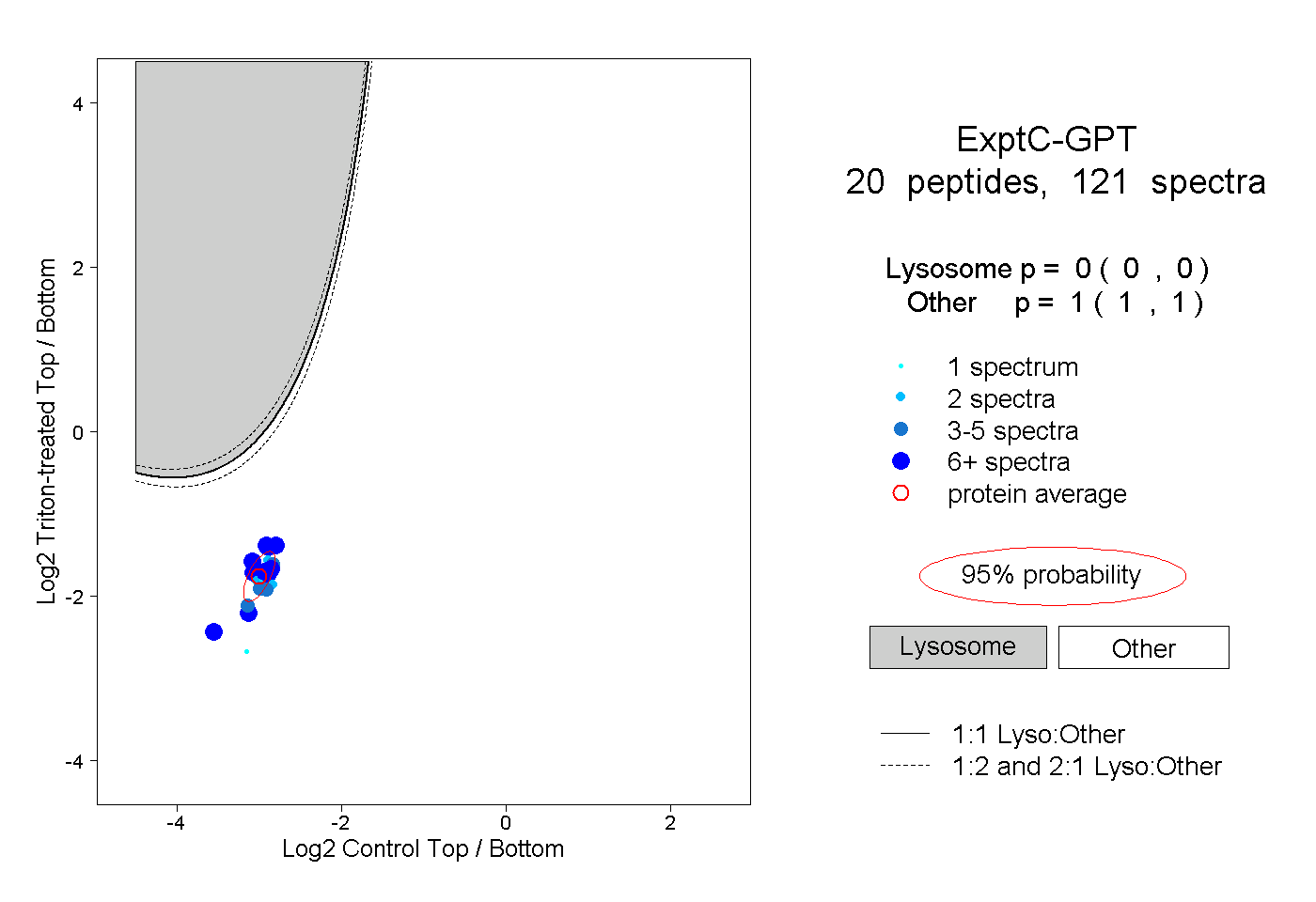
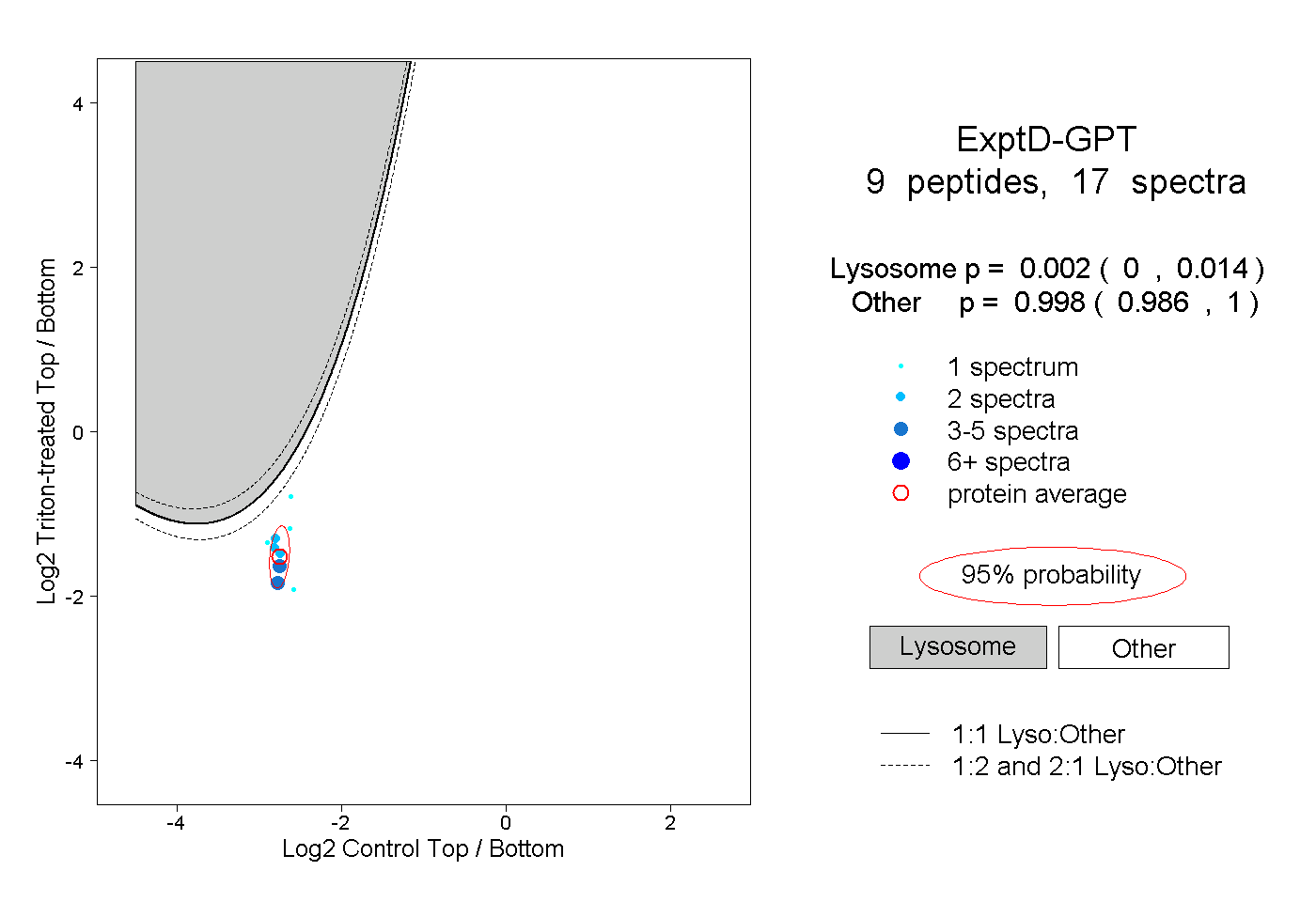
| 3 spectra, VLTLDTMNPCVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QEVLAELAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ECIEAVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, ALELEQELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, AWALDIAELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VEYAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, EDVAQYIER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FTHEYS |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, KPFTEVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ALCQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ANIGDAQAMGQRPITFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, LLVSGEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LTEQVFNEAPGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VLCVINPGNPTGQVQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GPLVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, QFQAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GGYVEVVNMDAEVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MTILPPMEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GPIVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, GYMGECGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |