peptides
spectra
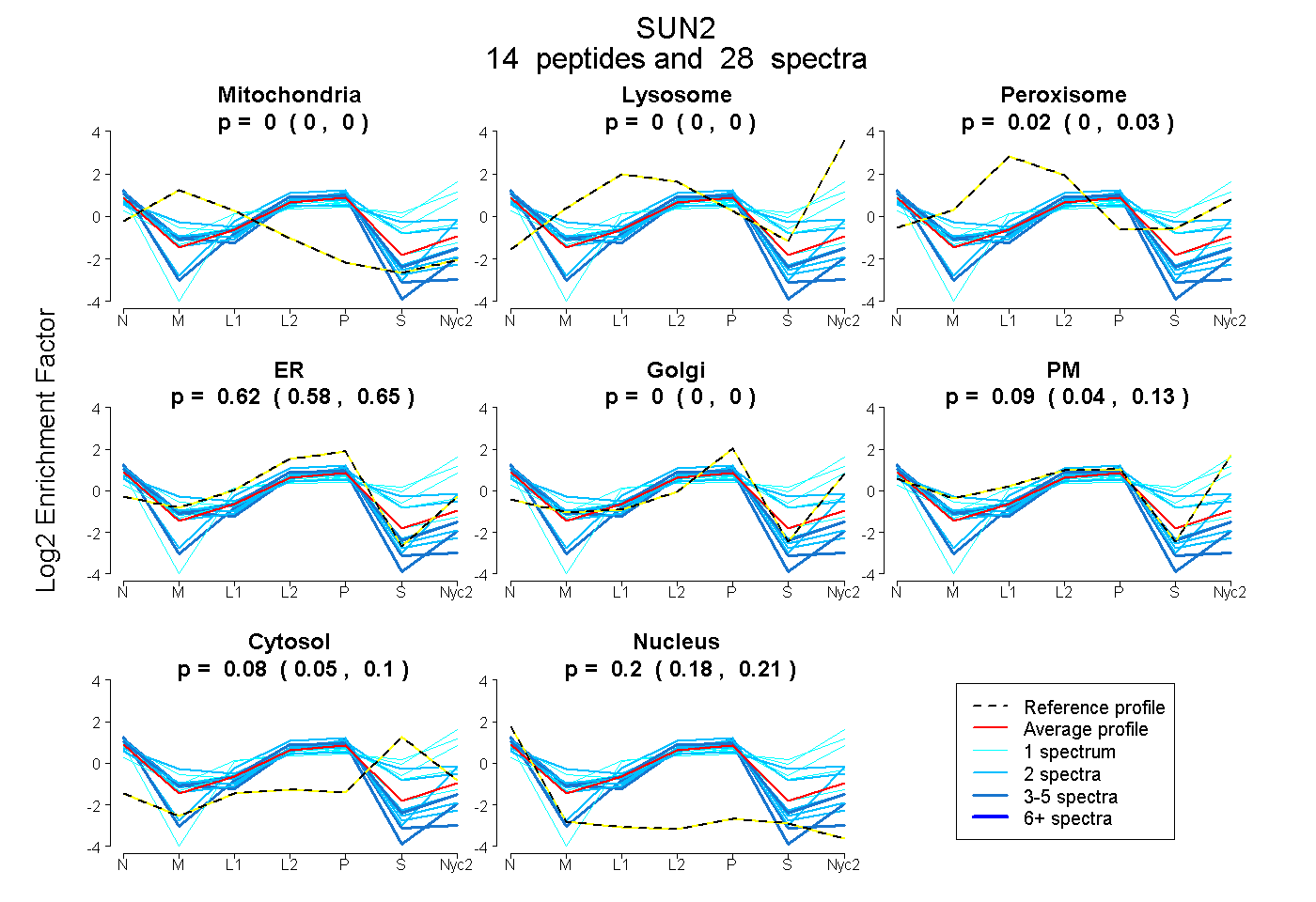
0.000 | 0.000
0.000 | 0.000
0.001 | 0.031
0.577 | 0.648
0.000 | 0.000
0.042 | 0.134
0.052 | 0.096
0.184 | 0.212
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.017 0.001 | 0.031 |
0.617 0.577 | 0.648 |
0.000 0.000 | 0.000 |
0.091 0.042 | 0.134 |
0.075 0.052 | 0.096 |
0.200 0.184 | 0.212 |
| 2 spectra, DASSHLQAEQR | 0.000 | 0.000 | 0.000 | 0.493 | 0.000 | 0.183 | 0.270 | 0.053 | ||
| 1 spectrum, EGIVGVTEEQVHR | 0.041 | 0.000 | 0.091 | 0.567 | 0.000 | 0.053 | 0.008 | 0.240 | ||
| 2 spectra, AEHHQDSEDLFK | 0.000 | 0.000 | 0.000 | 0.726 | 0.000 | 0.000 | 0.000 | 0.274 | ||
| 2 spectra, SMTQEAFQESSVK | 0.062 | 0.000 | 0.000 | 0.478 | 0.000 | 0.348 | 0.000 | 0.111 | ||
| 3 spectra, DEMHAQLQELENK | 0.000 | 0.000 | 0.000 | 0.619 | 0.000 | 0.000 | 0.000 | 0.381 | ||
| 2 spectra, IVQASQESEAR | 0.000 | 0.000 | 0.000 | 0.707 | 0.000 | 0.000 | 0.000 | 0.293 | ||
| 2 spectra, VHSLER | 0.000 | 0.000 | 0.024 | 0.214 | 0.000 | 0.361 | 0.381 | 0.020 | ||
| 1 spectrum, SGLLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.666 | 0.334 | 0.000 | ||
| 4 spectra, IQEELATLR | 0.000 | 0.000 | 0.000 | 0.696 | 0.000 | 0.000 | 0.000 | 0.304 | ||
| 1 spectrum, EAAASLGQTLQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.556 | 0.444 | 0.000 | ||
| 1 spectrum, IRPTAVTLEHVPK | 0.000 | 0.000 | 0.040 | 0.337 | 0.000 | 0.296 | 0.251 | 0.076 | ||
| 4 spectra, VHGEPAH | 0.000 | 0.000 | 0.011 | 0.756 | 0.000 | 0.000 | 0.000 | 0.233 | ||
| 1 spectrum, ILTNWGHPEYTCIYR | 0.000 | 0.088 | 0.120 | 0.000 | 0.000 | 0.432 | 0.359 | 0.000 | ||
| 2 spectra, LEAQLAGLR | 0.000 | 0.000 | 0.008 | 0.720 | 0.000 | 0.000 | 0.000 | 0.272 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
14 spectra |
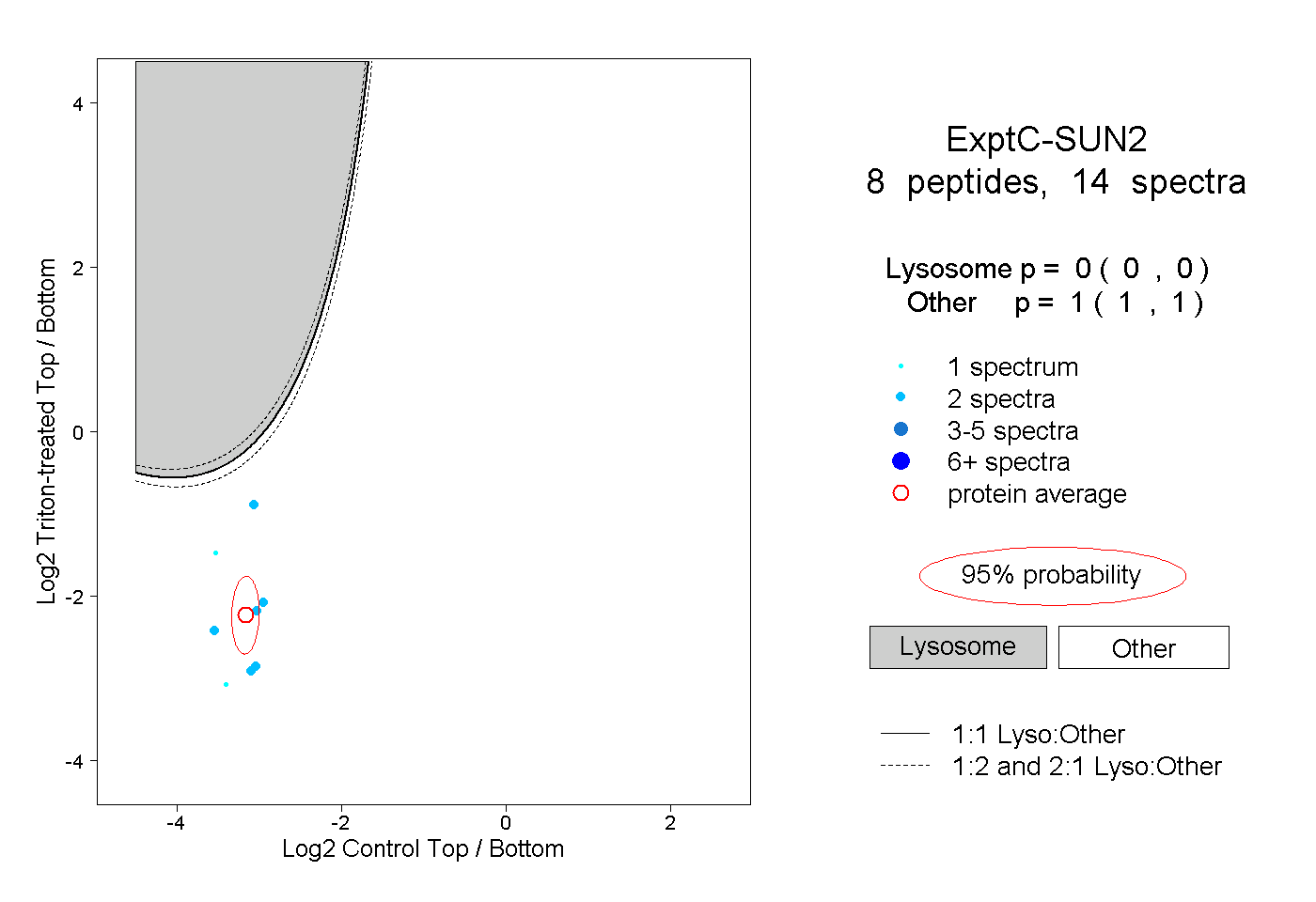 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |