peptides
spectra
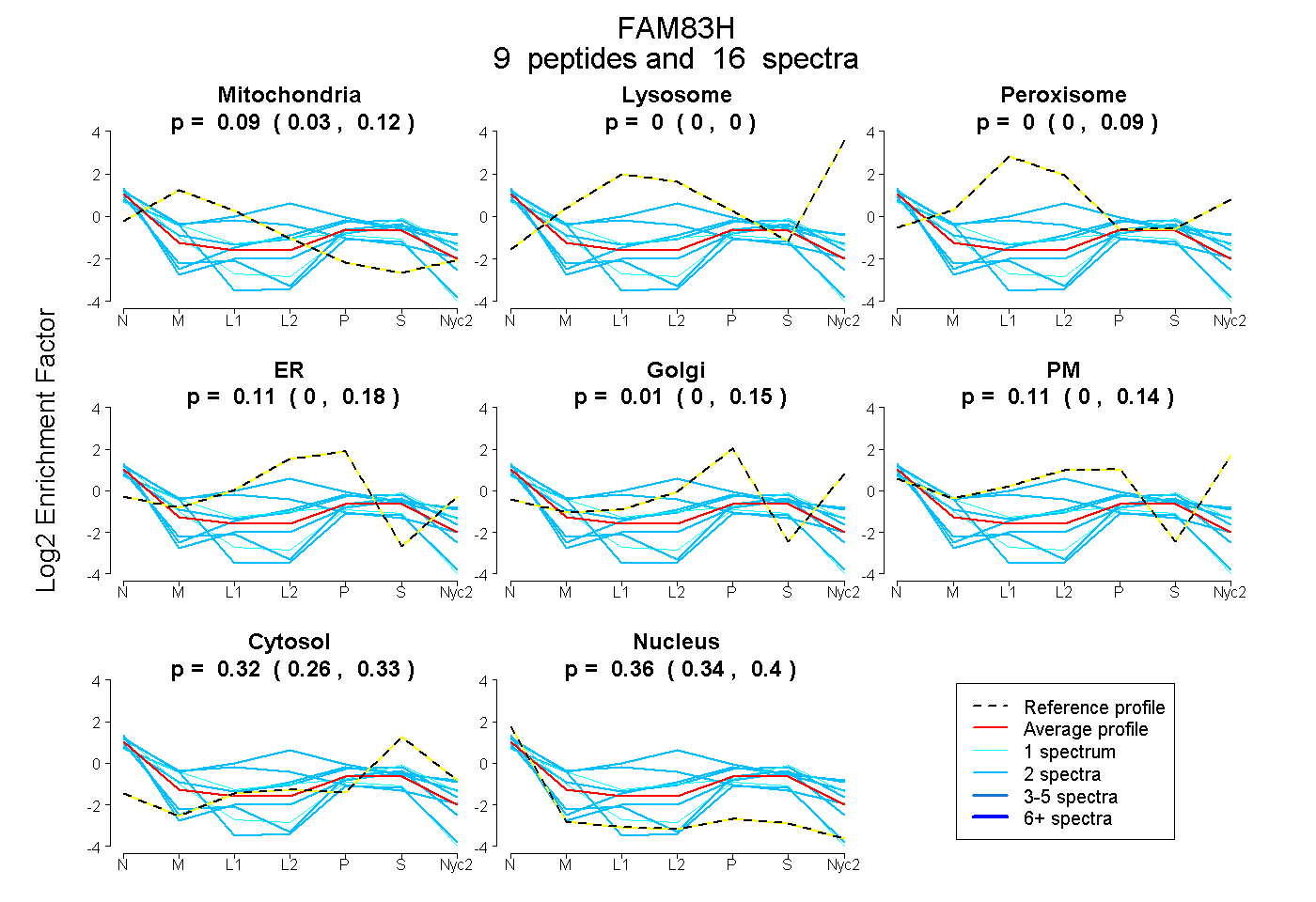
0.026 | 0.120
0.000 | 0.000
0.000 | 0.090
0.000 | 0.177
0.000 | 0.149
0.000 | 0.140
0.264 | 0.330
0.344 | 0.405
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
16 spectra |
 |
0.086 0.026 | 0.120 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.090 |
0.114 0.000 | 0.177 |
0.010 0.000 | 0.149 |
0.105 0.000 | 0.140 |
0.320 0.264 | 0.330 |
0.364 0.344 | 0.405 |
| 2 spectra, LAVDALTEGGQEAYNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | 0.401 | 0.515 | ||
| 1 spectrum, GPKPGSGSGGGDSSER | 0.150 | 0.000 | 0.000 | 0.024 | 0.007 | 0.000 | 0.167 | 0.652 | ||
| 2 spectra, GSPTPAYPER | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | 0.176 | 0.408 | 0.388 | ||
| 2 spectra, VNLHHVDFLR | 0.168 | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | 0.131 | 0.695 | ||
| 2 spectra, DSFAQQLHQEAER | 0.111 | 0.000 | 0.000 | 0.159 | 0.000 | 0.118 | 0.398 | 0.213 | ||
| 2 spectra, GSPTSTYPDR | 0.000 | 0.000 | 0.000 | 0.145 | 0.000 | 0.183 | 0.355 | 0.316 | ||
| 2 spectra, EEVVAPGGAGAER | 0.000 | 0.000 | 0.374 | 0.253 | 0.000 | 0.044 | 0.145 | 0.184 | ||
| 2 spectra, GFFQSR | 0.152 | 0.000 | 0.373 | 0.084 | 0.000 | 0.000 | 0.000 | 0.392 | ||
| 1 spectrum, HLEMDAFK | 0.246 | 0.000 | 0.000 | 0.000 | 0.000 | 0.198 | 0.420 | 0.136 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
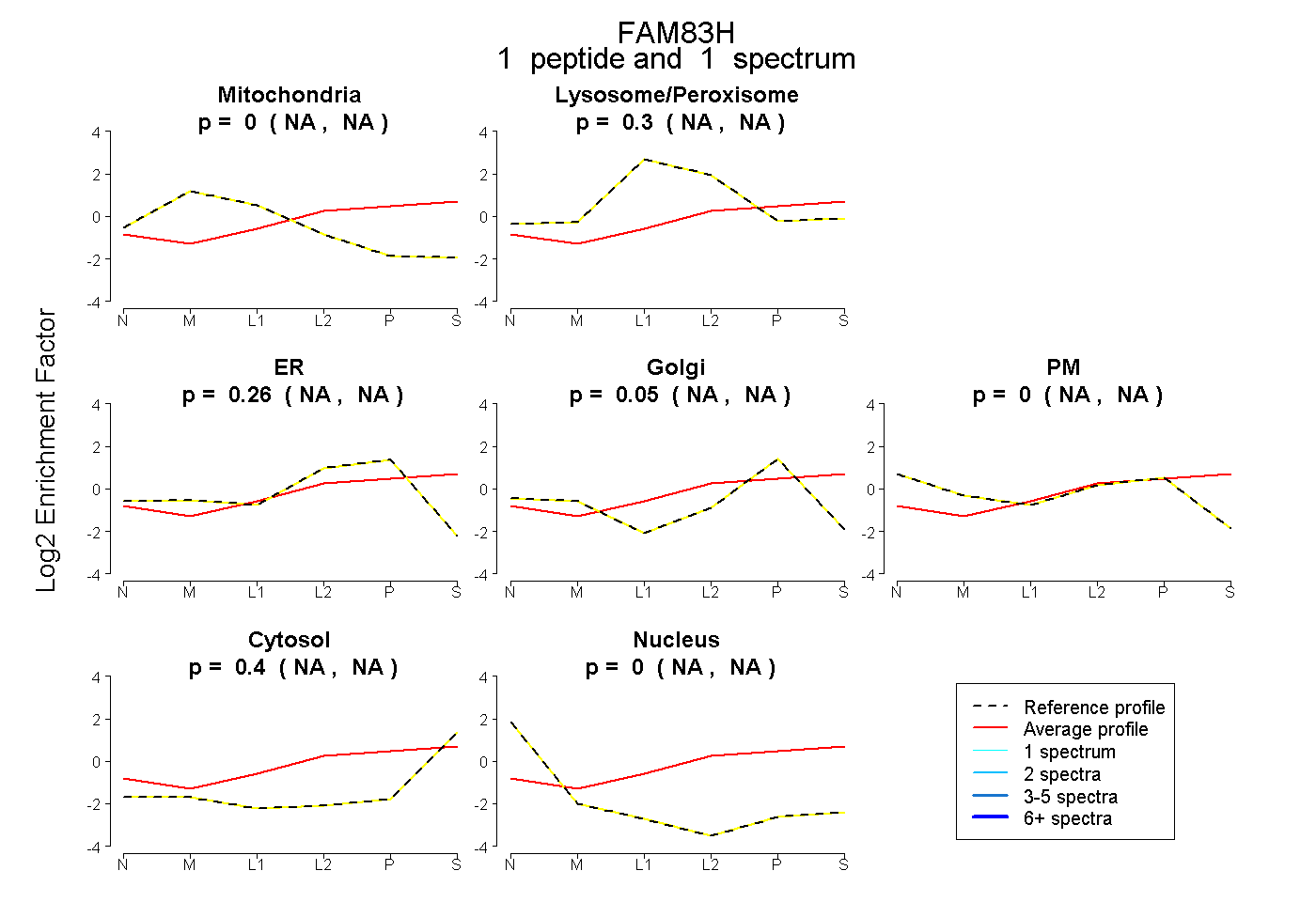 |
0.000 NA | NA |
0.296 NA | NA |
0.256 NA | NA |
0.048 NA | NA |
0.000 NA | NA |
0.401 NA | NA |
0.000 NA | NA |