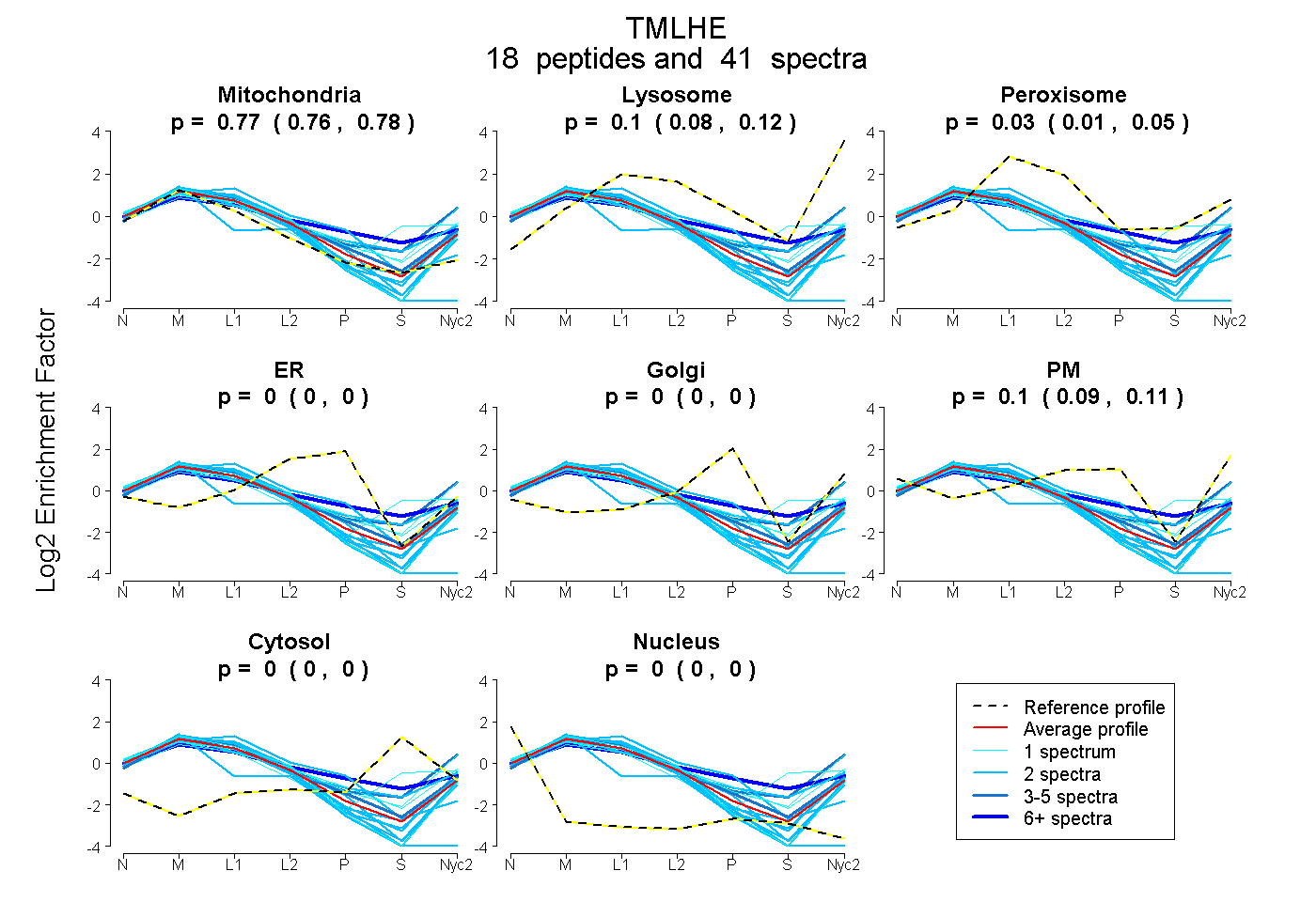
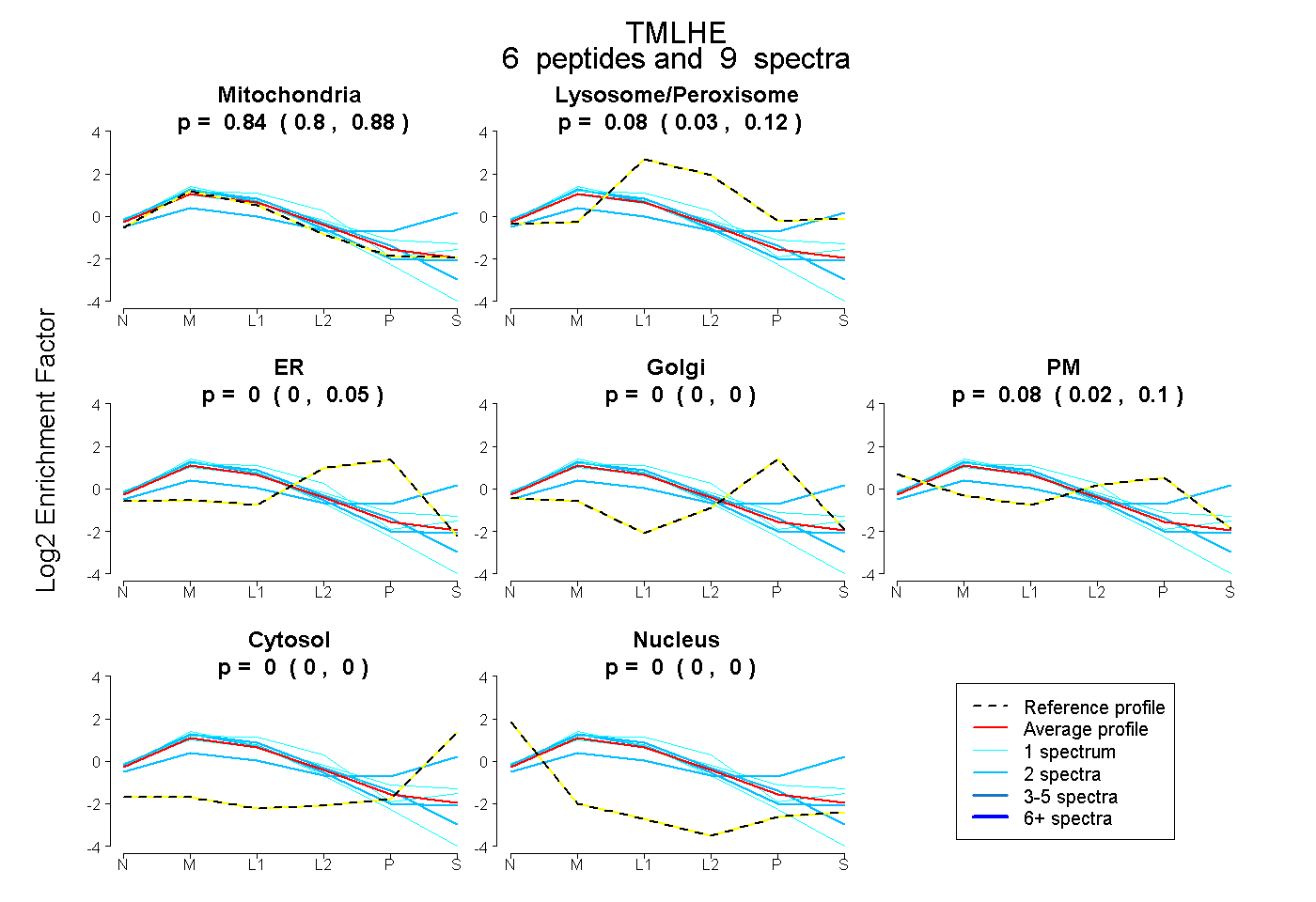
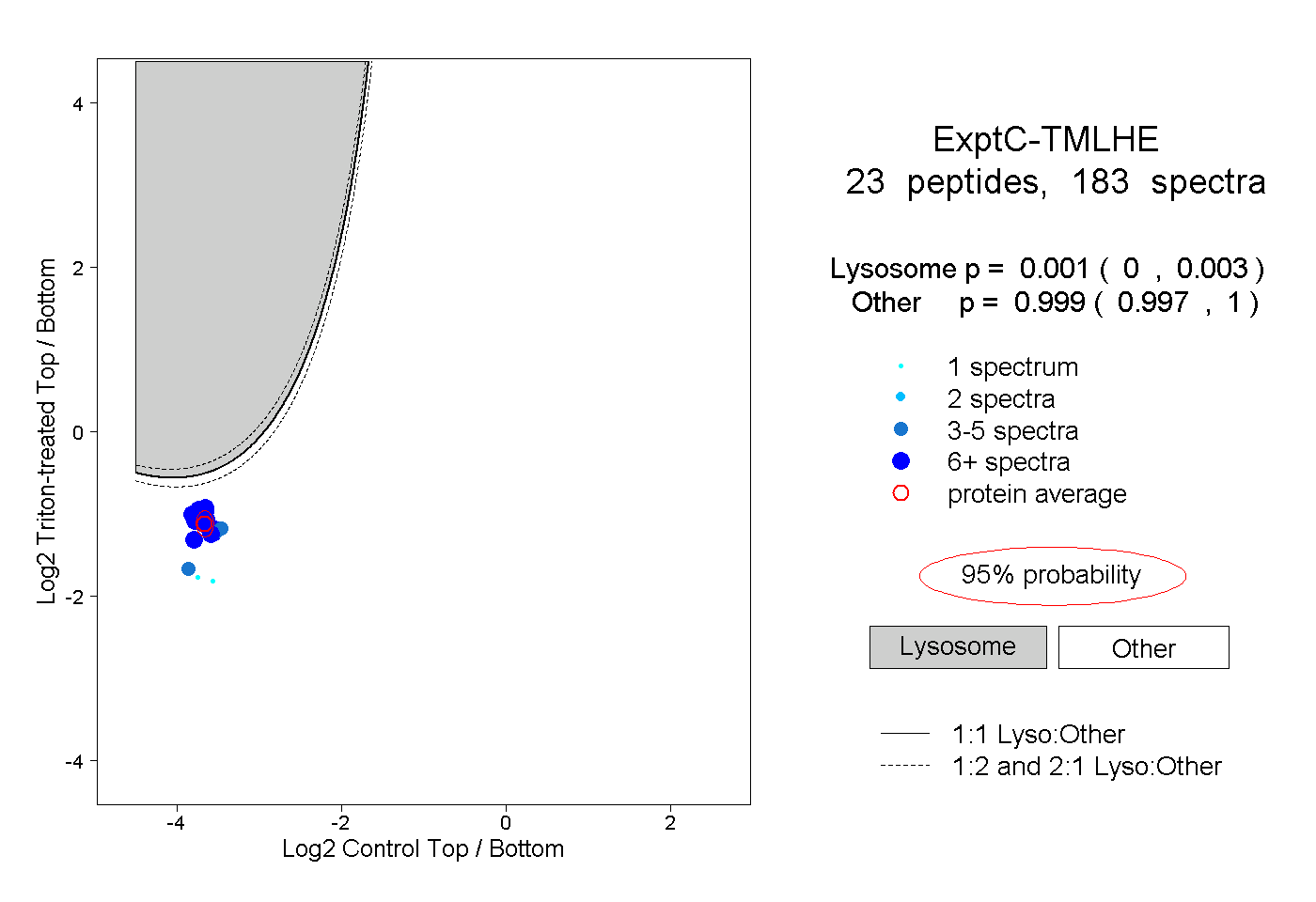
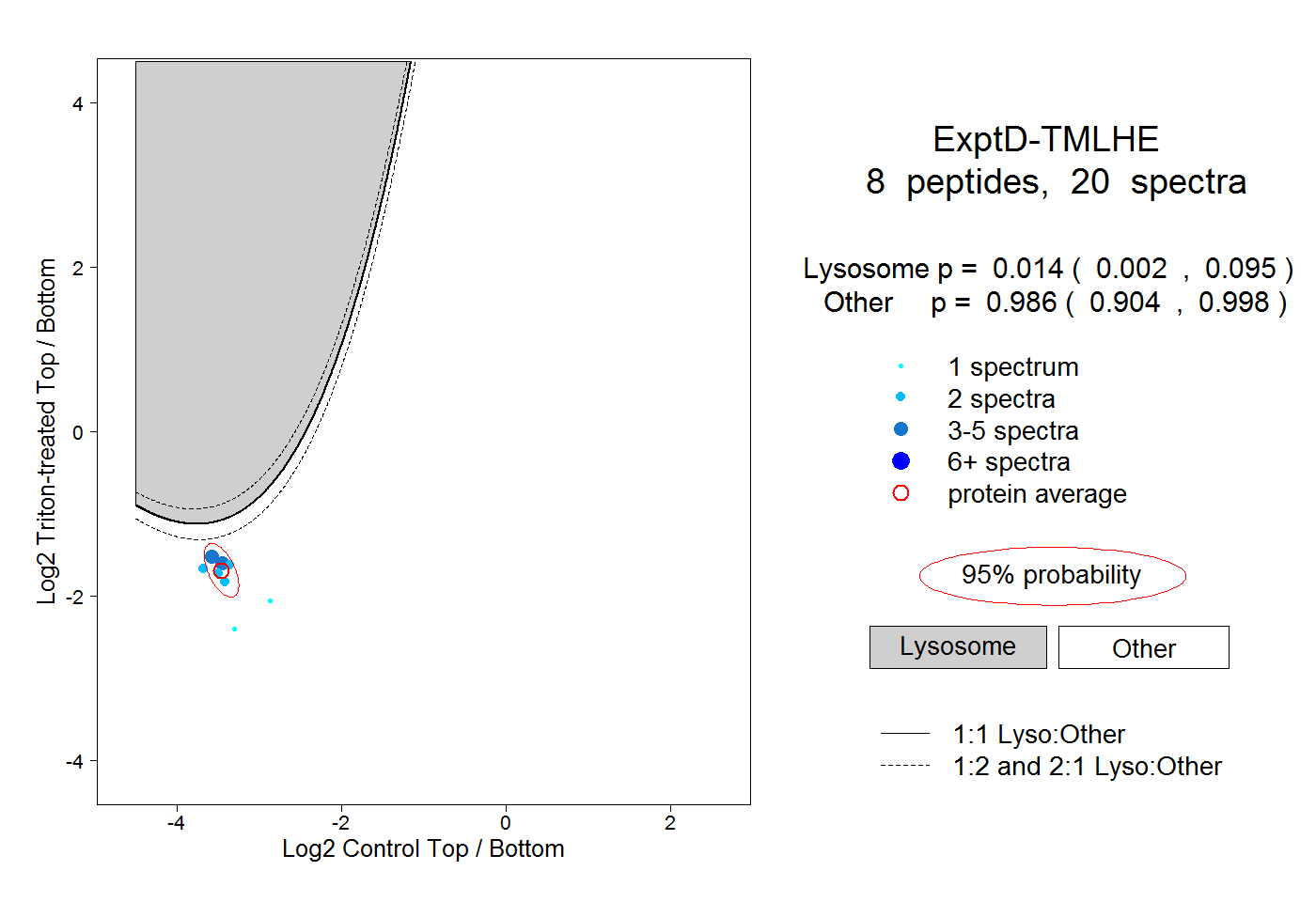
| 3 spectra, SLDTASVDLCIKPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, ILGLHA |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 10 spectra, GDTAYTK |
|
0.007 |
|
|
|
|
|
|
|
0.993 |
| 11 spectra, YDLDWLVK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 9 spectra, SASCYNSK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 3 spectra, RPENELWVK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 1 spectrum, LDESTLFFTWPDGHVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FDYVWLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, WYAAHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, ESFTGYR |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 4 spectra, QLCGCYLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, DDVLNTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ELYLIR |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 8 spectra, AVINTVPYDVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, ETIYGR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 15 spectra, VLFIDNWR |
|
0.004 |
|
|
|
|
|
|
|
0.996 |
| 3 spectra, MWYFTSDFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TLLVDGFYAAQQVLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, NSYEGQK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 8 spectra, VLWNAK |
|
0.007 |
|
|
|
|
|
|
|
0.993 |
| 13 spectra, QEVIQPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YNNYDR |
|
0.004 |
|
|
|
|
|
|
|
0.996 |
| 10 spectra, TLTTELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |