peptides
spectra
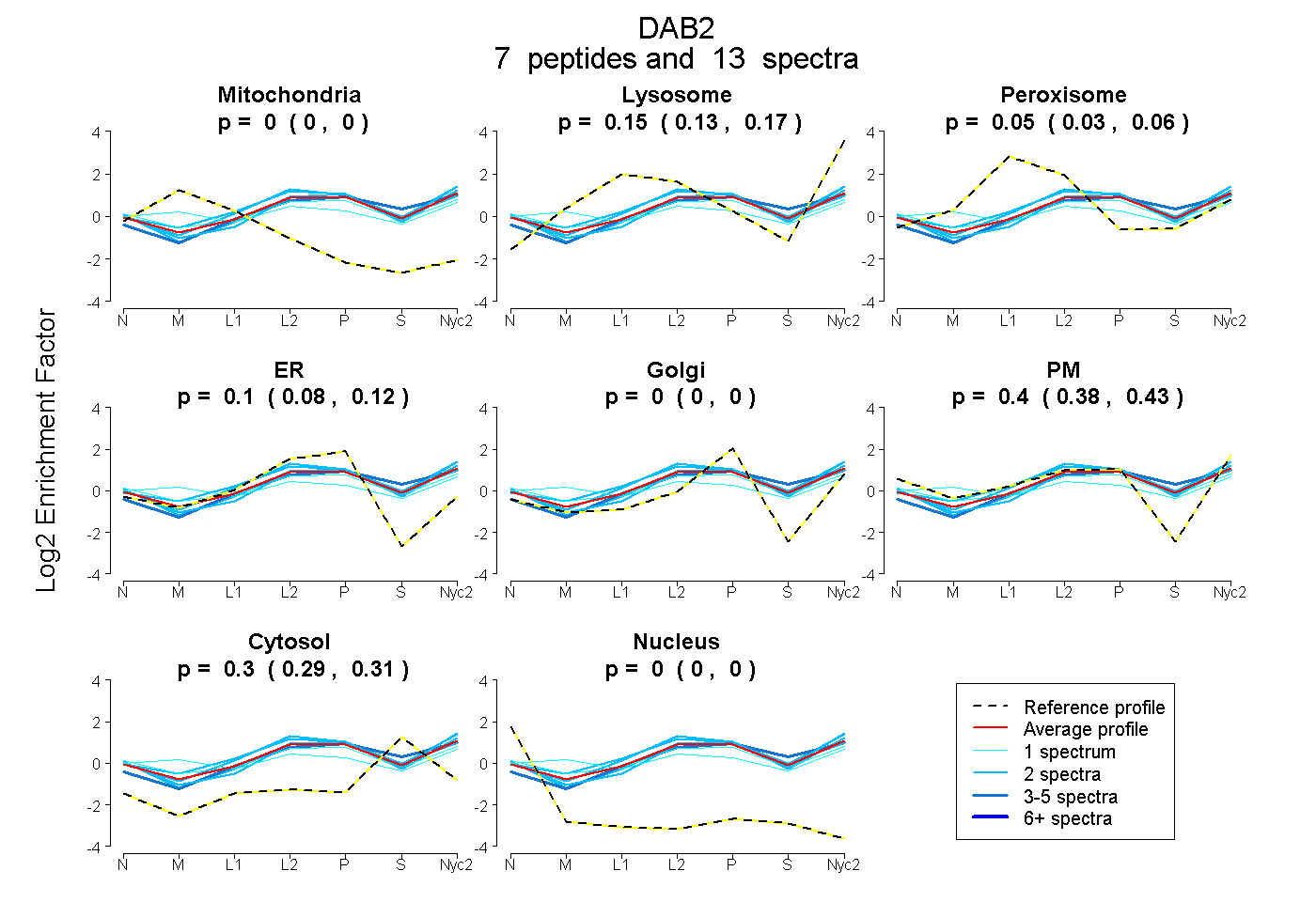
0.000 | 0.000
0.132 | 0.166
0.025 | 0.062
0.078 | 0.120
0.000 | 0.000
0.379 | 0.426
0.290 | 0.307
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
13 spectra |
 |
0.000 0.000 | 0.000 |
0.151 0.132 | 0.166 |
0.045 0.025 | 0.062 |
0.102 0.078 | 0.120 |
0.000 0.000 | 0.000 |
0.403 0.379 | 0.426 |
0.299 0.290 | 0.307 |
0.000 0.000 | 0.000 |
| 1 spectrum, TGVIEHEHPVNK | 0.059 | 0.034 | 0.153 | 0.000 | 0.000 | 0.474 | 0.280 | 0.000 | ||
| 2 spectra, INEPPKPAPR | 0.000 | 0.191 | 0.103 | 0.155 | 0.000 | 0.341 | 0.211 | 0.000 | ||
| 2 spectra, TGQQAEPLVVDLK | 0.000 | 0.216 | 0.048 | 0.117 | 0.000 | 0.383 | 0.235 | 0.000 | ||
| 3 spectra, QPPLVPSR | 0.000 | 0.251 | 0.000 | 0.188 | 0.016 | 0.157 | 0.387 | 0.000 | ||
| 1 spectrum, SQGQHK | 0.000 | 0.000 | 0.166 | 0.000 | 0.061 | 0.488 | 0.284 | 0.000 | ||
| 2 spectra, DVTDNR | 0.000 | 0.152 | 0.000 | 0.039 | 0.002 | 0.501 | 0.307 | 0.000 | ||
| 2 spectra, TDEYLLAR | 0.000 | 0.108 | 0.000 | 0.108 | 0.000 | 0.440 | 0.344 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
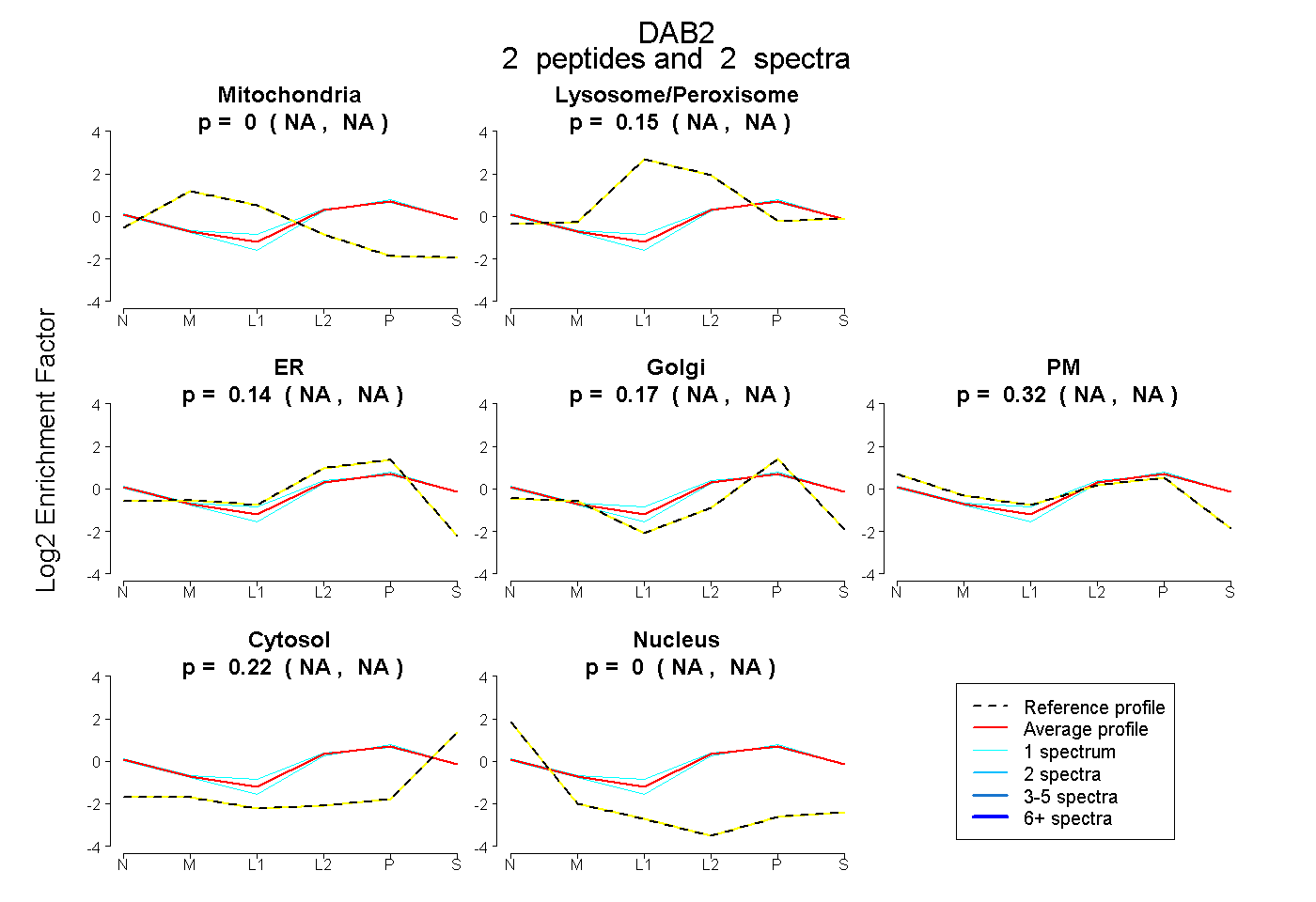 |
0.000 NA | NA |
0.147 NA | NA |
0.144 NA | NA |
0.171 NA | NA |
0.319 NA | NA |
0.219 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
17 spectra |
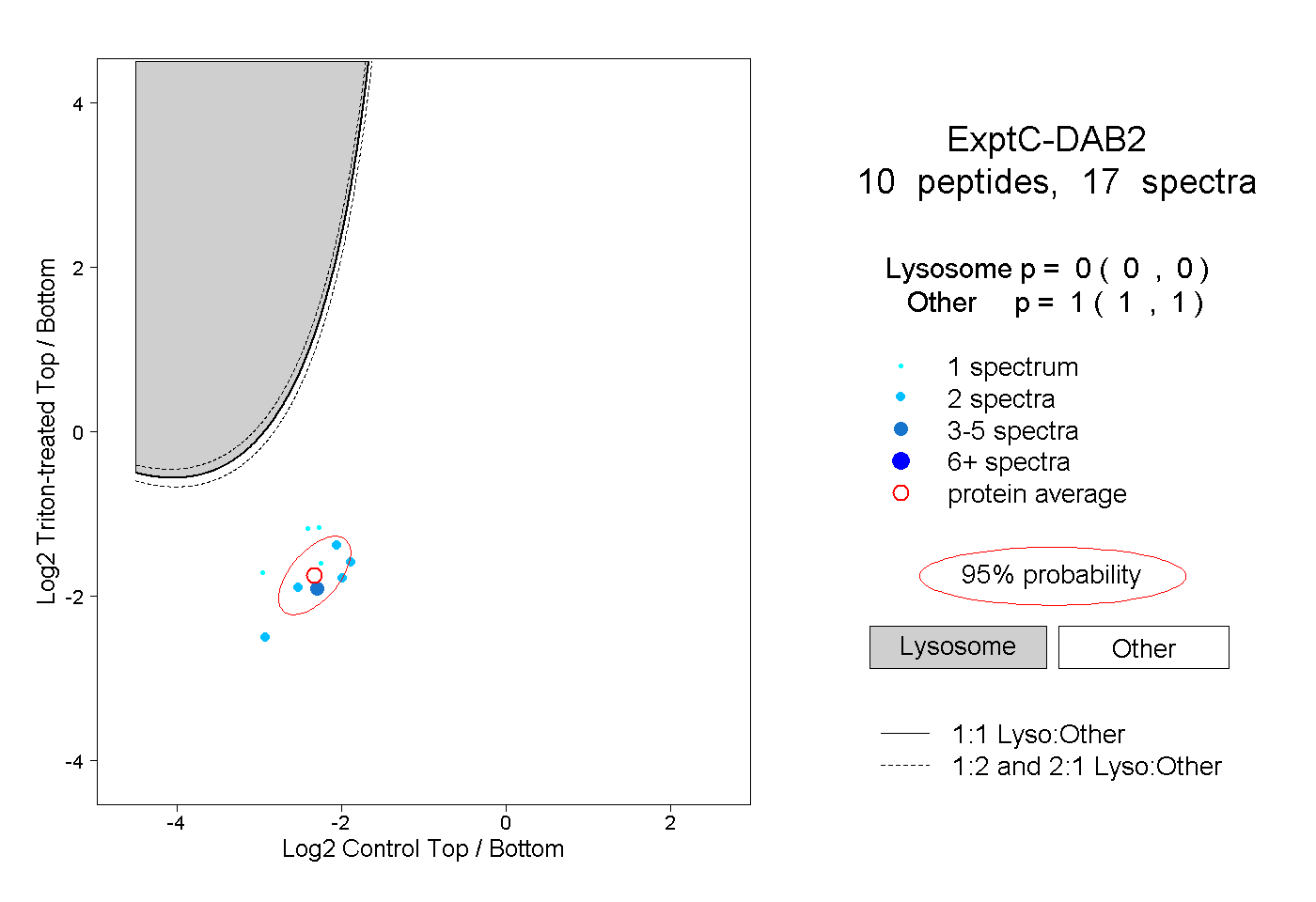 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
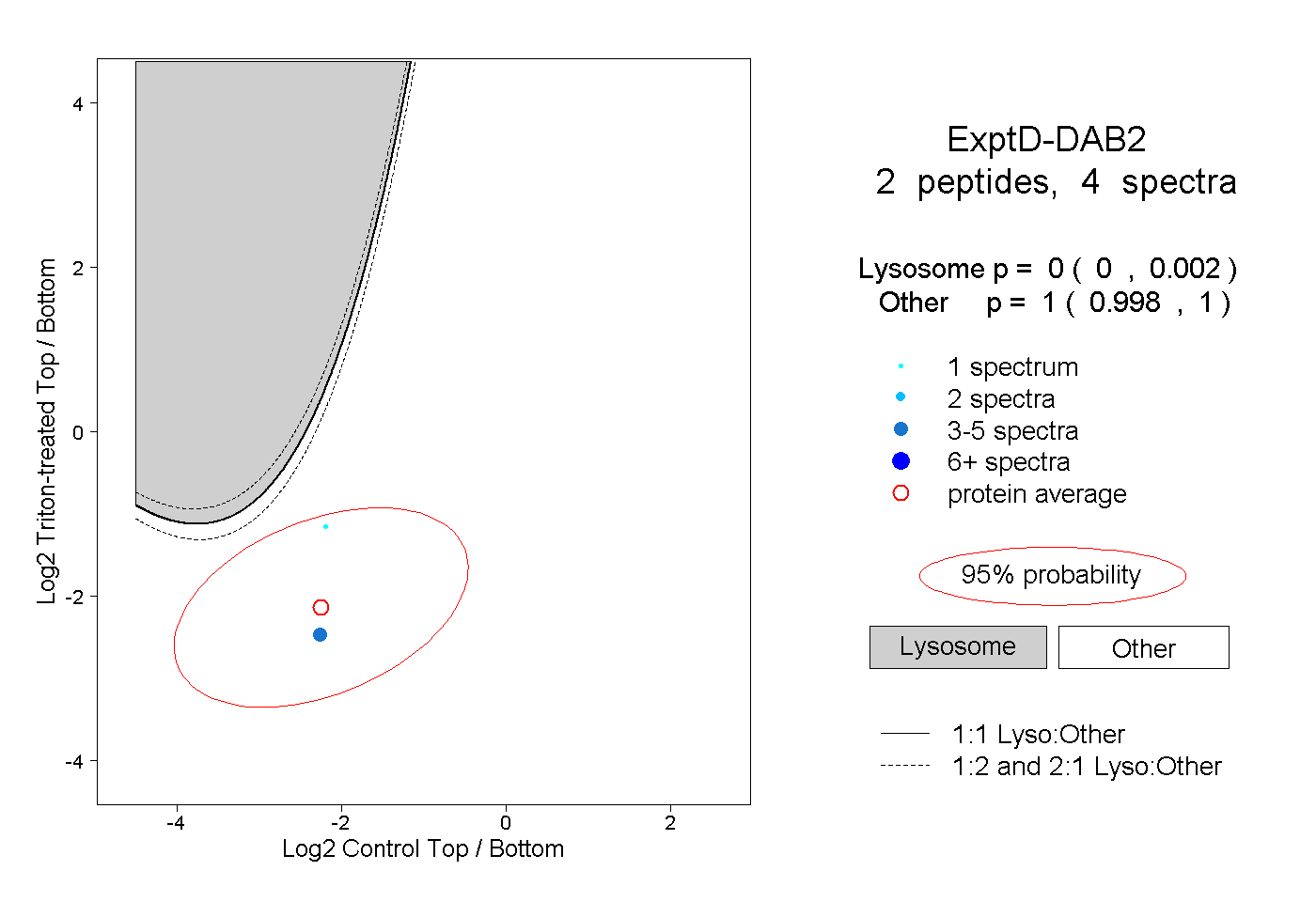 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |