peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.071 | 0.074
0.027 | 0.034
0.000 | 0.000
0.098 | 0.106
0.792 | 0.795
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.094 | 0.105
0.000 | 0.000
0.000 | 0.000
0.064 | 0.078
0.821 | 0.826
0.000 | 0.008
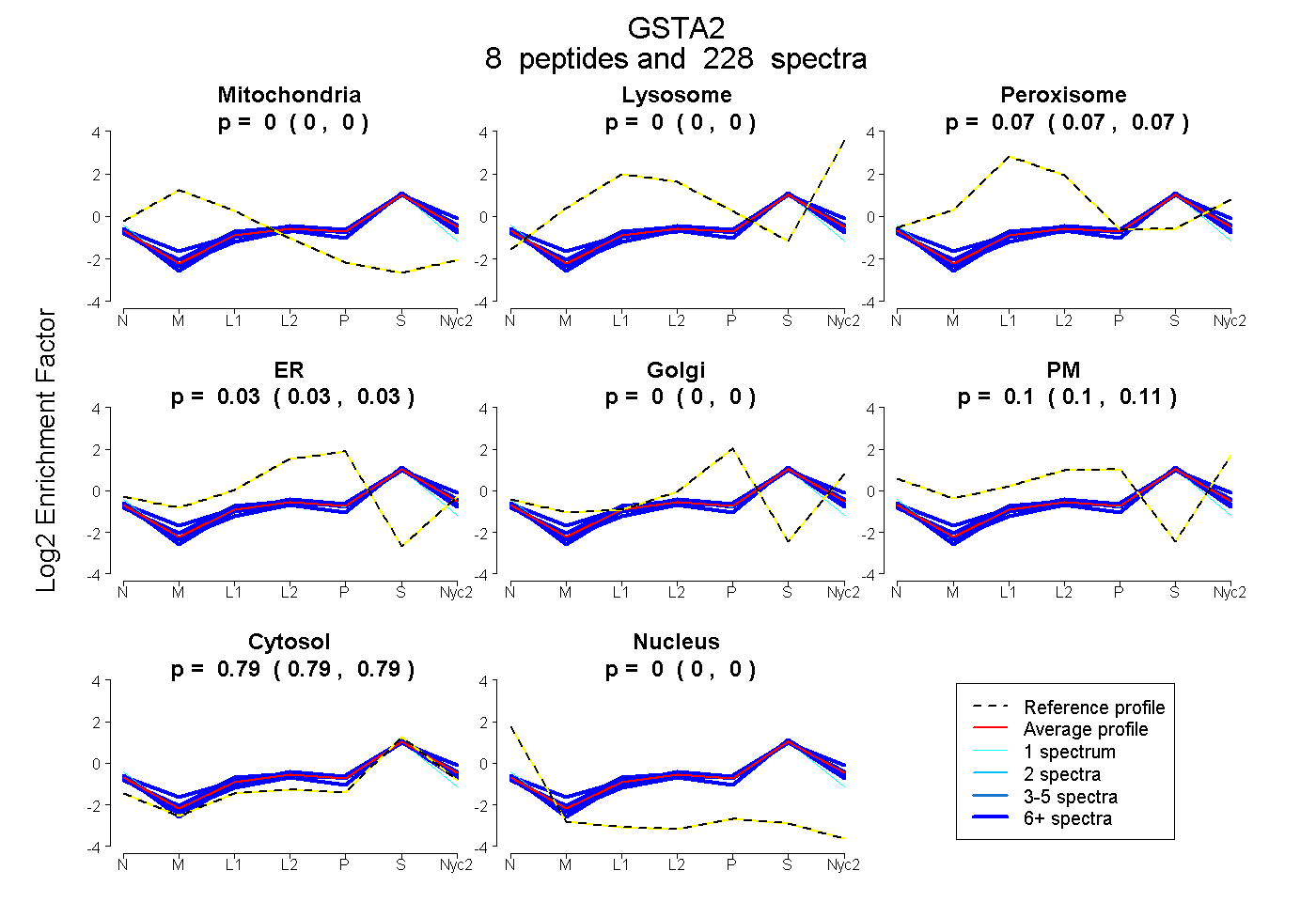
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
228 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.071 | 0.074 |
0.031 0.027 | 0.034 |
0.000 0.000 | 0.000 |
0.103 0.098 | 0.106 |
0.794 0.792 | 0.795 |
0.000 0.000 | 0.000 |
||
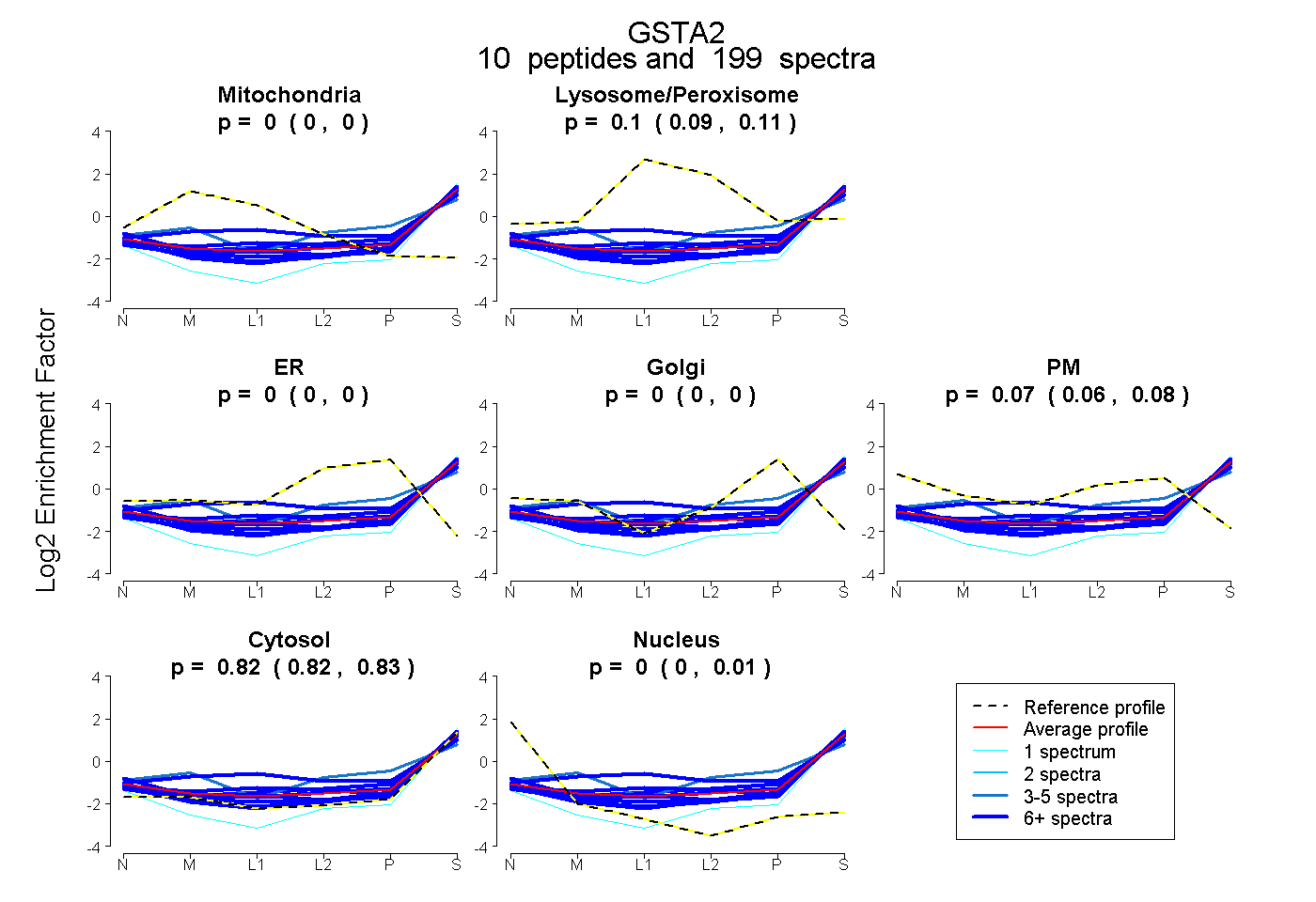
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
199 spectra |
 |
0.000 0.000 | 0.000 |
0.100 0.094 | 0.105 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.064 | 0.078 |
0.824 0.821 | 0.826 |
0.004 0.000 | 0.008 |
| 7 spectra, LIQSPEDLEK | 0.000 | 0.060 | 0.000 | 0.000 | 0.000 | 0.915 | 0.025 | |||
| 3 spectra, DGNLMFDQVPMVEIDGMK | 0.000 | 0.144 | 0.000 | 0.202 | 0.091 | 0.563 | 0.000 | |||
| 16 spectra, AILNYIATK | 0.000 | 0.127 | 0.000 | 0.000 | 0.114 | 0.759 | 0.000 | |||
| 18 spectra, QLEEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.068 | 0.917 | 0.015 | |||
| 15 spectra, WLLAAAGVEFEEK | 0.000 | 0.185 | 0.000 | 0.000 | 0.000 | 0.815 | 0.000 | |||
| 7 spectra, YLPAFEK | 0.000 | 0.019 | 0.000 | 0.000 | 0.029 | 0.922 | 0.030 | |||
| 49 spectra, FLQPGSQR | 0.000 | 0.106 | 0.000 | 0.000 | 0.070 | 0.793 | 0.031 | |||
| 42 spectra, SGKPVLHYFNAR | 0.000 | 0.110 | 0.000 | 0.000 | 0.000 | 0.845 | 0.044 | |||
| 1 spectrum, ISSLPNVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.945 | 0.055 | |||
| 41 spectra, SHGQDYLVGNR | 0.035 | 0.301 | 0.000 | 0.048 | 0.000 | 0.615 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
295 spectra |
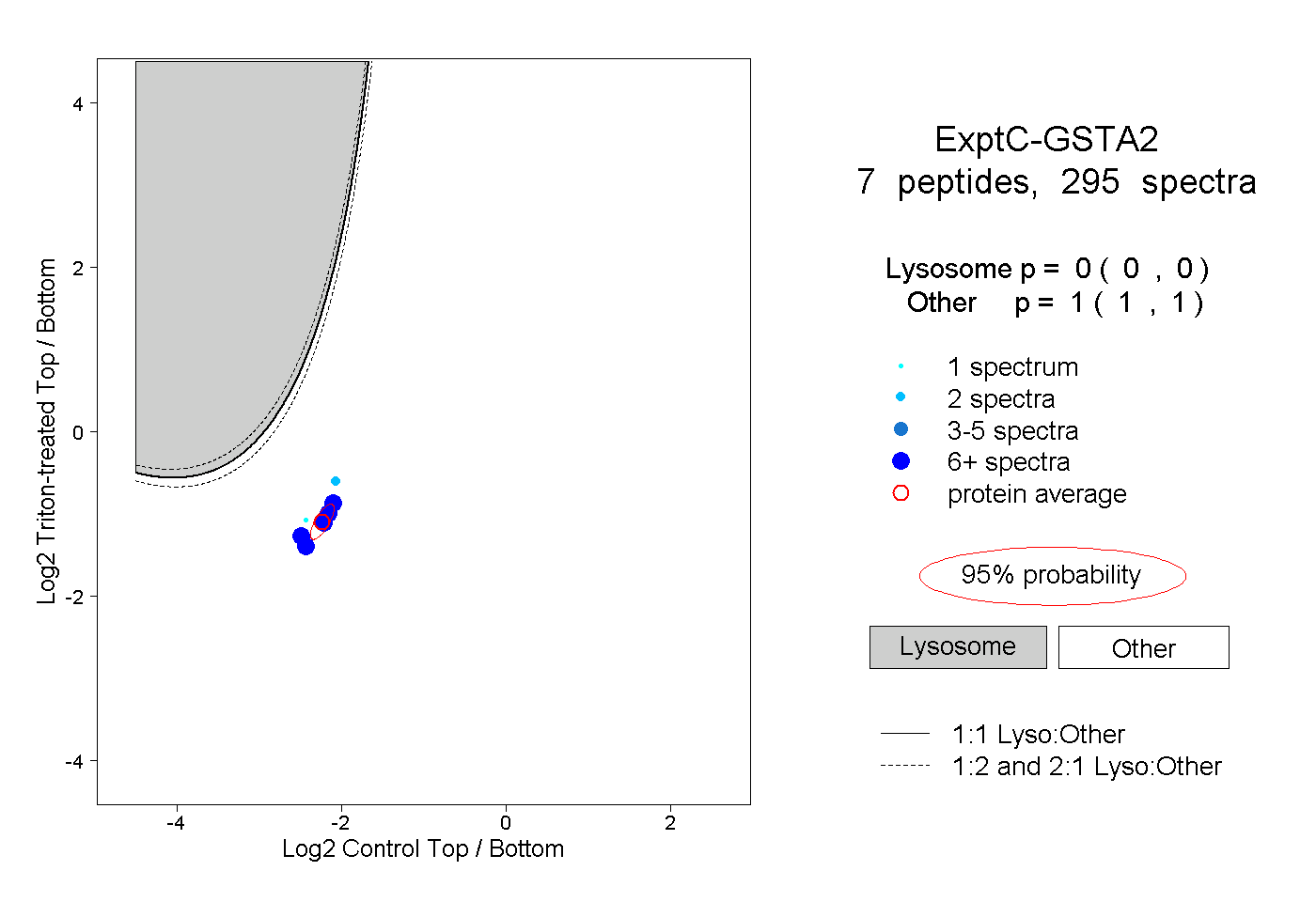 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
27 spectra |
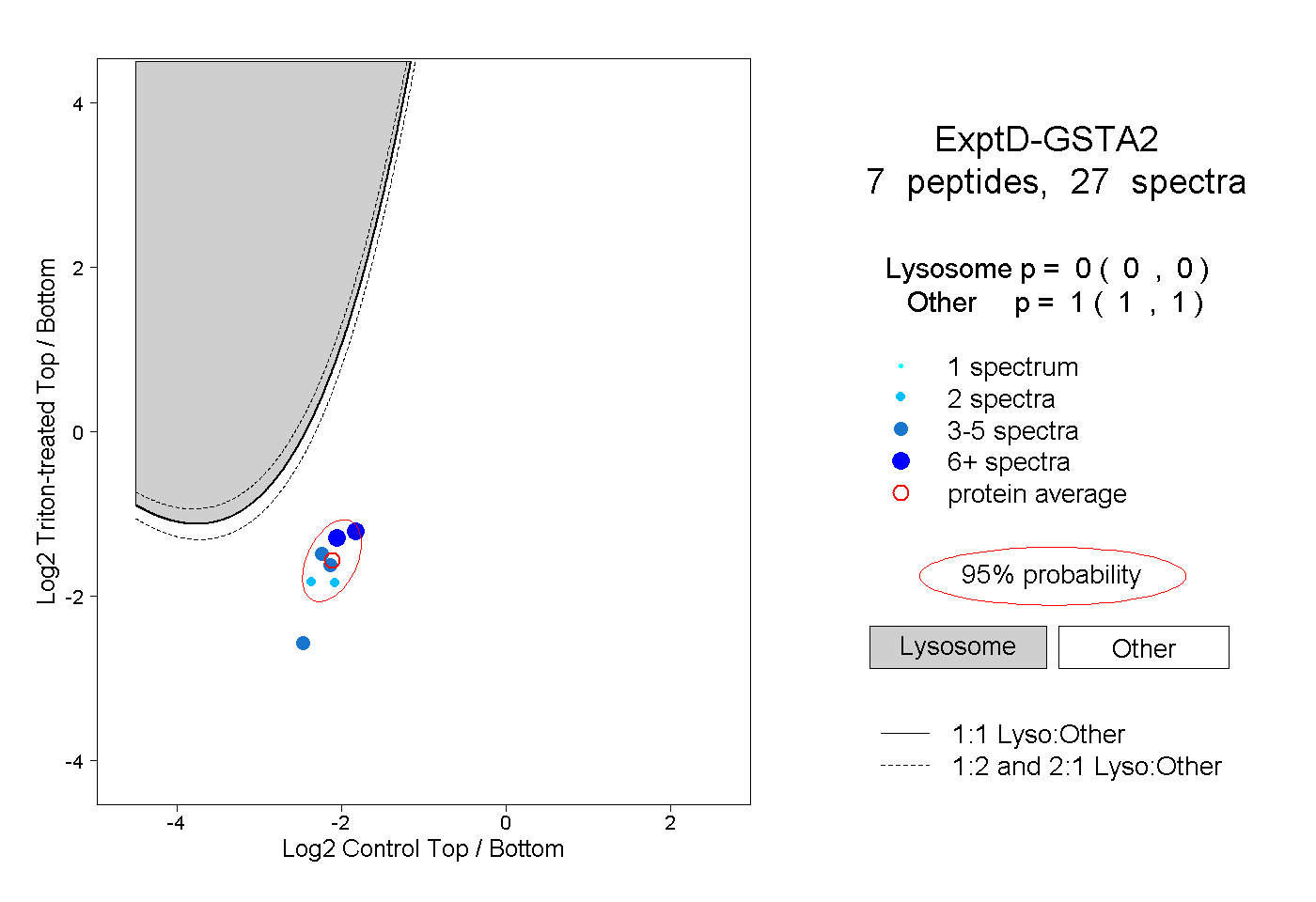 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |