peptides
spectra
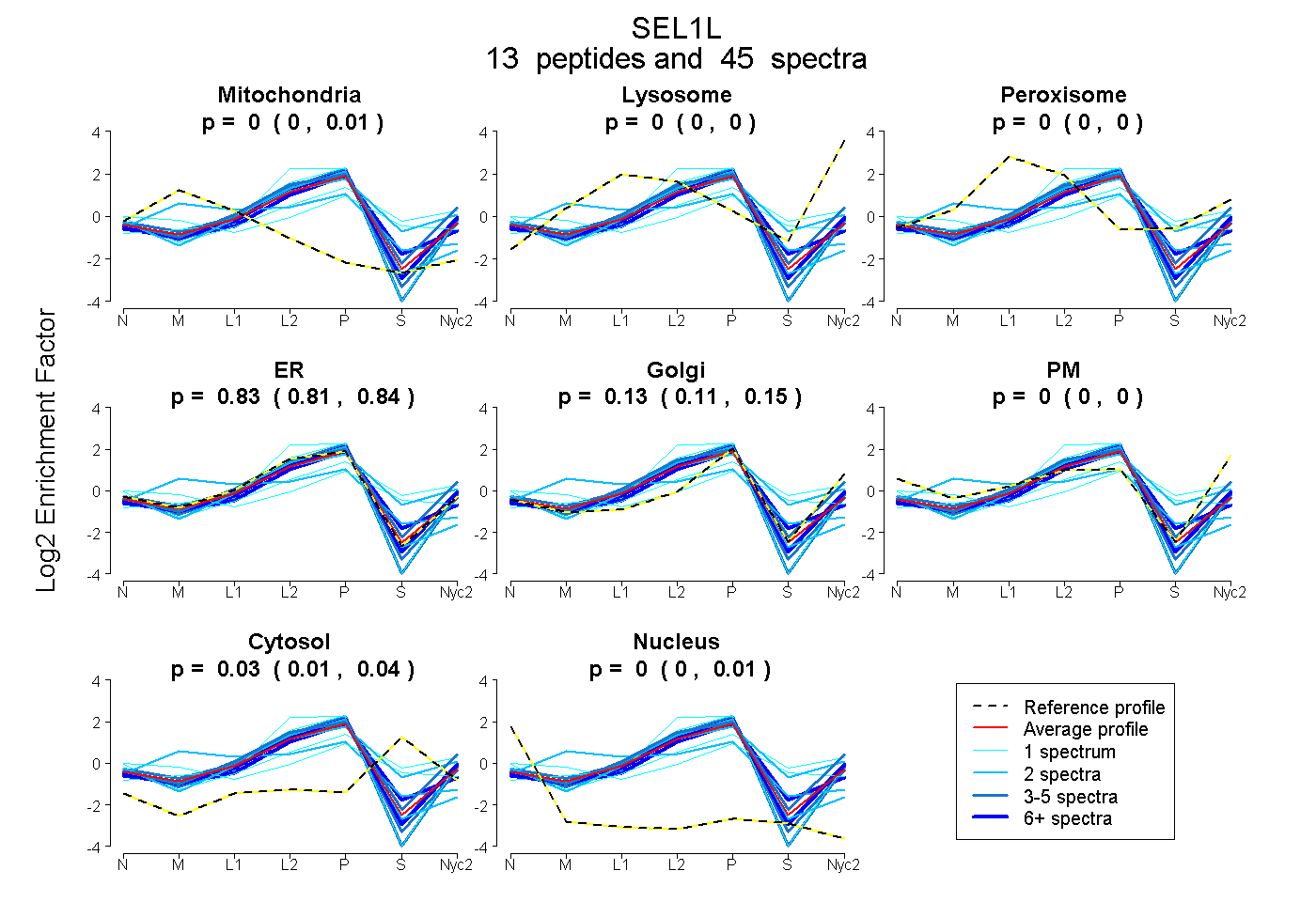
0.000 | 0.012
0.000 | 0.000
0.000 | 0.000
0.808 | 0.845
0.112 | 0.150
0.000 | 0.000
0.013 | 0.043
0.000 | 0.011
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
45 spectra |
 |
0.004 0.000 | 0.012 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.828 0.808 | 0.845 |
0.133 0.112 | 0.150 |
0.000 0.000 | 0.000 |
0.030 0.013 | 0.043 |
0.005 0.000 | 0.011 |
| 5 spectra, GVEQNHQR | 0.000 | 0.000 | 0.000 | 0.824 | 0.114 | 0.062 | 0.000 | 0.000 | ||
| 2 spectra, LWCATTYDYK | 0.000 | 0.000 | 0.000 | 0.936 | 0.000 | 0.000 | 0.000 | 0.064 | ||
| 1 spectrum, ILNGSTR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, WGFCETEEDAAK | 0.000 | 0.104 | 0.000 | 0.735 | 0.156 | 0.000 | 0.005 | 0.000 | ||
| 9 spectra, ALLHWNR | 0.000 | 0.000 | 0.000 | 0.809 | 0.036 | 0.000 | 0.155 | 0.000 | ||
| 2 spectra, GVQVNYDLALK | 0.308 | 0.000 | 0.074 | 0.570 | 0.000 | 0.000 | 0.048 | 0.000 | ||
| 1 spectrum, AFDYFNLAANAGNSHAMAFLGK | 0.000 | 0.000 | 0.000 | 0.971 | 0.029 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, QMQEAEAIYQSGMK | 0.000 | 0.082 | 0.000 | 0.681 | 0.000 | 0.000 | 0.237 | 0.000 | ||
| 5 spectra, AASQGYTVAR | 0.000 | 0.000 | 0.000 | 0.944 | 0.056 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, GALPTDGSVK | 0.000 | 0.000 | 0.000 | 0.892 | 0.095 | 0.000 | 0.000 | 0.013 | ||
| 1 spectrum, GDVQAQVGLGQLHLHGGR | 0.000 | 0.000 | 0.065 | 0.252 | 0.216 | 0.152 | 0.315 | 0.000 | ||
| 1 spectrum, LVANHVASDISLTGGSVVQR | 0.125 | 0.000 | 0.048 | 0.256 | 0.282 | 0.000 | 0.289 | 0.000 | ||
| 8 spectra, LTEEGSPK | 0.000 | 0.000 | 0.000 | 0.793 | 0.207 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
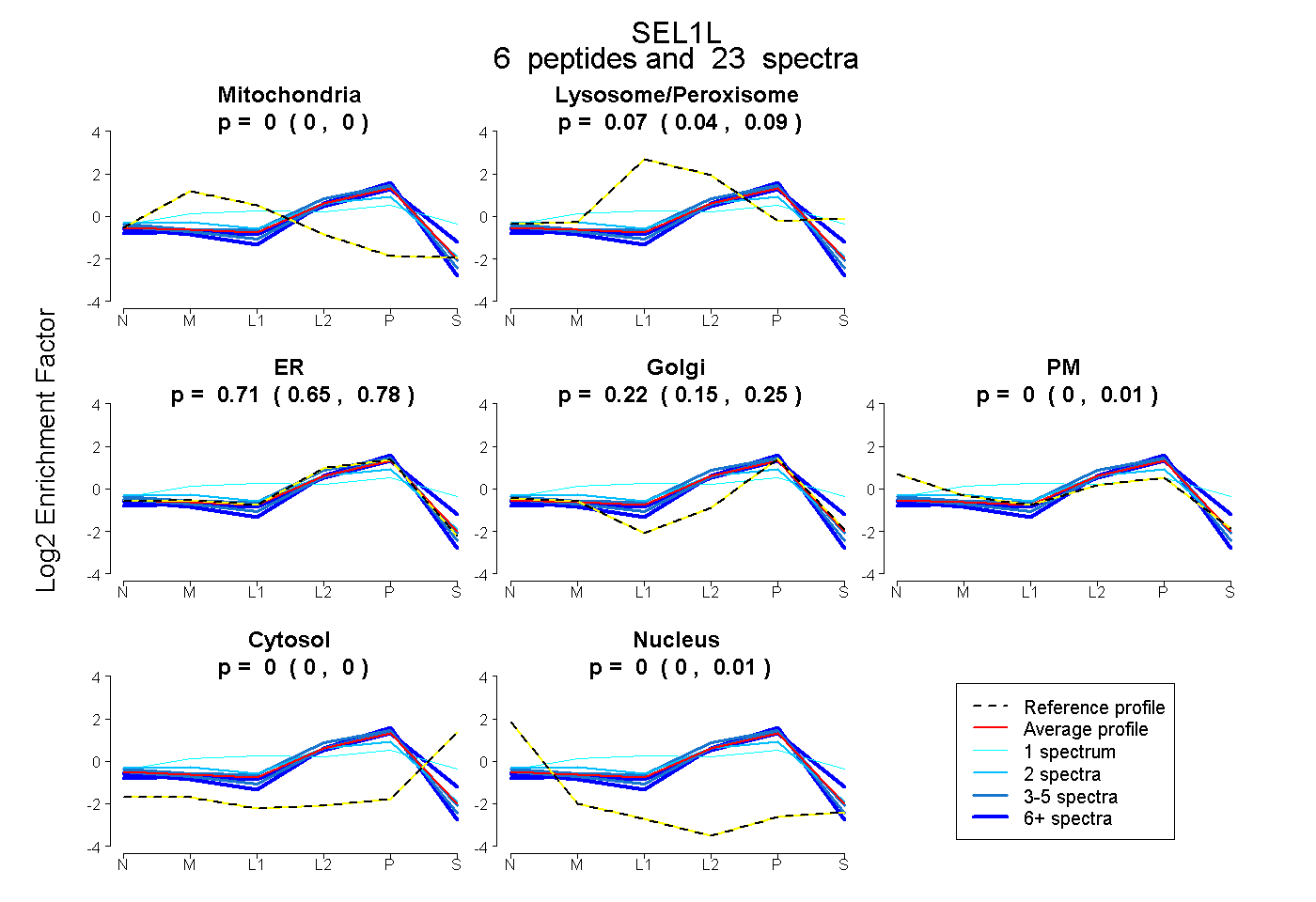 |
0.000 0.000 | 0.000 |
0.069 0.037 | 0.093 |
0.709 0.646 | 0.784 |
0.222 0.152 | 0.252 |
0.000 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.012 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
52 spectra |
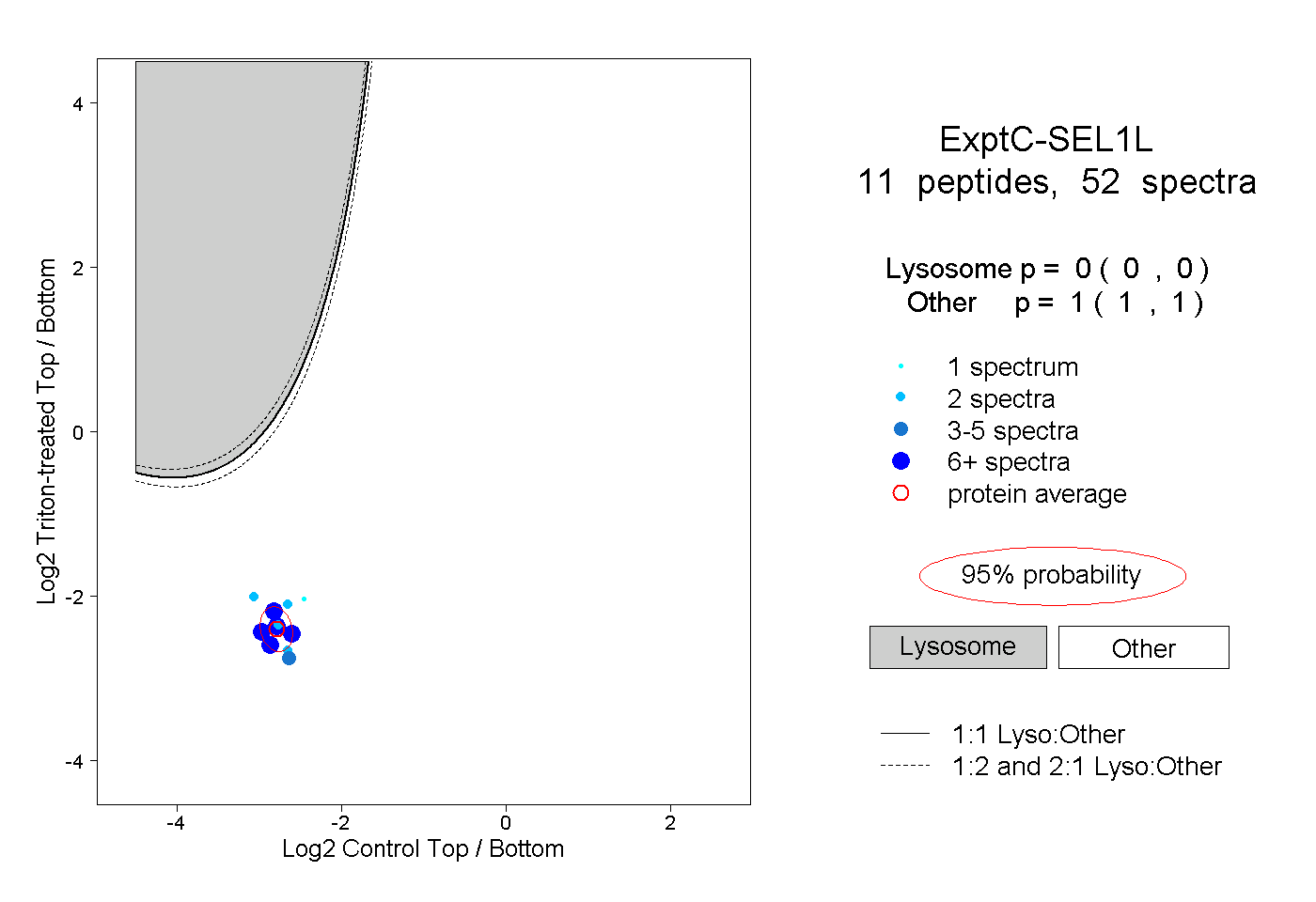 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
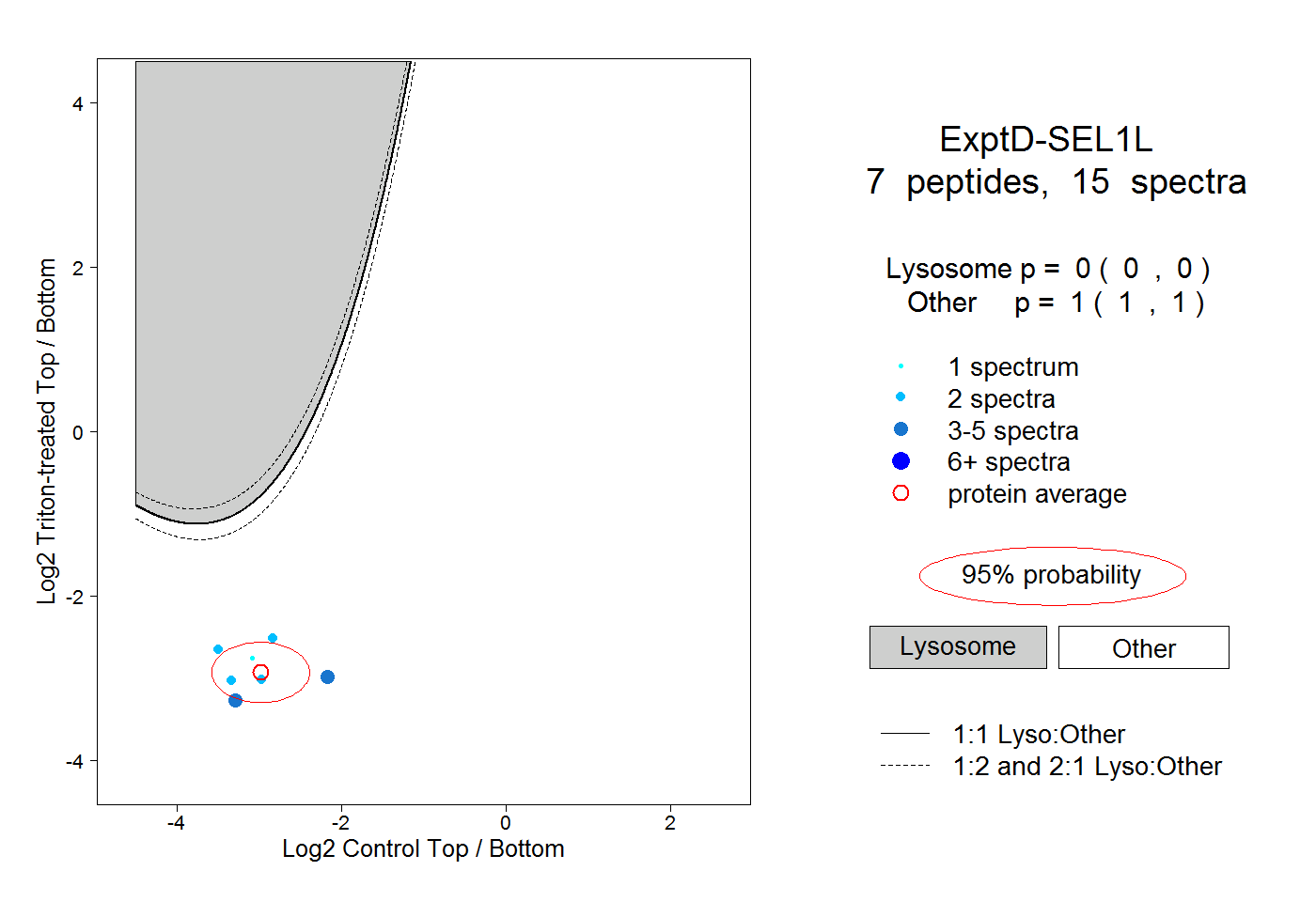 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |