peptides
spectra
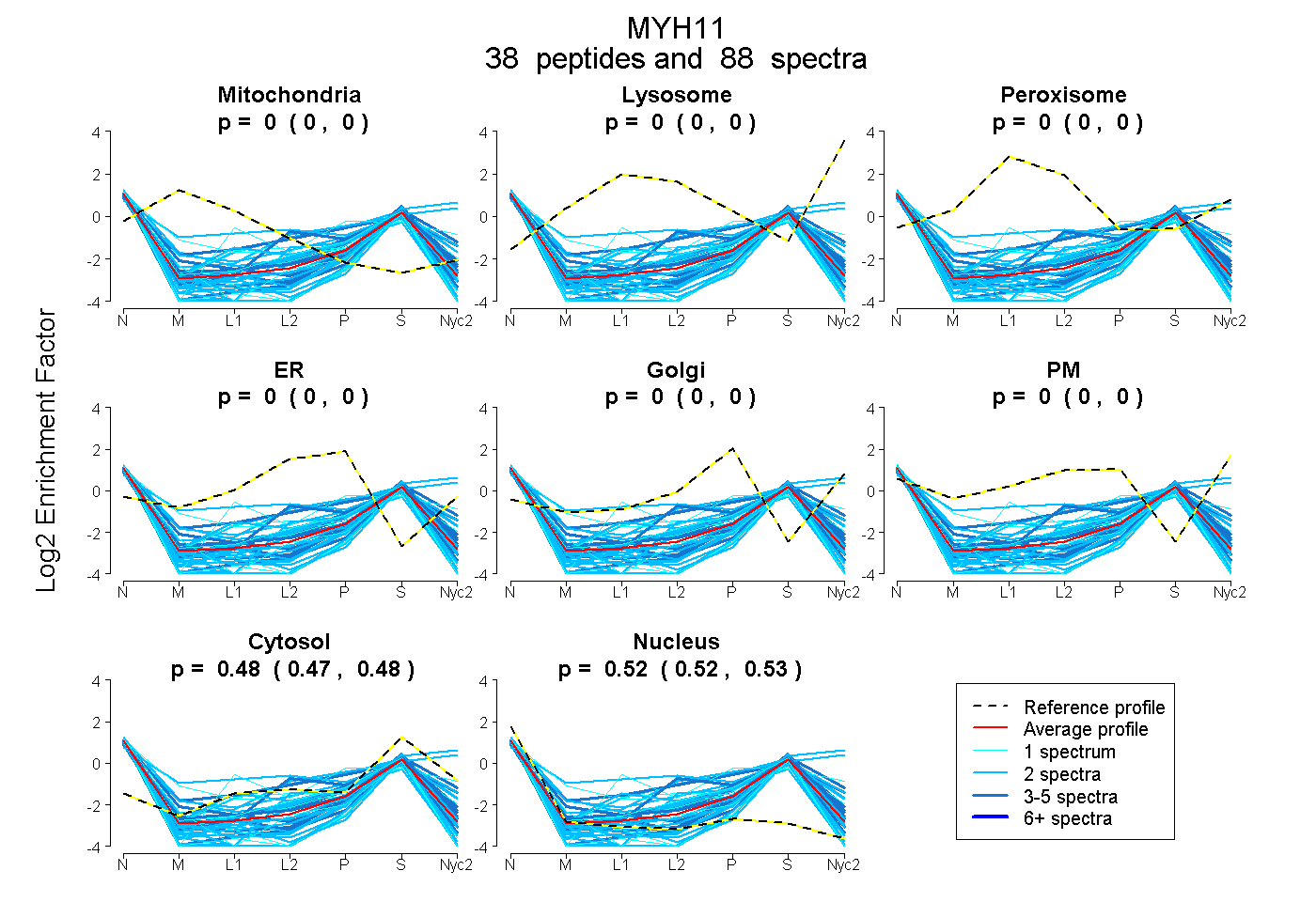
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.472 | 0.478
0.521 | 0.527
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
88 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.475 0.472 | 0.478 |
0.525 0.521 | 0.527 |
| 5 spectra, LQEVEGAVK | 0.000 | 0.000 | 0.000 | 0.030 | 0.023 | 0.000 | 0.469 | 0.477 | ||
| 2 spectra, GQLSDDEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.432 | 0.568 | ||
| 2 spectra, FVADLWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.239 | 0.761 | ||
| 1 spectrum, QEVEHK | 0.000 | 0.000 | 0.035 | 0.000 | 0.000 | 0.000 | 0.477 | 0.488 | ||
| 4 spectra, ALEEALEAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.586 | 0.368 | ||
| 2 spectra, LCSEQGNHPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.455 | 0.545 | ||
| 2 spectra, HLPIYSEK | 0.000 | 0.000 | 0.101 | 0.000 | 0.000 | 0.354 | 0.440 | 0.105 | ||
| 4 spectra, ALELDPNLYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.507 | 0.493 | ||
| 1 spectrum, IVFQEFR | 0.151 | 0.000 | 0.058 | 0.000 | 0.000 | 0.035 | 0.397 | 0.359 | ||
| 2 spectra, NTTPNFVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.416 | 0.584 | ||
| 2 spectra, FLFVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.267 | 0.733 | ||
| 2 spectra, STVAALEAK | 0.000 | 0.000 | 0.019 | 0.000 | 0.000 | 0.086 | 0.522 | 0.373 | ||
| 2 spectra, ENADLAGELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.290 | 0.710 | ||
| 2 spectra, IVDMYK | 0.000 | 0.000 | 0.000 | 0.183 | 0.000 | 0.000 | 0.438 | 0.380 | ||
| 2 spectra, VDYNASAWLTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.495 | 0.505 | ||
| 5 spectra, VKPLLQVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.539 | 0.461 | ||
| 2 spectra, SQQLQAER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.157 | 0.615 | 0.228 | ||
| 1 spectrum, NCAAYLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.424 | 0.576 | ||
| 2 spectra, ELDEATESNEAMGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.260 | 0.740 | ||
| 2 spectra, ELDDAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.406 | 0.594 | ||
| 1 spectrum, LQDLASTIEVMEEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | 0.226 | 0.478 | 0.282 | ||
| 2 spectra, VCHLVGINVTDFTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.365 | 0.635 | ||
| 2 spectra, LDEEITQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.302 | 0.698 | ||
| 5 spectra, EMEGLGQQYEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.486 | 0.514 | ||
| 2 spectra, ALETQMEEMR | 0.000 | 0.000 | 0.000 | 0.179 | 0.000 | 0.000 | 0.547 | 0.274 | ||
| 2 spectra, ALAAAAK | 0.043 | 0.000 | 0.000 | 0.045 | 0.000 | 0.000 | 0.344 | 0.568 | ||
| 3 spectra, SHEAQVQEMR | 0.000 | 0.000 | 0.000 | 0.110 | 0.000 | 0.000 | 0.487 | 0.403 | ||
| 1 spectrum, VEDMAELTCLNEASVLHNLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.324 | 0.676 | ||
| 2 spectra, GNEASFVPSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.167 | 0.501 | 0.333 | ||
| 4 spectra, ALDEETR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.359 | 0.641 | ||
| 1 spectrum, VSDLTTNLAEEEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.456 | 0.544 | ||
| 3 spectra, EQEVTMLK | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.197 | 0.468 | 0.273 | ||
| 2 spectra, EVLLQVEDER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.346 | 0.654 | ||
| 5 spectra, DSSITGELEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.403 | 0.597 | ||
| 1 spectrum, LDAFLVLEQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.273 | 0.727 | ||
| 1 spectrum, IVQLEEQIEQEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.267 | 0.733 | ||
| 2 spectra, TGVLAHLEEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.337 | 0.663 | ||
| 2 spectra, NVHELEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.450 | 0.550 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
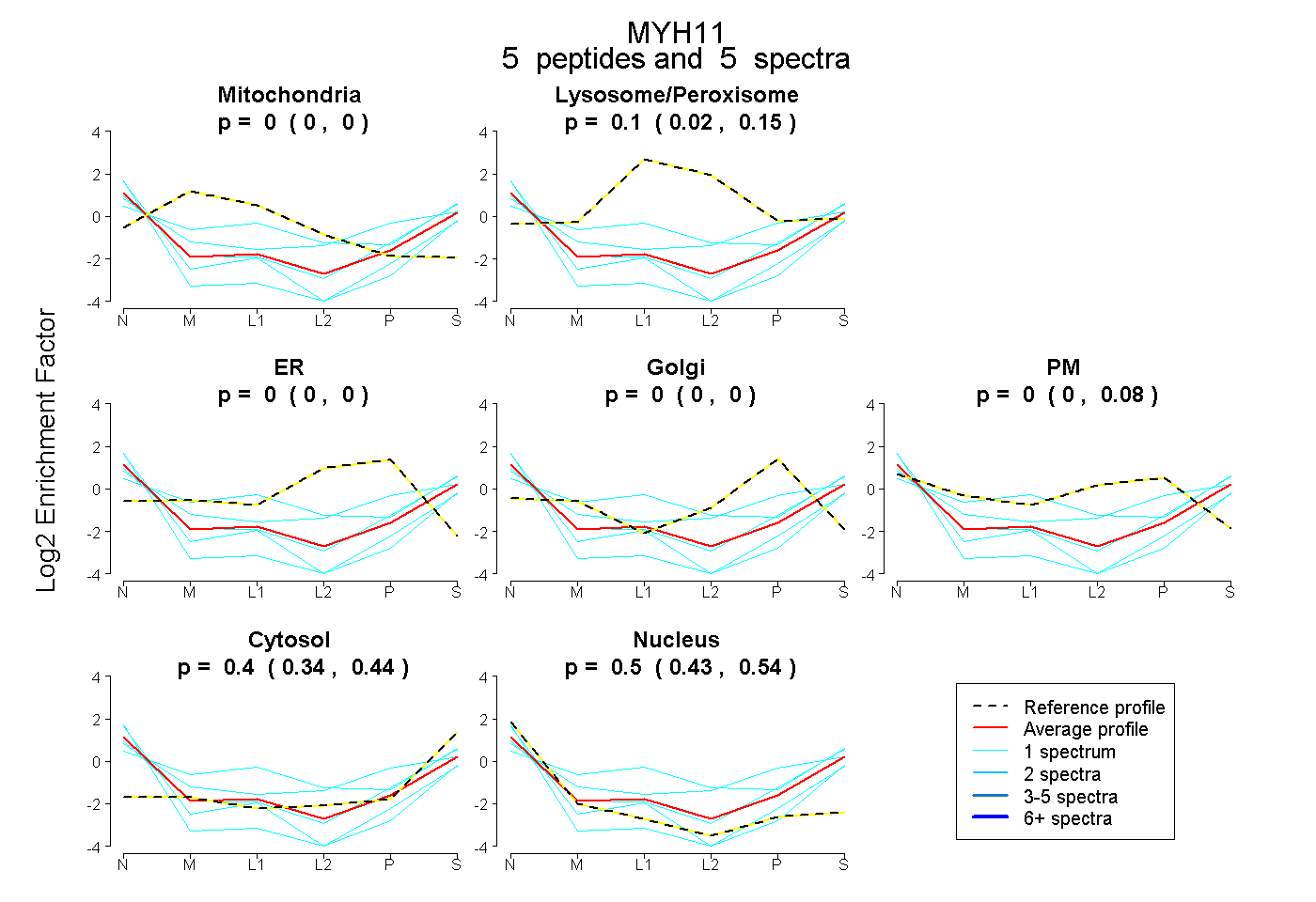 |
0.000 0.000 | 0.000 |
0.100 0.016 | 0.151 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.081 |
0.396 0.338 | 0.442 |
0.504 0.433 | 0.539 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
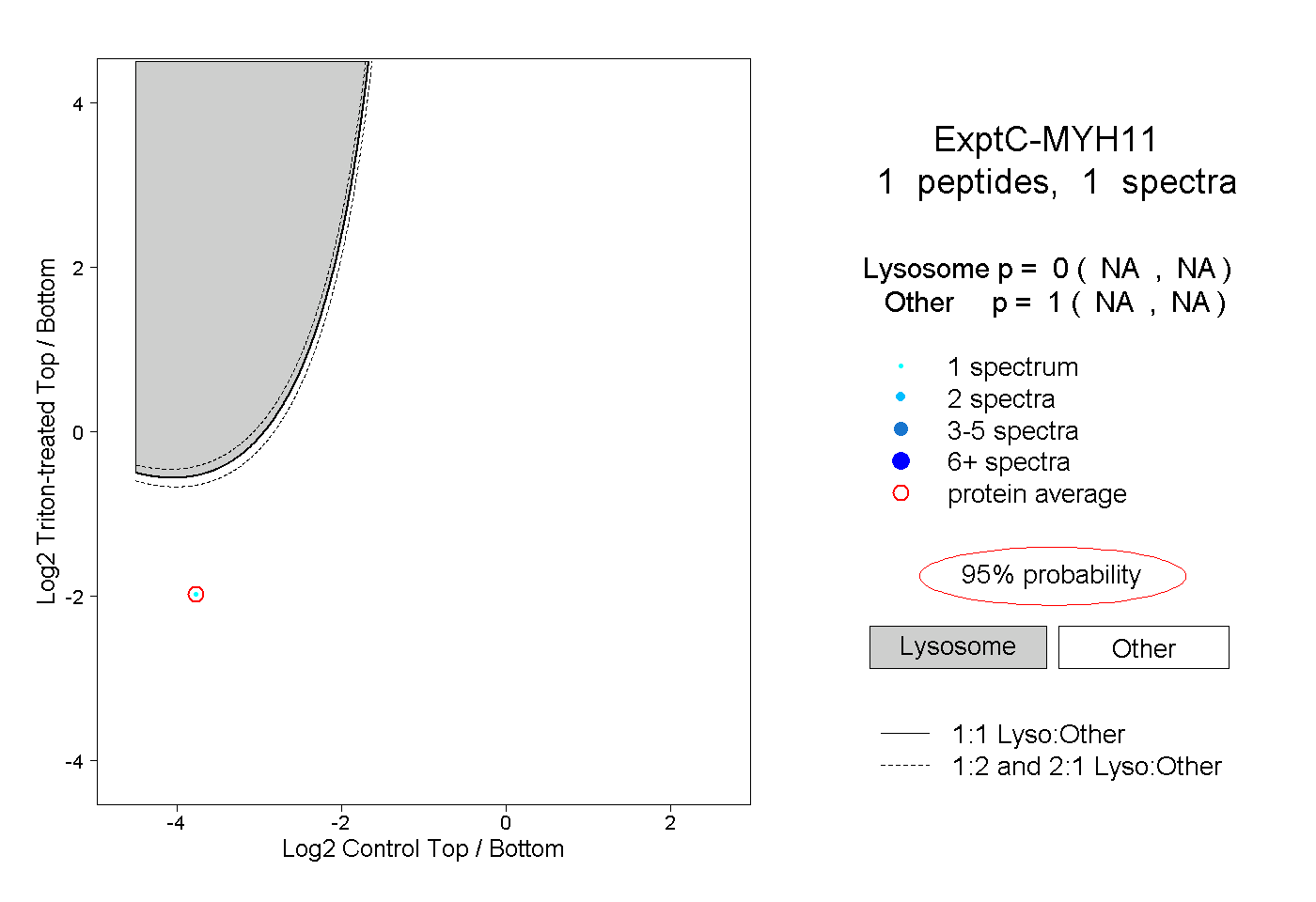 |
0.000 NA | NA |
1.000 NA | NA |