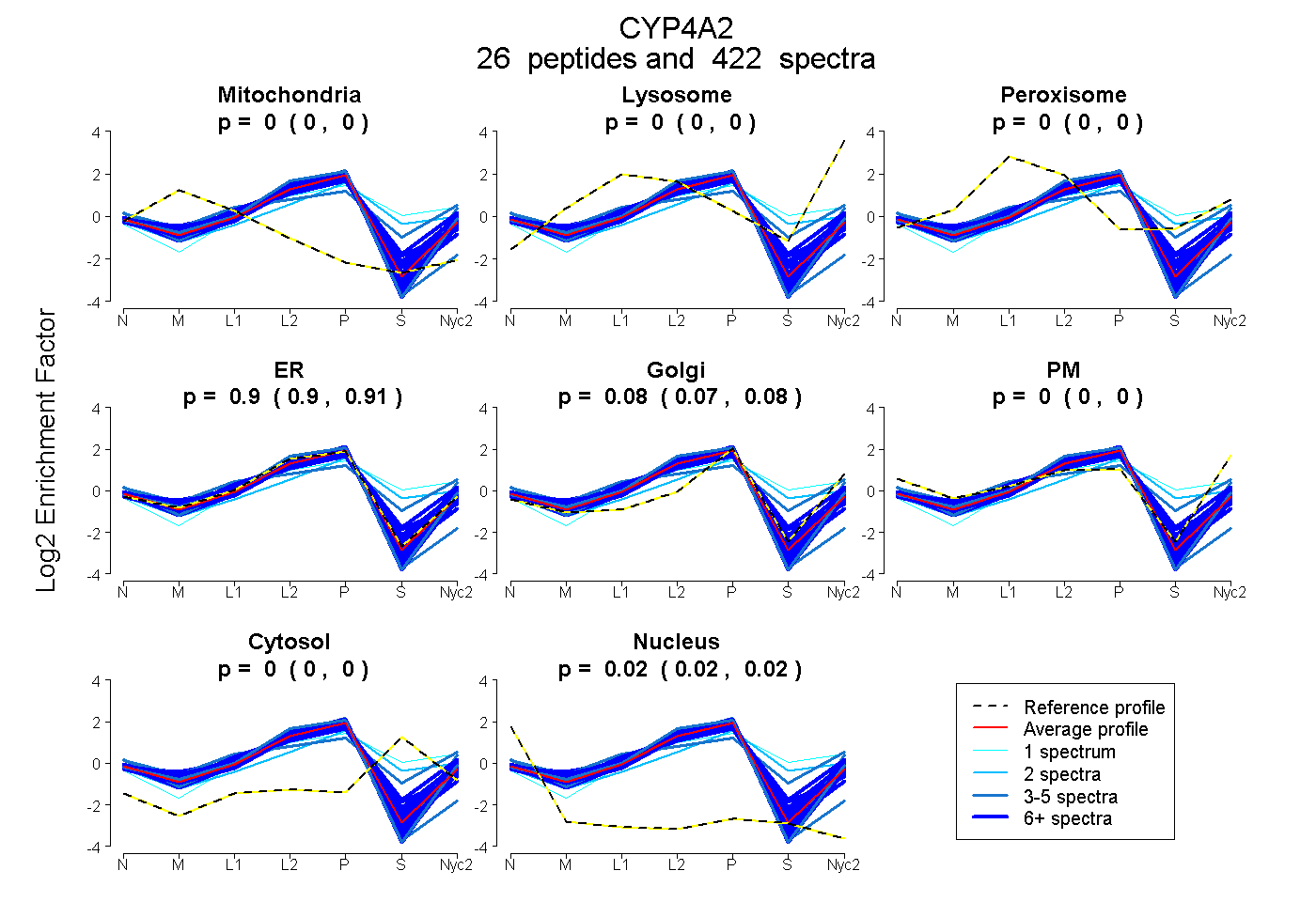
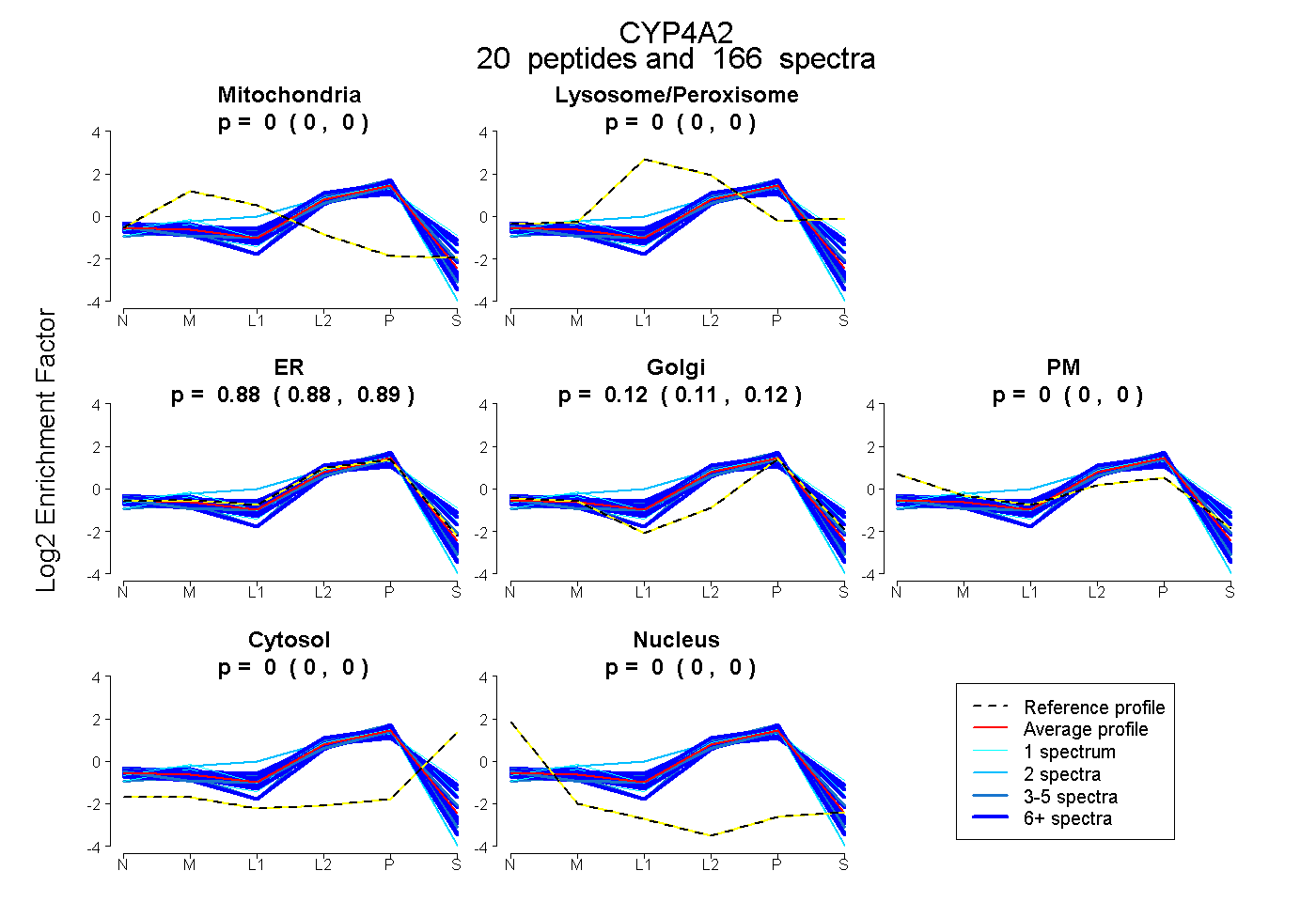
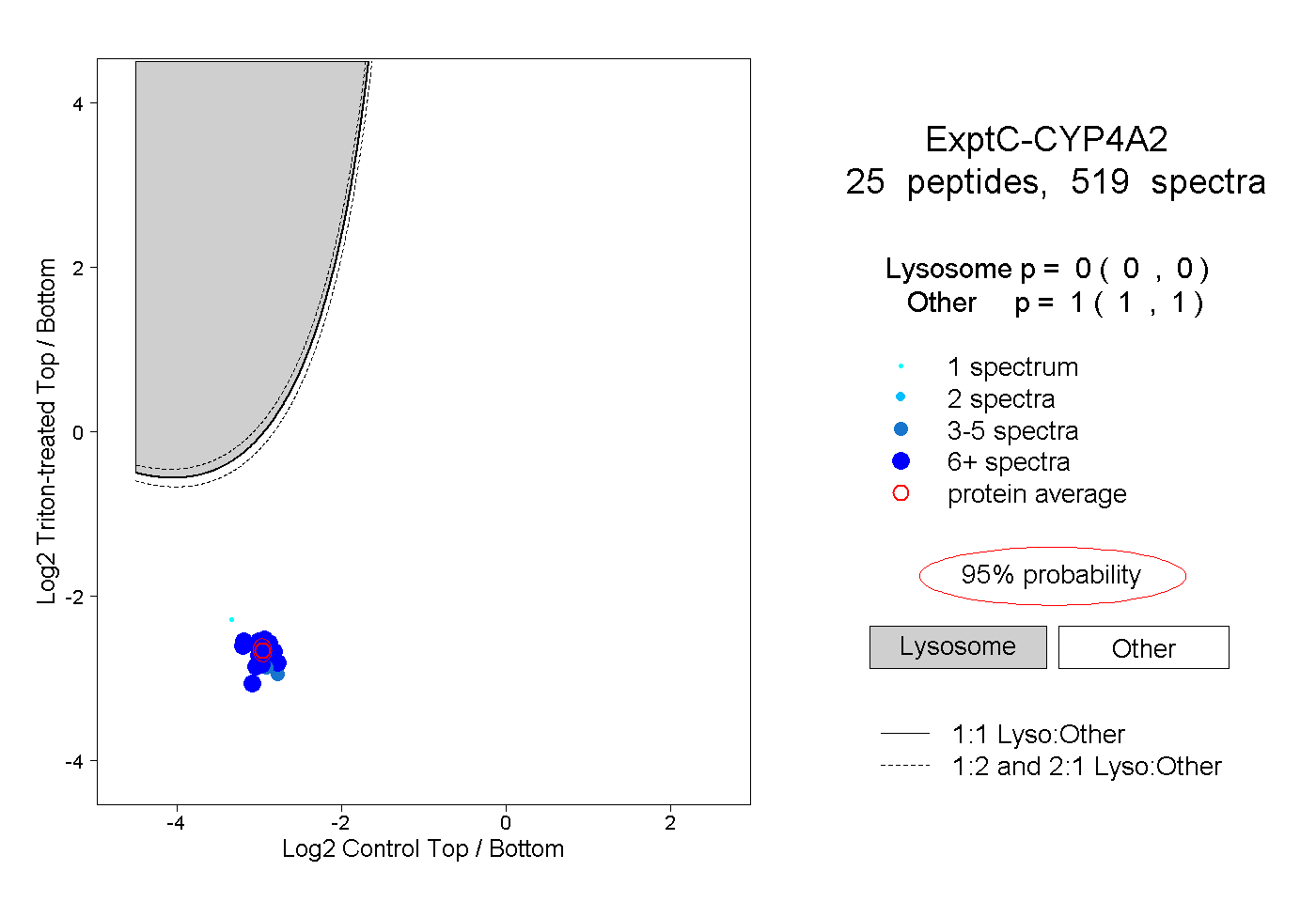
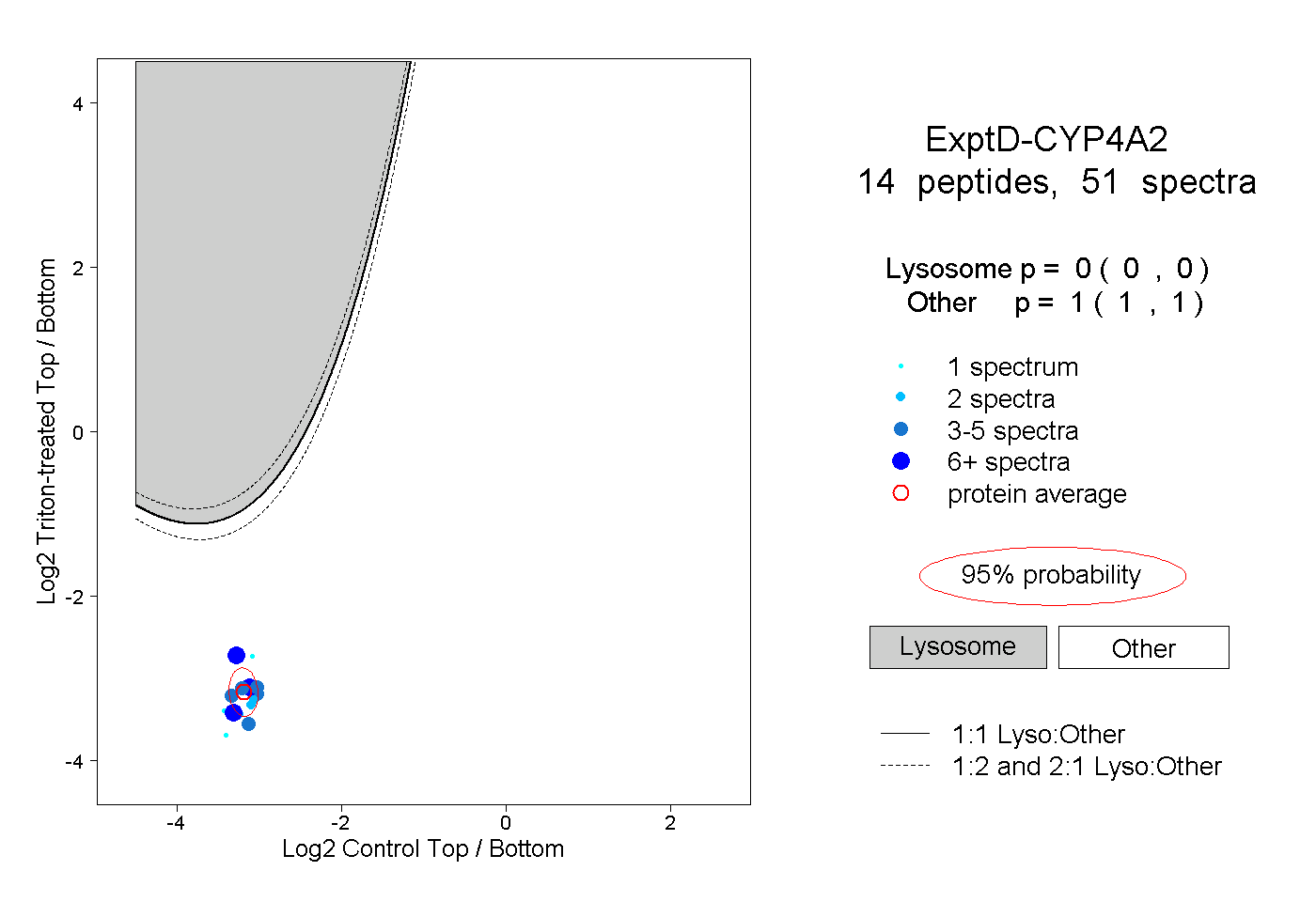
| 35 spectra, FELLPDPTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, ACQIAHEHTDGVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FPGACLQWLSGSTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 42 spectra, ELSSPVTFPDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, SAFYGNSIIYNMSSDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, QFAMNELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, IPVPMAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 58 spectra, FSPDSPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, AQLQNEEELQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, GFSVFSPTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, VAVALTLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, VFDPSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 39 spectra, VLLYDPDYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, CAFSHQGSVQLDVNSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, AVEDLNNLIFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, NGIHLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 60 spectra, SLSDEDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, MLTPAFHYDILKPYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, WFQHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AQLQDEEELQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, EFQQVLTWVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IMADSVSIMLDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AVQFYLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LYSPVPSVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HLDFLDILLFAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |