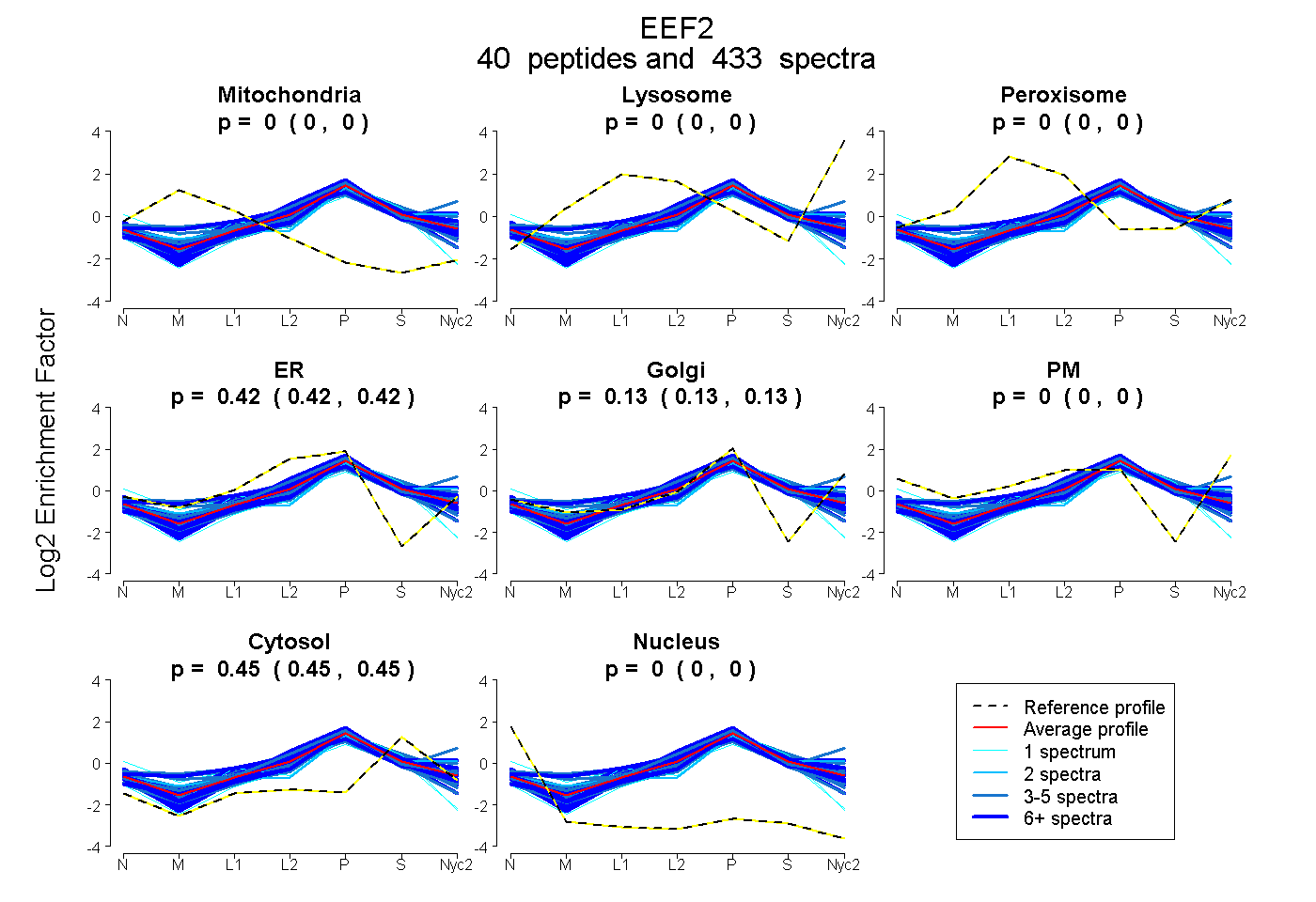
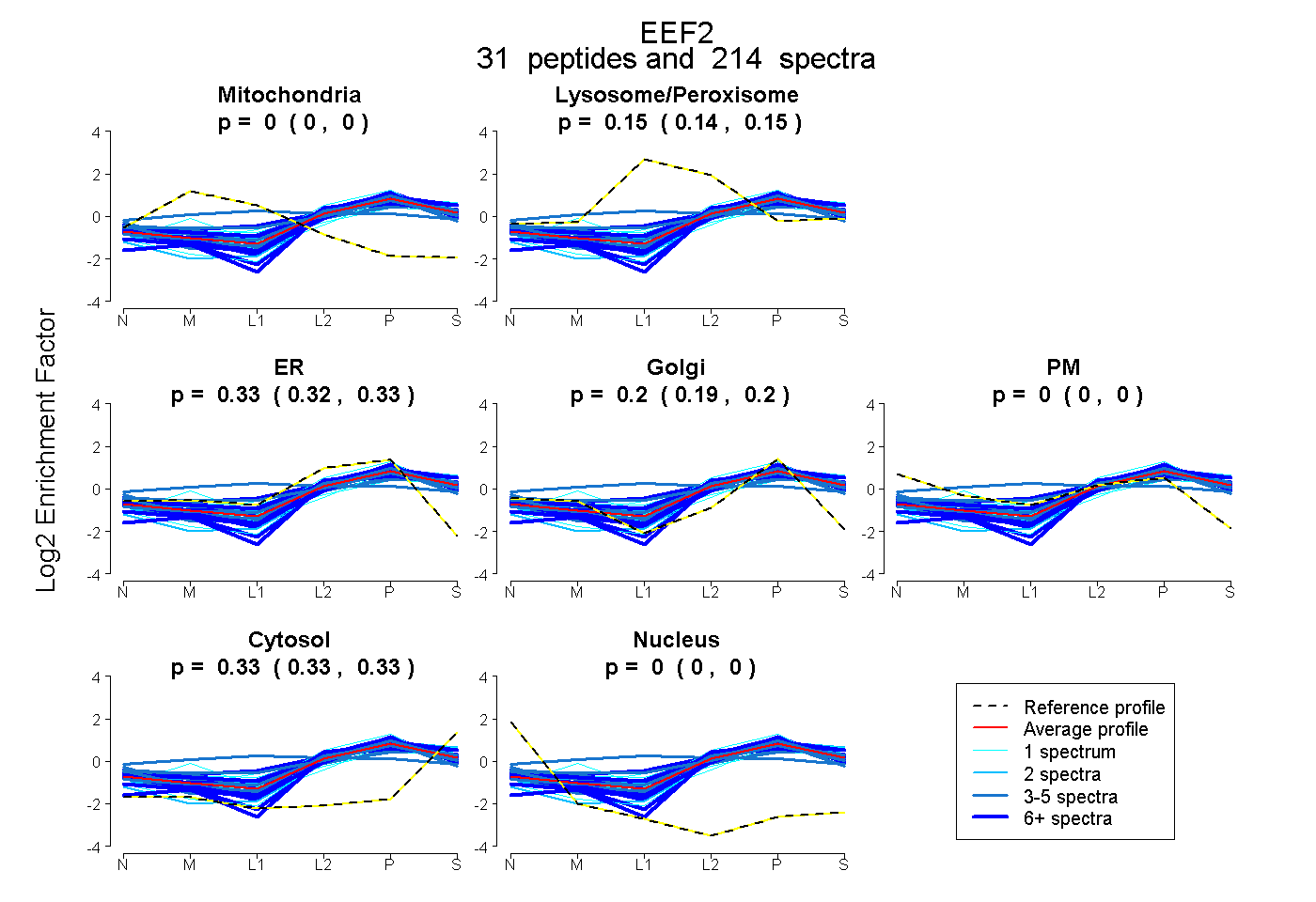
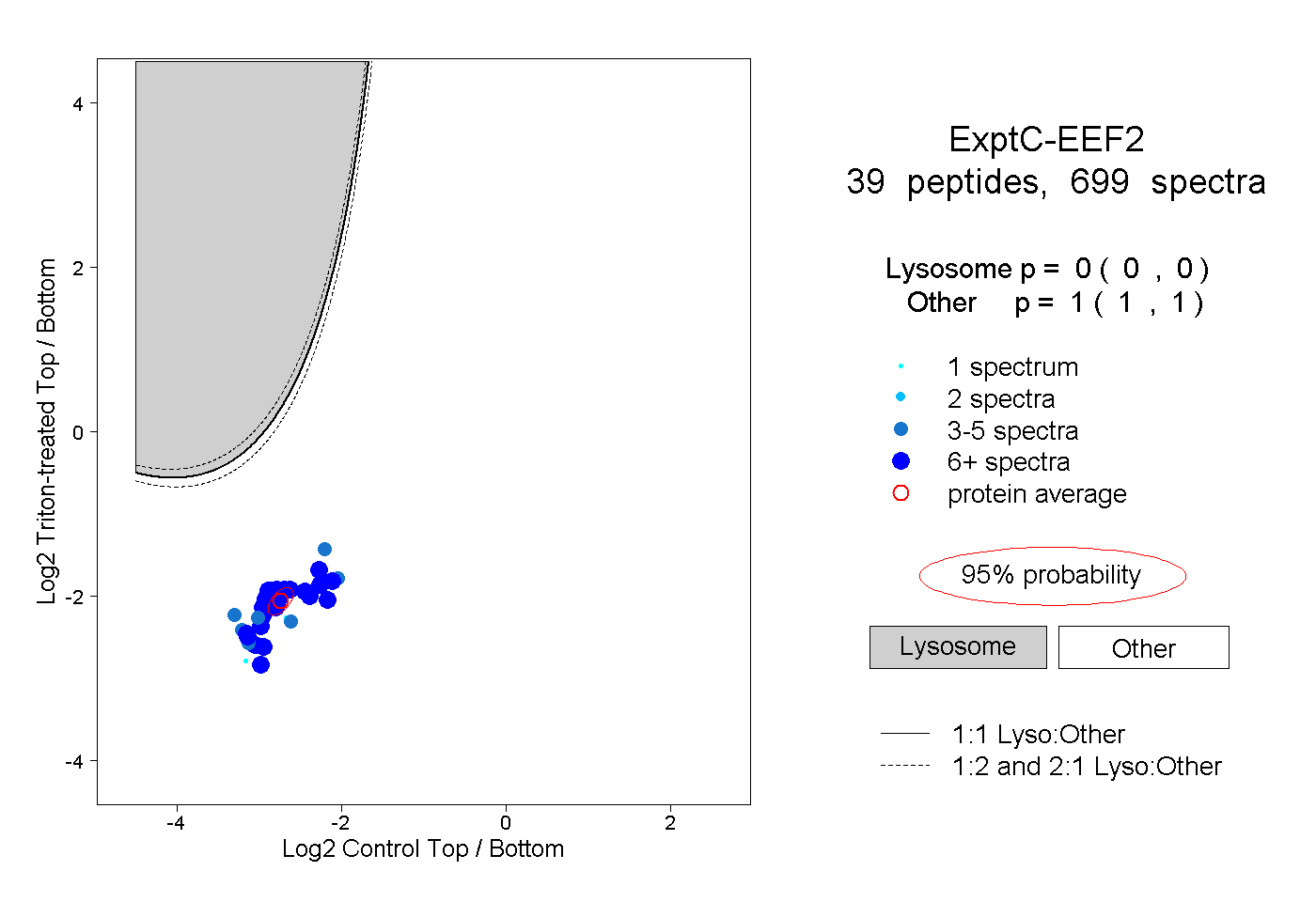
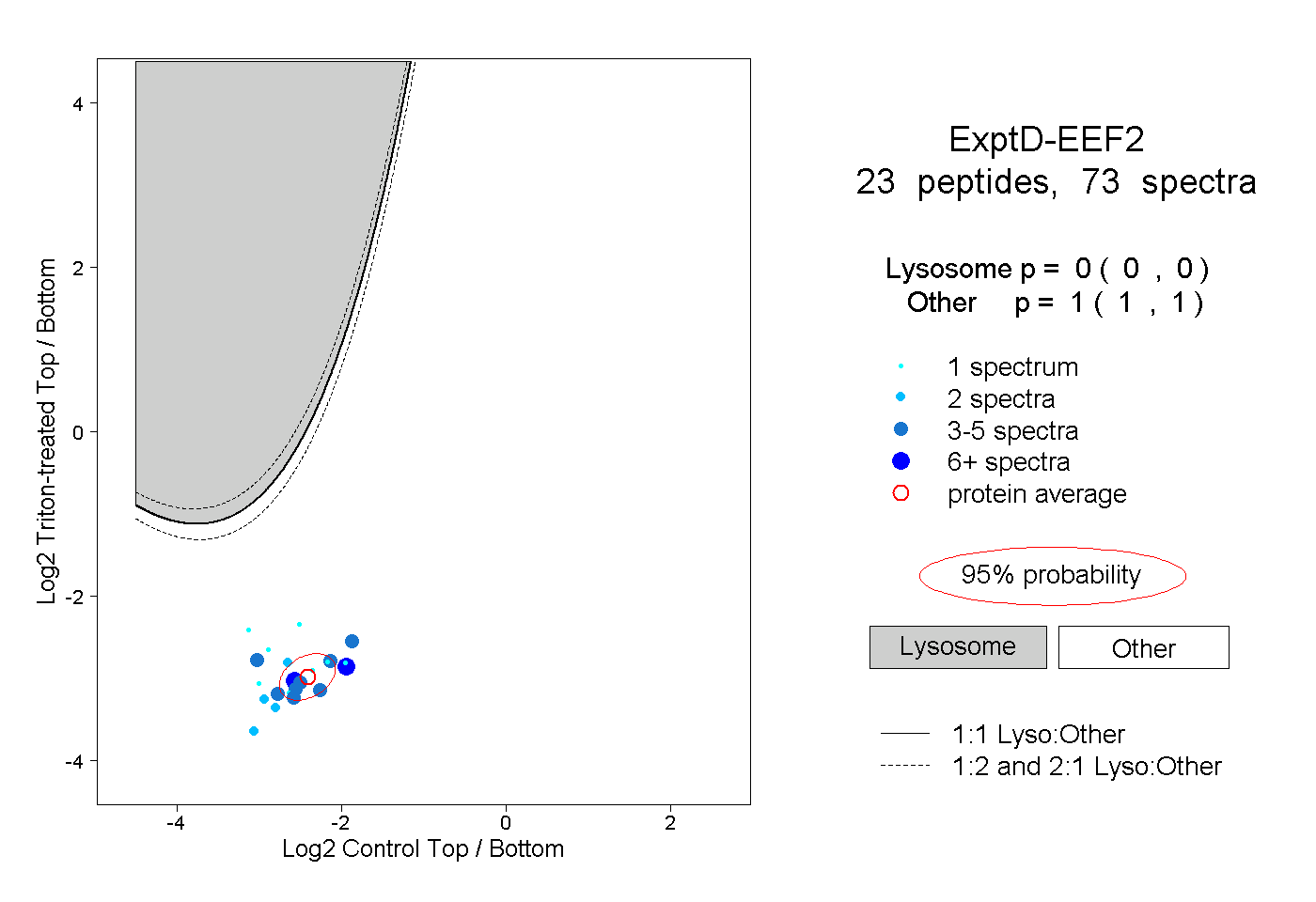
| 2 spectra, YEWDVAEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VEDMMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VFDAIMNFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IWCFGPDGTGPNILTDITK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EDLYLKPIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GVQYLNEIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GEGQLGAAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TGTITTFEHAHNMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EGALCEENMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ETVSEESNVLCLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AGIIASAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QFAEMYVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YFDPANGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VFSGVVSTGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SDPVVSYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TFCQLILDPIFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VNFTVDQIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SANSPDGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FYAFGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GPLMMYISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, GGGQIIPTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FSVSPVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, STLTDSLVCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |