peptides
spectra
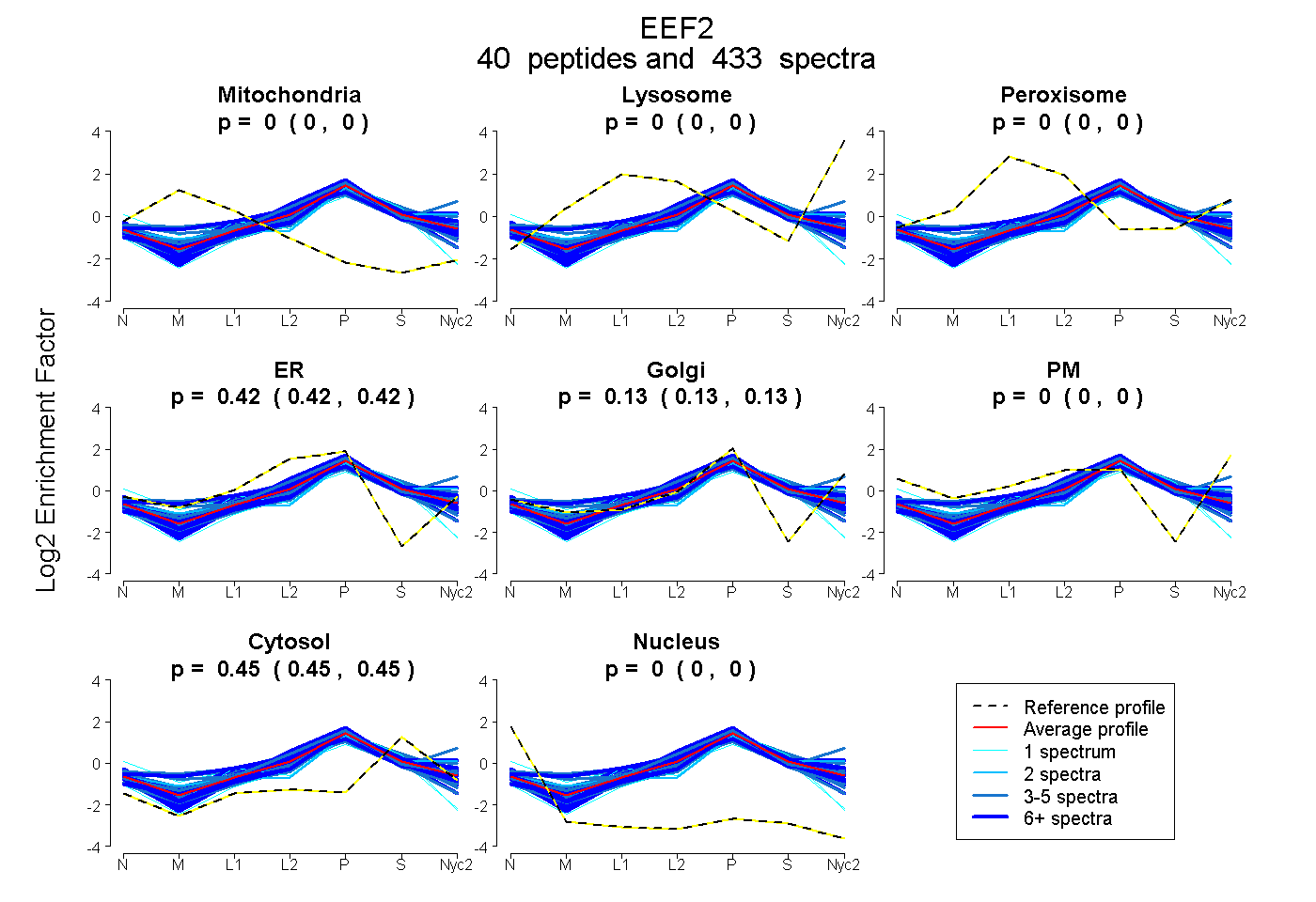
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.417 | 0.421
0.127 | 0.132
0.000 | 0.000
0.450 | 0.451
0.000 | 0.000
peptides
spectra
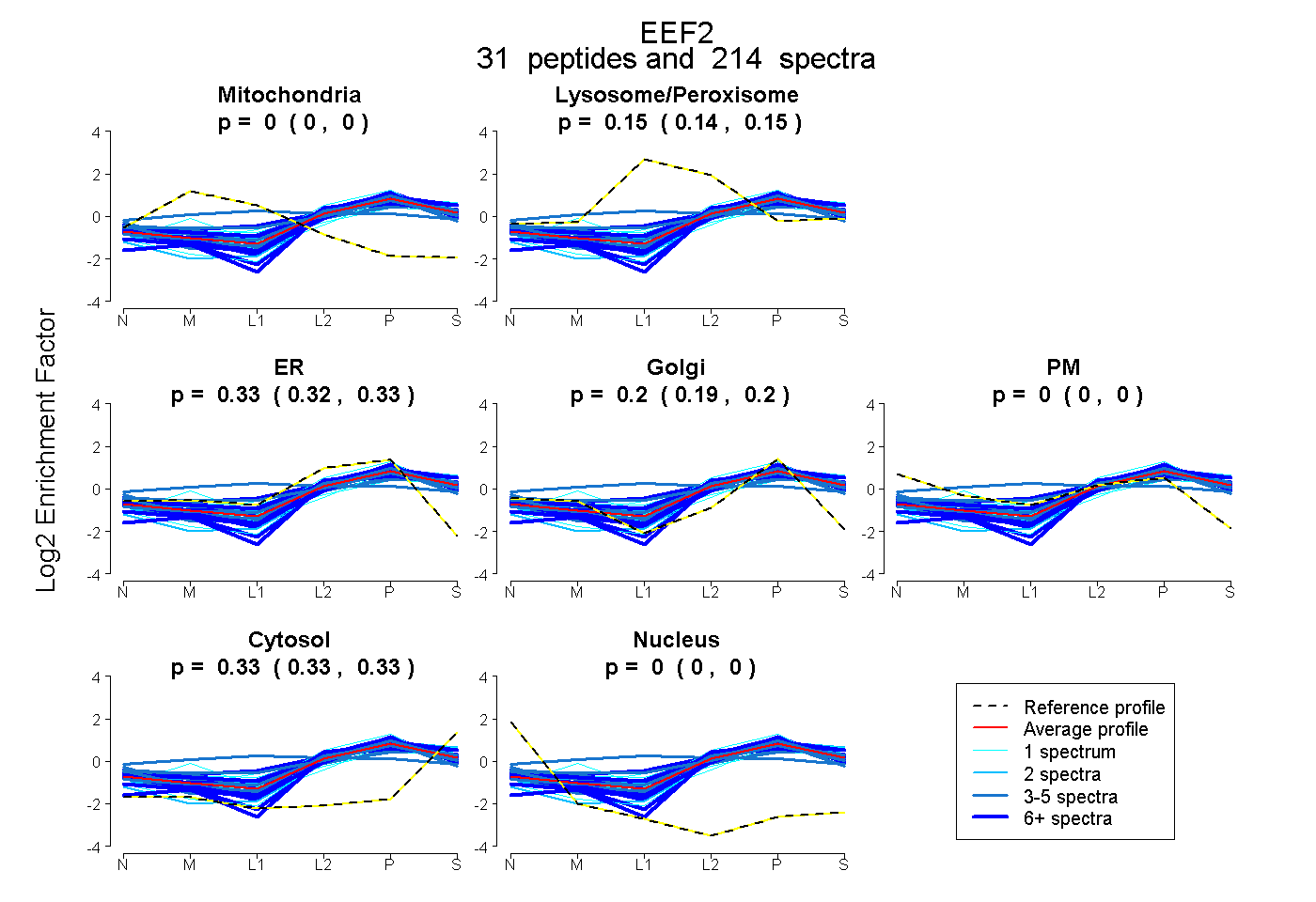
0.000 | 0.000
0.144 | 0.152
0.318 | 0.332
0.191 | 0.203
0.000 | 0.000
0.326 | 0.331
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
433 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.419 0.417 | 0.421 |
0.130 0.127 | 0.132 |
0.000 0.000 | 0.000 |
0.451 0.450 | 0.451 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
214 spectra |
 |
0.000 0.000 | 0.000 |
0.148 0.144 | 0.152 |
0.325 0.318 | 0.332 |
0.198 0.191 | 0.203 |
0.000 0.000 | 0.000 |
0.328 0.326 | 0.331 |
0.000 0.000 | 0.000 |
| 1 spectrum, EGKPLLK | 0.000 | 0.365 | 0.000 | 0.380 | 0.000 | 0.255 | 0.000 | |||
| 5 spectra, YEWDVAEAR | 0.000 | 0.152 | 0.351 | 0.180 | 0.000 | 0.316 | 0.000 | |||
| 1 spectrum, NPADLPK | 0.000 | 0.176 | 0.000 | 0.529 | 0.000 | 0.295 | 0.000 | |||
| 13 spectra, VFDAIMNFR | 0.000 | 0.046 | 0.519 | 0.000 | 0.000 | 0.435 | 0.000 | |||
| 21 spectra, GEGQLGAAER | 0.000 | 0.230 | 0.228 | 0.321 | 0.000 | 0.220 | 0.000 | |||
| 4 spectra, TGTITTFEHAHNMR | 0.055 | 0.422 | 0.000 | 0.176 | 0.185 | 0.162 | 0.000 | |||
| 5 spectra, ETVSEESNVLCLSK | 0.000 | 0.282 | 0.000 | 0.419 | 0.000 | 0.298 | 0.000 | |||
| 2 spectra, QFAEMYVAK | 0.000 | 0.189 | 0.336 | 0.126 | 0.000 | 0.349 | 0.000 | |||
| 3 spectra, YFDPANGK | 0.000 | 0.362 | 0.000 | 0.444 | 0.000 | 0.194 | 0.000 | |||
| 5 spectra, VFSGVVSTGLK | 0.000 | 0.120 | 0.406 | 0.112 | 0.000 | 0.362 | 0.000 | |||
| 12 spectra, TFCQLILDPIFK | 0.000 | 0.264 | 0.187 | 0.251 | 0.000 | 0.298 | 0.000 | |||
| 13 spectra, TILMMGR | 0.000 | 0.000 | 0.425 | 0.105 | 0.000 | 0.470 | 0.000 | |||
| 2 spectra, DSVVAGFQWATK | 0.000 | 0.139 | 0.372 | 0.123 | 0.000 | 0.366 | 0.000 | |||
| 1 spectrum, CELLYEGPPDDEAAMGIK | 0.000 | 0.343 | 0.006 | 0.399 | 0.000 | 0.252 | 0.000 | |||
| 6 spectra, GPLMMYISK | 0.000 | 0.394 | 0.000 | 0.397 | 0.000 | 0.209 | 0.000 | |||
| 2 spectra, DLEEDHACIPIK | 0.000 | 0.000 | 0.485 | 0.000 | 0.000 | 0.515 | 0.000 | |||
| 20 spectra, FSVSPVVR | 0.000 | 0.000 | 0.384 | 0.288 | 0.000 | 0.328 | 0.000 | |||
| 1 spectrum, CLYASVLTAQPR | 0.000 | 0.113 | 0.326 | 0.241 | 0.000 | 0.320 | 0.000 | |||
| 4 spectra, EDLYLKPIQR | 0.000 | 0.215 | 0.266 | 0.278 | 0.000 | 0.241 | 0.000 | |||
| 1 spectrum, IKPVLMMNK | 0.000 | 0.262 | 0.000 | 0.410 | 0.000 | 0.328 | 0.000 | |||
| 3 spectra, IWCFGPDGTGPNILTDITK | 0.000 | 0.313 | 0.000 | 0.335 | 0.018 | 0.333 | 0.000 | |||
| 5 spectra, EGALCEENMR | 0.000 | 0.055 | 0.497 | 0.000 | 0.000 | 0.448 | 0.000 | |||
| 17 spectra, AGIIASAR | 0.000 | 0.007 | 0.465 | 0.186 | 0.000 | 0.343 | 0.000 | |||
| 1 spectrum, GHVFEESQVAGTPMFVVK | 0.000 | 0.000 | 0.495 | 0.000 | 0.000 | 0.505 | 0.000 | |||
| 6 spectra, SDPVVSYR | 0.000 | 0.079 | 0.308 | 0.308 | 0.000 | 0.304 | 0.000 | |||
| 2 spectra, EGIPALDNFLDK | 0.000 | 0.190 | 0.366 | 0.160 | 0.000 | 0.284 | 0.000 | |||
| 18 spectra, VNFTVDQIR | 0.000 | 0.013 | 0.482 | 0.150 | 0.000 | 0.355 | 0.000 | |||
| 1 spectrum, SANSPDGK | 0.000 | 0.047 | 0.664 | 0.017 | 0.000 | 0.272 | 0.000 | |||
| 20 spectra, FYAFGR | 0.000 | 0.145 | 0.422 | 0.143 | 0.000 | 0.291 | 0.000 | |||
| 16 spectra, GGGQIIPTAR | 0.000 | 0.222 | 0.088 | 0.448 | 0.000 | 0.242 | 0.000 | |||
| 3 spectra, STLTDSLVCK | 0.000 | 0.183 | 0.182 | 0.427 | 0.000 | 0.207 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
699 spectra |
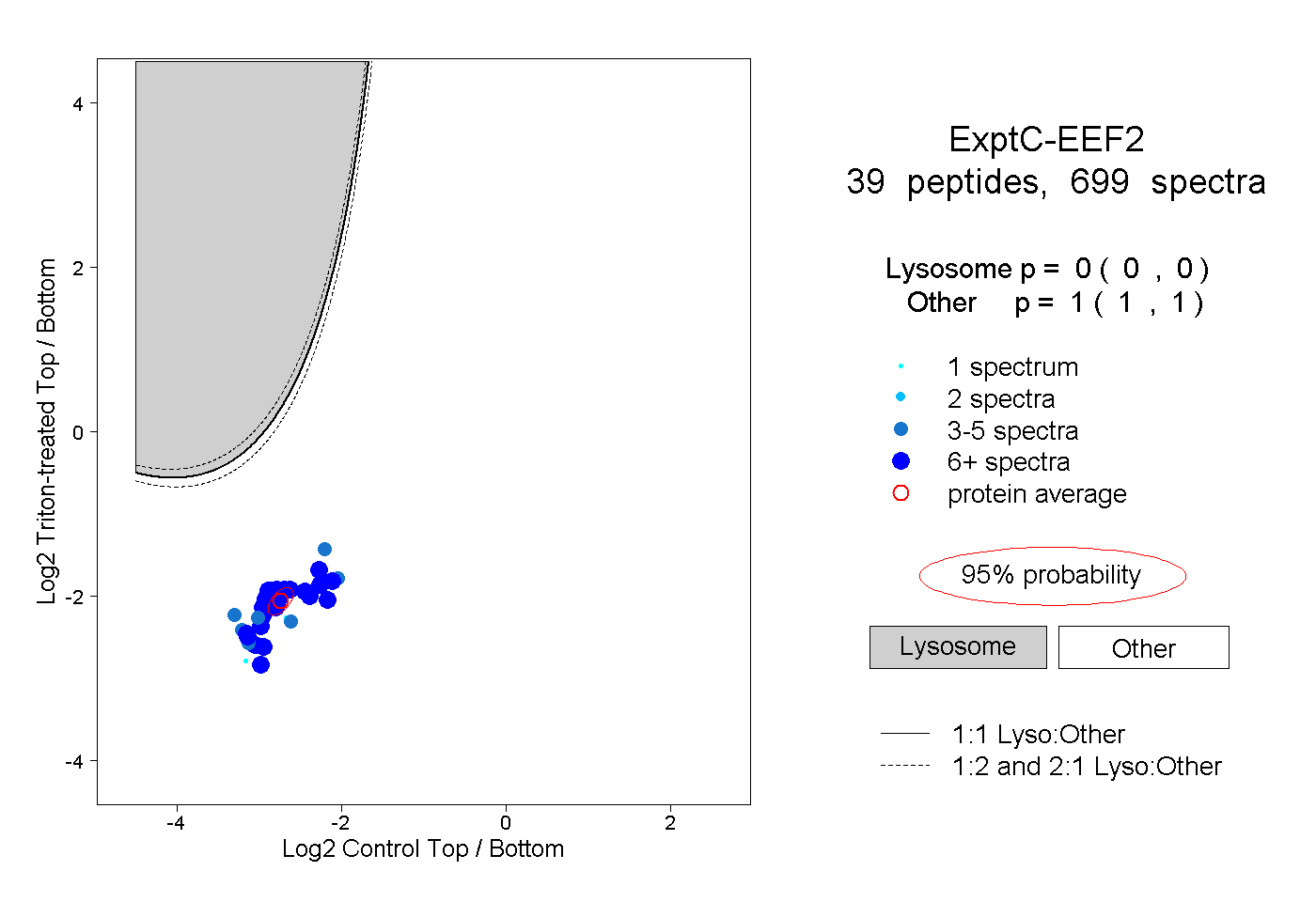 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
73 spectra |
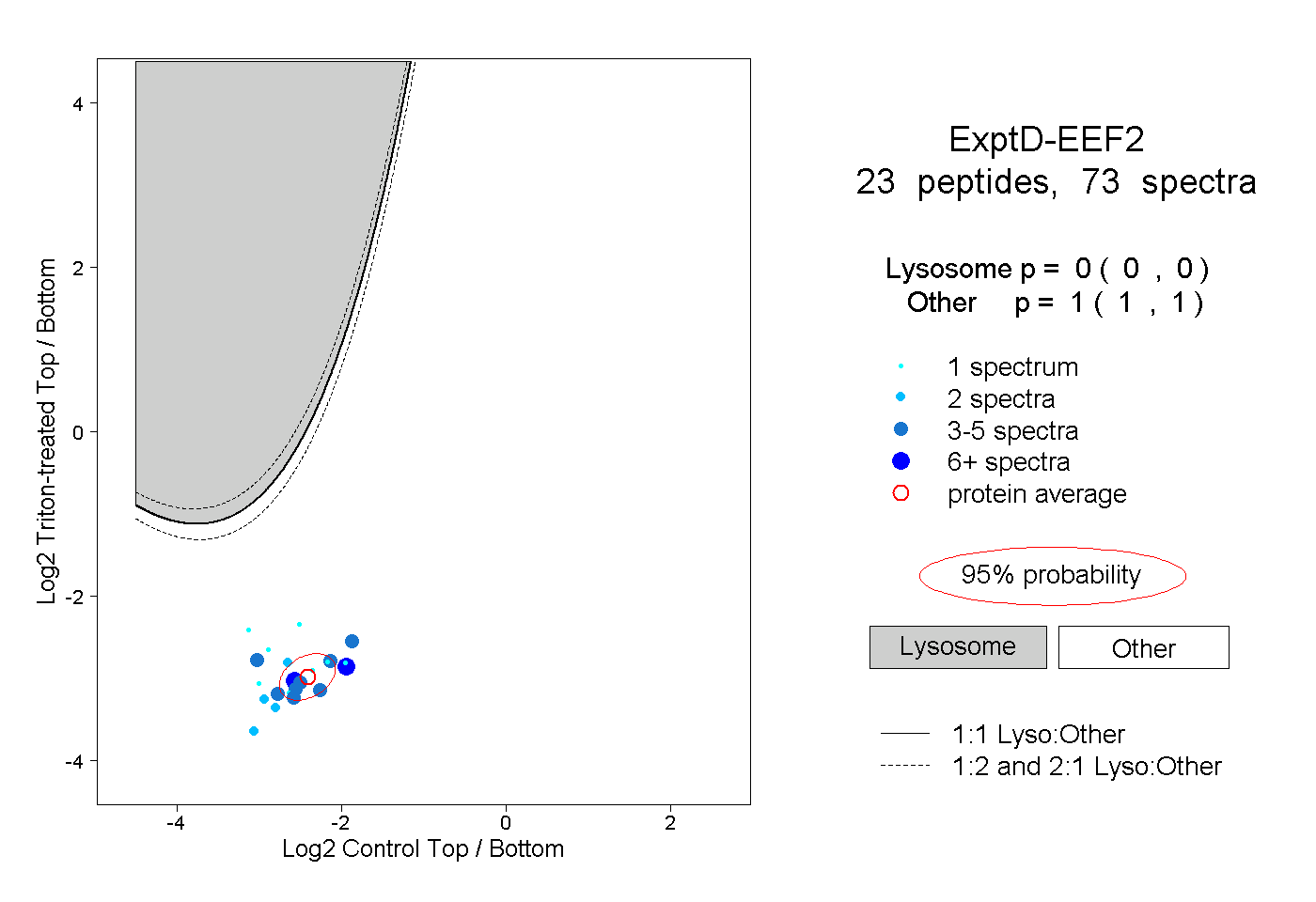 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |