peptides
spectra
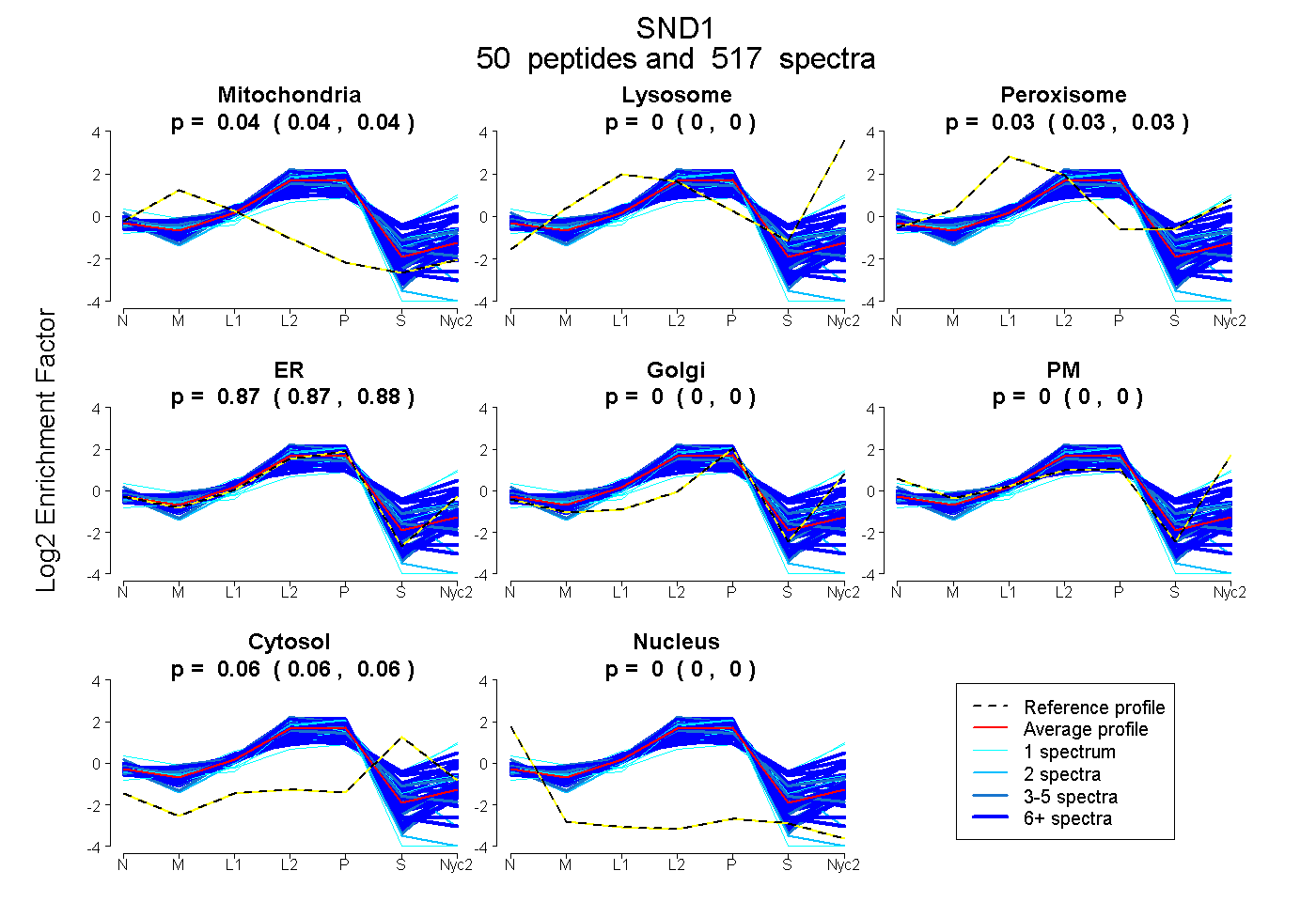
0.035 | 0.038
0.000 | 0.000
0.027 | 0.029
0.873 | 0.876
0.000 | 0.000
0.000 | 0.000
0.060 | 0.062
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
517 spectra |
 |
0.037 0.035 | 0.038 |
0.000 0.000 | 0.000 |
0.028 0.027 | 0.029 |
0.874 0.873 | 0.876 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.061 0.060 | 0.062 |
0.000 0.000 | 0.000 |
| 1 spectrum, SAYYKPLLSAEEAAK | 0.000 | 0.264 | 0.000 | 0.547 | 0.000 | 0.035 | 0.155 | 0.000 | ||
| 13 spectra, FVDGEWYR | 0.013 | 0.000 | 0.055 | 0.899 | 0.000 | 0.000 | 0.033 | 0.000 | ||
| 4 spectra, VITEYLNAQESAK | 0.065 | 0.000 | 0.023 | 0.843 | 0.000 | 0.000 | 0.069 | 0.000 | ||
| 27 spectra, LGALPPAFSTR | 0.040 | 0.000 | 0.000 | 0.952 | 0.000 | 0.000 | 0.000 | 0.008 | ||
| 13 spectra, EILPSTR | 0.059 | 0.000 | 0.008 | 0.912 | 0.000 | 0.000 | 0.021 | 0.000 | ||
| 2 spectra, VSVTVDYIRPASPATETVPAFSER | 0.073 | 0.000 | 0.000 | 0.820 | 0.000 | 0.000 | 0.000 | 0.107 | ||
| 8 spectra, TIHLSSIRPPR | 0.000 | 0.000 | 0.274 | 0.443 | 0.173 | 0.000 | 0.110 | 0.000 | ||
| 3 spectra, VHFTAER | 0.002 | 0.000 | 0.200 | 0.682 | 0.000 | 0.000 | 0.116 | 0.000 | ||
| 27 spectra, QINLSNIR | 0.000 | 0.000 | 0.004 | 0.996 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, NLPGLVQEGEPFSEEATLFTK | 0.160 | 0.000 | 0.058 | 0.542 | 0.000 | 0.062 | 0.178 | 0.000 | ||
| 1 spectrum, SILTSPR | 0.004 | 0.000 | 0.115 | 0.701 | 0.000 | 0.000 | 0.180 | 0.000 | ||
| 8 spectra, EVCFTIENK | 0.016 | 0.000 | 0.000 | 0.852 | 0.000 | 0.000 | 0.128 | 0.005 | ||
| 14 spectra, LSECEEQAK | 0.036 | 0.000 | 0.046 | 0.808 | 0.000 | 0.000 | 0.080 | 0.030 | ||
| 21 spectra, QFLPFLQR | 0.030 | 0.000 | 0.000 | 0.968 | 0.000 | 0.000 | 0.000 | 0.001 | ||
| 14 spectra, VADISGDTQK | 0.035 | 0.000 | 0.032 | 0.911 | 0.000 | 0.000 | 0.022 | 0.000 | ||
| 3 spectra, DYVPPTANLDQK | 0.000 | 0.000 | 0.034 | 0.870 | 0.000 | 0.000 | 0.049 | 0.047 | ||
| 16 spectra, YTIENPR | 0.002 | 0.000 | 0.000 | 0.962 | 0.000 | 0.000 | 0.036 | 0.000 | ||
| 2 spectra, DTNGENIAESLVAEGLASR | 0.000 | 0.000 | 0.000 | 0.806 | 0.000 | 0.000 | 0.136 | 0.058 | ||
| 8 spectra, DGSVVR | 0.000 | 0.000 | 0.142 | 0.711 | 0.045 | 0.029 | 0.073 | 0.000 | ||
| 9 spectra, VESPAK | 0.050 | 0.000 | 0.003 | 0.907 | 0.000 | 0.000 | 0.040 | 0.000 | ||
| 17 spectra, LRPLYDIPYMFEAR | 0.057 | 0.000 | 0.002 | 0.902 | 0.000 | 0.000 | 0.038 | 0.000 | ||
| 9 spectra, EVPIHR | 0.012 | 0.000 | 0.147 | 0.790 | 0.000 | 0.000 | 0.051 | 0.000 | ||
| 1 spectrum, LMENMR | 0.000 | 0.000 | 0.069 | 0.840 | 0.000 | 0.000 | 0.091 | 0.000 | ||
| 11 spectra, LNSGDYK | 0.063 | 0.000 | 0.000 | 0.935 | 0.000 | 0.000 | 0.000 | 0.002 | ||
| 68 spectra, ADDADEFGYSR | 0.016 | 0.000 | 0.000 | 0.912 | 0.000 | 0.000 | 0.000 | 0.072 | ||
| 4 spectra, ELVLQR | 0.000 | 0.000 | 0.034 | 0.837 | 0.000 | 0.000 | 0.129 | 0.000 | ||
| 10 spectra, EVEVEVESMDK | 0.000 | 0.000 | 0.112 | 0.699 | 0.000 | 0.000 | 0.189 | 0.000 | ||
| 14 spectra, LEGDNIQDK | 0.000 | 0.000 | 0.063 | 0.768 | 0.000 | 0.000 | 0.169 | 0.000 | ||
| 8 spectra, VHVFYIDYGNR | 0.000 | 0.000 | 0.293 | 0.304 | 0.127 | 0.074 | 0.201 | 0.000 | ||
| 6 spectra, ANNPEQNR | 0.000 | 0.000 | 0.000 | 0.988 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 8 spectra, AAATQPDGK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, CPTFR | 0.000 | 0.000 | 0.187 | 0.644 | 0.017 | 0.000 | 0.152 | 0.000 | ||
| 21 spectra, EGLVMVEVR | 0.038 | 0.000 | 0.015 | 0.869 | 0.000 | 0.000 | 0.079 | 0.000 | ||
| 2 spectra, EYGMIYLGK | 0.024 | 0.000 | 0.058 | 0.879 | 0.000 | 0.000 | 0.039 | 0.000 | ||
| 6 spectra, GDVGLGLVK | 0.000 | 0.000 | 0.044 | 0.772 | 0.000 | 0.000 | 0.184 | 0.000 | ||
| 8 spectra, SDISSHPPVEGAYAPR | 0.000 | 0.000 | 0.356 | 0.126 | 0.320 | 0.044 | 0.153 | 0.000 | ||
| 14 spectra, SEAVVEYVFSGSR | 0.058 | 0.000 | 0.000 | 0.921 | 0.000 | 0.000 | 0.012 | 0.009 | ||
| 5 spectra, DTPDEPWAFPAR | 0.033 | 0.000 | 0.000 | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, TDAVDSVVR | 0.042 | 0.000 | 0.019 | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, ETCLITFLLAGIECPR | 0.000 | 0.054 | 0.315 | 0.111 | 0.151 | 0.225 | 0.144 | 0.000 | ||
| 4 spectra, FFTESR | 0.020 | 0.000 | 0.000 | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, GLATVIR | 0.069 | 0.000 | 0.000 | 0.923 | 0.000 | 0.000 | 0.007 | 0.000 | ||
| 14 spectra, AGNLAR | 0.000 | 0.000 | 0.112 | 0.721 | 0.000 | 0.000 | 0.167 | 0.000 | ||
| 5 spectra, ETDGSETPEPFAAEAK | 0.000 | 0.000 | 0.000 | 0.875 | 0.000 | 0.000 | 0.115 | 0.010 | ||
| 27 spectra, MVLSGCAIIVR | 0.120 | 0.000 | 0.000 | 0.846 | 0.000 | 0.000 | 0.000 | 0.034 | ||
| 10 spectra, GGPPPER | 0.022 | 0.000 | 0.000 | 0.895 | 0.000 | 0.000 | 0.063 | 0.019 | ||
| 6 spectra, CVDWSIAVYTR | 0.052 | 0.000 | 0.000 | 0.871 | 0.000 | 0.000 | 0.064 | 0.012 | ||
| 9 spectra, VMQVLNADAIVVK | 0.057 | 0.000 | 0.000 | 0.882 | 0.000 | 0.000 | 0.000 | 0.061 | ||
| 13 spectra, SSHYDELLAAEAR | 0.000 | 0.000 | 0.221 | 0.565 | 0.000 | 0.009 | 0.206 | 0.000 | ||
| 1 spectrum, VWAHYEEQPVEEVMPVLEEK | 0.009 | 0.000 | 0.000 | 0.825 | 0.000 | 0.000 | 0.000 | 0.166 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
194 spectra |
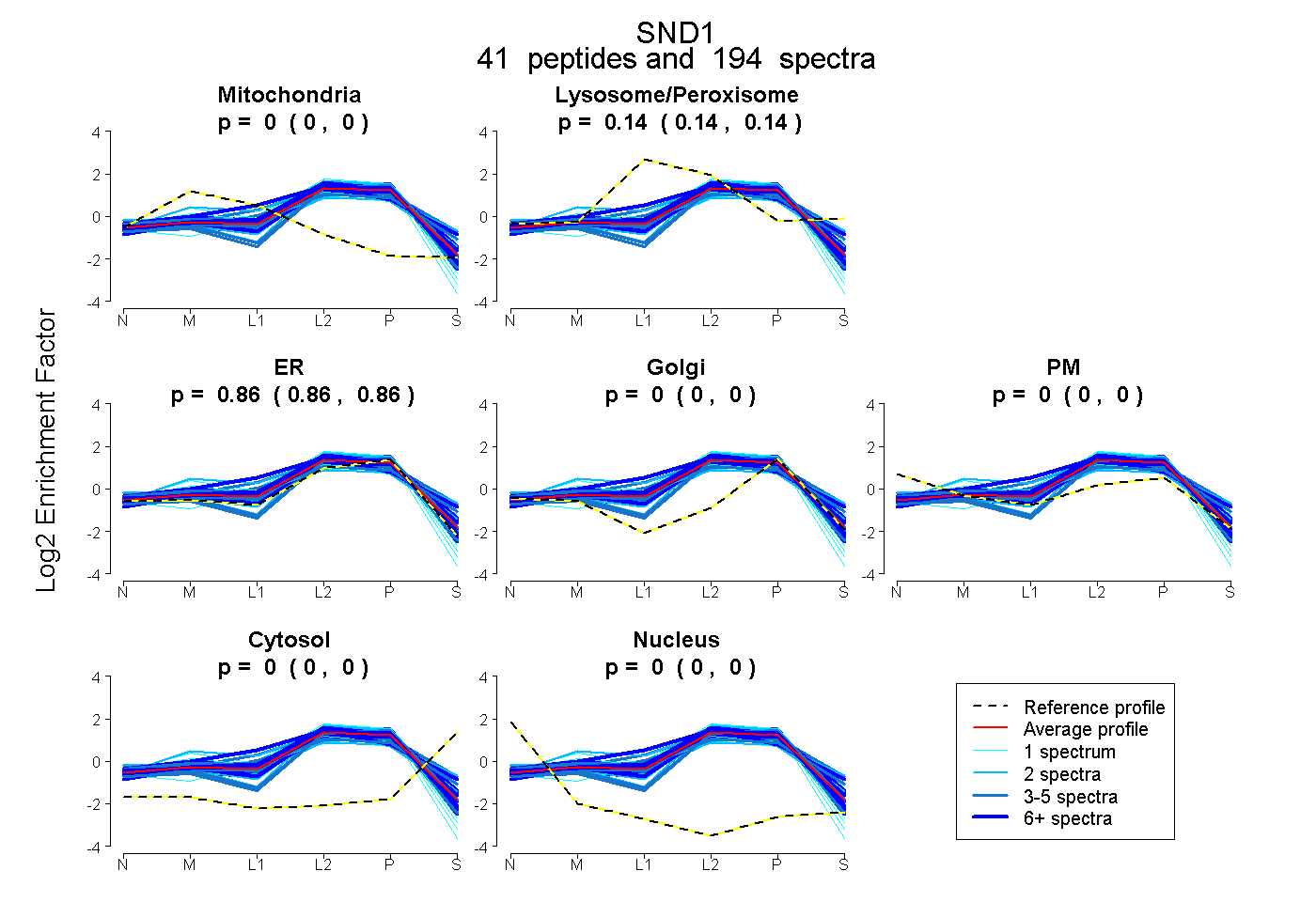 |
0.000 0.000 | 0.000 |
0.139 0.137 | 0.141 |
0.861 0.859 | 0.862 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
634 spectra |
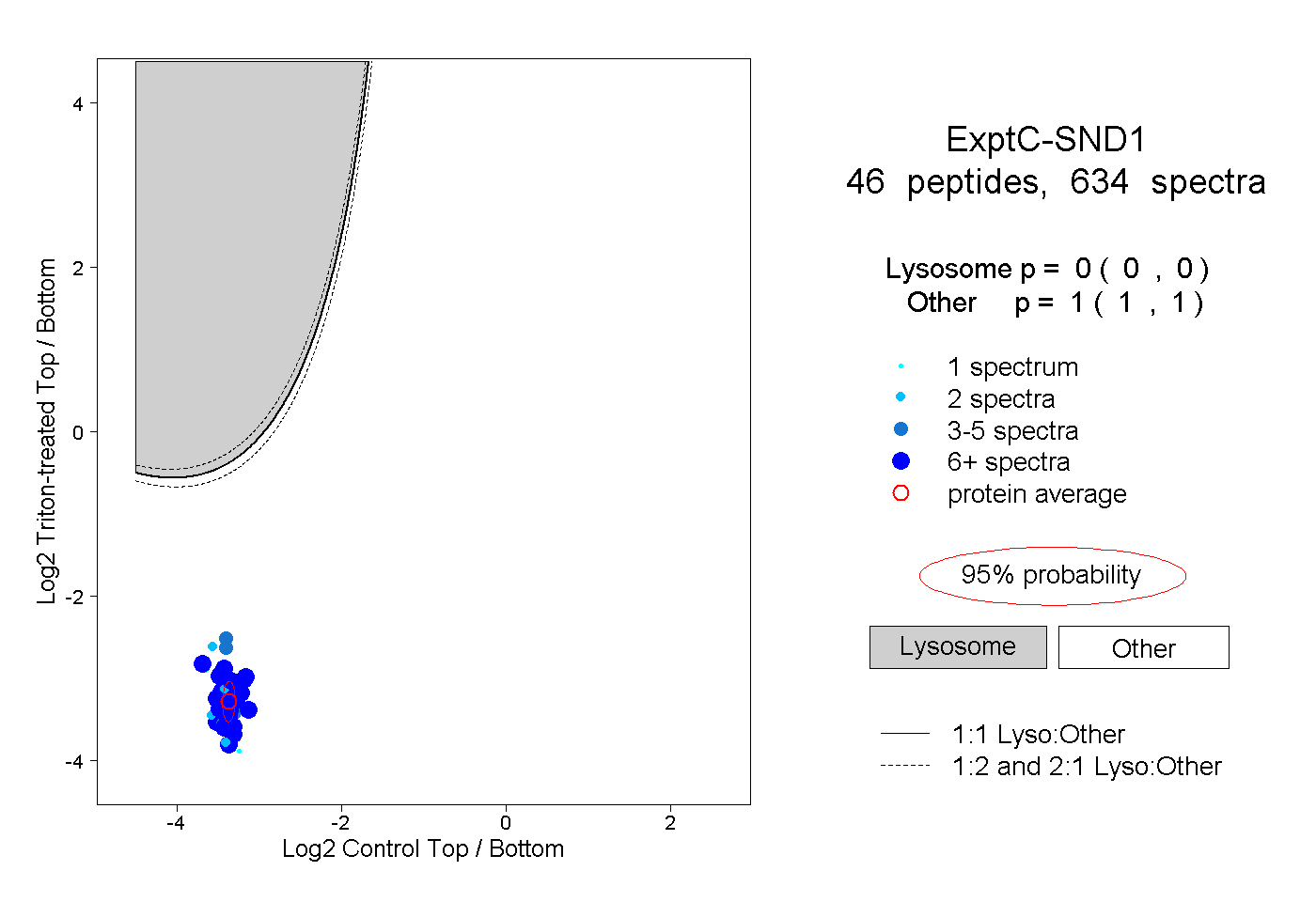 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
89 spectra |
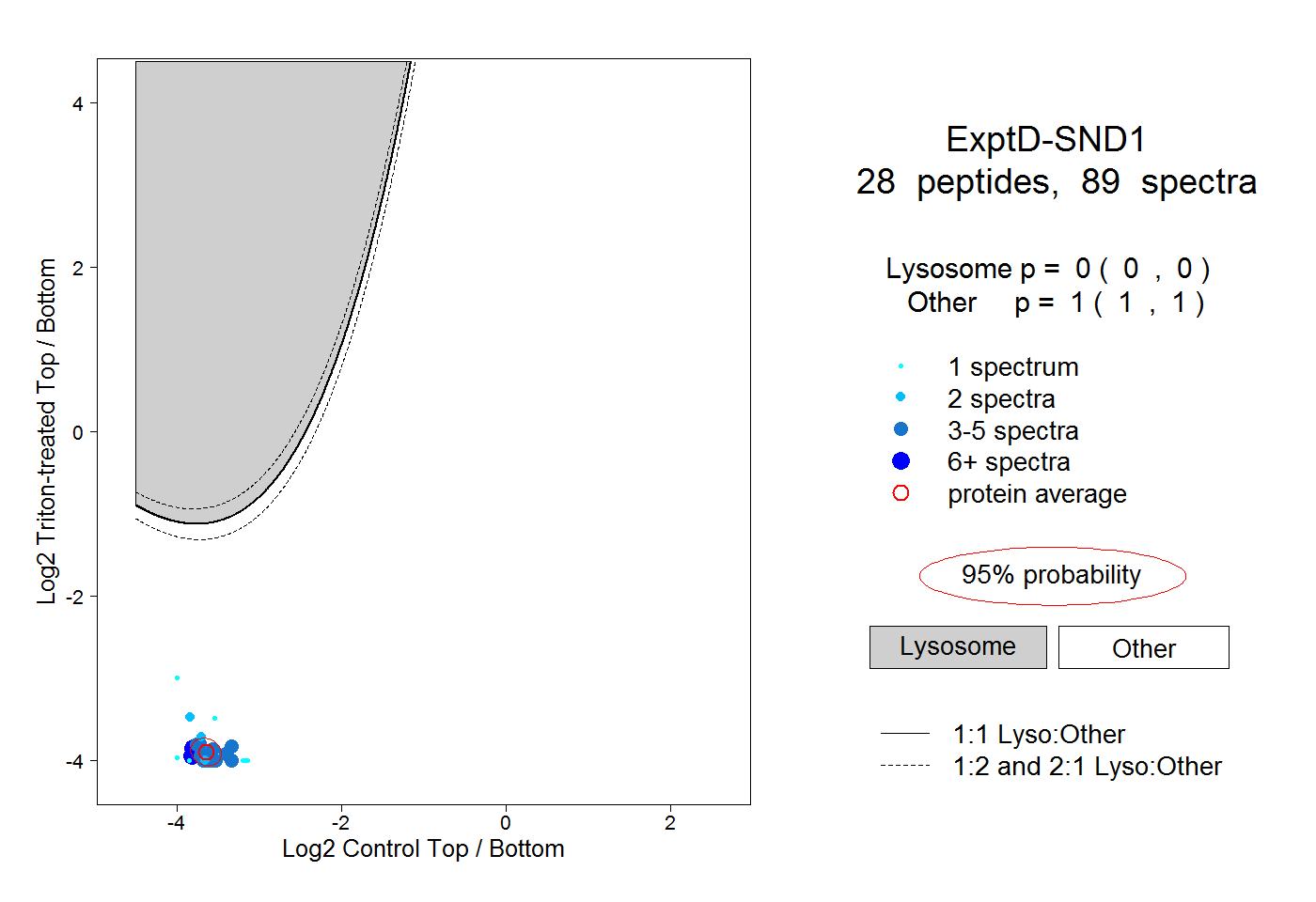 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |