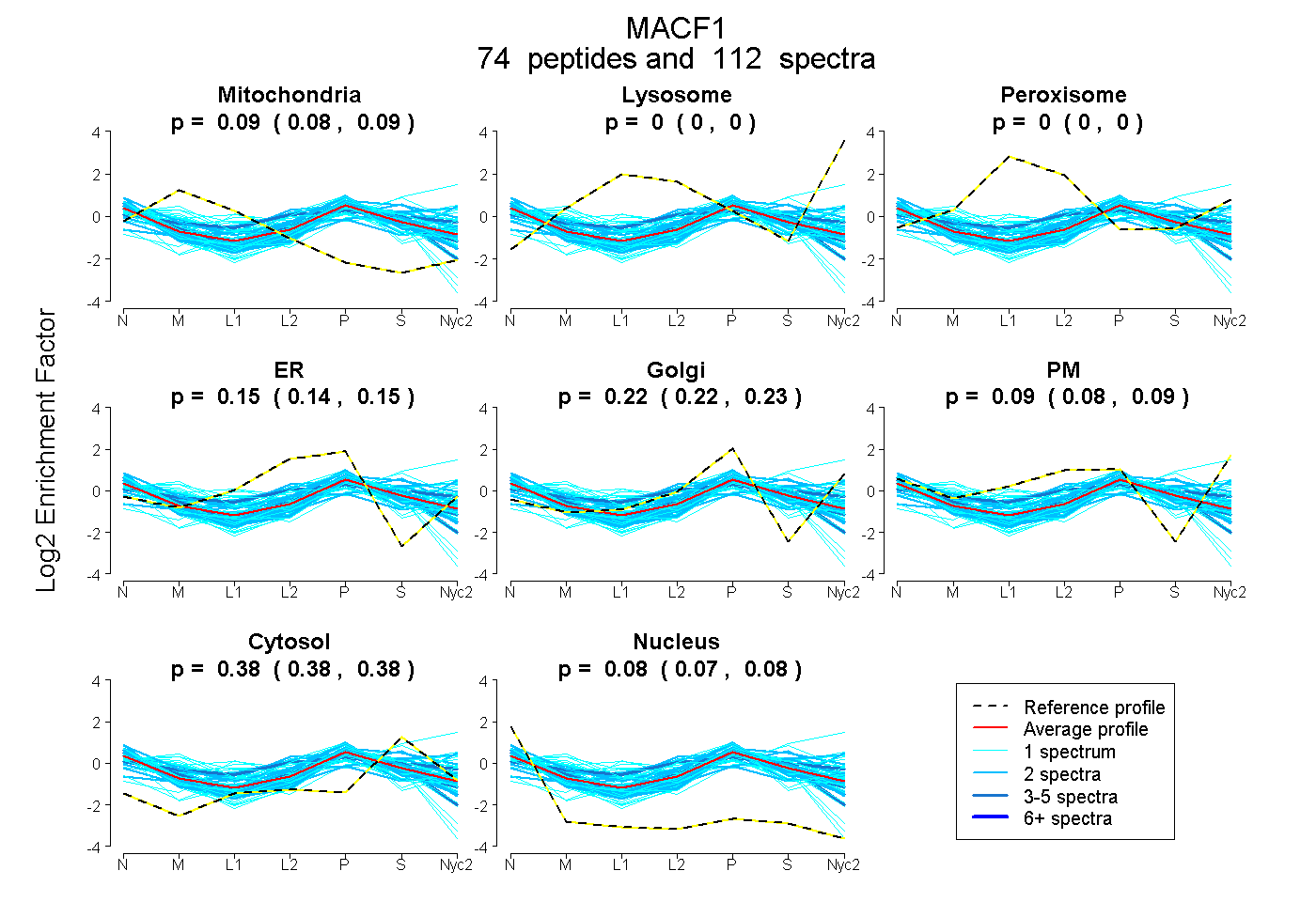
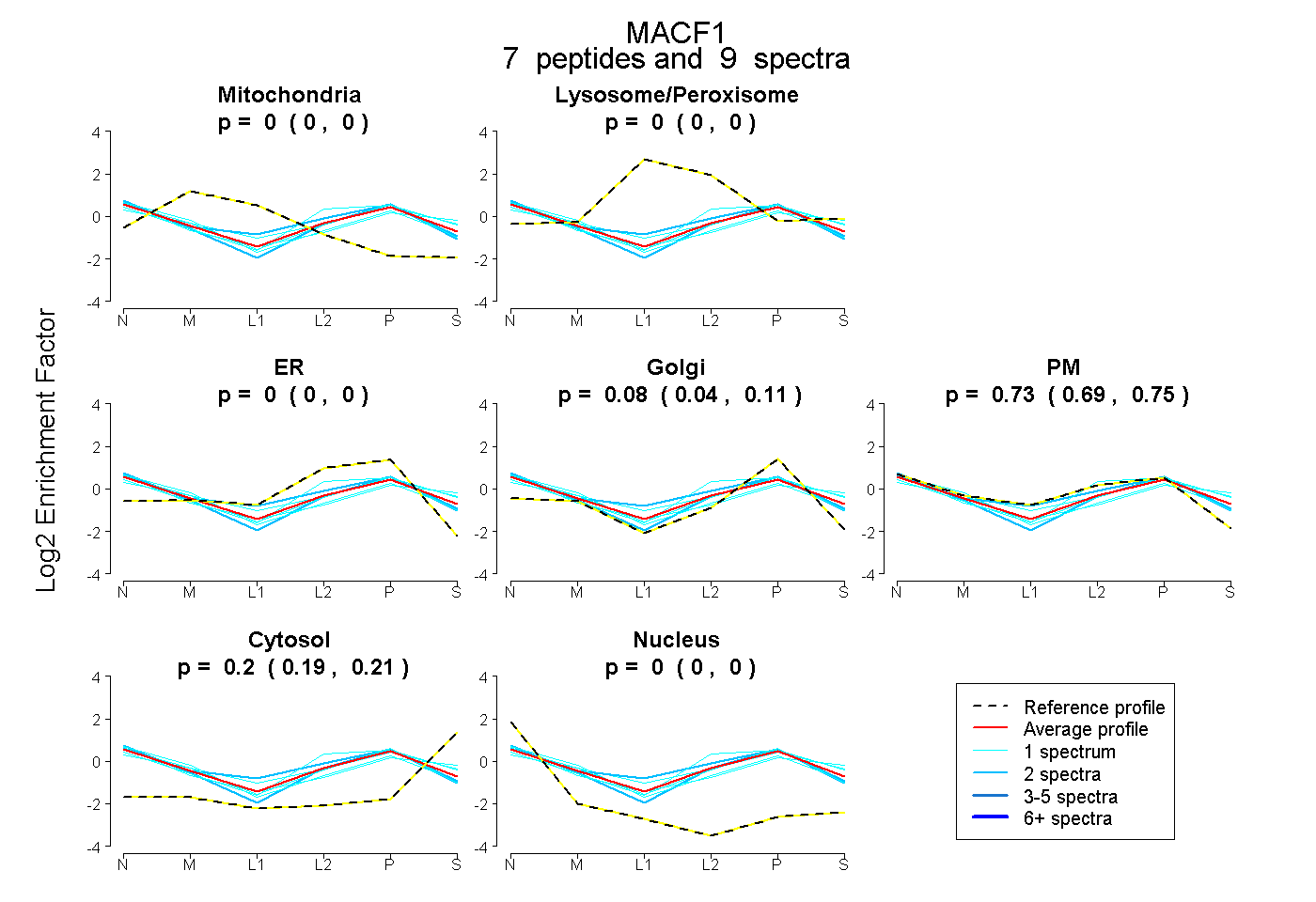
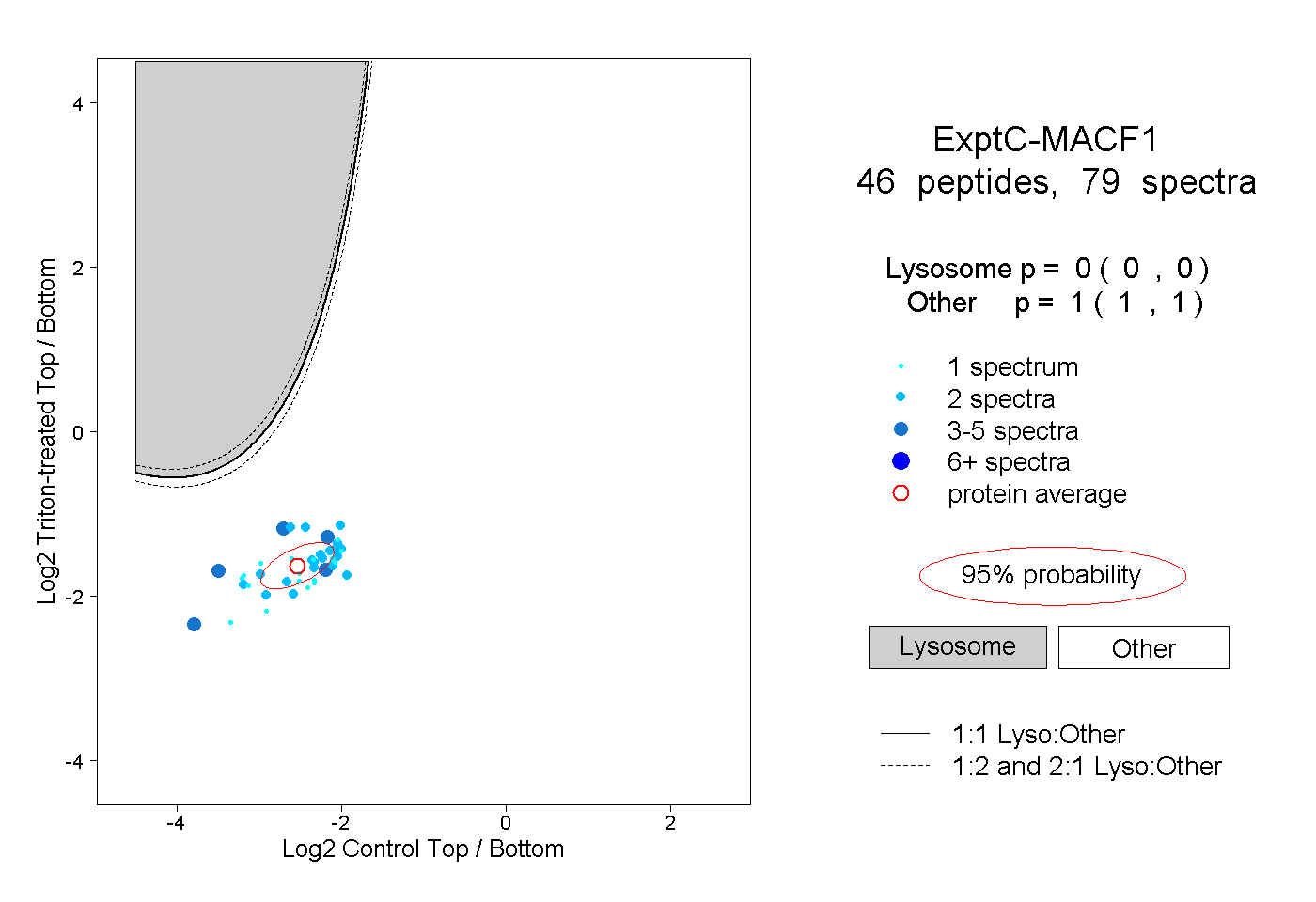
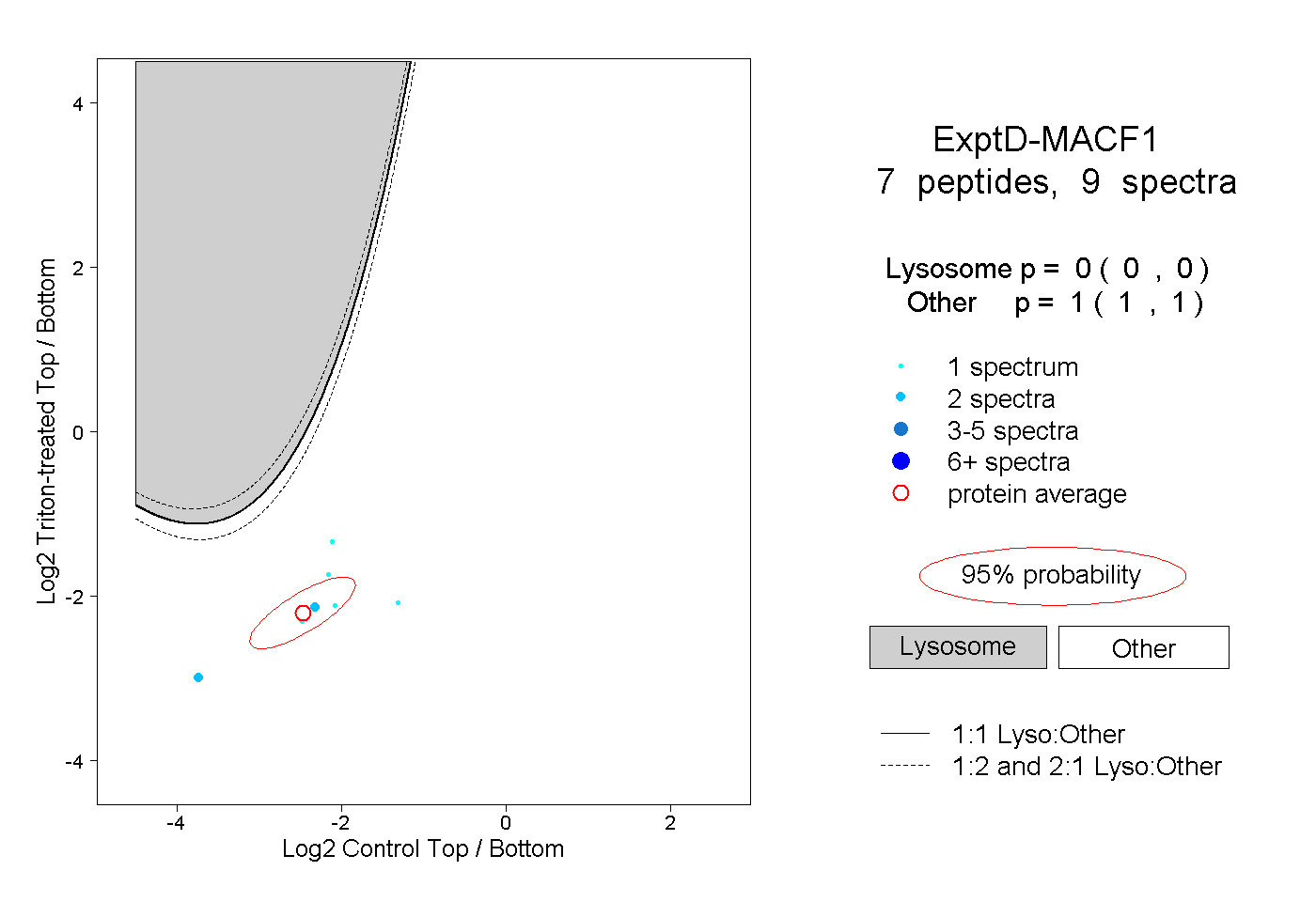
| 2 spectra, TSASTDIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VQIQSNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EVMEHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LANSEPVGTQTAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SALIQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VDSLIPWIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LDNLLGEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NIEPTHAPFIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LSQQYSTTVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QVAQCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LLDDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ELQALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VDEIDAAIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NDDITDGNPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, STLSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DTDSLQSQIEDIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VEQSYQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ETTESIFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QQLEETSEIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LIVEMLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AQAESNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LDIEDSEAECR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QSQQAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EQVDPLQVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VIAQLETR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DIEDSIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GDSGSGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, STVMVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, STQIDQAIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SLRPAVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IEDEVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QDVALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ATEVTVAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, AAEPNLDLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LQLQQQEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VYISELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VMDFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DQEPIPQNIDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IAEQEHVQEDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TGTVQVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LSQEEAVPADLSALESHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ELNPEEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LDQCQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YYQLEELAFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AQIQEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GEIFSTCGEEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |