peptides
spectra
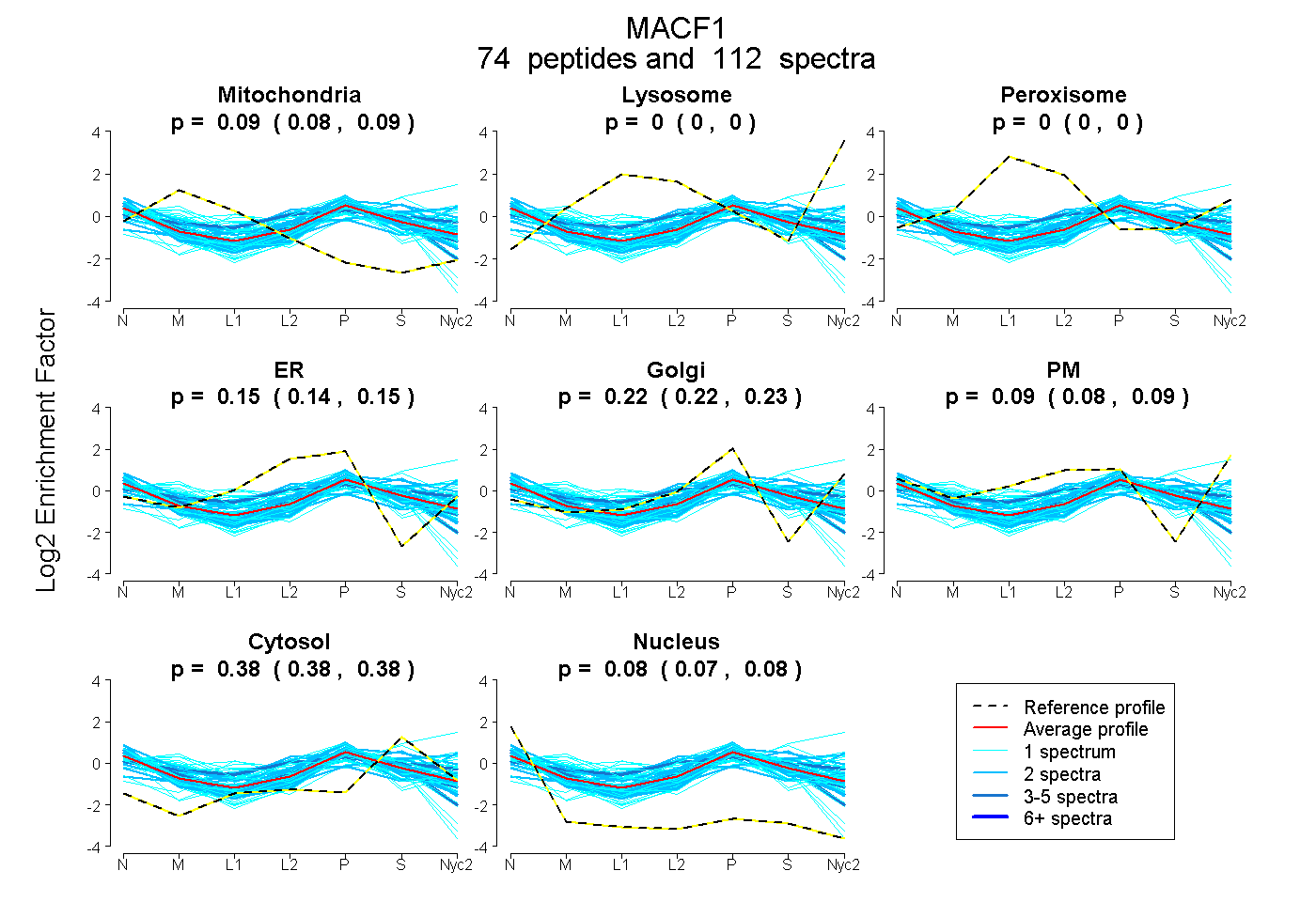
0.084 | 0.089
0.000 | 0.000
0.000 | 0.000
0.140 | 0.152
0.218 | 0.228
0.082 | 0.093
0.378 | 0.382
0.074 | 0.077
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.086 0.084 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.146 0.140 | 0.152 |
0.224 0.218 | 0.228 |
0.088 0.082 | 0.093 |
0.380 0.378 | 0.382 |
0.075 0.074 | 0.077 |
| 2 spectra, GVLVEEINTK | 0.000 | 0.000 | 0.087 | 0.000 | 0.392 | 0.000 | 0.520 | 0.000 | ||
| 1 spectrum, VPEGGEGISATEVDSR | 0.000 | 0.006 | 0.077 | 0.188 | 0.000 | 0.085 | 0.644 | 0.000 | ||
| 1 spectrum, CTTFLQQSPSGSSATTLR | 0.000 | 0.000 | 0.229 | 0.061 | 0.129 | 0.236 | 0.253 | 0.093 | ||
| 1 spectrum, QESLQTVLSR | 0.293 | 0.000 | 0.000 | 0.110 | 0.298 | 0.032 | 0.250 | 0.017 | ||
| 3 spectra, EQYEGLQDR | 0.061 | 0.000 | 0.000 | 0.233 | 0.185 | 0.000 | 0.346 | 0.175 | ||
| 1 spectrum, MLEEEGTLDLLGLK | 0.218 | 0.000 | 0.042 | 0.000 | 0.482 | 0.000 | 0.258 | 0.000 | ||
| 1 spectrum, SDLGQLDDEMK | 0.113 | 0.000 | 0.000 | 0.080 | 0.381 | 0.000 | 0.407 | 0.020 | ||
| 1 spectrum, WTELLSK | 0.364 | 0.000 | 0.000 | 0.000 | 0.324 | 0.103 | 0.209 | 0.000 | ||
| 2 spectra, QSEVESIQEVLR | 0.079 | 0.000 | 0.000 | 0.000 | 0.411 | 0.032 | 0.297 | 0.181 | ||
| 1 spectrum, LEQALK | 0.115 | 0.000 | 0.000 | 0.000 | 0.092 | 0.436 | 0.357 | 0.000 | ||
| 2 spectra, EQYAASLAQSEAK | 0.195 | 0.000 | 0.000 | 0.144 | 0.000 | 0.288 | 0.345 | 0.028 | ||
| 1 spectrum, DYELQLMTYK | 0.000 | 0.000 | 0.197 | 0.000 | 0.334 | 0.103 | 0.367 | 0.000 | ||
| 2 spectra, NTQGTTTSSR | 0.000 | 0.000 | 0.000 | 0.279 | 0.106 | 0.000 | 0.436 | 0.179 | ||
| 2 spectra, ETTESIFSR | 0.011 | 0.000 | 0.000 | 0.000 | 0.232 | 0.225 | 0.451 | 0.081 | ||
| 1 spectrum, WVELTDK | 0.008 | 0.000 | 0.000 | 0.063 | 0.379 | 0.041 | 0.448 | 0.061 | ||
| 1 spectrum, EFANFDFDVWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.396 | 0.429 | 0.049 | ||
| 1 spectrum, GEELIGR | 0.055 | 0.007 | 0.000 | 0.000 | 0.098 | 0.384 | 0.456 | 0.000 | ||
| 2 spectra, EFENWLER | 0.086 | 0.000 | 0.000 | 0.115 | 0.224 | 0.000 | 0.446 | 0.128 | ||
| 2 spectra, NVDQAIK | 0.205 | 0.000 | 0.021 | 0.000 | 0.083 | 0.202 | 0.489 | 0.000 | ||
| 2 spectra, IEDEVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.651 | 0.287 | 0.062 | ||
| 1 spectrum, NDECVLEDNSQR | 0.033 | 0.000 | 0.000 | 0.333 | 0.000 | 0.000 | 0.281 | 0.352 | ||
| 1 spectrum, YRPDLVDMER | 0.043 | 0.000 | 0.000 | 0.000 | 0.344 | 0.055 | 0.454 | 0.103 | ||
| 2 spectra, LQDELVTLR | 0.000 | 0.000 | 0.000 | 0.157 | 0.259 | 0.000 | 0.380 | 0.205 | ||
| 1 spectrum, TLEQAR | 0.000 | 0.000 | 0.000 | 0.096 | 0.290 | 0.153 | 0.306 | 0.156 | ||
| 1 spectrum, TELVAISSSEDEGSLR | 0.111 | 0.000 | 0.000 | 0.137 | 0.240 | 0.000 | 0.377 | 0.135 | ||
| 1 spectrum, NPDHVLK | 0.069 | 0.000 | 0.000 | 0.339 | 0.134 | 0.000 | 0.399 | 0.059 | ||
| 1 spectrum, LLLWTQK | 0.000 | 0.000 | 0.000 | 0.032 | 0.370 | 0.000 | 0.395 | 0.204 | ||
| 2 spectra, AVAEQLHHR | 0.000 | 0.000 | 0.000 | 0.000 | 0.060 | 0.459 | 0.481 | 0.000 | ||
| 1 spectrum, LMALGPIR | 0.206 | 0.000 | 0.000 | 0.302 | 0.287 | 0.055 | 0.145 | 0.005 | ||
| 2 spectra, DLESFLR | 0.000 | 0.000 | 0.000 | 0.180 | 0.283 | 0.000 | 0.350 | 0.188 | ||
| 1 spectrum, AFLAELEQNSPK | 0.056 | 0.000 | 0.146 | 0.000 | 0.000 | 0.404 | 0.394 | 0.000 | ||
| 1 spectrum, AQIQEQK | 0.151 | 0.000 | 0.200 | 0.000 | 0.255 | 0.163 | 0.231 | 0.000 | ||
| 1 spectrum, NLLVSVQSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.347 | 0.251 | 0.287 | 0.115 | ||
| 1 spectrum, VEDFYSK | 0.262 | 0.000 | 0.131 | 0.000 | 0.208 | 0.153 | 0.246 | 0.000 | ||
| 2 spectra, DLLGWVSTLAR | 0.045 | 0.000 | 0.000 | 0.238 | 0.147 | 0.000 | 0.423 | 0.148 | ||
| 2 spectra, EASSVLQWLESK | 0.137 | 0.000 | 0.000 | 0.000 | 0.446 | 0.063 | 0.306 | 0.047 | ||
| 2 spectra, EVMEHR | 0.000 | 0.000 | 0.180 | 0.277 | 0.000 | 0.000 | 0.543 | 0.000 | ||
| 1 spectrum, VDSLIPWIR | 0.071 | 0.000 | 0.000 | 0.128 | 0.301 | 0.081 | 0.248 | 0.170 | ||
| 1 spectrum, NIEPTHAPFIEK | 0.000 | 0.000 | 0.000 | 0.079 | 0.196 | 0.132 | 0.510 | 0.083 | ||
| 2 spectra, SLISWNYLR | 0.028 | 0.000 | 0.000 | 0.000 | 0.429 | 0.006 | 0.406 | 0.131 | ||
| 2 spectra, VIEVELAK | 0.000 | 0.000 | 0.000 | 0.204 | 0.263 | 0.042 | 0.355 | 0.135 | ||
| 2 spectra, GLLDDWAGK | 0.062 | 0.000 | 0.000 | 0.376 | 0.000 | 0.000 | 0.374 | 0.189 | ||
| 1 spectrum, AQAESNK | 0.004 | 0.000 | 0.000 | 0.288 | 0.150 | 0.071 | 0.356 | 0.129 | ||
| 1 spectrum, LIVEMLER | 0.000 | 0.000 | 0.000 | 0.145 | 0.258 | 0.000 | 0.340 | 0.257 | ||
| 2 spectra, QQLEETSEIR | 0.011 | 0.000 | 0.000 | 0.296 | 0.170 | 0.000 | 0.317 | 0.206 | ||
| 1 spectrum, LDIEDSEAECR | 0.000 | 0.000 | 0.000 | 0.322 | 0.000 | 0.000 | 0.289 | 0.389 | ||
| 1 spectrum, DIEGFLEENQNK | 0.071 | 0.000 | 0.000 | 0.223 | 0.140 | 0.000 | 0.328 | 0.238 | ||
| 4 spectra, MFNALIHR | 0.093 | 0.000 | 0.000 | 0.254 | 0.234 | 0.000 | 0.311 | 0.107 | ||
| 1 spectrum, QPVYDTTIR | 0.000 | 0.000 | 0.000 | 0.271 | 0.184 | 0.019 | 0.425 | 0.100 | ||
| 4 spectra, HWITIIR | 0.071 | 0.000 | 0.000 | 0.371 | 0.000 | 0.000 | 0.394 | 0.164 | ||
| 1 spectrum, DIEDSIK | 0.000 | 0.411 | 0.000 | 0.000 | 0.000 | 0.013 | 0.576 | 0.000 | ||
| 2 spectra, STVMVR | 0.000 | 0.000 | 0.000 | 0.348 | 0.197 | 0.000 | 0.324 | 0.130 | ||
| 1 spectrum, TCDVQGLEHDMEEVNTR | 0.009 | 0.000 | 0.018 | 0.131 | 0.248 | 0.306 | 0.177 | 0.110 | ||
| 1 spectrum, NSVFSVLDEEISK | 0.240 | 0.000 | 0.000 | 0.001 | 0.075 | 0.339 | 0.345 | 0.000 | ||
| 1 spectrum, LEECEQR | 0.097 | 0.000 | 0.000 | 0.000 | 0.267 | 0.190 | 0.409 | 0.038 | ||
| 2 spectra, VGGGWMALDEFLVK | 0.173 | 0.000 | 0.000 | 0.000 | 0.000 | 0.466 | 0.246 | 0.115 | ||
| 1 spectrum, ALYNQYIHFK | 0.066 | 0.000 | 0.000 | 0.000 | 0.224 | 0.222 | 0.472 | 0.015 | ||
| 2 spectra, VMDFFR | 0.000 | 0.000 | 0.000 | 0.242 | 0.231 | 0.119 | 0.300 | 0.108 | ||
| 1 spectrum, MESQLSASKPTGGLPETAR | 0.084 | 0.000 | 0.000 | 0.273 | 0.302 | 0.000 | 0.224 | 0.116 | ||
| 1 spectrum, FLDVLELAEK | 0.000 | 0.000 | 0.000 | 0.252 | 0.203 | 0.000 | 0.327 | 0.218 | ||
| 2 spectra, DQEPIPQNIDR | 0.007 | 0.000 | 0.000 | 0.112 | 0.271 | 0.143 | 0.303 | 0.165 | ||
| 2 spectra, TIVQLKPR | 0.017 | 0.000 | 0.000 | 0.141 | 0.273 | 0.087 | 0.346 | 0.136 | ||
| 2 spectra, AFSIDIIR | 0.000 | 0.000 | 0.000 | 0.111 | 0.370 | 0.000 | 0.348 | 0.171 | ||
| 3 spectra, QHADHLALNEEIINR | 0.085 | 0.000 | 0.088 | 0.131 | 0.000 | 0.291 | 0.405 | 0.000 | ||
| 1 spectrum, IAEQEHVQEDLK | 0.000 | 0.000 | 0.000 | 0.372 | 0.145 | 0.000 | 0.336 | 0.147 | ||
| 2 spectra, LMLLSR | 0.000 | 0.000 | 0.000 | 0.244 | 0.235 | 0.000 | 0.403 | 0.117 | ||
| 1 spectrum, HINDLYEDLR | 0.394 | 0.000 | 0.000 | 0.153 | 0.000 | 0.000 | 0.314 | 0.139 | ||
| 2 spectra, LVSDTVGQR | 0.075 | 0.000 | 0.000 | 0.114 | 0.274 | 0.053 | 0.353 | 0.131 | ||
| 1 spectrum, ENLEQAFEVAER | 0.031 | 0.000 | 0.112 | 0.090 | 0.031 | 0.298 | 0.438 | 0.000 | ||
| 1 spectrum, AAHDLMDIEGEPSLDCTPIR | 0.335 | 0.000 | 0.000 | 0.167 | 0.119 | 0.121 | 0.258 | 0.000 | ||
| 2 spectra, IAQAAELADR | 0.088 | 0.000 | 0.000 | 0.098 | 0.297 | 0.096 | 0.353 | 0.067 | ||
| 1 spectrum, YYQLEELAFR | 0.000 | 0.000 | 0.000 | 0.497 | 0.041 | 0.000 | 0.369 | 0.093 | ||
| 1 spectrum, LQQFVEHK | 0.185 | 0.000 | 0.000 | 0.258 | 0.147 | 0.000 | 0.349 | 0.061 | ||
| 2 spectra, QLQEELAEHQVPVEK | 0.000 | 0.000 | 0.000 | 0.176 | 0.219 | 0.107 | 0.372 | 0.127 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
9 spectra |
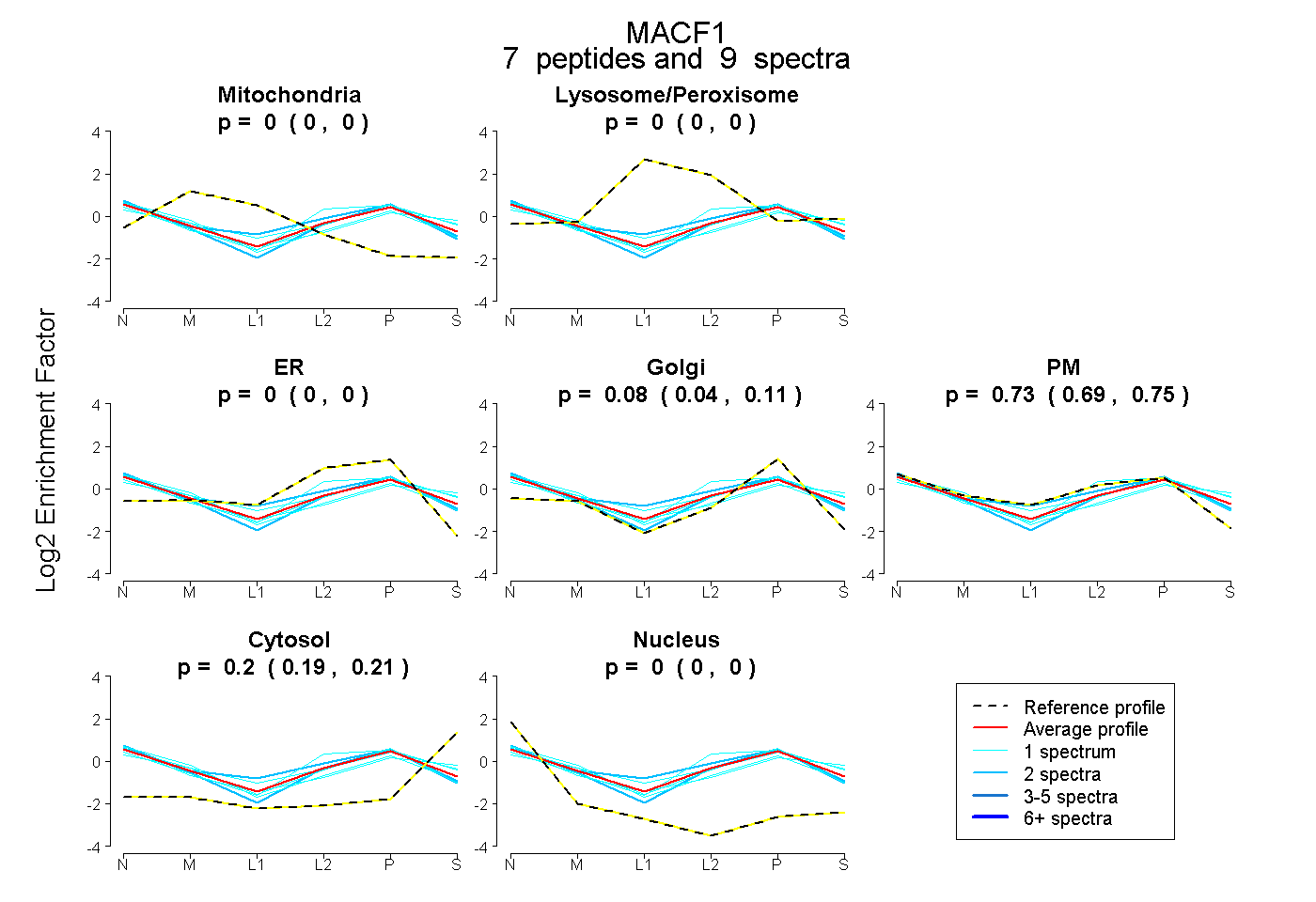 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.076 0.040 | 0.106 |
0.726 0.691 | 0.753 |
0.198 0.185 | 0.210 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
79 spectra |
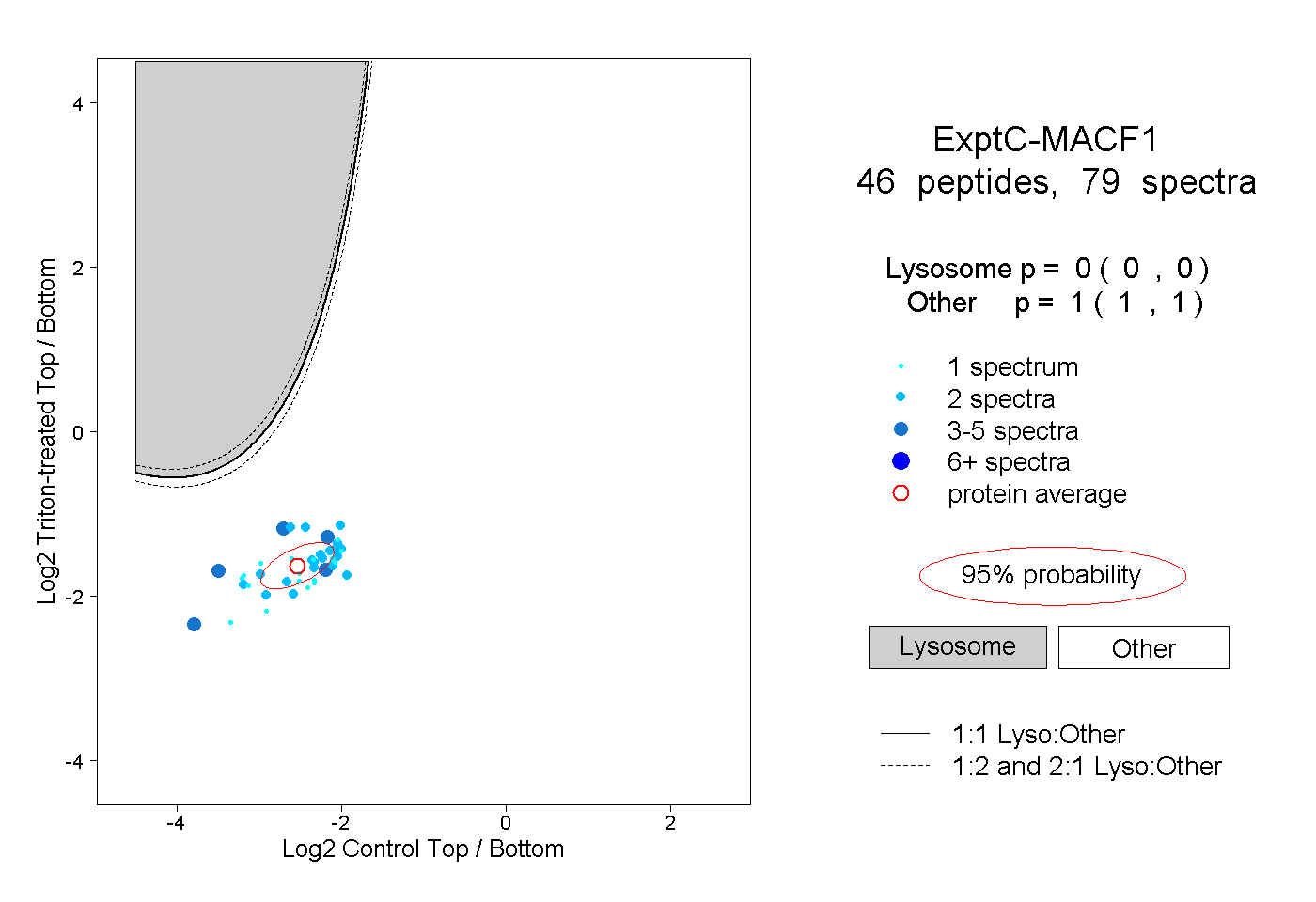 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
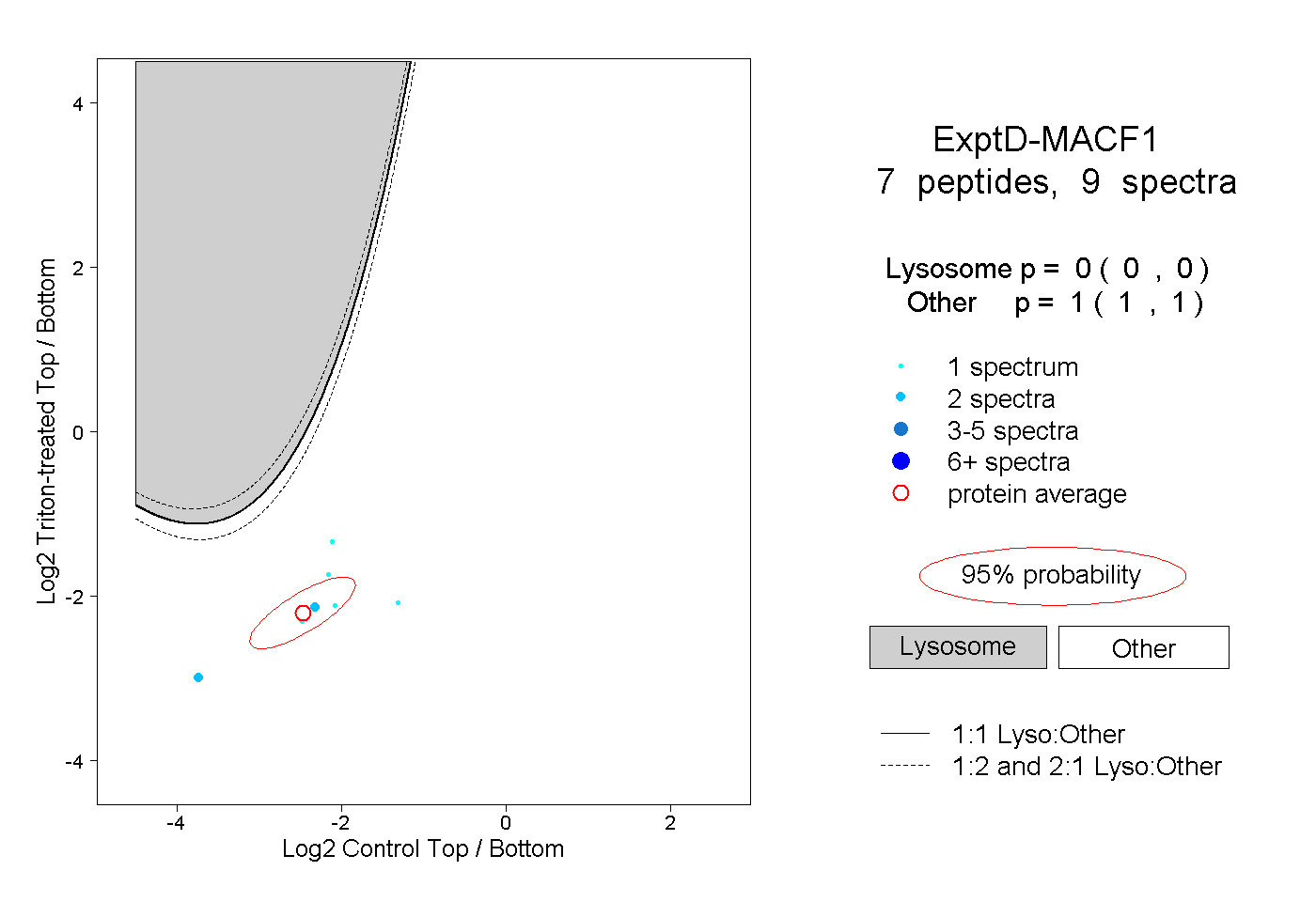 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |